peptides
spectra
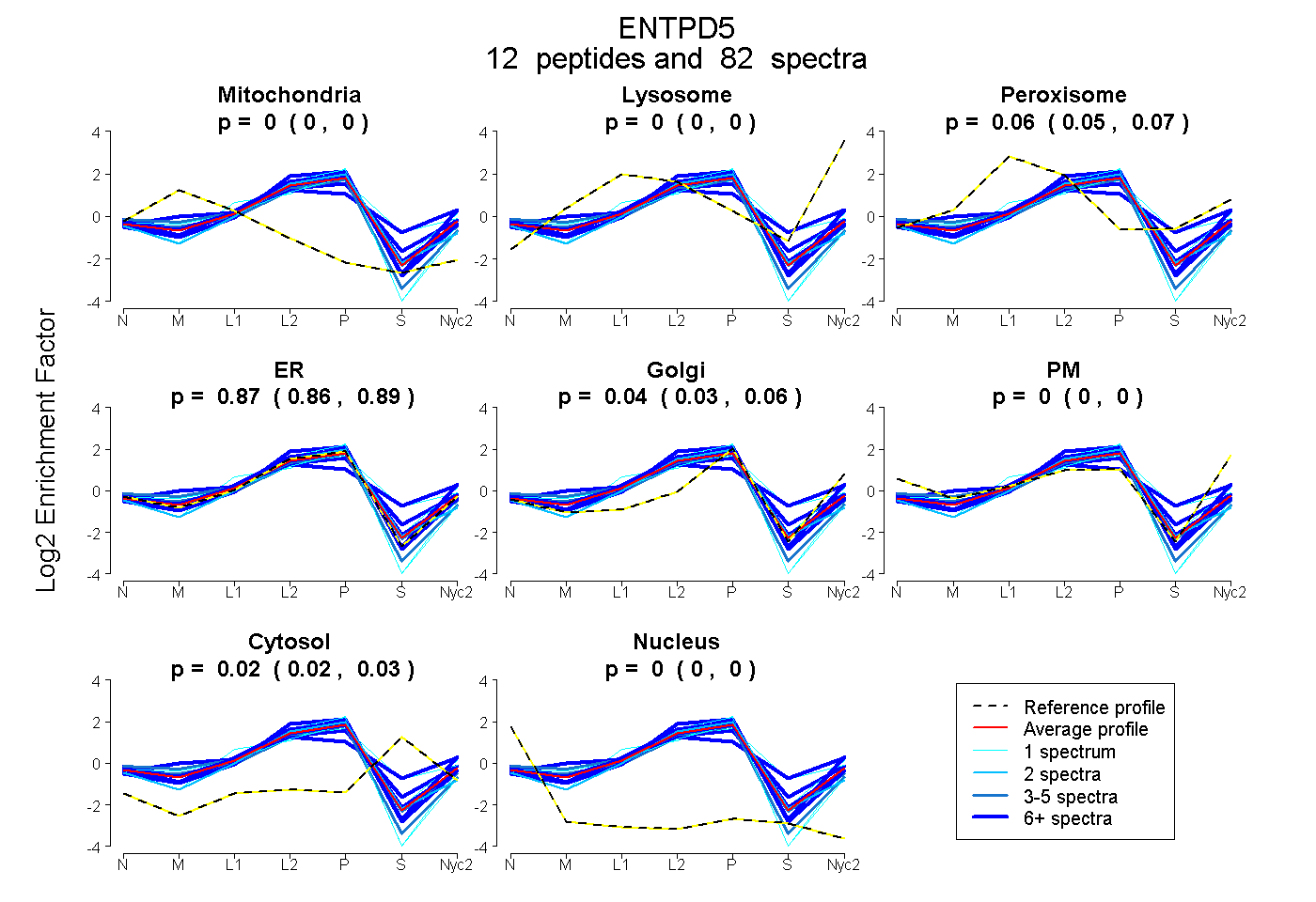
0.000 | 0.000
0.000 | 0.000
0.054 | 0.065
0.856 | 0.885
0.032 | 0.056
0.000 | 0.000
0.015 | 0.027
0.000 | 0.000
peptides
spectra
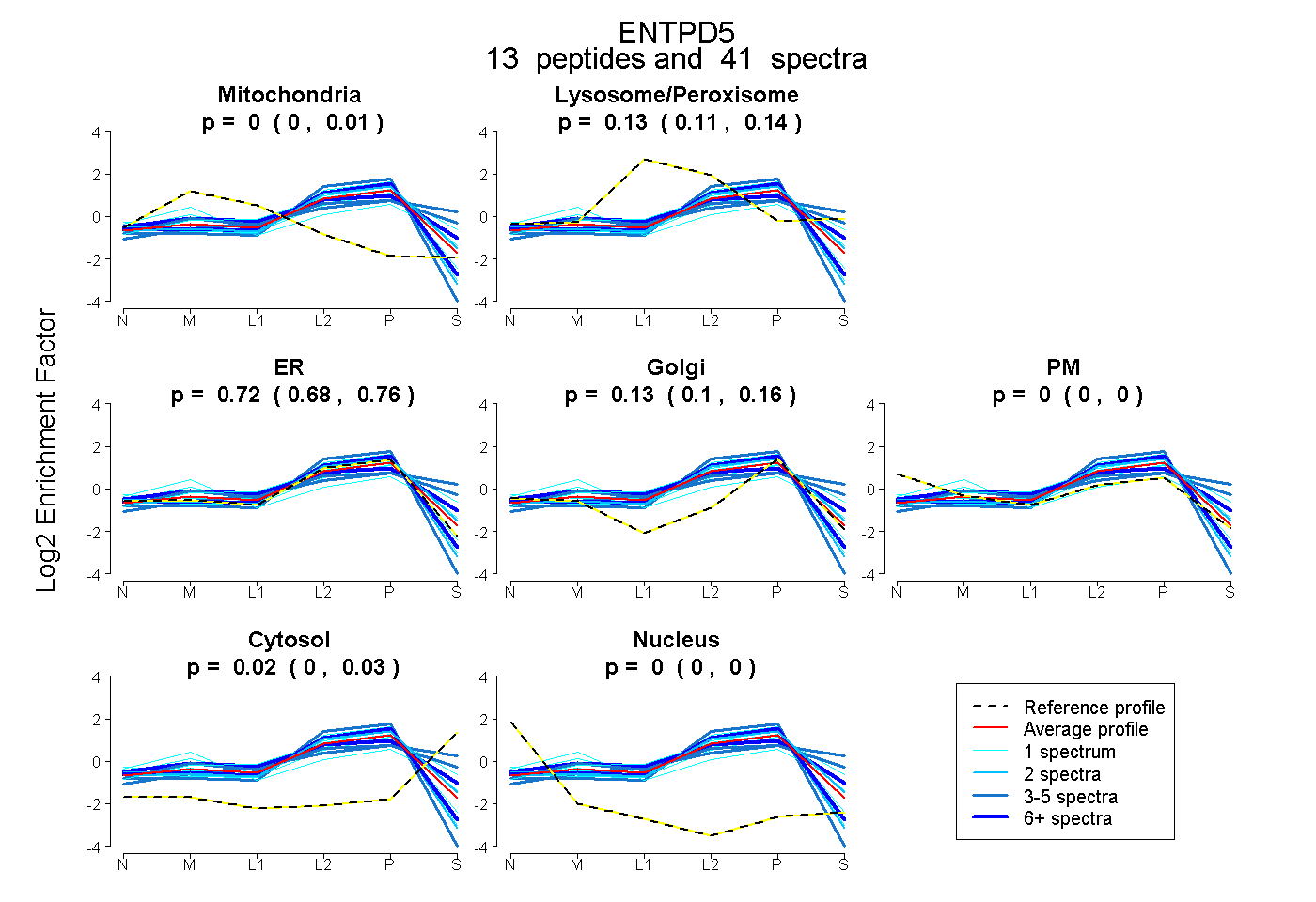
0.000 | 0.008
0.105 | 0.141
0.682 | 0.760
0.102 | 0.157
0.000 | 0.000
0.004 | 0.025
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
82 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.060 0.054 | 0.065 |
0.873 0.856 | 0.885 |
0.045 0.032 | 0.056 |
0.000 0.000 | 0.000 |
0.022 0.015 | 0.027 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
41 spectra |
 |
0.000 0.000 | 0.008 |
0.128 0.105 | 0.141 |
0.723 0.682 | 0.760 |
0.134 0.102 | 0.157 |
0.000 0.000 | 0.000 |
0.016 0.004 | 0.025 |
0.000 0.000 | 0.000 |
| 4 spectra, LHQPEEIR | 0.000 | 0.343 | 0.249 | 0.252 | 0.000 | 0.156 | 0.000 | |||
| 3 spectra, AQTLLLEVEEIFK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, IHVYTFVQR | 0.000 | 0.359 | 0.191 | 0.194 | 0.000 | 0.255 | 0.000 | |||
| 1 spectrum, ATAGLR | 0.000 | 0.246 | 0.328 | 0.321 | 0.000 | 0.105 | 0.000 | |||
| 1 spectrum, AAETHLIDYEK | 0.090 | 0.104 | 0.617 | 0.189 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DGFGFEDGTLLQLTK | 0.000 | 0.032 | 0.875 | 0.000 | 0.093 | 0.000 | 0.000 | |||
| 1 spectrum, GSSFYAFSYYYDR | 0.144 | 0.231 | 0.000 | 0.550 | 0.055 | 0.021 | 0.000 | |||
| 2 spectra, WLEAEWIFGGVK | 0.000 | 0.075 | 0.871 | 0.000 | 0.000 | 0.054 | 0.000 | |||
| 2 spectra, LLPEQK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, LATLGALEAEGTDGHTFR | 0.000 | 0.349 | 0.280 | 0.366 | 0.000 | 0.006 | 0.000 | |||
| 1 spectrum, TLEQTPK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LYTHSYLGFGLK | 0.000 | 0.253 | 0.544 | 0.203 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, VEDFER | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
115 spectra |
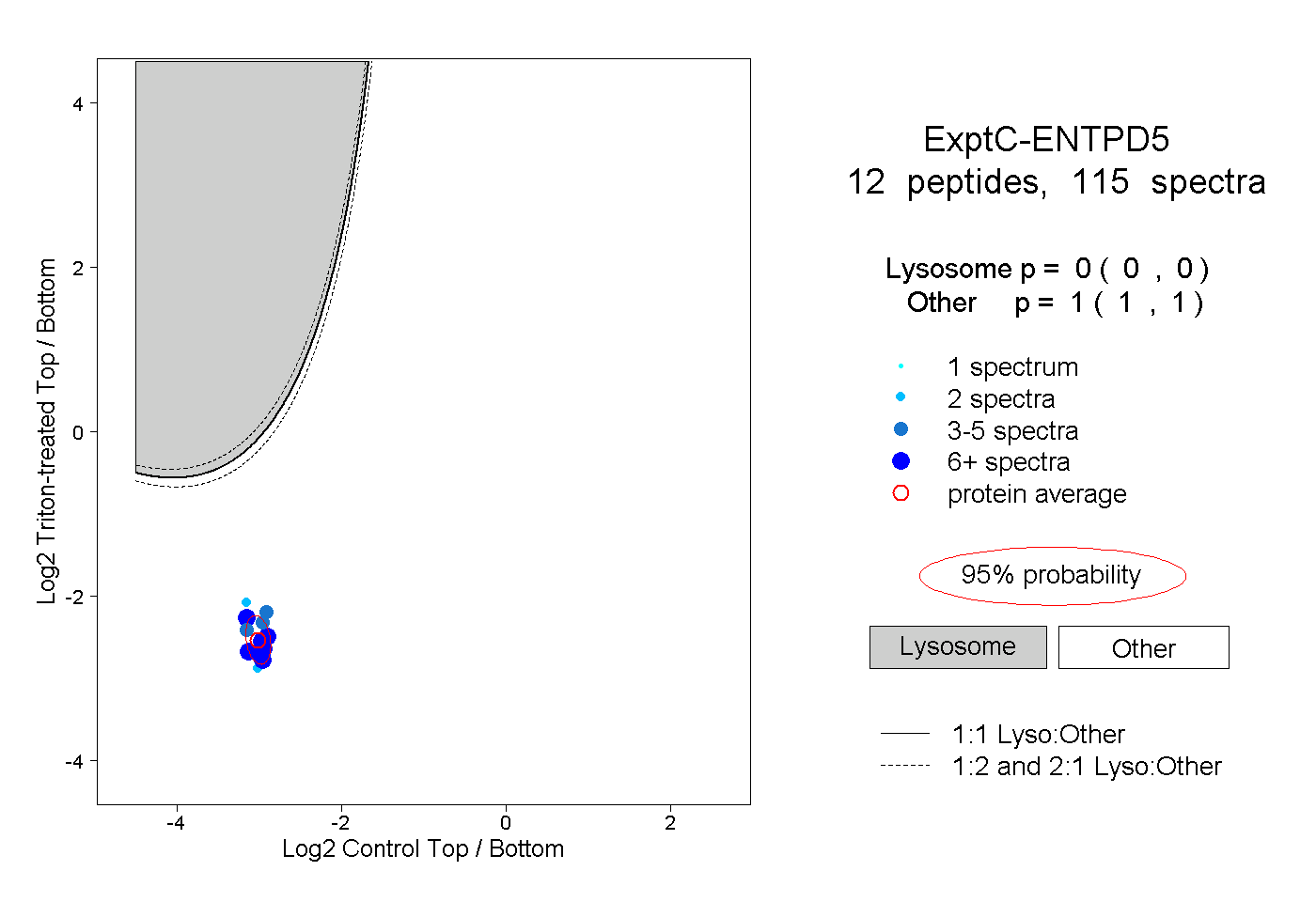 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
19 spectra |
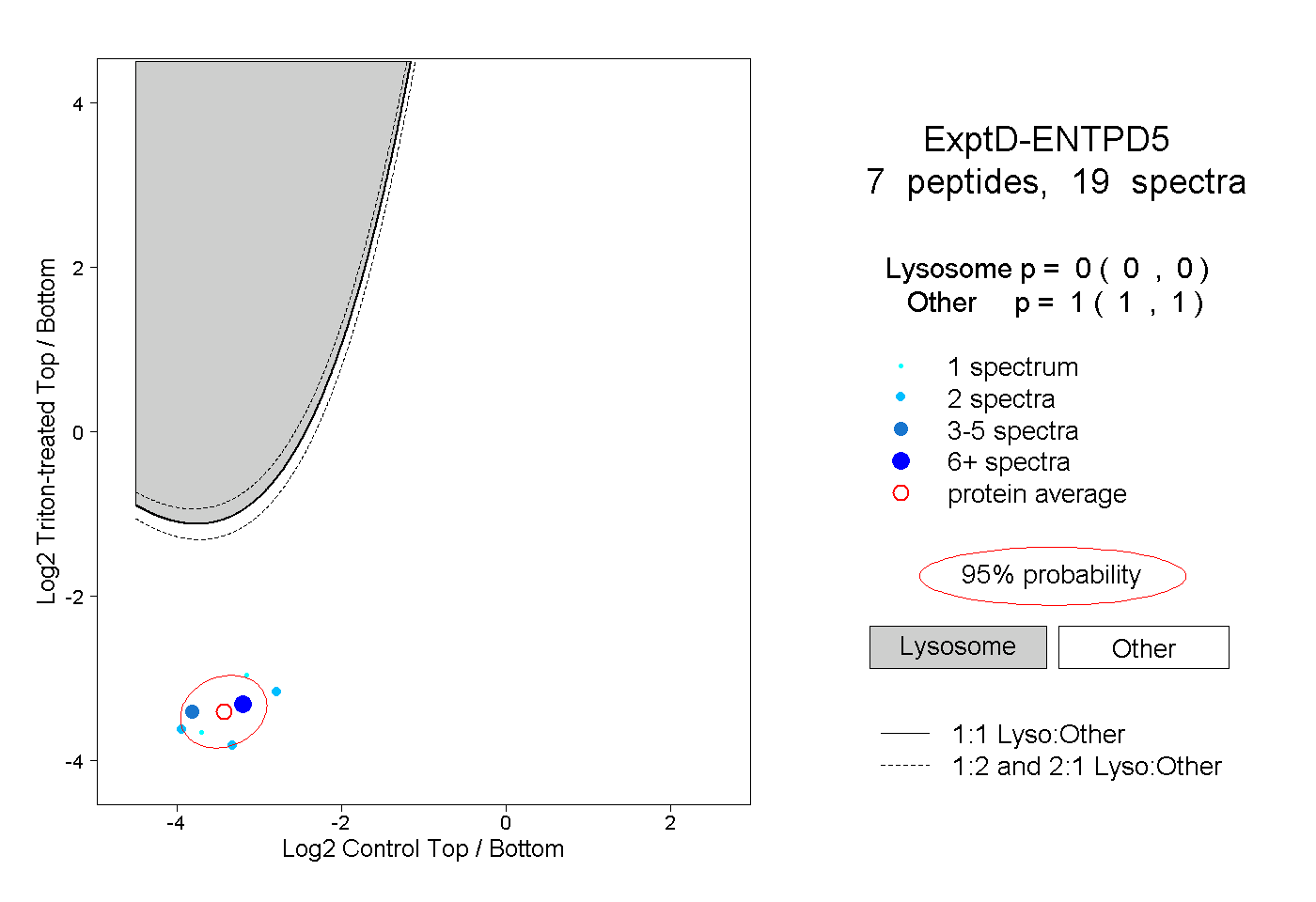 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |