peptides
spectra
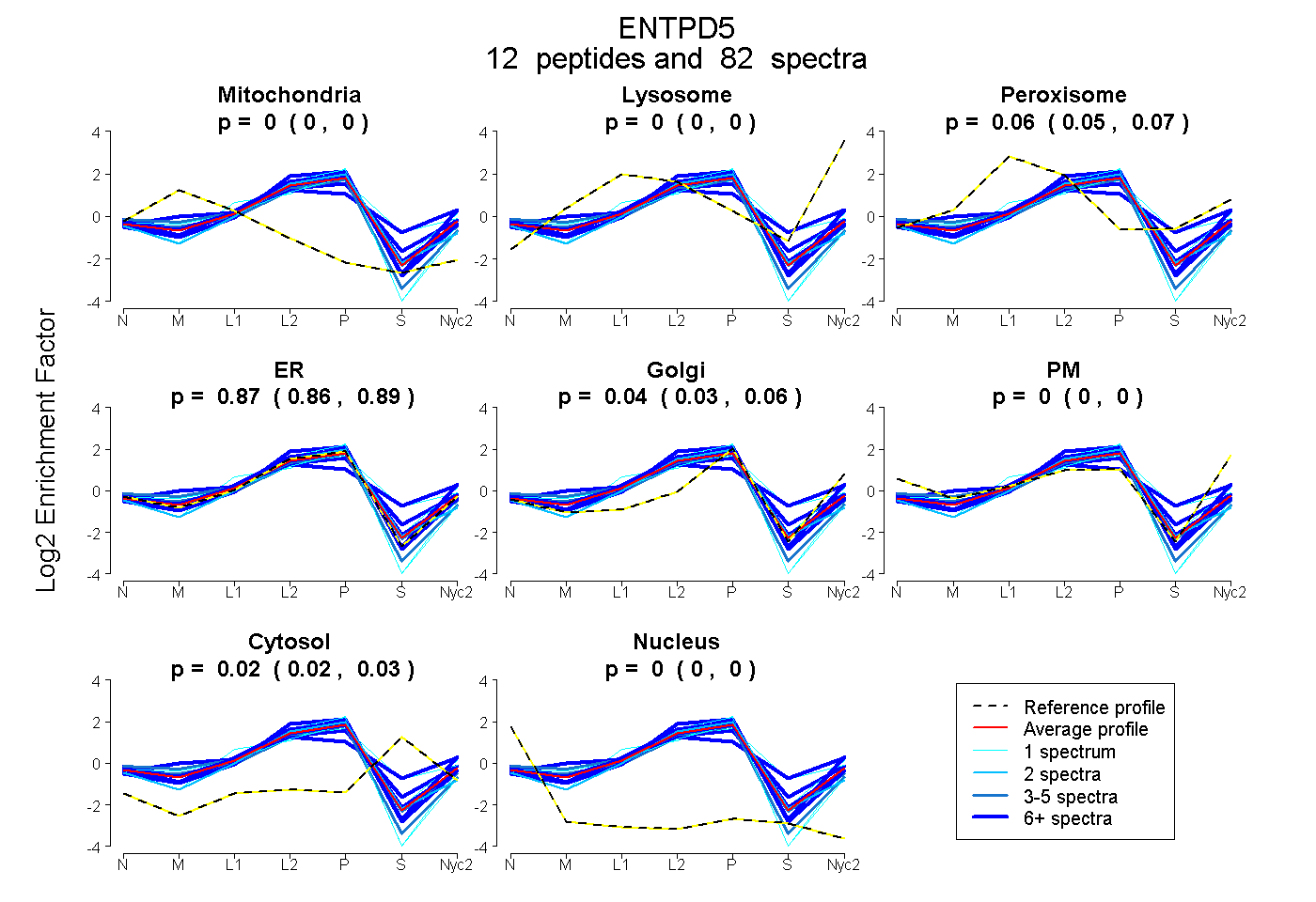
0.000 | 0.000
0.000 | 0.000
0.054 | 0.065
0.856 | 0.885
0.032 | 0.056
0.000 | 0.000
0.015 | 0.027
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
82 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.060 0.054 | 0.065 |
0.873 0.856 | 0.885 |
0.045 0.032 | 0.056 |
0.000 0.000 | 0.000 |
0.022 0.015 | 0.027 |
0.000 0.000 | 0.000 |
| 6 spectra, IHVYTFVQR | 0.000 | 0.056 | 0.284 | 0.366 | 0.158 | 0.000 | 0.136 | 0.000 | ||
| 1 spectrum, ATAGLR | 0.000 | 0.050 | 0.066 | 0.684 | 0.000 | 0.000 | 0.201 | 0.000 | ||
| 12 spectra, AAETHLIDYEK | 0.000 | 0.000 | 0.108 | 0.738 | 0.017 | 0.041 | 0.097 | 0.000 | ||
| 3 spectra, DGFGFEDGTLLQLTK | 0.054 | 0.000 | 0.000 | 0.892 | 0.016 | 0.000 | 0.038 | 0.000 | ||
| 1 spectrum, GSSFYAFSYYYDR | 0.000 | 0.000 | 0.000 | 0.998 | 0.000 | 0.000 | 0.000 | 0.002 | ||
| 2 spectra, WLEAEWIFGGVK | 0.000 | 0.000 | 0.000 | 0.927 | 0.000 | 0.000 | 0.073 | 0.000 | ||
| 3 spectra, LLPEQK | 0.093 | 0.000 | 0.000 | 0.907 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, TLEQTPK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, SACLPR | 0.000 | 0.000 | 0.058 | 0.902 | 0.000 | 0.000 | 0.040 | 0.000 | ||
| 1 spectrum, TPVVLK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LYTHSYLGFGLK | 0.000 | 0.002 | 0.136 | 0.581 | 0.281 | 0.000 | 0.000 | 0.000 | ||
| 38 spectra, VEDFER | 0.000 | 0.059 | 0.000 | 0.857 | 0.000 | 0.084 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
41 spectra |
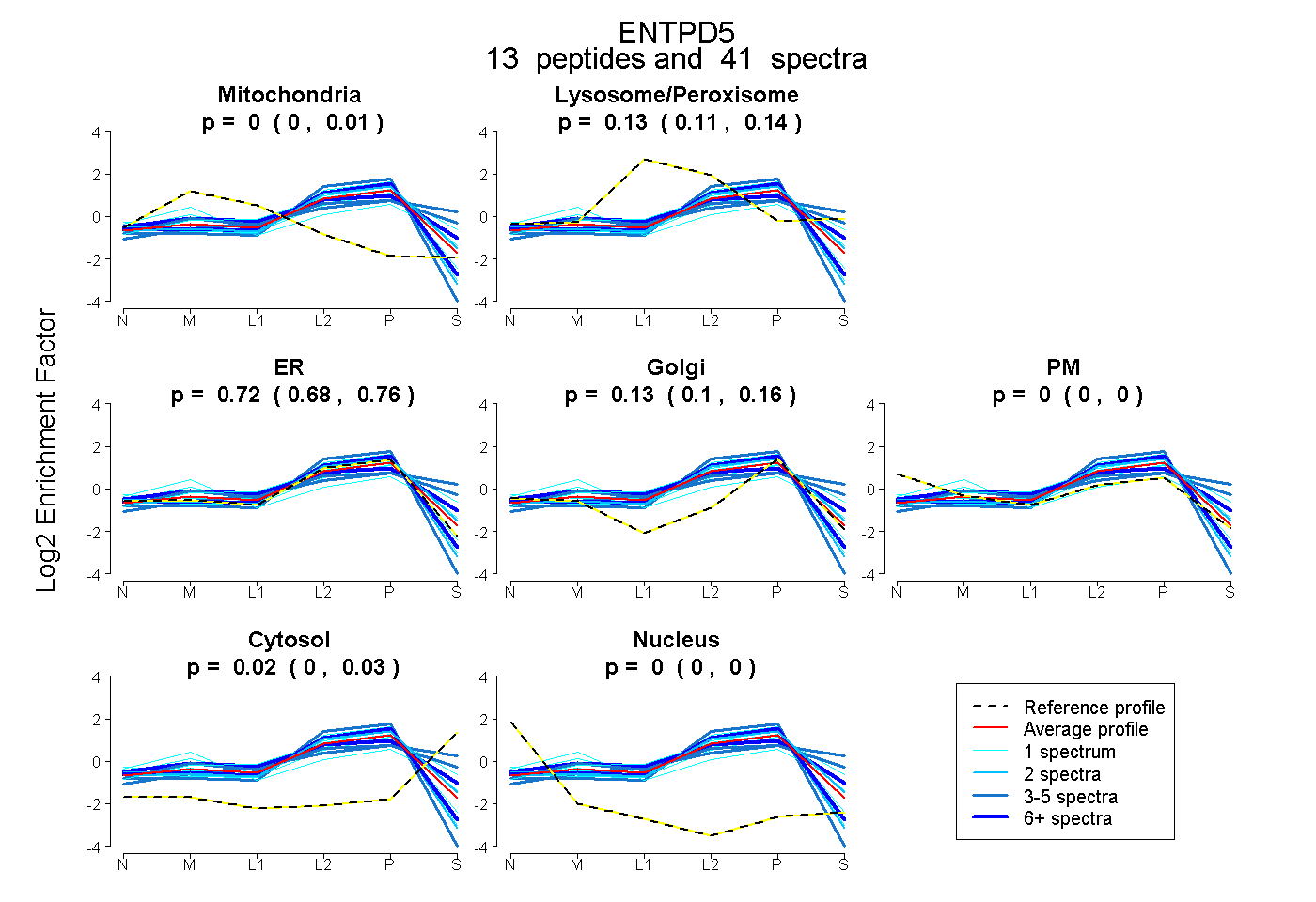 |
0.000 0.000 | 0.008 |
0.128 0.105 | 0.141 |
0.723 0.682 | 0.760 |
0.134 0.102 | 0.157 |
0.000 0.000 | 0.000 |
0.016 0.004 | 0.025 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
115 spectra |
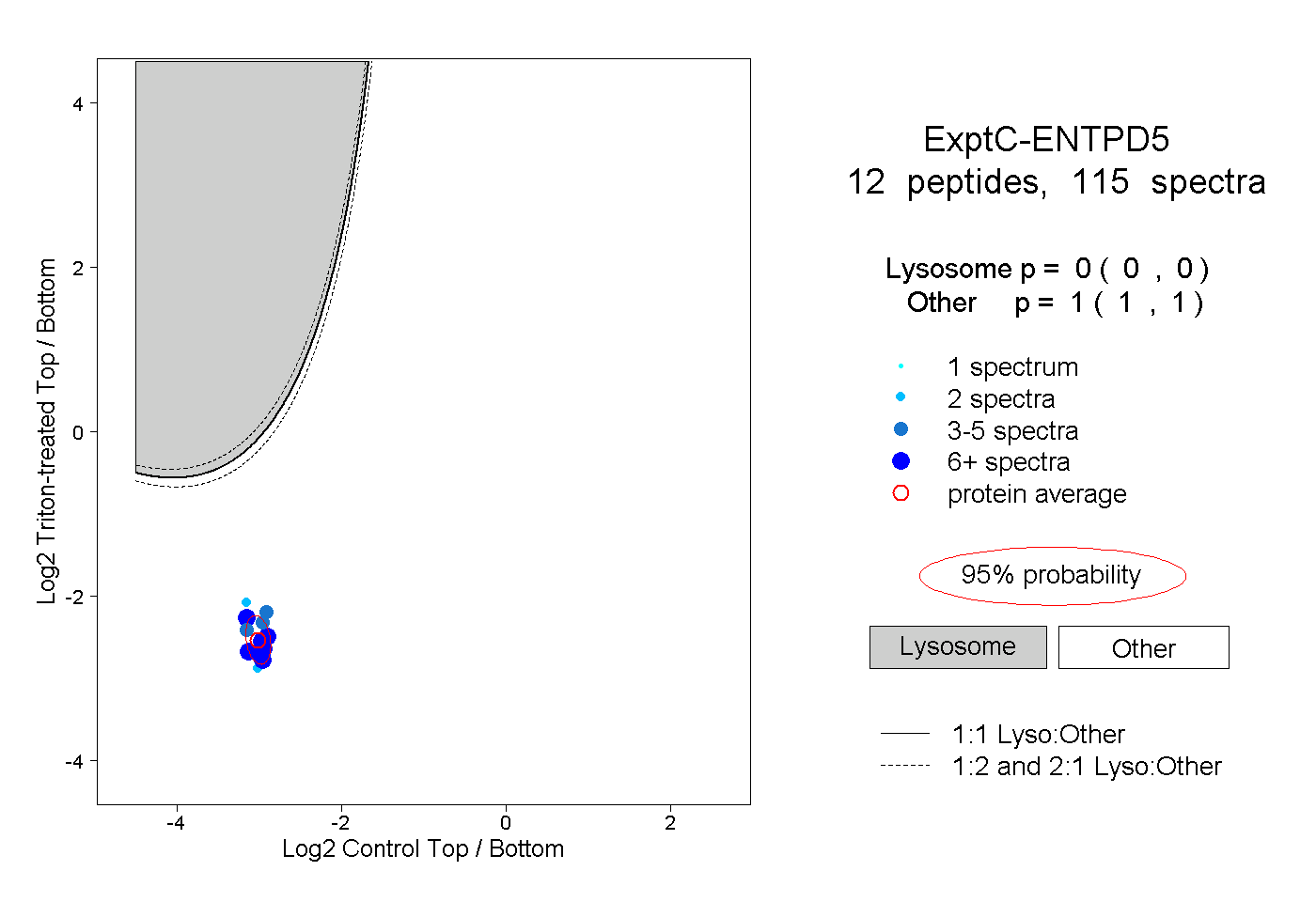 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
19 spectra |
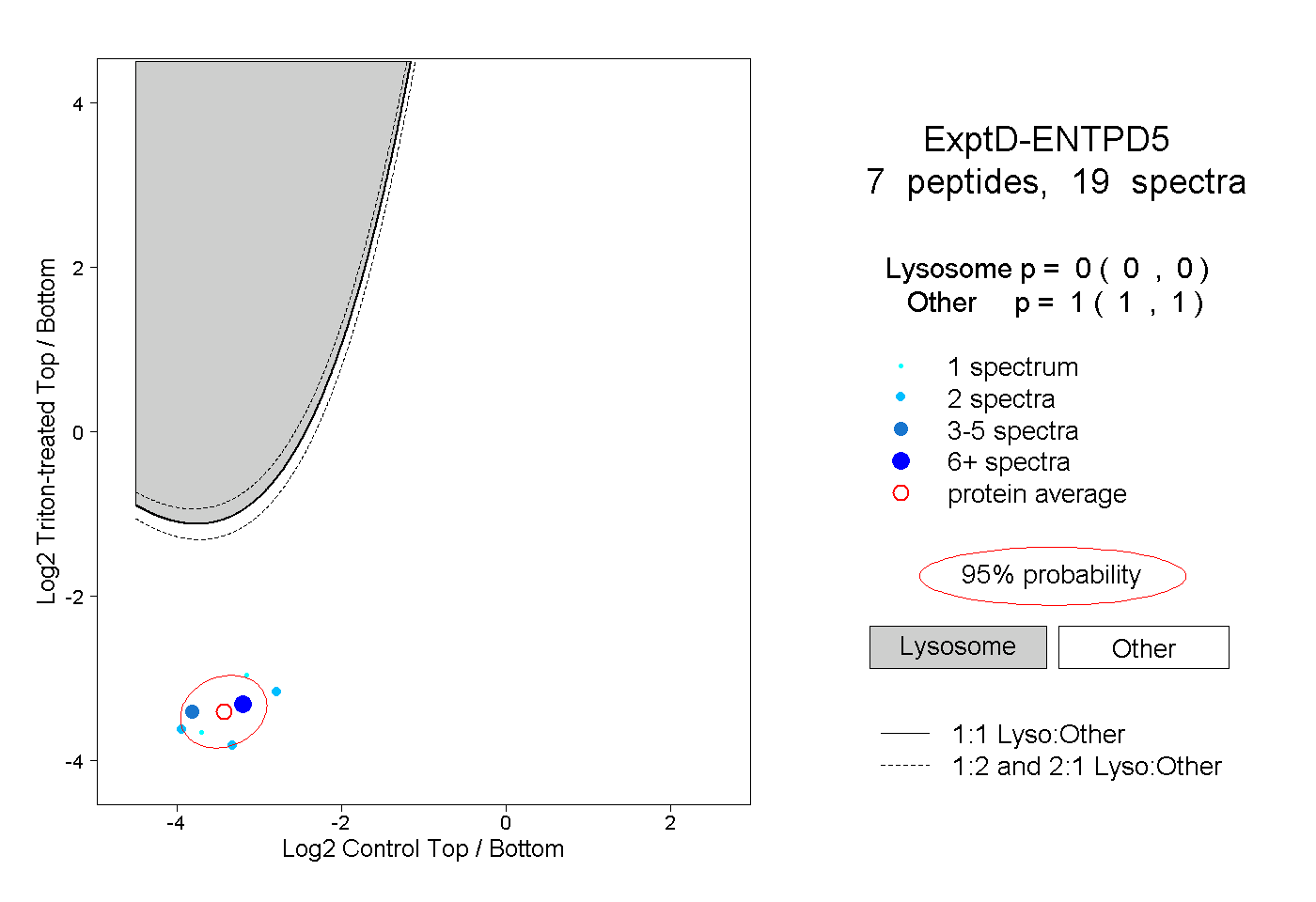 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |