peptides
spectra
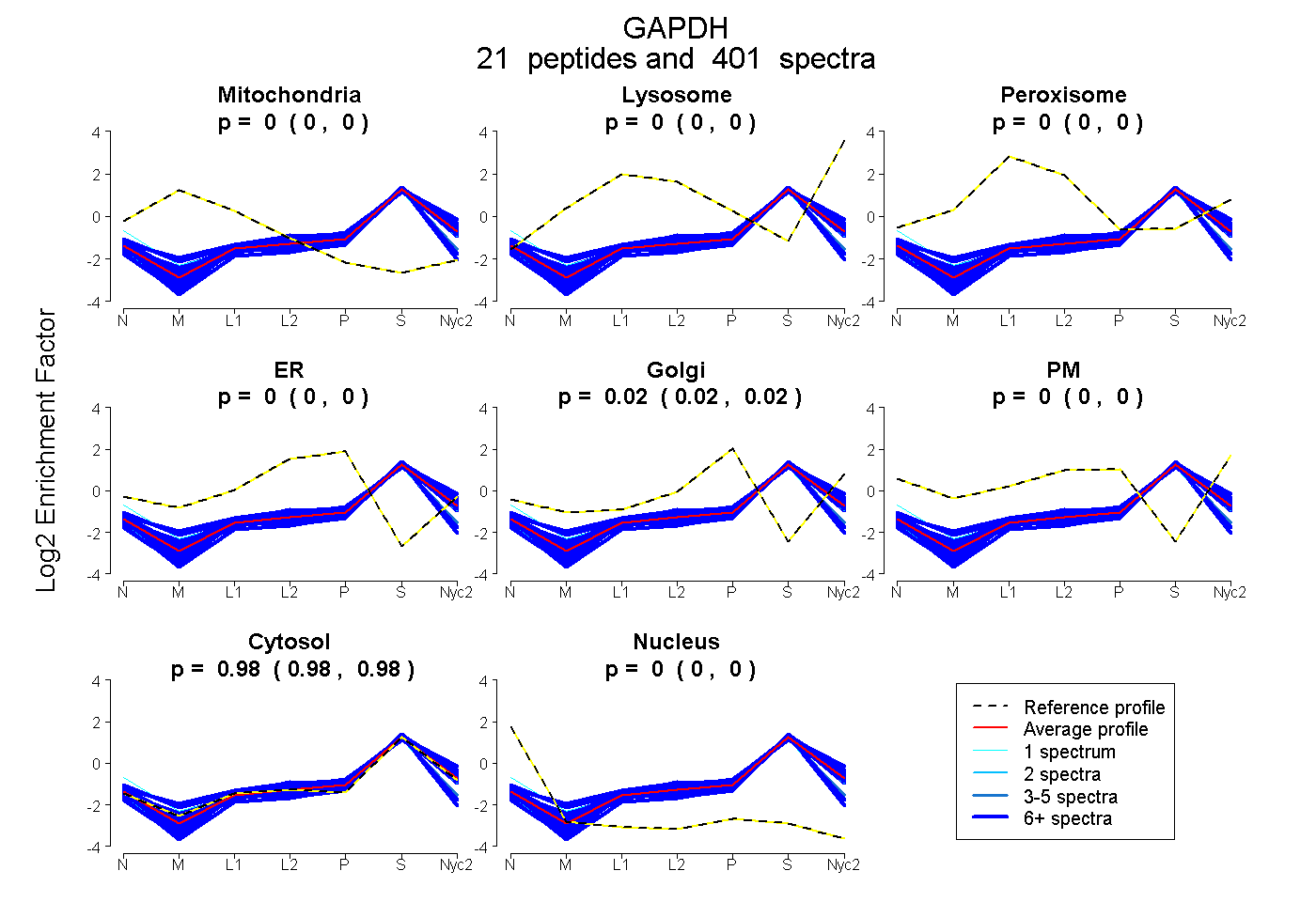
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.021 | 0.022
0.000 | 0.000
0.978 | 0.979
0.000 | 0.000
peptides
spectra
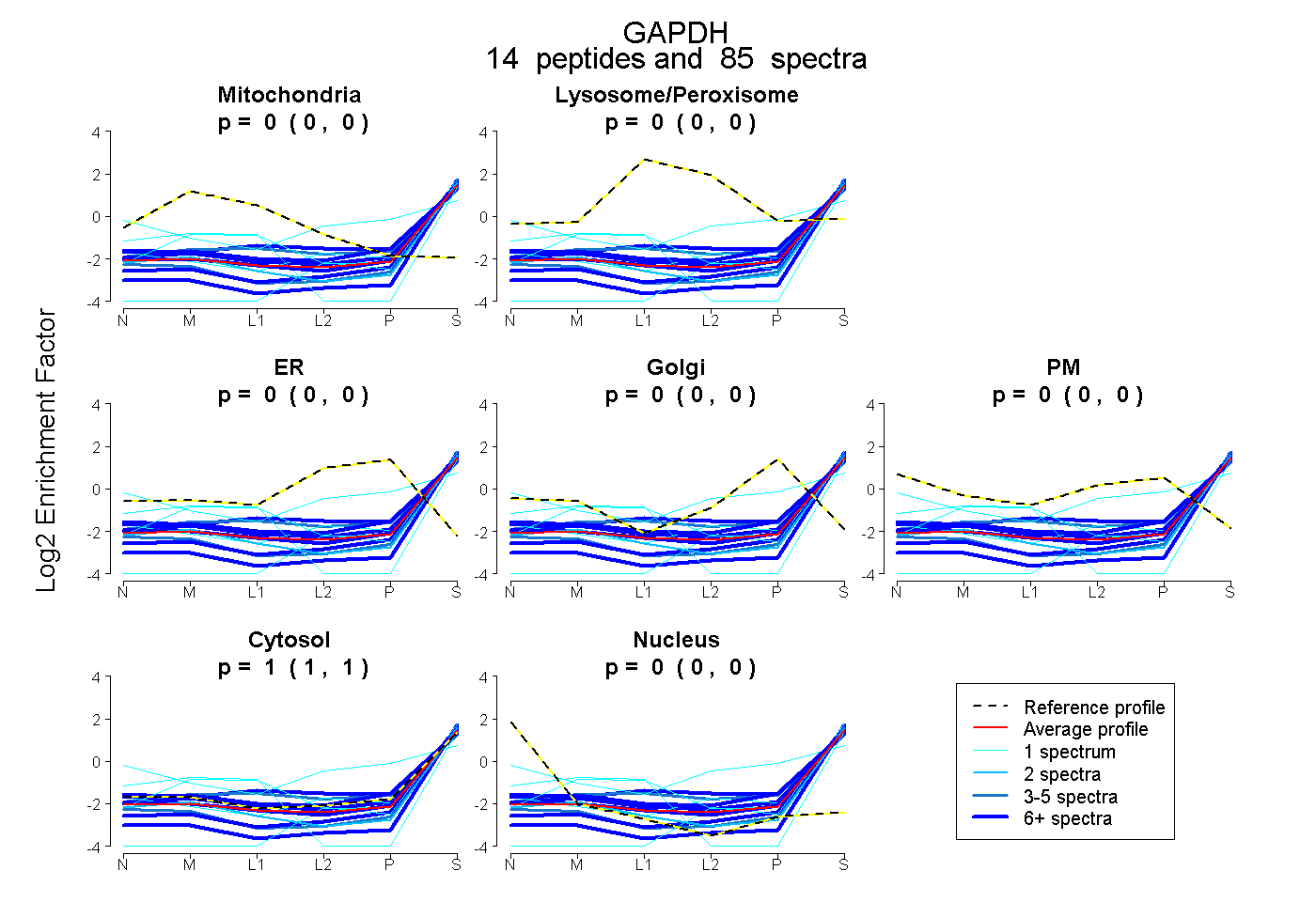
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
401 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.021 0.021 | 0.022 |
0.000 0.000 | 0.000 |
0.979 0.978 | 0.979 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
85 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 4 spectra, AGAHLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 9 spectra, VGVNGFGR | 0.000 | 0.026 | 0.000 | 0.020 | 0.000 | 0.954 | 0.000 | |||
| 9 spectra, LISWYDNEYGYSNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, YDNSLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 6 spectra, VPTPNVSVVDLTCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LTGTAFR | 0.000 | 0.104 | 0.000 | 0.034 | 0.359 | 0.503 | 0.000 | |||
| 1 spectrum, VIPELNGK | 0.101 | 0.000 | 0.000 | 0.000 | 0.000 | 0.756 | 0.143 | |||
| 23 spectra, LTGMAFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VVDLMAYMASK | 0.141 | 0.038 | 0.000 | 0.000 | 0.000 | 0.821 | 0.000 | |||
| 1 spectrum, VIHDNFGIVEGLMTTVHAITATQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 5 spectra, IVSNASCTTNCLAPLAK | 0.000 | 0.107 | 0.000 | 0.000 | 0.000 | 0.893 | 0.000 | |||
| 16 spectra, GAAQNIIPASTGAAK | 0.000 | 0.143 | 0.000 | 0.000 | 0.000 | 0.857 | 0.000 | |||
| 6 spectra, LVINGKPITIFQER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, TVDGPSGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
782 spectra |
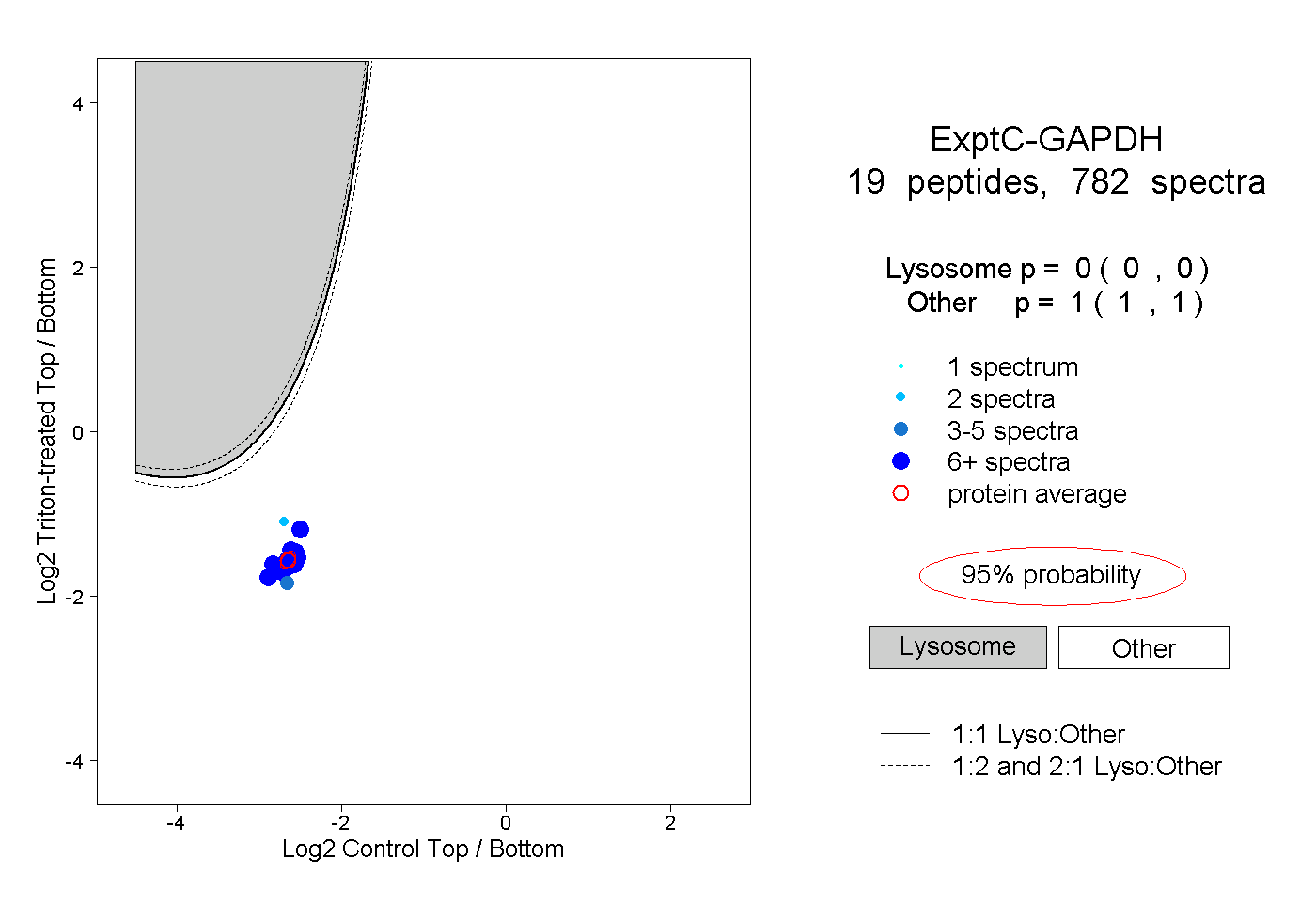 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
34 spectra |
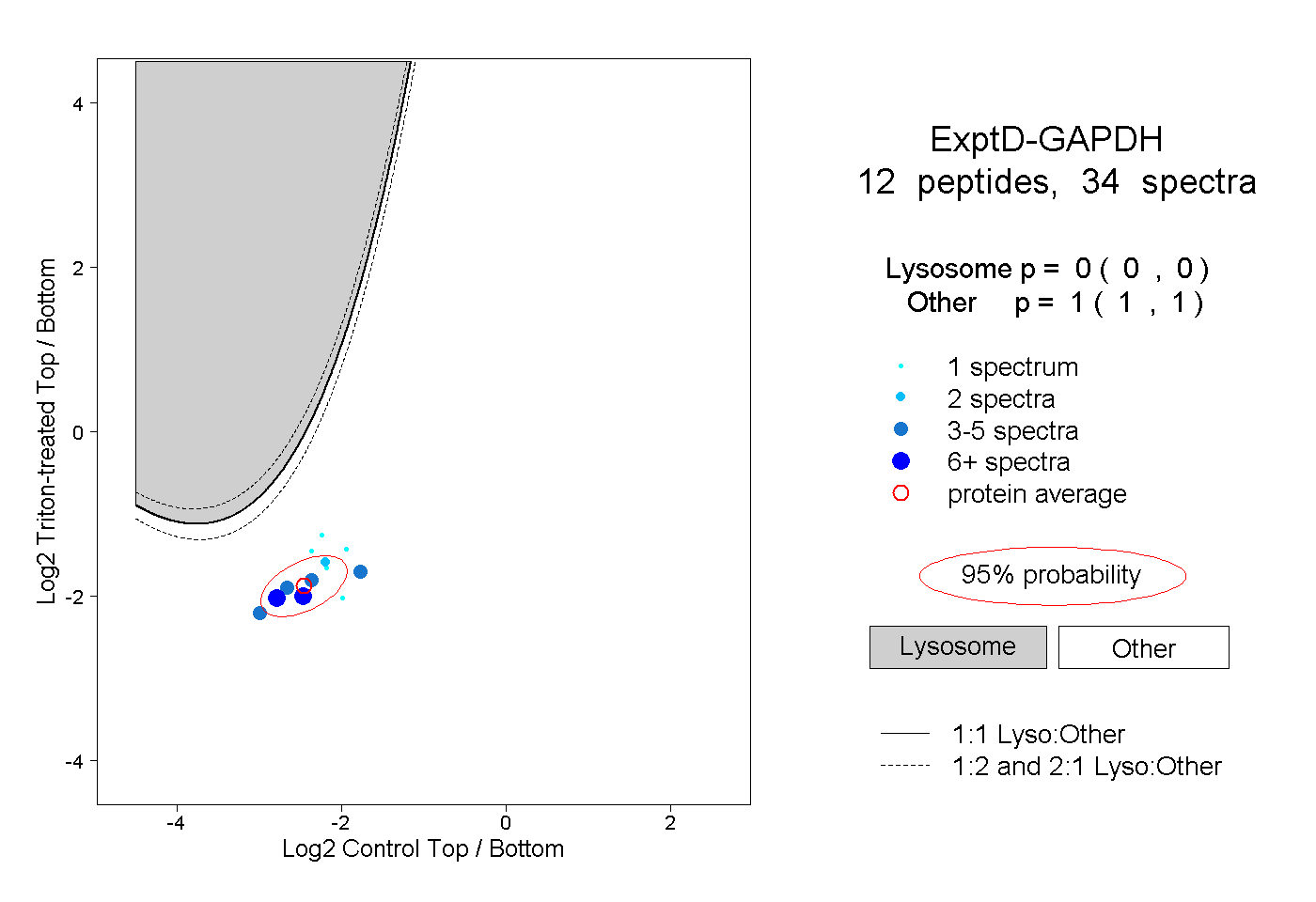 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |