peptides
spectra
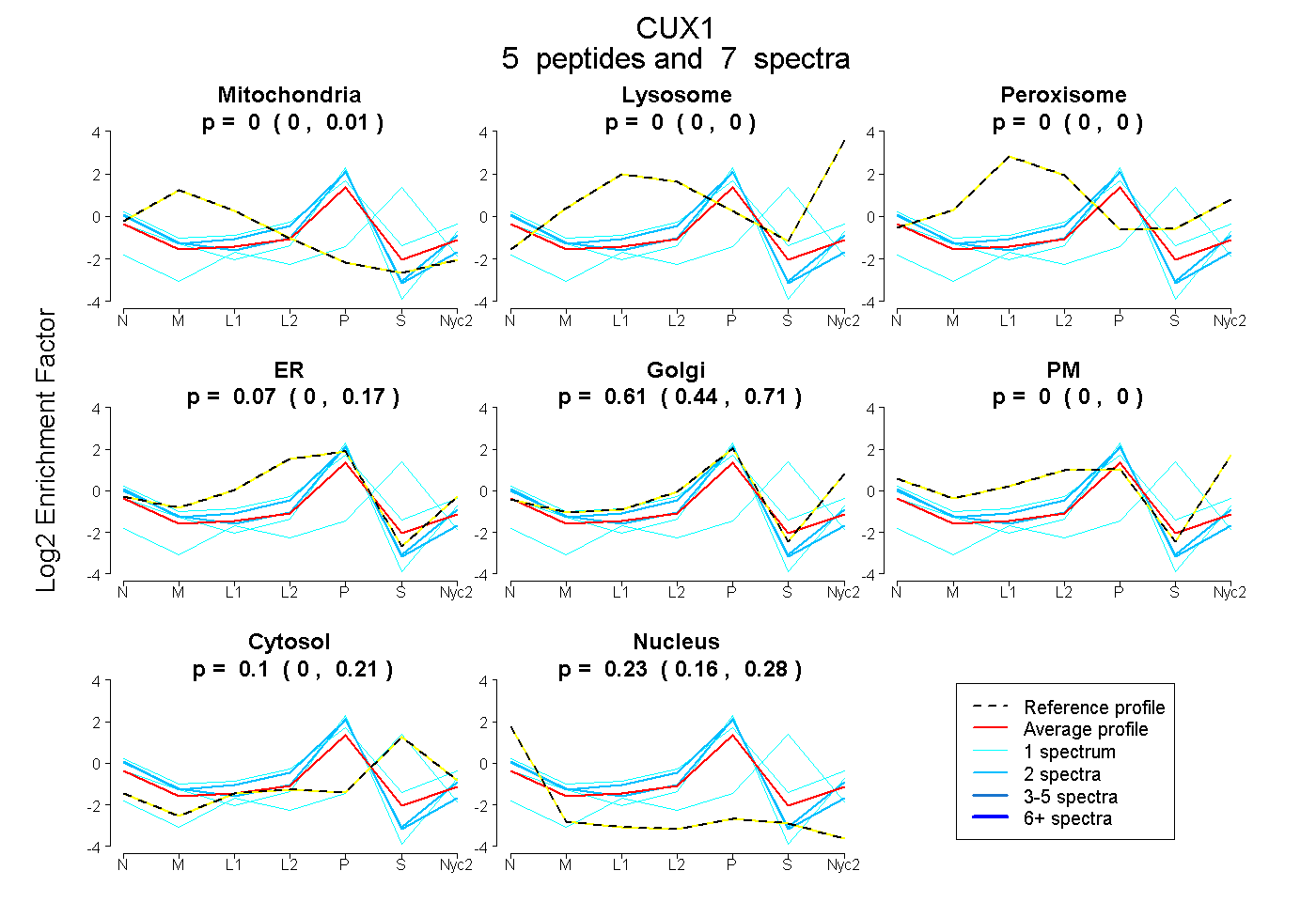
0.000 | 0.008
0.000 | 0.000
0.000 | 0.000
0.000 | 0.171
0.442 | 0.713
0.000 | 0.000
0.000 | 0.207
0.160 | 0.281
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
7 spectra |
 |
0.000 0.000 | 0.008 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.072 0.000 | 0.171 |
0.605 0.442 | 0.713 |
0.000 0.000 | 0.000 |
0.098 0.000 | 0.207 |
0.225 0.160 | 0.281 |
| 1 spectrum, LHDIETENQK | 0.000 | 0.000 | 0.000 | 0.242 | 0.537 | 0.000 | 0.145 | 0.076 | ||
| 2 spectra, LEEAEHK | 0.000 | 0.000 | 0.000 | 0.216 | 0.515 | 0.000 | 0.000 | 0.269 | ||
| 1 spectrum, APDVEQAIEVLTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.917 | 0.083 | ||
| 2 spectra, SLQSENATLR | 0.000 | 0.000 | 0.000 | 0.307 | 0.516 | 0.000 | 0.000 | 0.177 | ||
| 1 spectrum, FADHLHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.794 | 0.000 | 0.000 | 0.206 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
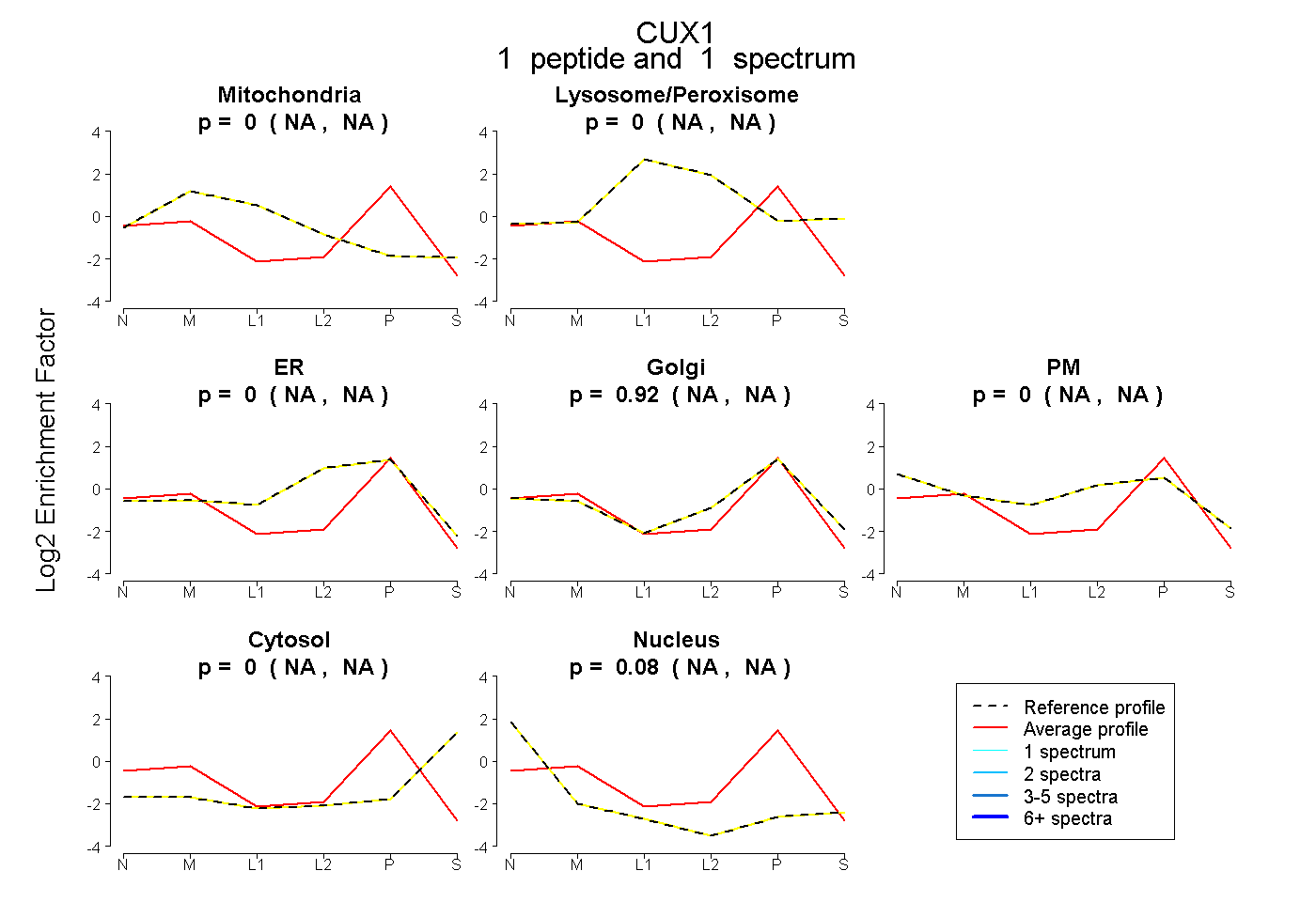 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.916 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.084 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3 spectra |
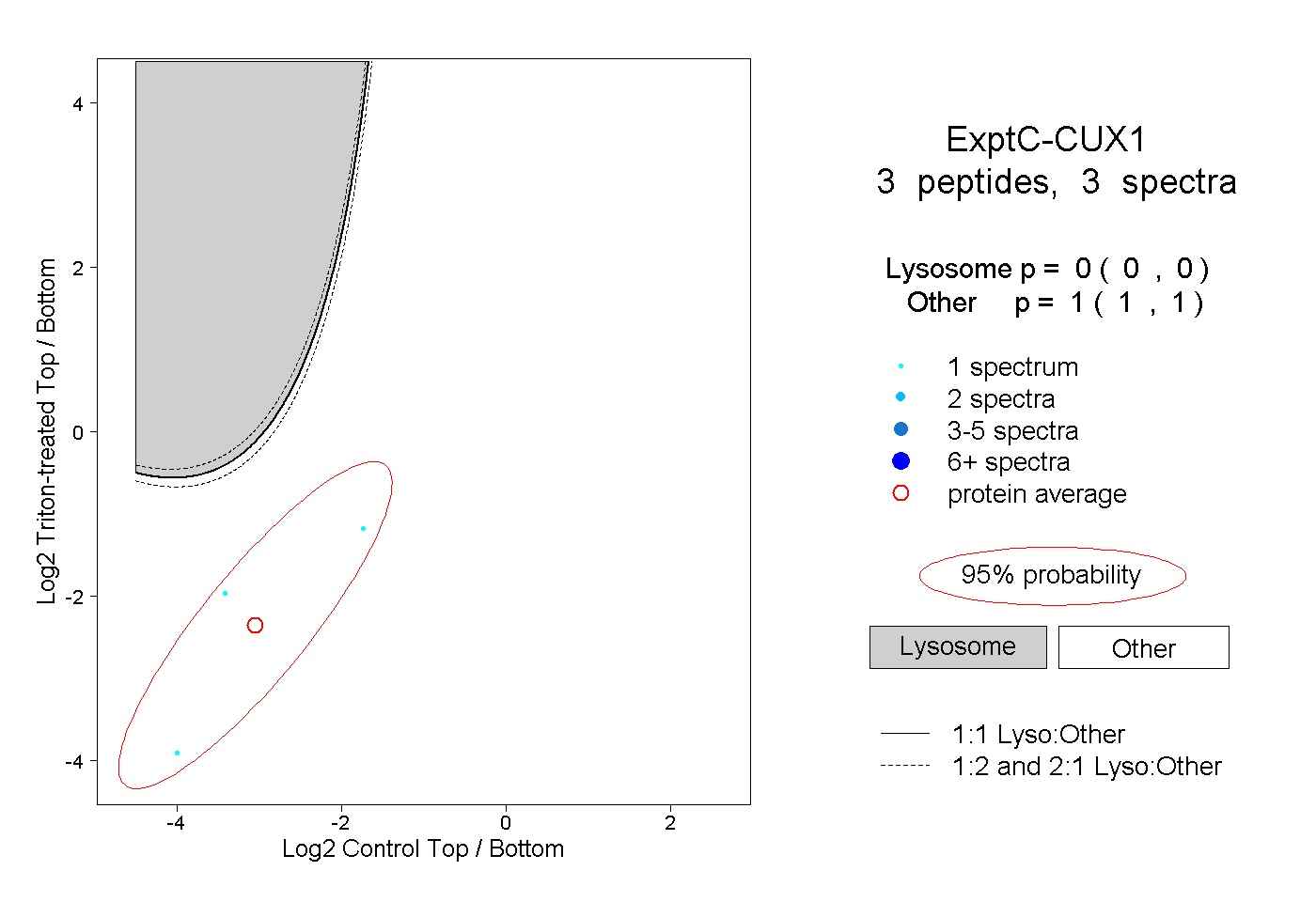 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |