peptides
spectra
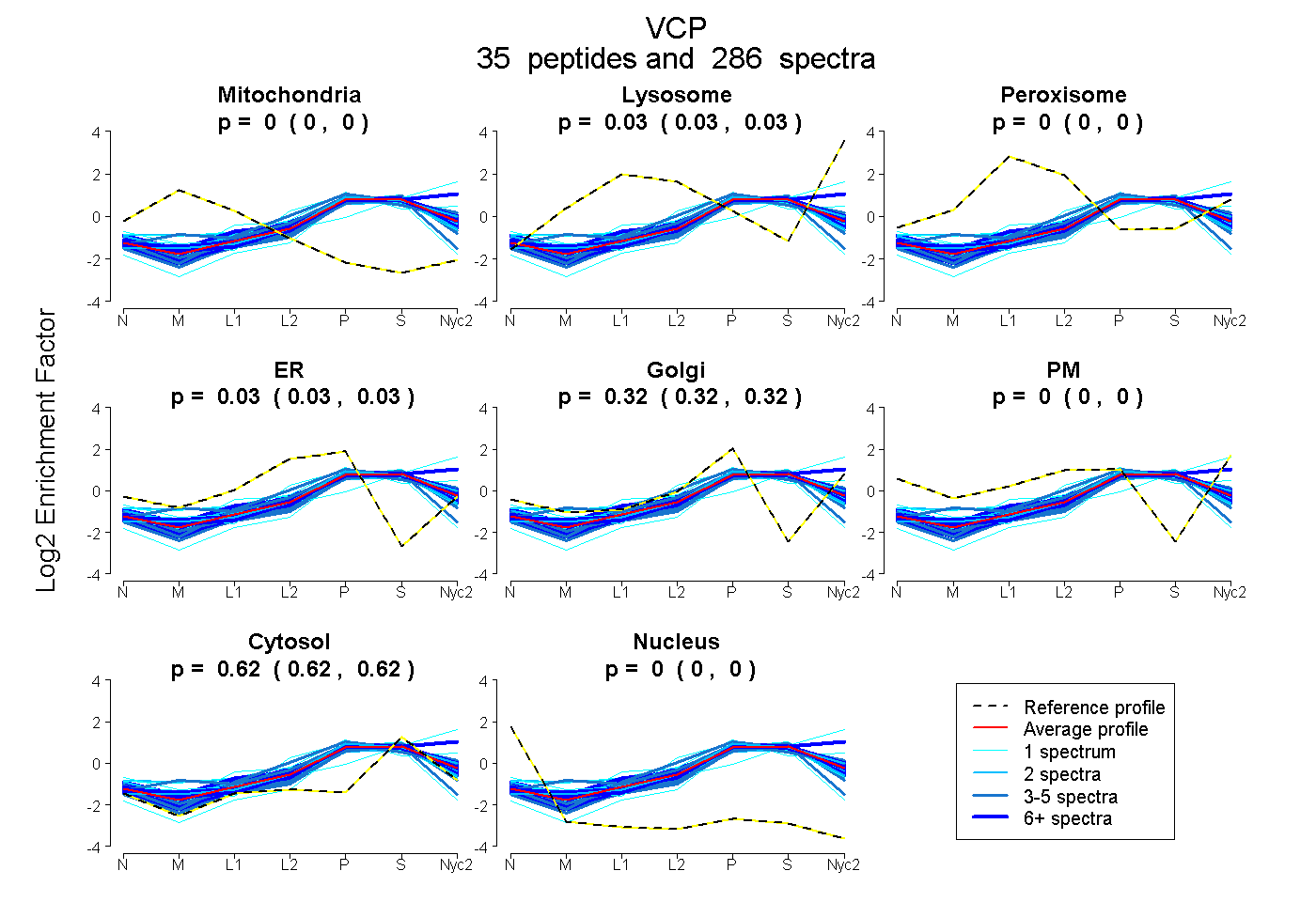
0.000 | 0.000
0.026 | 0.029
0.000 | 0.000
0.026 | 0.033
0.316 | 0.323
0.000 | 0.000
0.622 | 0.624
0.000 | 0.000
peptides
spectra
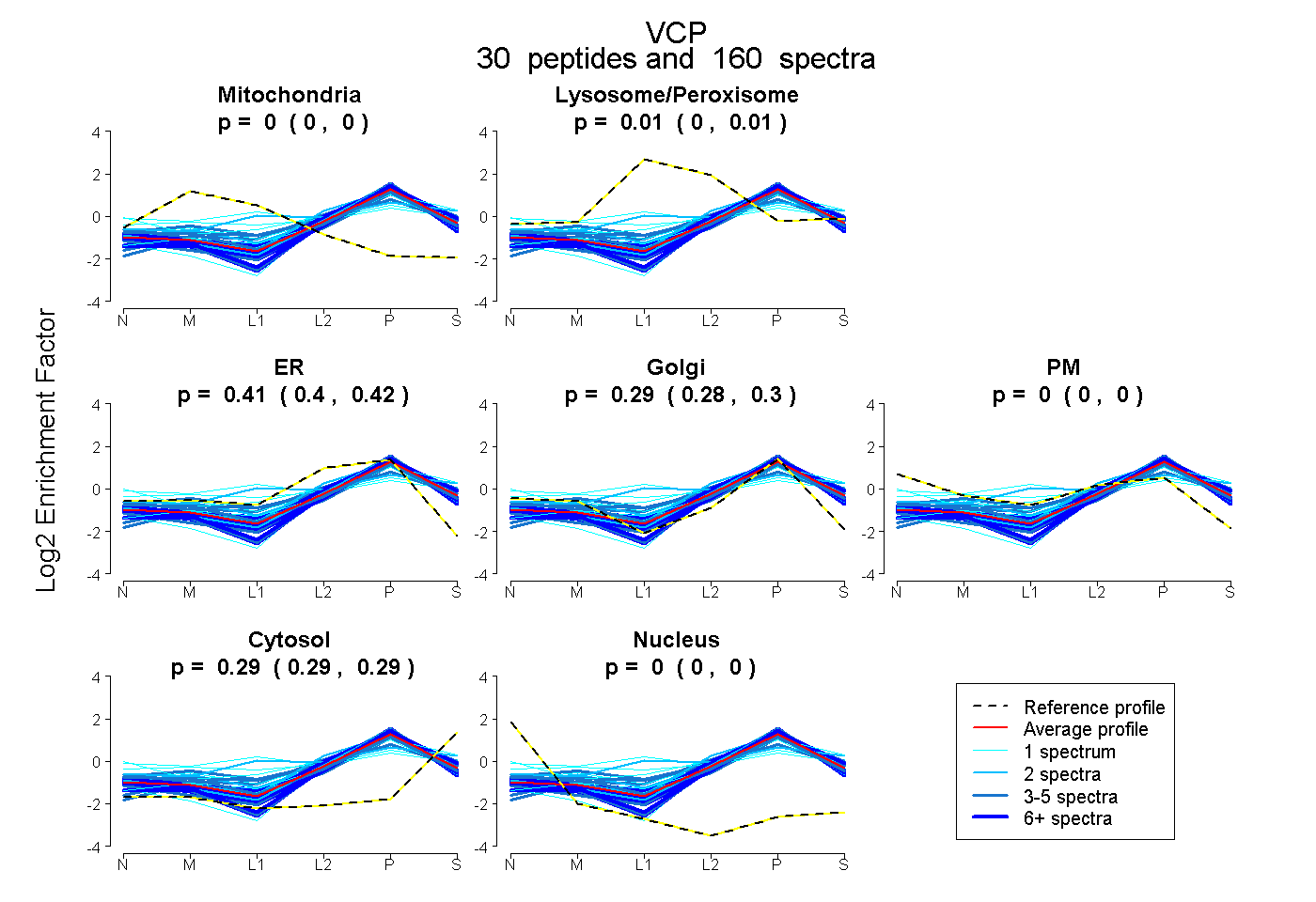
0.000 | 0.000
0.004 | 0.014
0.402 | 0.420
0.281 | 0.295
0.000 | 0.000
0.287 | 0.293
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
286 spectra |
 |
0.000 0.000 | 0.000 |
0.028 0.026 | 0.029 |
0.000 0.000 | 0.000 |
0.030 0.026 | 0.033 |
0.320 0.316 | 0.323 |
0.000 0.000 | 0.000 |
0.623 0.622 | 0.624 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
160 spectra |
 |
0.000 0.000 | 0.000 |
0.009 0.004 | 0.014 |
0.412 0.402 | 0.420 |
0.289 0.281 | 0.295 |
0.000 0.000 | 0.000 |
0.290 0.287 | 0.293 |
0.000 0.000 | 0.000 |
| 7 spectra, ESIESEIR | 0.000 | 0.000 | 0.450 | 0.273 | 0.000 | 0.277 | 0.000 | |||
| 15 spectra, AIGVKPPR | 0.000 | 0.068 | 0.288 | 0.449 | 0.000 | 0.195 | 0.000 | |||
| 2 spectra, IVSQLLTLMDGLK | 0.000 | 0.000 | 0.632 | 0.038 | 0.000 | 0.330 | 0.000 | |||
| 4 spectra, GLLLYGPPGTGK | 0.000 | 0.264 | 0.000 | 0.586 | 0.000 | 0.150 | 0.000 | |||
| 1 spectrum, ELQELVQYPVEHPDK | 0.000 | 0.000 | 0.174 | 0.564 | 0.000 | 0.262 | 0.000 | |||
| 2 spectra, EAVCIVLSDDTCSDEK | 0.000 | 0.167 | 0.142 | 0.510 | 0.000 | 0.180 | 0.000 | |||
| 1 spectrum, AVANETGAFFFLINGPEIMSK | 0.000 | 0.209 | 0.072 | 0.616 | 0.000 | 0.103 | 0.000 | |||
| 5 spectra, LAGESESNLR | 0.000 | 0.000 | 0.144 | 0.611 | 0.000 | 0.245 | 0.000 | |||
| 1 spectrum, GDTVLLK | 0.000 | 0.068 | 0.259 | 0.468 | 0.000 | 0.205 | 0.000 | |||
| 4 spectra, WALSQSNPSALR | 0.000 | 0.114 | 0.127 | 0.554 | 0.000 | 0.205 | 0.000 | |||
| 2 spectra, QIAQLK | 0.000 | 0.000 | 0.371 | 0.410 | 0.000 | 0.219 | 0.000 | |||
| 8 spectra, GFGSFR | 0.000 | 0.000 | 0.228 | 0.537 | 0.000 | 0.235 | 0.000 | |||
| 1 spectrum, VINQILTEMDGMSTK | 0.000 | 0.125 | 0.236 | 0.268 | 0.000 | 0.371 | 0.000 | |||
| 1 spectrum, FGMTPSK | 0.000 | 0.375 | 0.000 | 0.412 | 0.000 | 0.212 | 0.000 | |||
| 3 spectra, GVLFYGPPGCGK | 0.000 | 0.289 | 0.000 | 0.524 | 0.000 | 0.187 | 0.000 | |||
| 3 spectra, AIANECQANFISIK | 0.000 | 0.135 | 0.000 | 0.631 | 0.000 | 0.235 | 0.000 | |||
| 9 spectra, NVFIIGATNRPDIIDPAILRPGR | 0.000 | 0.000 | 0.406 | 0.352 | 0.000 | 0.242 | 0.000 | |||
| 5 spectra, AHVIVMAATNRPNSIDPALR | 0.000 | 0.058 | 0.588 | 0.000 | 0.000 | 0.354 | 0.000 | |||
| 4 spectra, DHFEEAMR | 0.000 | 0.000 | 0.482 | 0.164 | 0.000 | 0.354 | 0.000 | |||
| 5 spectra, GDIFLVR | 0.000 | 0.000 | 0.291 | 0.363 | 0.000 | 0.346 | 0.000 | |||
| 14 spectra, DVDLEFLAK | 0.000 | 0.116 | 0.200 | 0.471 | 0.000 | 0.214 | 0.000 | |||
| 8 spectra, QAAPCVLFFDELDSIAK | 0.000 | 0.000 | 0.279 | 0.463 | 0.000 | 0.258 | 0.000 | |||
| 1 spectrum, LGDVISIQPCPDVK | 0.000 | 0.311 | 0.000 | 0.530 | 0.063 | 0.095 | 0.000 | |||
| 4 spectra, LEILQIHTK | 0.000 | 0.000 | 0.314 | 0.422 | 0.000 | 0.265 | 0.000 | |||
| 12 spectra, EMVELPLR | 0.000 | 0.000 | 0.195 | 0.488 | 0.000 | 0.317 | 0.000 | |||
| 17 spectra, MDELQLFR | 0.000 | 0.000 | 0.512 | 0.146 | 0.000 | 0.342 | 0.000 | |||
| 2 spectra, MTNGFSGADLTEICQR | 0.000 | 0.439 | 0.000 | 0.338 | 0.000 | 0.223 | 0.000 | |||
| 1 spectrum, GDDLSTAILK | 0.000 | 0.415 | 0.000 | 0.249 | 0.150 | 0.186 | 0.000 | |||
| 8 spectra, GGNIGDGGGAADR | 0.000 | 0.000 | 0.296 | 0.487 | 0.000 | 0.217 | 0.000 | |||
| 10 spectra, SVSDNDIR | 0.000 | 0.000 | 0.177 | 0.590 | 0.000 | 0.233 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
381 spectra |
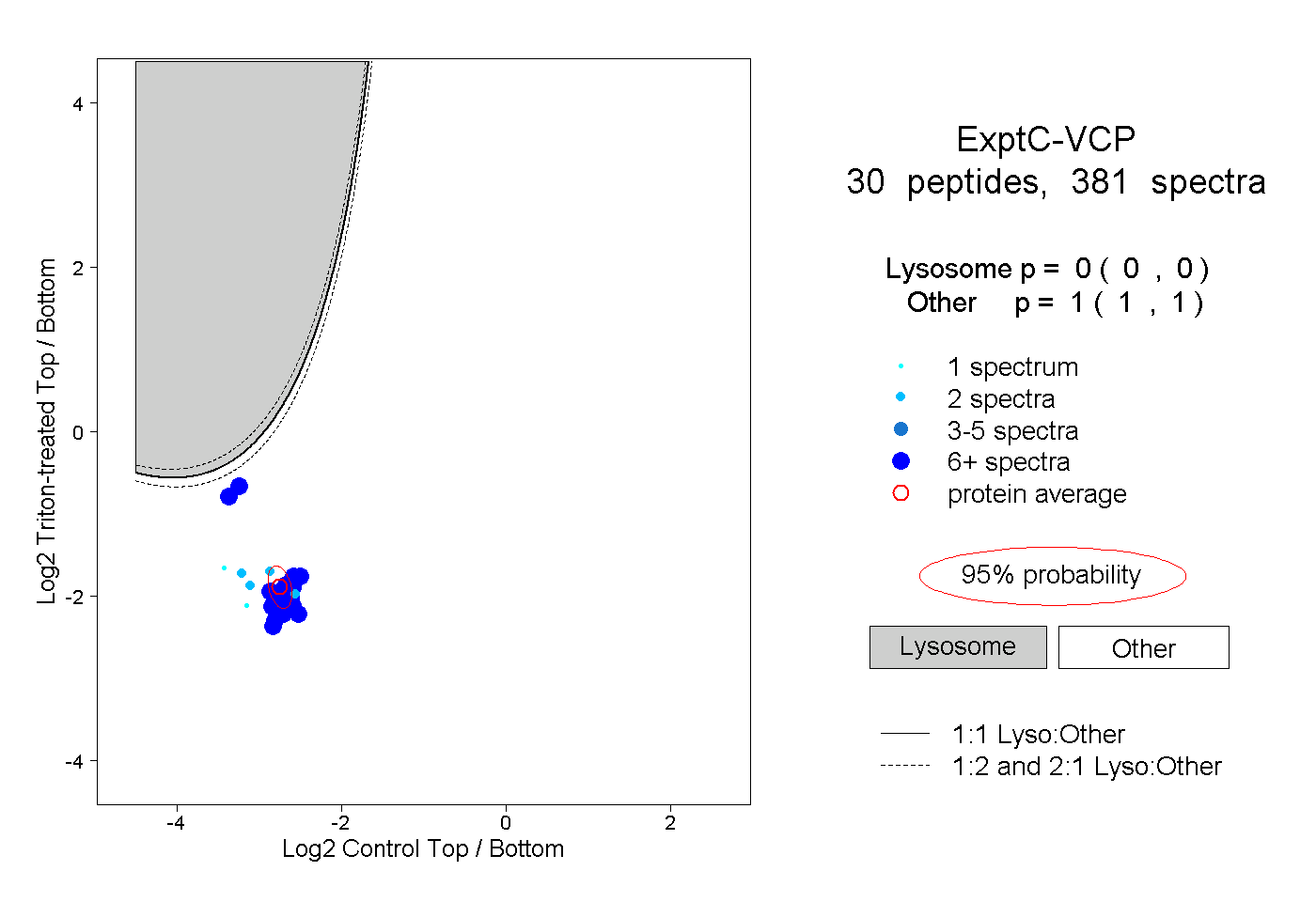 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
57 spectra |
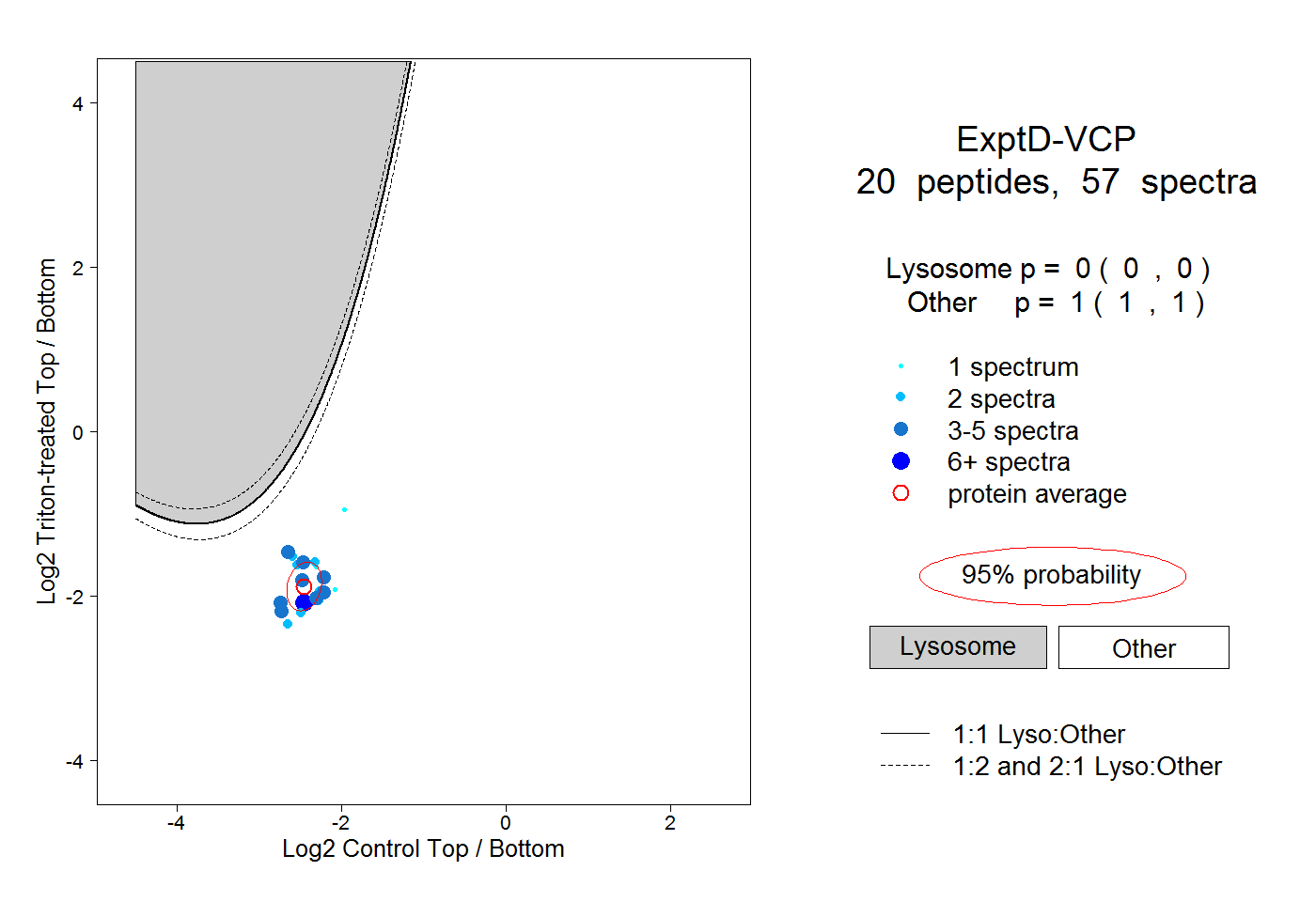 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |