peptides
spectra
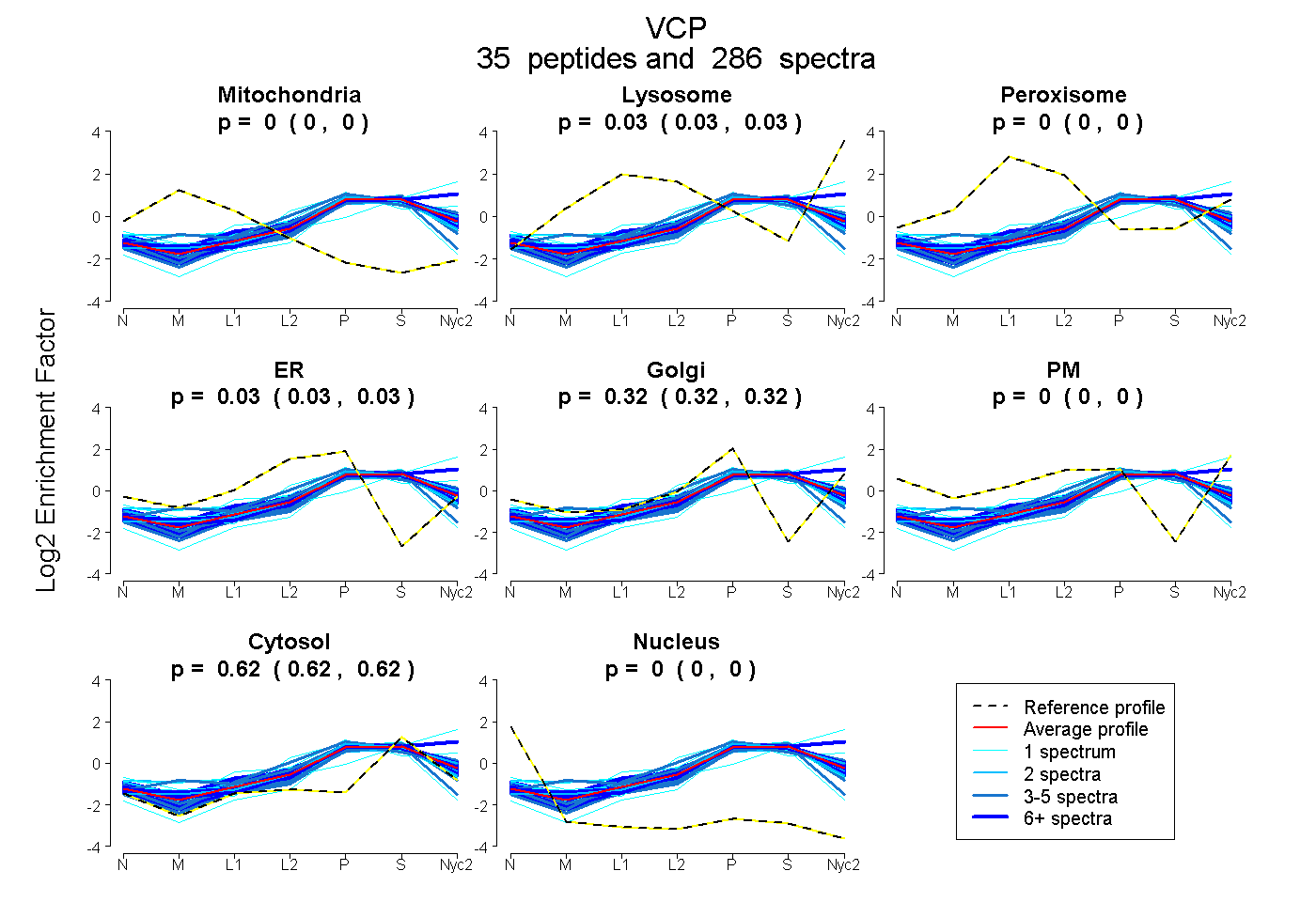
0.000 | 0.000
0.026 | 0.029
0.000 | 0.000
0.026 | 0.033
0.316 | 0.323
0.000 | 0.000
0.622 | 0.624
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
286 spectra |
 |
0.000 0.000 | 0.000 |
0.028 0.026 | 0.029 |
0.000 0.000 | 0.000 |
0.030 0.026 | 0.033 |
0.320 0.316 | 0.323 |
0.000 0.000 | 0.000 |
0.623 0.622 | 0.624 |
0.000 0.000 | 0.000 |
| 15 spectra, ESIESEIR | 0.000 | 0.011 | 0.000 | 0.026 | 0.319 | 0.000 | 0.644 | 0.000 | ||
| 35 spectra, AIGVKPPR | 0.000 | 0.000 | 0.000 | 0.065 | 0.285 | 0.000 | 0.650 | 0.000 | ||
| 2 spectra, YEMFAQTLQQSR | 0.000 | 0.052 | 0.000 | 0.000 | 0.365 | 0.000 | 0.583 | 0.000 | ||
| 1 spectrum, IVSQLLTLMDGLK | 0.000 | 0.154 | 0.023 | 0.000 | 0.409 | 0.000 | 0.414 | 0.000 | ||
| 3 spectra, GLLLYGPPGTGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.288 | 0.000 | 0.712 | 0.000 | ||
| 2 spectra, ELQELVQYPVEHPDK | 0.000 | 0.026 | 0.099 | 0.000 | 0.359 | 0.000 | 0.516 | 0.000 | ||
| 2 spectra, EAVCIVLSDDTCSDEK | 0.000 | 0.000 | 0.014 | 0.237 | 0.089 | 0.000 | 0.659 | 0.000 | ||
| 1 spectrum, LAGESESNLR | 0.000 | 0.338 | 0.000 | 0.000 | 0.153 | 0.000 | 0.509 | 0.000 | ||
| 1 spectrum, GDTVLLK | 0.000 | 0.208 | 0.000 | 0.000 | 0.235 | 0.000 | 0.557 | 0.000 | ||
| 22 spectra, WALSQSNPSALR | 0.000 | 0.048 | 0.000 | 0.016 | 0.333 | 0.000 | 0.604 | 0.000 | ||
| 6 spectra, QIAQLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.394 | 0.000 | 0.606 | 0.000 | ||
| 10 spectra, GFGSFR | 0.000 | 0.006 | 0.000 | 0.071 | 0.283 | 0.000 | 0.640 | 0.000 | ||
| 3 spectra, VINQILTEMDGMSTK | 0.000 | 0.116 | 0.000 | 0.053 | 0.317 | 0.000 | 0.514 | 0.000 | ||
| 12 spectra, FGMTPSK | 0.000 | 0.016 | 0.000 | 0.000 | 0.360 | 0.000 | 0.623 | 0.000 | ||
| 2 spectra, GVLFYGPPGCGK | 0.000 | 0.000 | 0.076 | 0.000 | 0.331 | 0.000 | 0.593 | 0.000 | ||
| 8 spectra, AFEEAEK | 0.000 | 0.011 | 0.082 | 0.000 | 0.352 | 0.000 | 0.555 | 0.000 | ||
| 1 spectrum, NAPAIIFIDELDAIAPK | 0.000 | 0.000 | 0.097 | 0.000 | 0.235 | 0.010 | 0.657 | 0.000 | ||
| 3 spectra, NVFIIGATNRPDIIDPAILRPGR | 0.000 | 0.076 | 0.000 | 0.121 | 0.242 | 0.000 | 0.561 | 0.000 | ||
| 7 spectra, EVDIGIPDATGR | 0.000 | 0.020 | 0.000 | 0.000 | 0.332 | 0.000 | 0.648 | 0.000 | ||
| 7 spectra, AHVIVMAATNRPNSIDPALR | 0.000 | 0.096 | 0.000 | 0.054 | 0.257 | 0.000 | 0.593 | 0.000 | ||
| 27 spectra, DHFEEAMR | 0.000 | 0.050 | 0.000 | 0.137 | 0.206 | 0.000 | 0.607 | 0.000 | ||
| 3 spectra, GDIFLVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.270 | 0.000 | 0.730 | 0.000 | ||
| 9 spectra, DVDLEFLAK | 0.000 | 0.000 | 0.000 | 0.018 | 0.335 | 0.000 | 0.647 | 0.000 | ||
| 24 spectra, HPALFK | 0.000 | 0.047 | 0.000 | 0.058 | 0.275 | 0.000 | 0.620 | 0.000 | ||
| 1 spectrum, GPELLTMWFGESEANVR | 0.000 | 0.000 | 0.000 | 0.042 | 0.340 | 0.000 | 0.618 | 0.000 | ||
| 4 spectra, QAAPCVLFFDELDSIAK | 0.000 | 0.000 | 0.000 | 0.238 | 0.025 | 0.000 | 0.737 | 0.000 | ||
| 1 spectrum, LDQLIYIPLPDEK | 0.000 | 0.006 | 0.000 | 0.070 | 0.295 | 0.000 | 0.630 | 0.000 | ||
| 2 spectra, LGDVISIQPCPDVK | 0.000 | 0.000 | 0.000 | 0.086 | 0.273 | 0.000 | 0.642 | 0.000 | ||
| 8 spectra, LEILQIHTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.346 | 0.000 | 0.654 | 0.000 | ||
| 22 spectra, EMVELPLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.358 | 0.000 | 0.642 | 0.000 | ||
| 17 spectra, MDELQLFR | 0.000 | 0.239 | 0.000 | 0.000 | 0.231 | 0.000 | 0.530 | 0.000 | ||
| 1 spectrum, MTNGFSGADLTEICQR | 0.000 | 0.000 | 0.000 | 0.401 | 0.000 | 0.000 | 0.599 | 0.000 | ||
| 8 spectra, SVSDNDIR | 0.000 | 0.048 | 0.000 | 0.000 | 0.349 | 0.000 | 0.603 | 0.000 | ||
| 1 spectrum, GDDLSTAILK | 0.000 | 0.000 | 0.000 | 0.000 | 0.235 | 0.000 | 0.765 | 0.000 | ||
| 15 spectra, GGNIGDGGGAADR | 0.000 | 0.000 | 0.000 | 0.016 | 0.315 | 0.000 | 0.669 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
160 spectra |
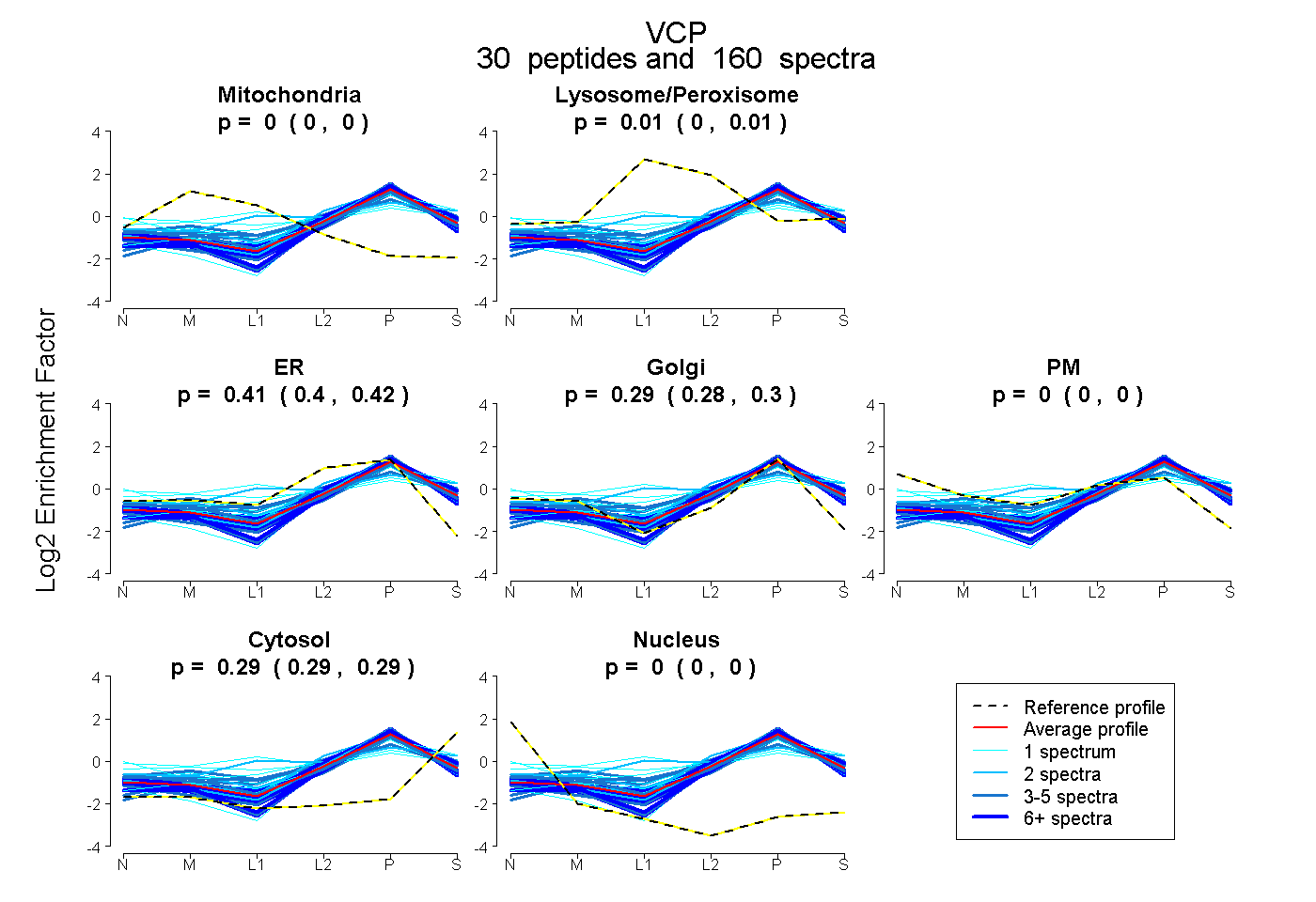 |
0.000 0.000 | 0.000 |
0.009 0.004 | 0.014 |
0.412 0.402 | 0.420 |
0.289 0.281 | 0.295 |
0.000 0.000 | 0.000 |
0.290 0.287 | 0.293 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
381 spectra |
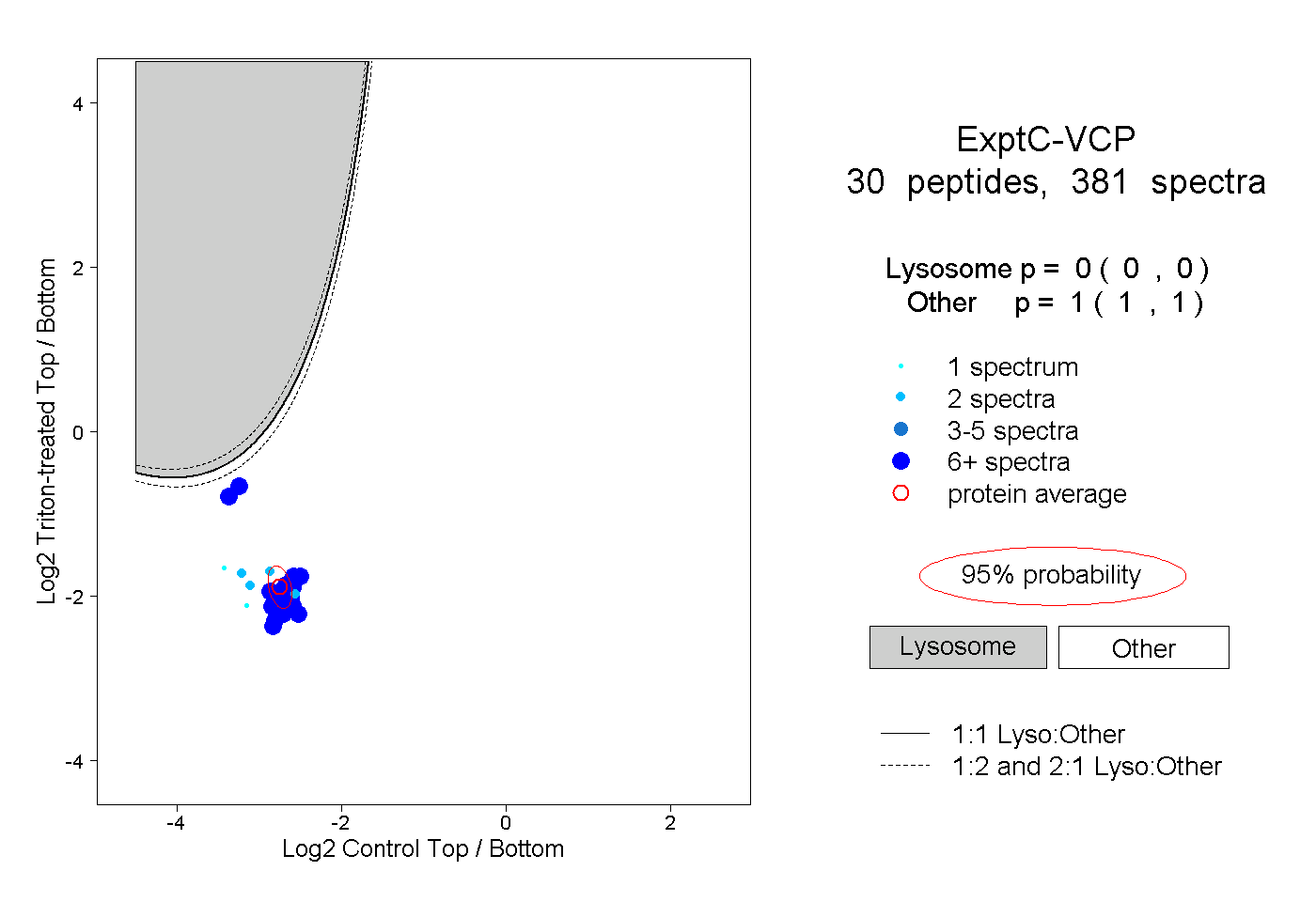 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
57 spectra |
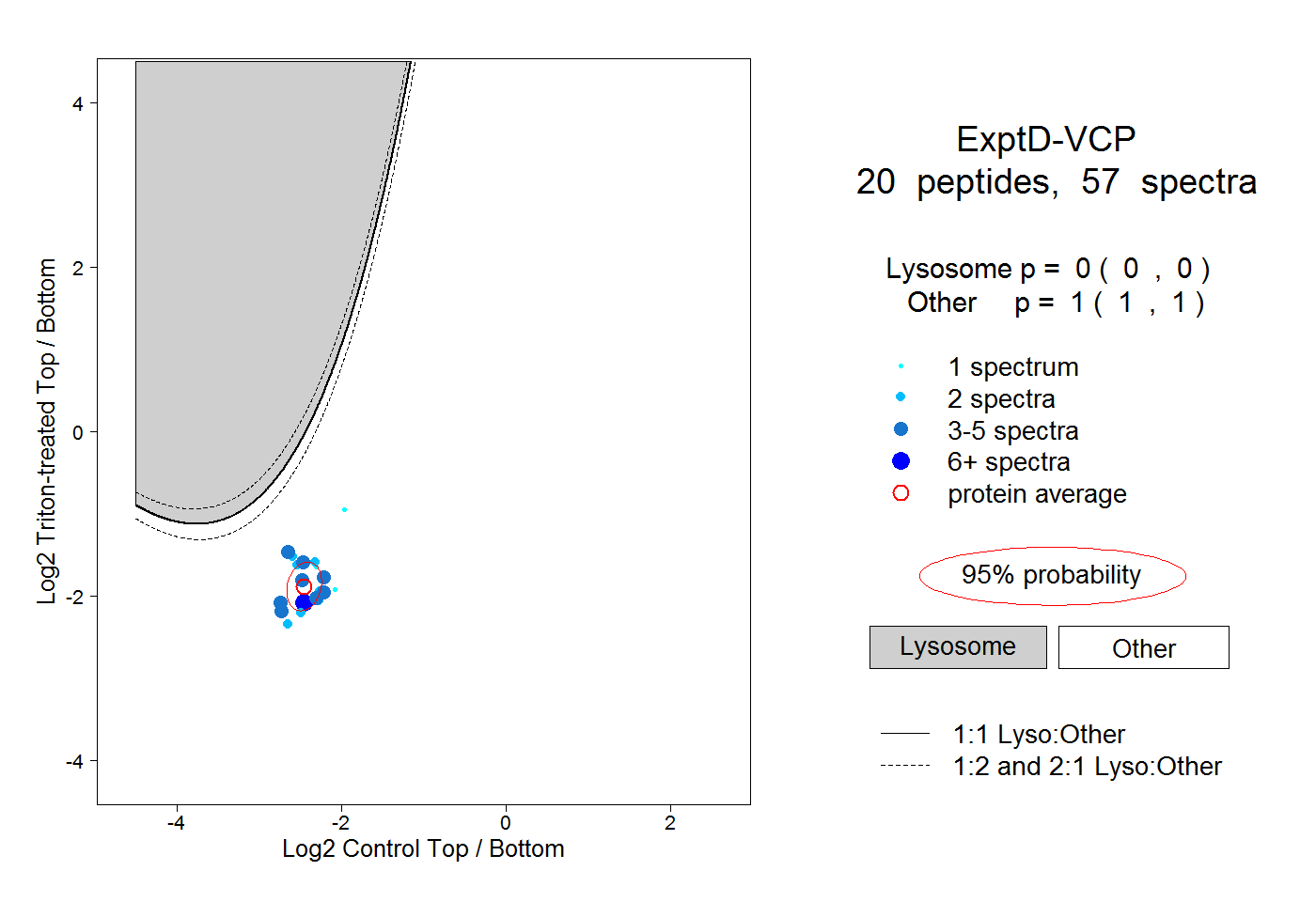 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |