STT3A
[ENSRNOP00000040087]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 23
23
peptides |
240
spectra |
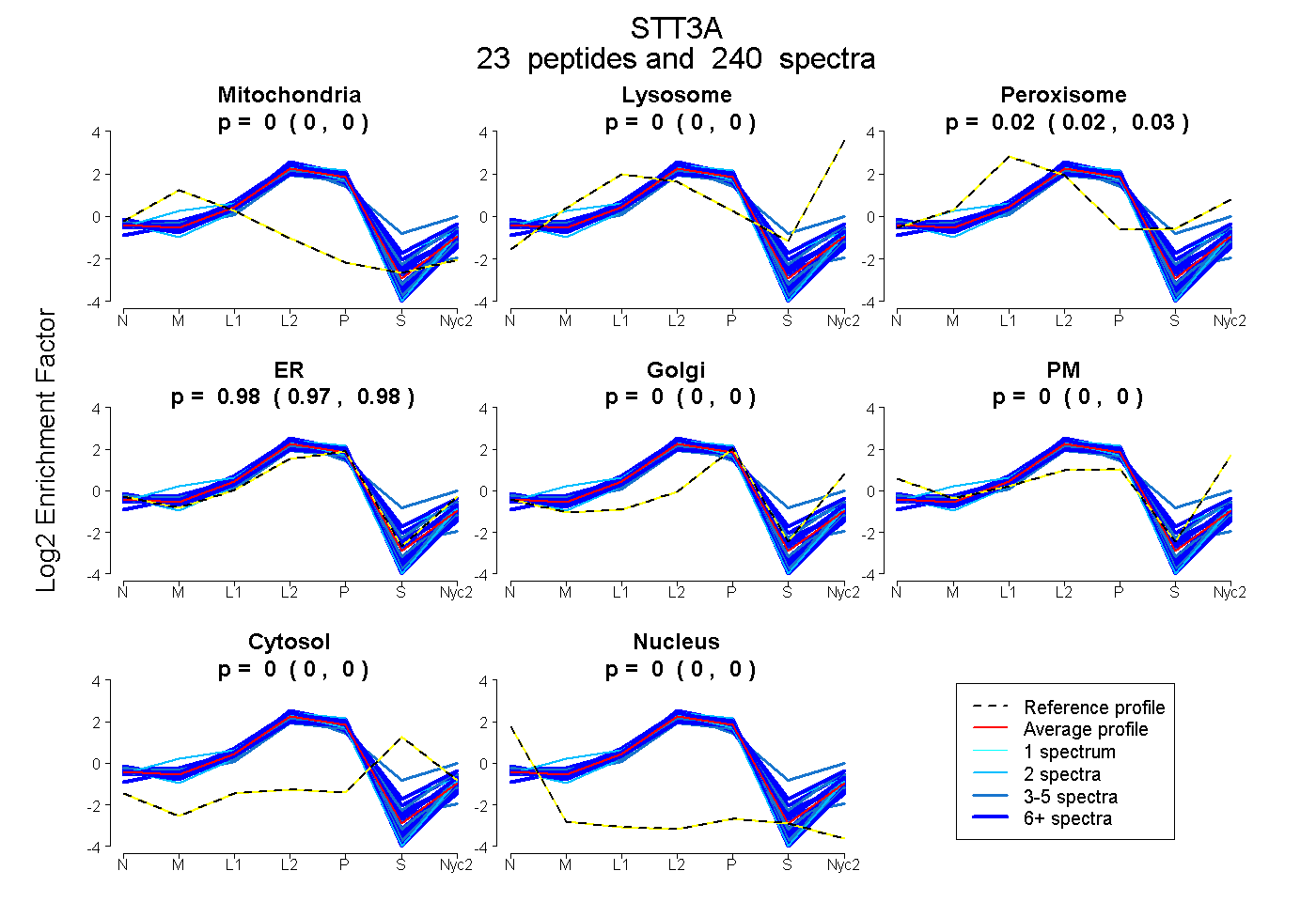 |
0.000
0.000 | 0.001 |
0.000
0.000 | 0.000 |
|
0.025
0.022 | 0.027 |
0.975
0.973 | 0.977 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 20
20
peptides |
80
spectra |
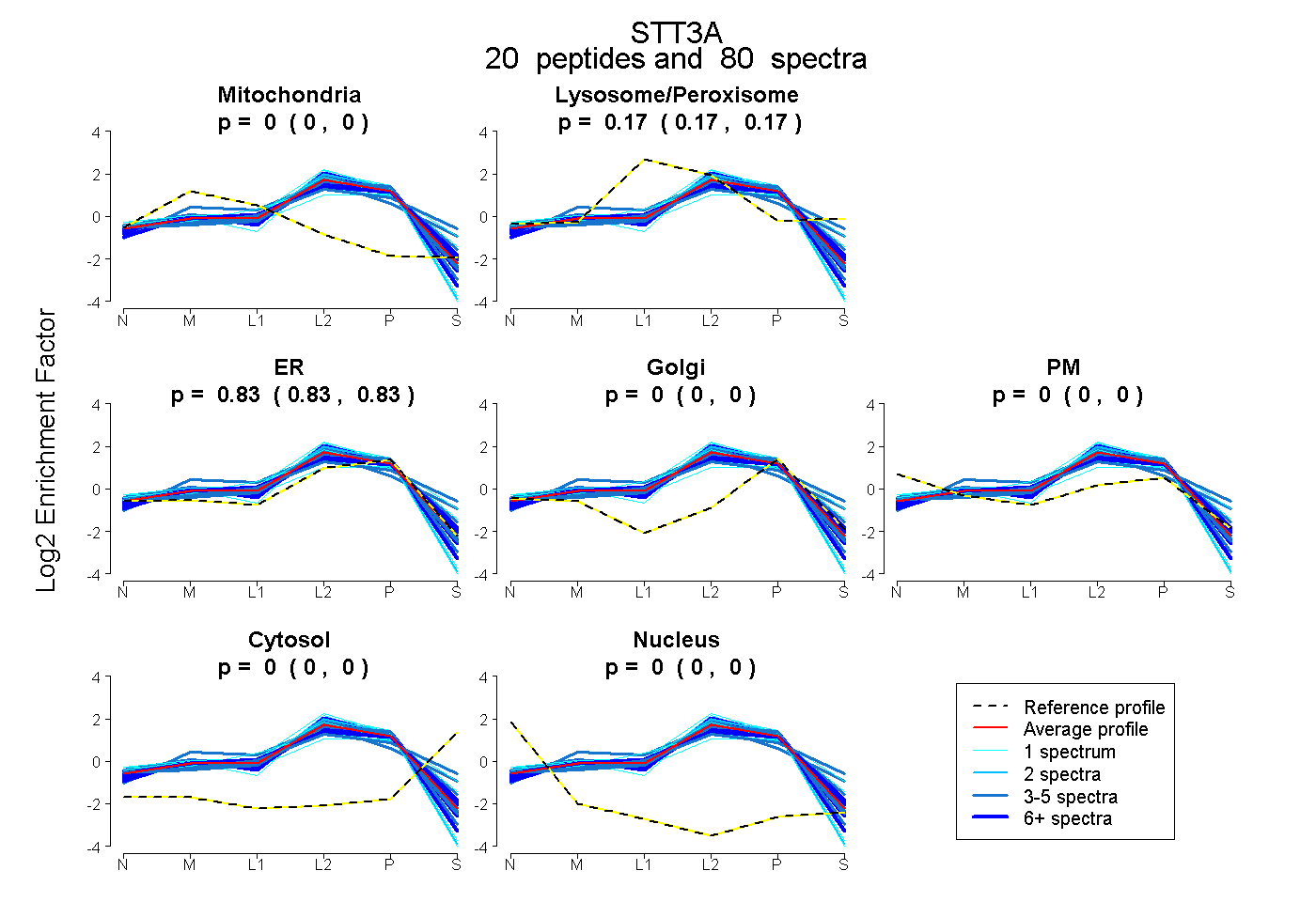 |
0.000
0.000 | 0.000 |
|
0.170
0.166 | 0.174 |
|
0.830
0.825 | 0.834 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
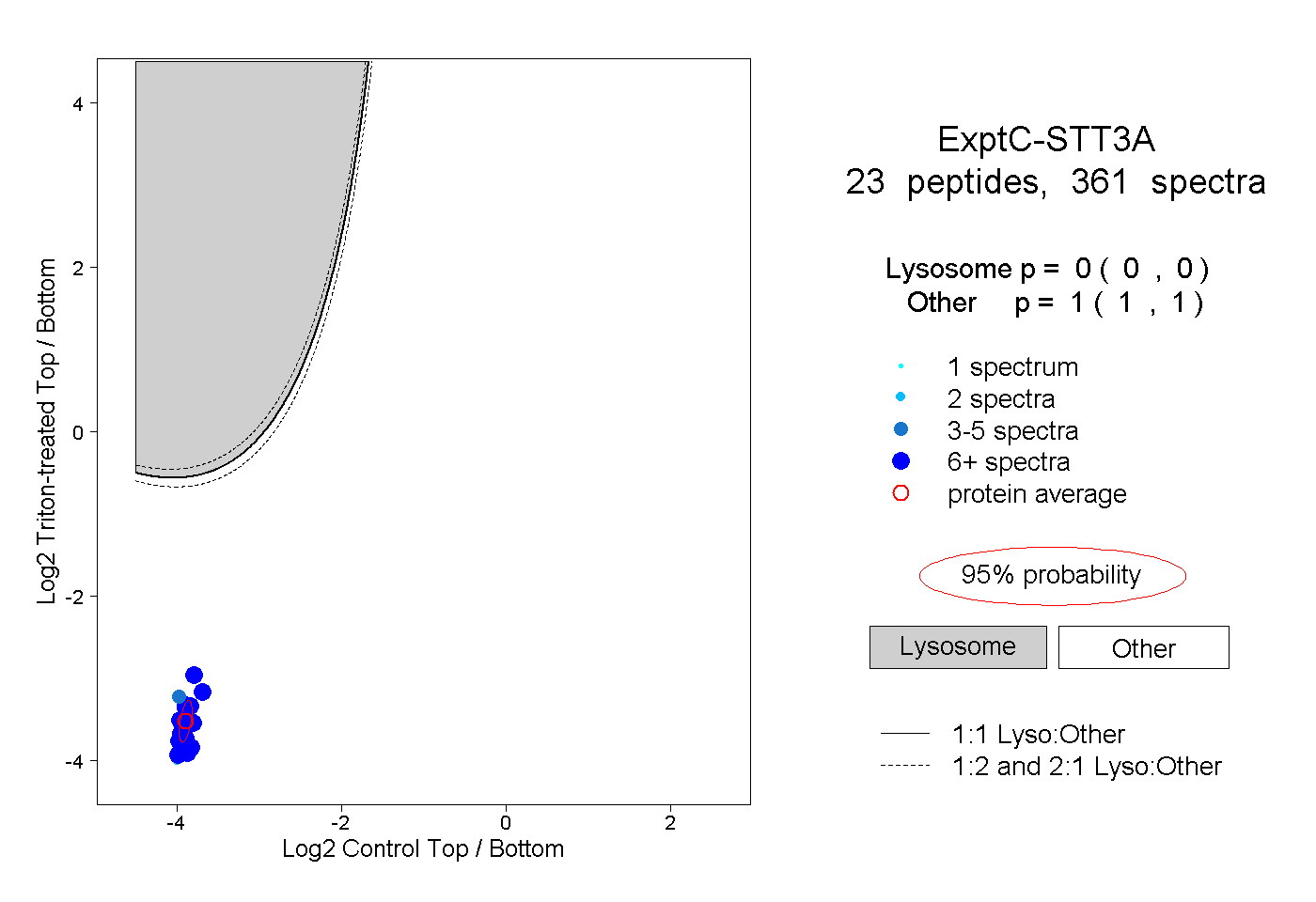
| Expt C |
 23
23
peptides |
361
spectra |
 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| 4 spectra, TGSIYWAAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, EAYYWLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, HNTPEDAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, FHNWFDDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, LFAVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 49 spectra, RPPGFDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 31 spectra, IIFDDFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, FGQVYTEAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, FLAEEGFYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QDTLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, FYSLLDPSYAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, VGQAMASTEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, AWYPLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, NLDISRPDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, QQDSTYPIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ISPWTGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, LNPQQFEVLFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 32 spectra, NAEIGNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, ENDYYTPTGEFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EGSPVLLNCLMYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, FLWMVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, IGGSTETGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, AYEIMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
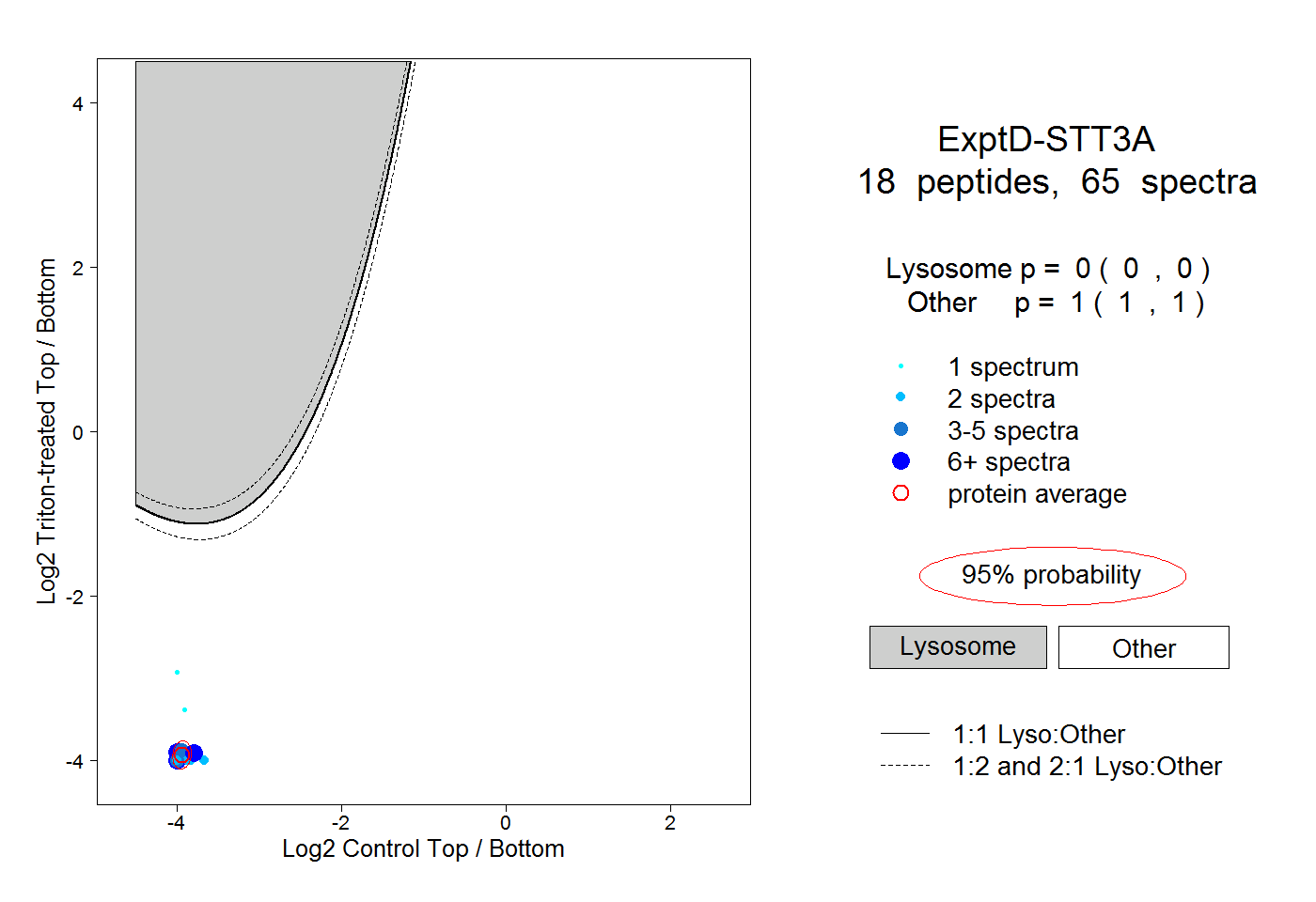
| Expt D |
 18
18
peptides |
65
spectra |
 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |



