peptides
spectra
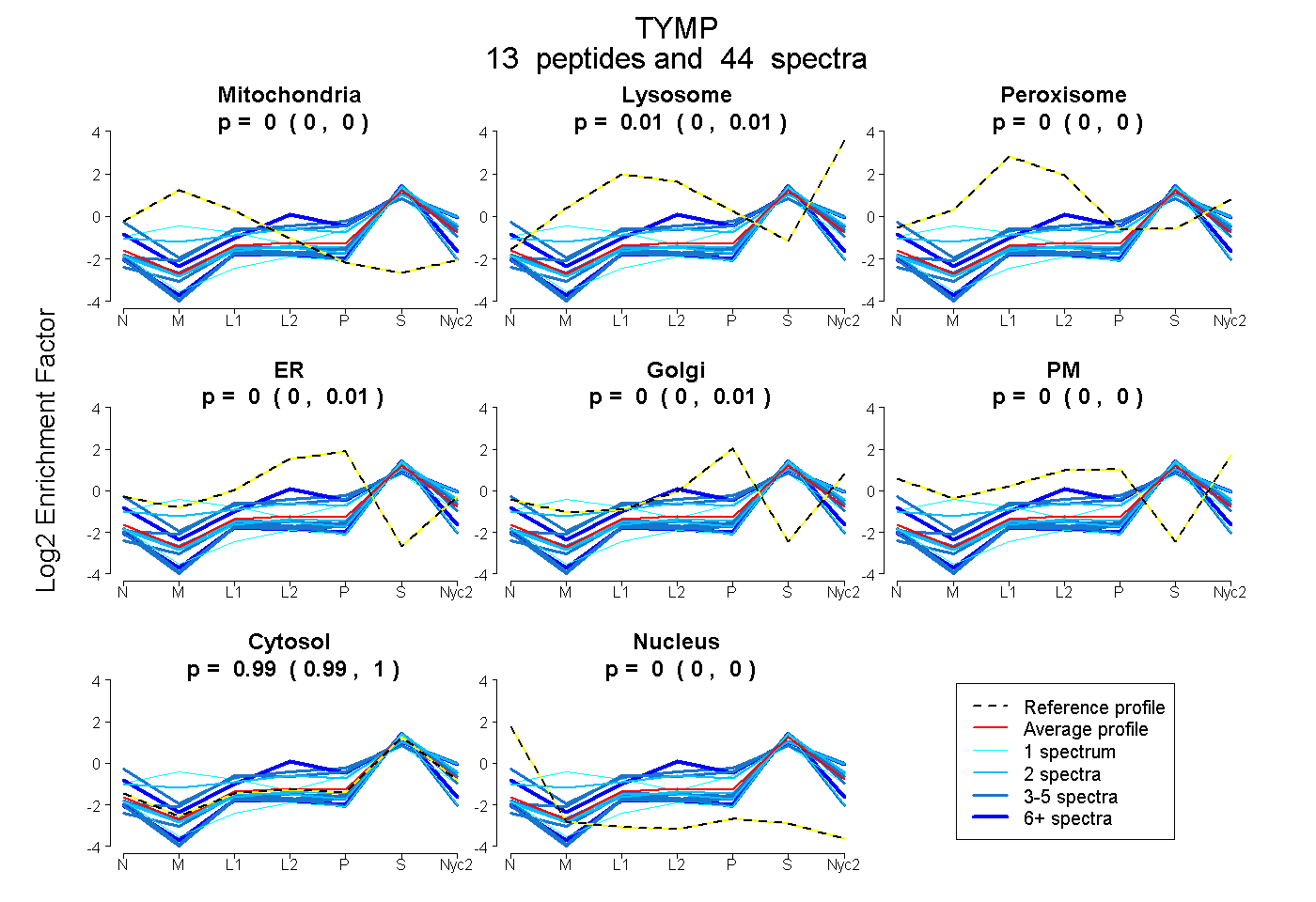
0.000 | 0.000
0.000 | 0.012
0.000 | 0.000
0.000 | 0.006
0.000 | 0.005
0.000 | 0.000
0.985 | 0.998
0.000 | 0.000
peptides
spectra
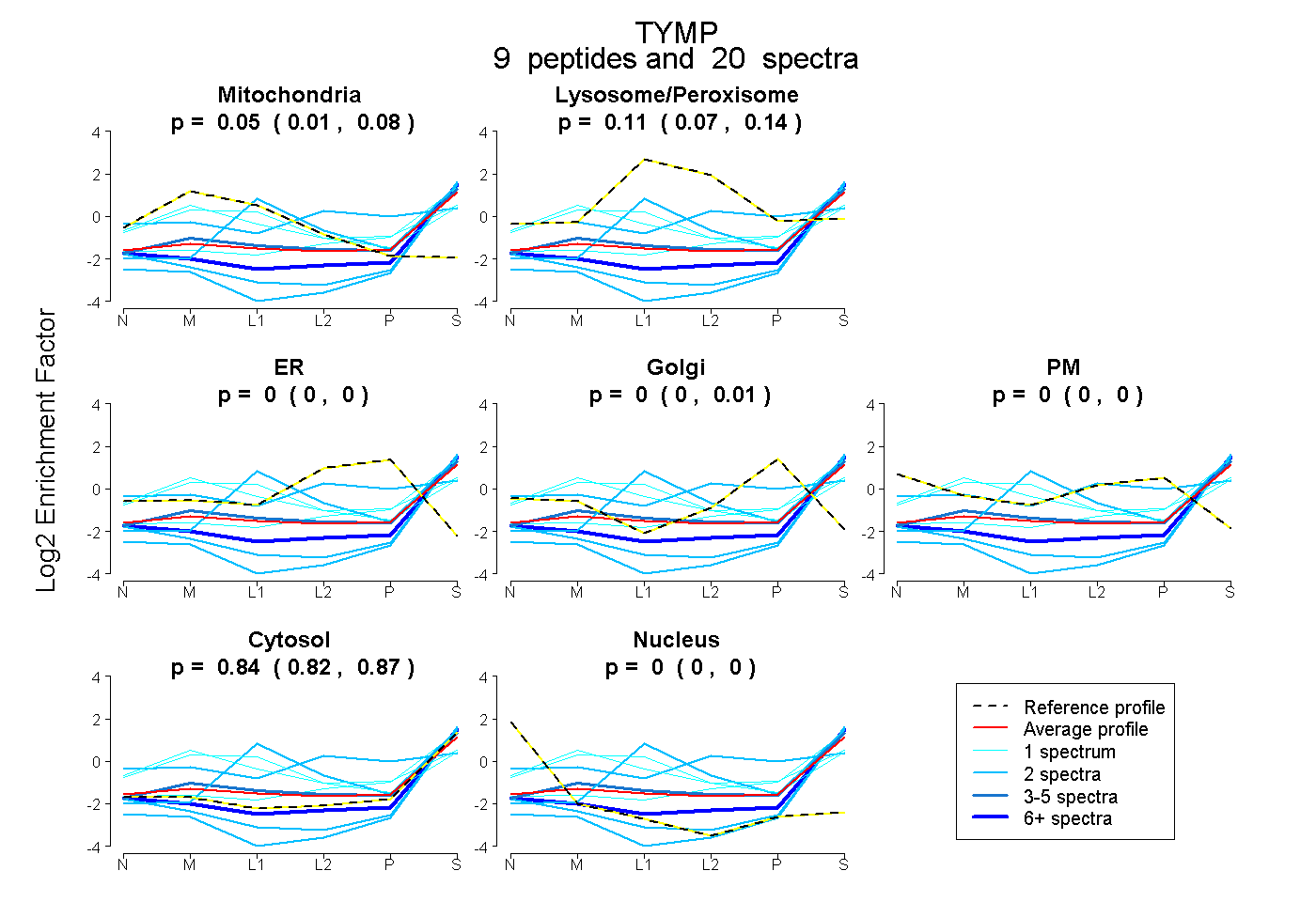
0.011 | 0.077
0.071 | 0.139
0.000 | 0.001
0.000 | 0.014
0.000 | 0.000
0.815 | 0.866
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
44 spectra |
 |
0.000 0.000 | 0.000 |
0.007 0.000 | 0.012 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.006 |
0.000 0.000 | 0.005 |
0.000 0.000 | 0.000 |
0.993 0.985 | 0.998 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
 |
0.050 0.011 | 0.077 |
0.108 0.071 | 0.139 |
0.000 0.000 | 0.001 |
0.000 0.000 | 0.014 |
0.000 0.000 | 0.000 |
0.842 0.815 | 0.866 |
0.000 0.000 | 0.000 |
| 1 spectrum, VPMISGR | 0.427 | 0.149 | 0.000 | 0.000 | 0.000 | 0.424 | 0.000 | |||
| 1 spectrum, DVTATVDSVPLITASILSK | 0.000 | 0.078 | 0.083 | 0.000 | 0.000 | 0.839 | 0.000 | |||
| 2 spectra, ALCSGSPTQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.006 | |||
| 1 spectrum, VHLDGPALSSQQR | 0.318 | 0.281 | 0.000 | 0.000 | 0.000 | 0.401 | 0.000 | |||
| 2 spectra, QLLPHAR | 0.000 | 0.410 | 0.000 | 0.000 | 0.000 | 0.590 | 0.000 | |||
| 6 spectra, ALPLACVLHELGAGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.989 | 0.011 | |||
| 2 spectra, AQDTQIGAMLMAIR | 0.000 | 0.304 | 0.000 | 0.143 | 0.232 | 0.321 | 0.000 | |||
| 2 spectra, LVPADGILYAAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.936 | 0.064 | |||
| 3 spectra, NFVHALMDGR | 0.046 | 0.126 | 0.000 | 0.000 | 0.000 | 0.828 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
29 spectra |
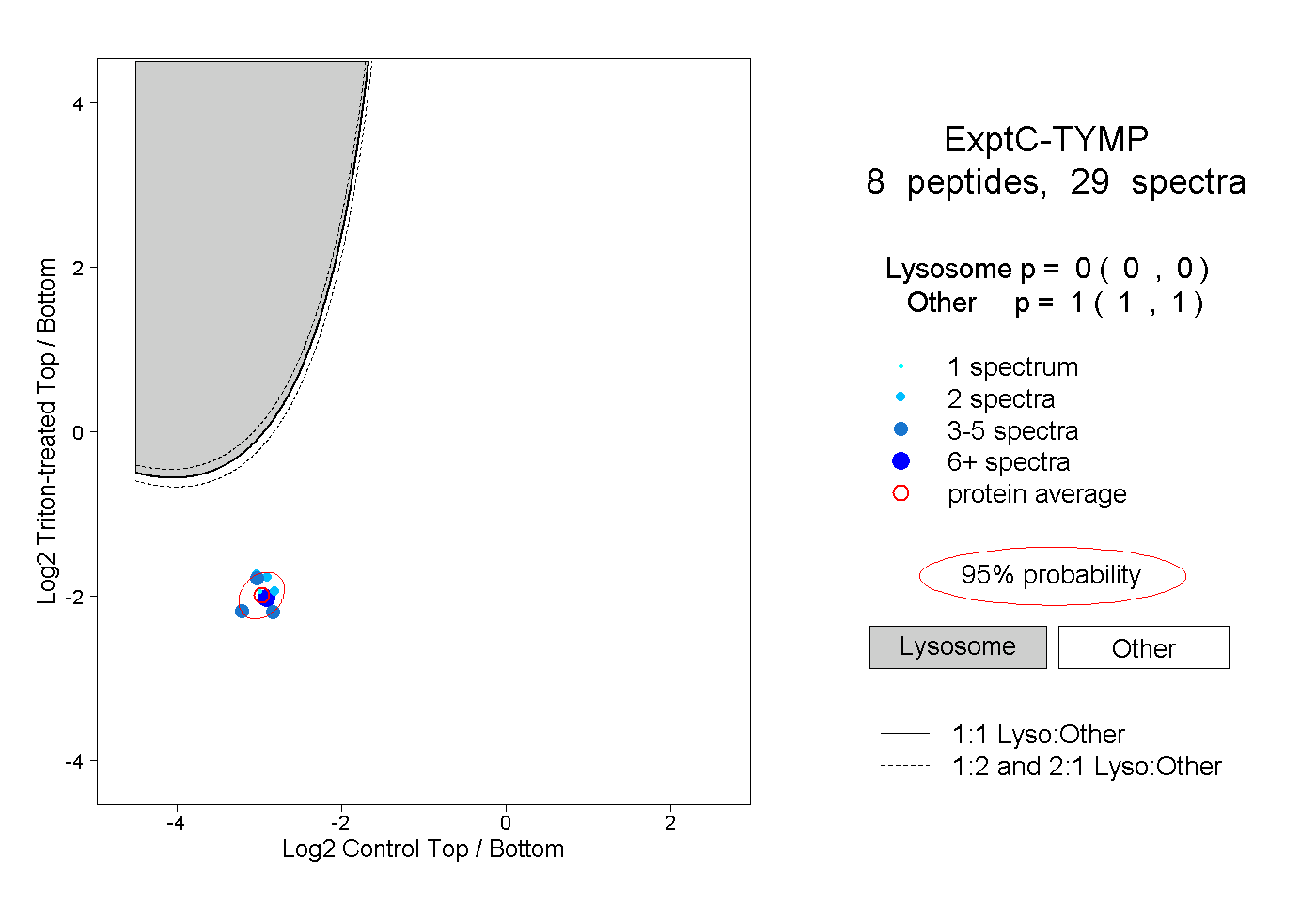 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
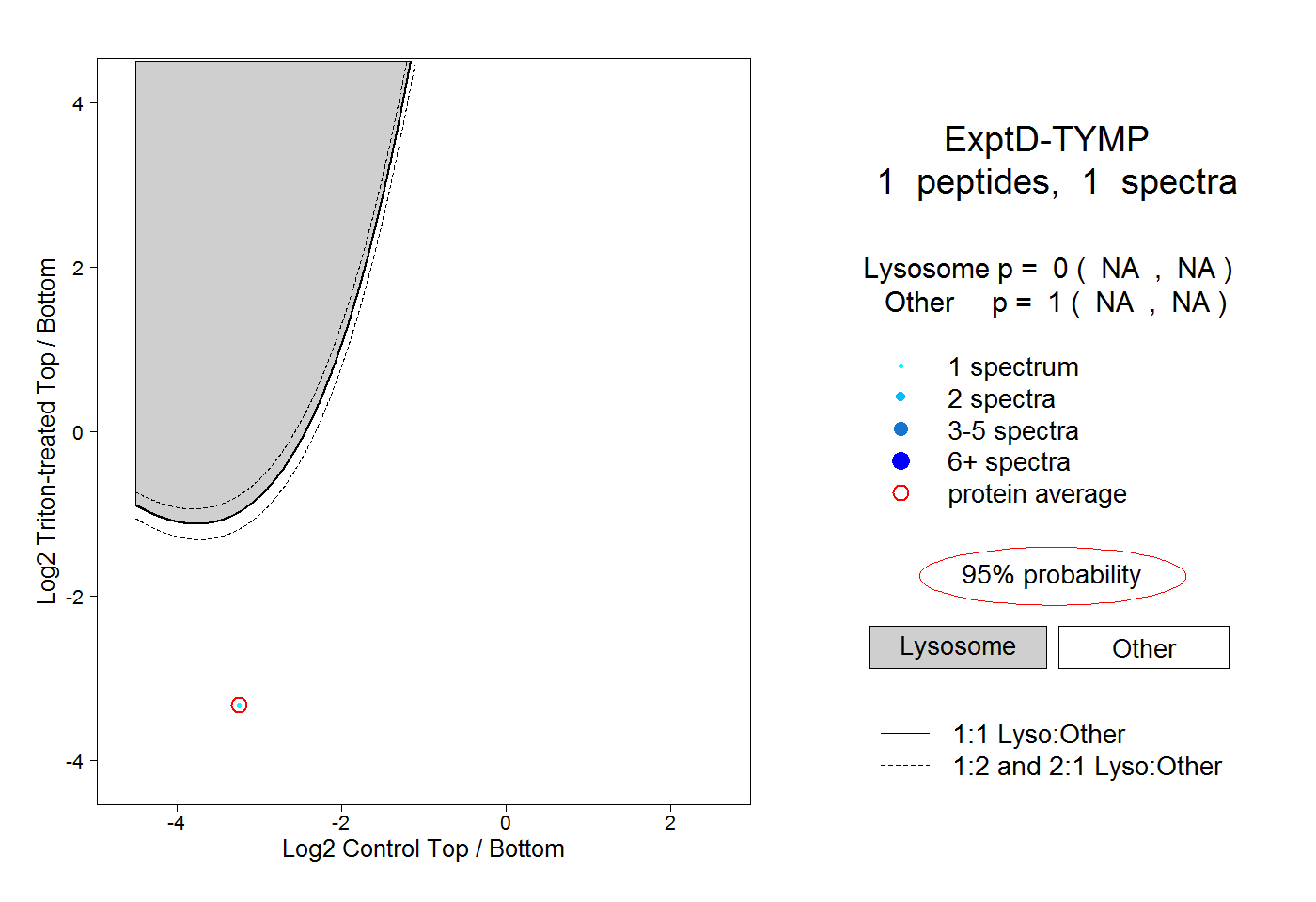 |
0.000 NA | NA |
1.000 NA | NA |