peptides
spectra
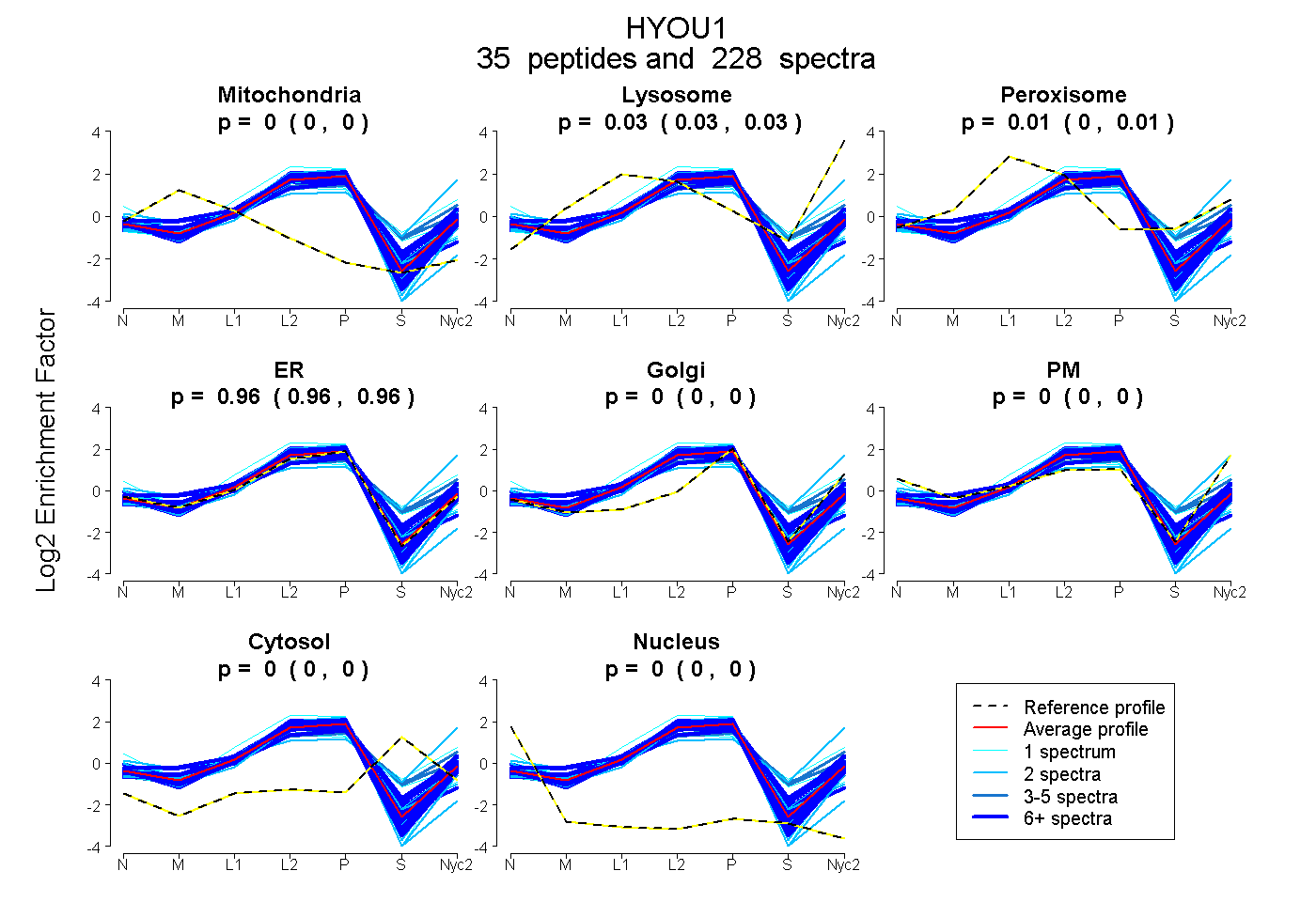
0.000 | 0.000
0.027 | 0.032
0.004 | 0.010
0.960 | 0.964
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
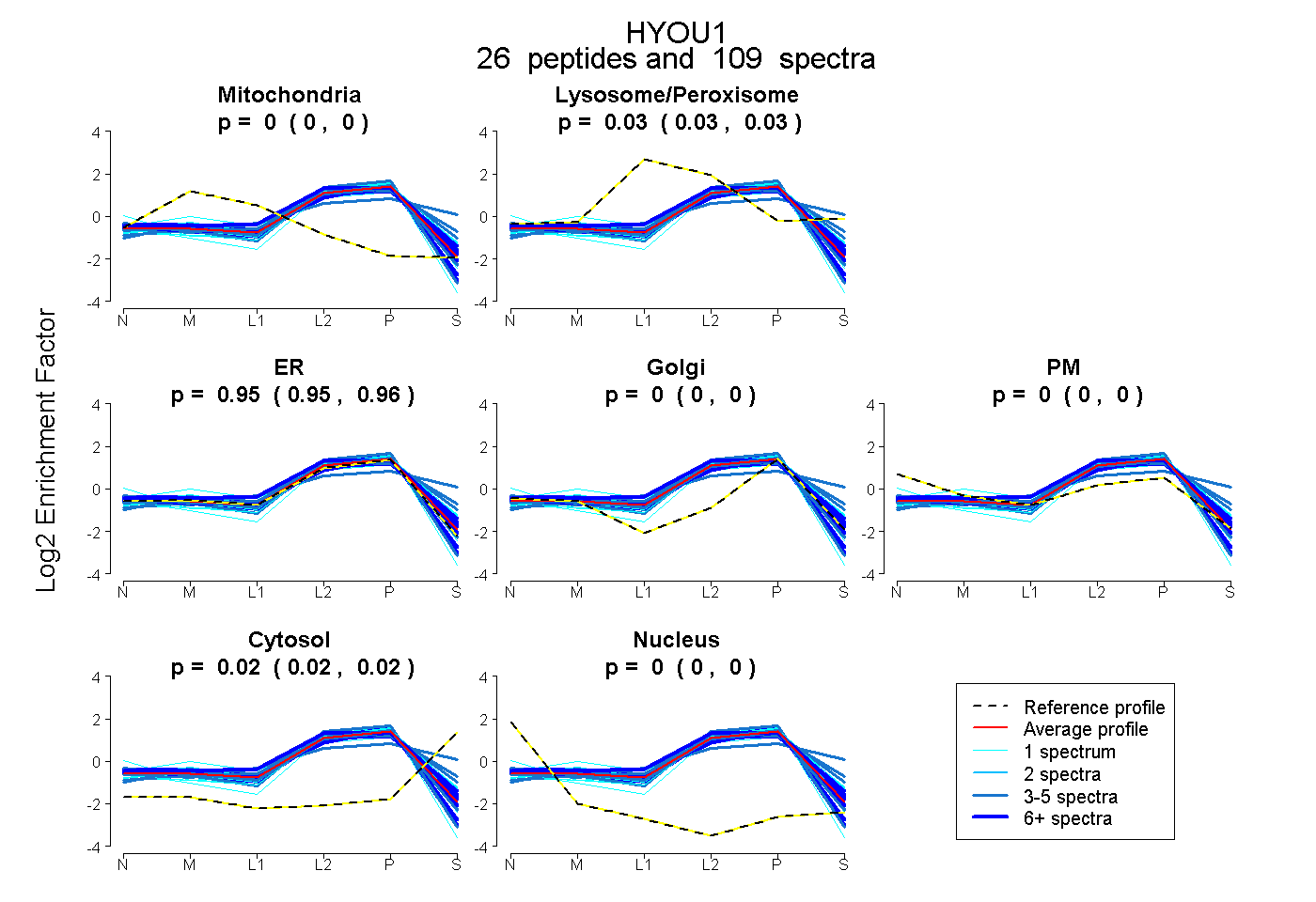
0.000 | 0.000
0.028 | 0.034
0.946 | 0.956
0.000 | 0.000
0.000 | 0.000
0.015 | 0.020
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
228 spectra |
 |
0.000 0.000 | 0.000 |
0.030 0.027 | 0.032 |
0.008 0.004 | 0.010 |
0.963 0.960 | 0.964 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
109 spectra |
 |
0.000 0.000 | 0.000 |
0.031 0.028 | 0.034 |
0.951 0.946 | 0.956 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.018 0.015 | 0.020 |
0.000 0.000 | 0.000 |
| 5 spectra, EAGTQPQLQIR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, AANSLEAFIFETQDK | 0.000 | 0.044 | 0.906 | 0.000 | 0.000 | 0.050 | 0.000 | |||
| 10 spectra, YFQHLLGK | 0.000 | 0.104 | 0.896 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, VQEVLLK | 0.000 | 0.043 | 0.873 | 0.000 | 0.085 | 0.000 | 0.000 | |||
| 9 spectra, QADNPHVALYR | 0.000 | 0.090 | 0.782 | 0.047 | 0.049 | 0.032 | 0.000 | |||
| 4 spectra, LFNEQR | 0.000 | 0.374 | 0.190 | 0.244 | 0.000 | 0.191 | 0.000 | |||
| 4 spectra, TLGGLEMELR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, YPDYESK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, EVQYLLNK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, VITFNR | 0.000 | 0.080 | 0.837 | 0.039 | 0.000 | 0.044 | 0.000 | |||
| 1 spectrum, DAVIYPILVEFTR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, TVLSANADHMAQIEGLMDDVDFK | 0.000 | 0.133 | 0.733 | 0.000 | 0.000 | 0.135 | 0.000 | |||
| 1 spectrum, GVGESFK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, MGPYPQR | 0.000 | 0.078 | 0.815 | 0.000 | 0.040 | 0.066 | 0.000 | |||
| 3 spectra, GVGFDR | 0.000 | 0.189 | 0.700 | 0.026 | 0.000 | 0.084 | 0.000 | |||
| 1 spectrum, VAIVKPGVPMEIVLNK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, EVEEEPGLR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TPVTVTLK | 0.000 | 0.011 | 0.899 | 0.000 | 0.000 | 0.090 | 0.000 | |||
| 1 spectrum, FLGDSAAGMAIK | 0.000 | 0.111 | 0.655 | 0.000 | 0.185 | 0.048 | 0.000 | |||
| 1 spectrum, SLAEDFAEQPIK | 0.000 | 0.000 | 0.844 | 0.153 | 0.000 | 0.003 | 0.000 | |||
| 7 spectra, LEDLTLR | 0.000 | 0.005 | 0.958 | 0.000 | 0.000 | 0.037 | 0.000 | |||
| 1 spectrum, LPATEKPVLLSK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LSATSTWLEDEGFGATTVMLK | 0.000 | 0.000 | 0.996 | 0.000 | 0.000 | 0.004 | 0.000 | |||
| 1 spectrum, FPEHELNVDPQR | 0.039 | 0.161 | 0.650 | 0.150 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AHFNLDESGVLSLDR | 0.000 | 0.129 | 0.819 | 0.000 | 0.000 | 0.052 | 0.000 | |||
| 7 spectra, LCQGLFFR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
368 spectra |
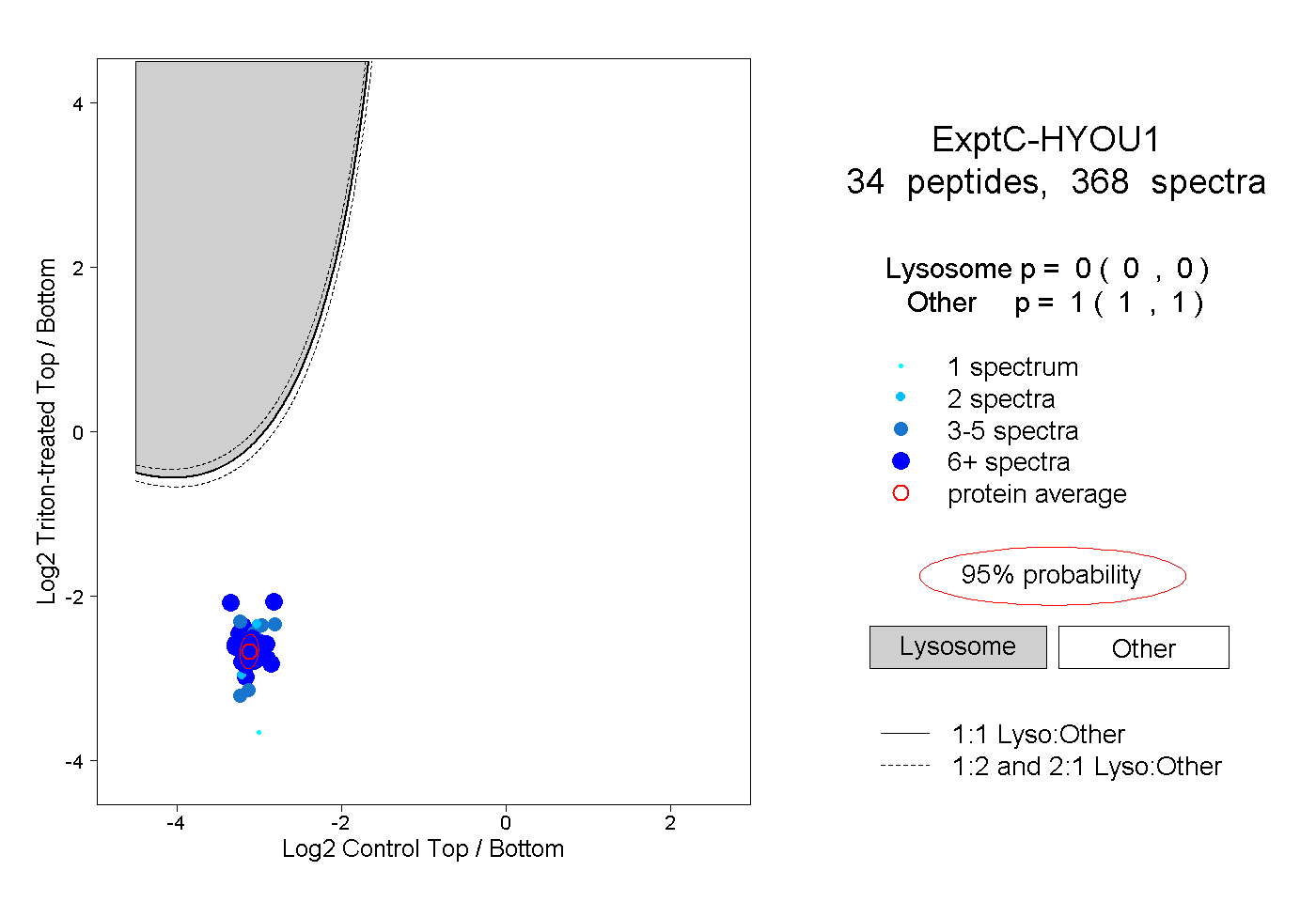 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
51 spectra |
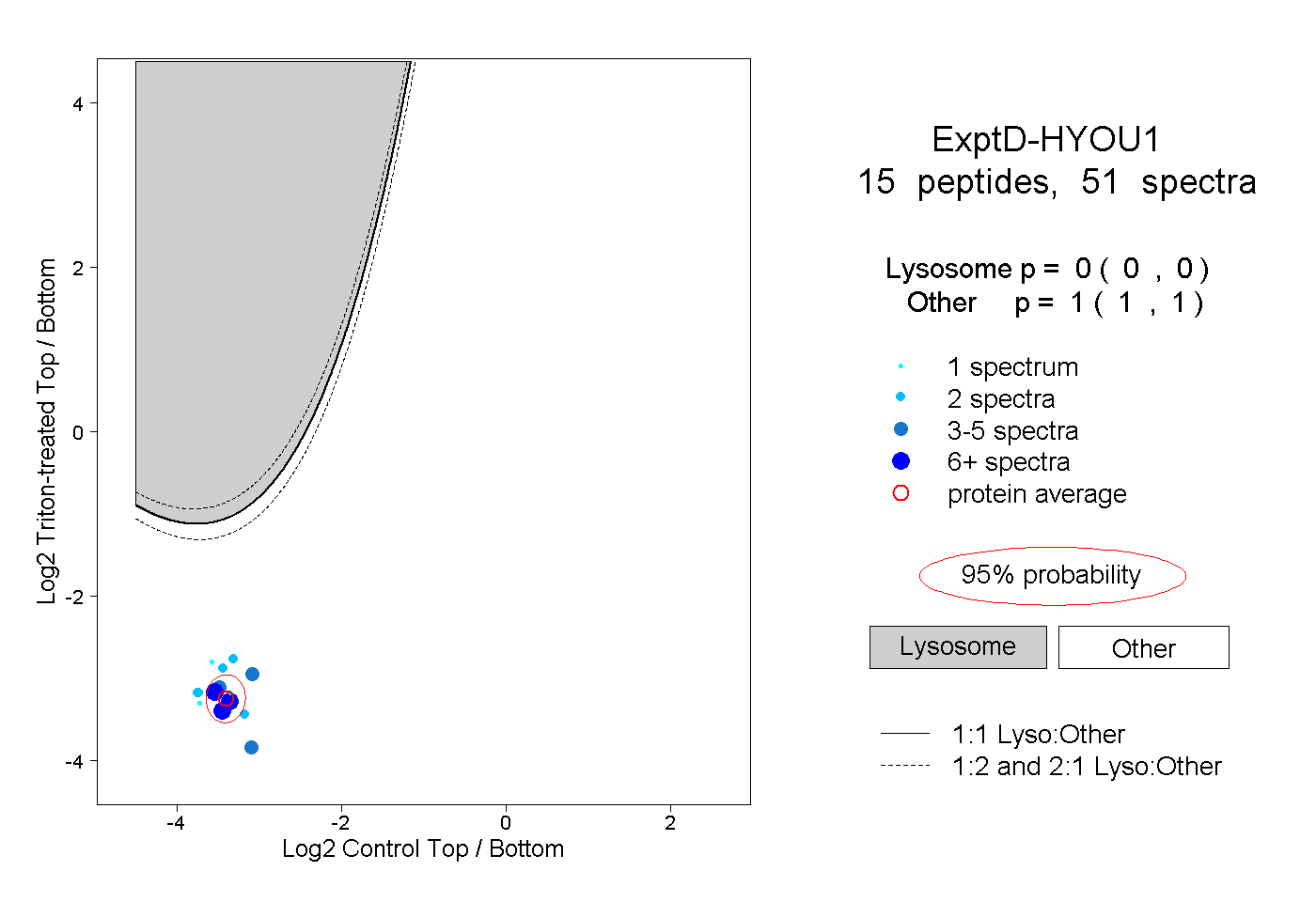 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |