peptides
spectra
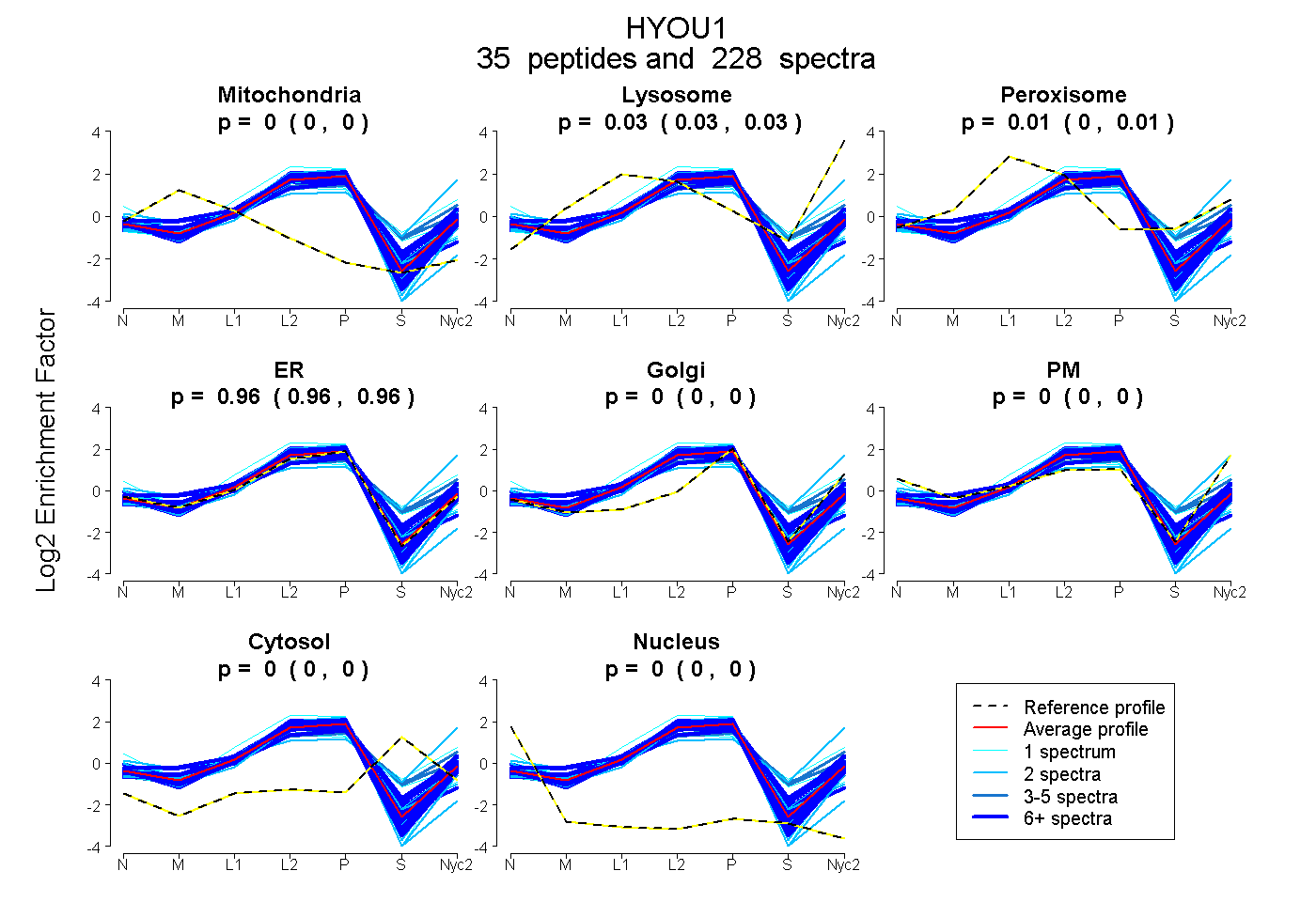
0.000 | 0.000
0.027 | 0.032
0.004 | 0.010
0.960 | 0.964
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
228 spectra |
 |
0.000 0.000 | 0.000 |
0.030 0.027 | 0.032 |
0.008 0.004 | 0.010 |
0.963 0.960 | 0.964 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 7 spectra, VQEVLLK | 0.000 | 0.007 | 0.000 | 0.975 | 0.000 | 0.018 | 0.000 | 0.000 | ||
| 7 spectra, QADNPHVALYR | 0.000 | 0.000 | 0.077 | 0.772 | 0.000 | 0.044 | 0.107 | 0.000 | ||
| 15 spectra, TLGGLEMELR | 0.000 | 0.028 | 0.000 | 0.972 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, GVGESFK | 0.000 | 0.080 | 0.000 | 0.834 | 0.000 | 0.000 | 0.086 | 0.000 | ||
| 2 spectra, VAIVKPGVPMEIVLNK | 0.000 | 0.000 | 0.000 | 0.969 | 0.000 | 0.000 | 0.031 | 0.000 | ||
| 21 spectra, EVEEEPGLR | 0.000 | 0.000 | 0.033 | 0.937 | 0.000 | 0.000 | 0.030 | 0.000 | ||
| 6 spectra, MMALDR | 0.000 | 0.039 | 0.000 | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, LFNEER | 0.000 | 0.196 | 0.078 | 0.000 | 0.081 | 0.543 | 0.103 | 0.000 | ||
| 2 spectra, TPVTVTLK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, VKPFVVR | 0.056 | 0.000 | 0.000 | 0.944 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LPATEKPVLLSK | 0.000 | 0.006 | 0.021 | 0.957 | 0.000 | 0.000 | 0.016 | 0.000 | ||
| 5 spectra, FPEHELNVDPQR | 0.000 | 0.000 | 0.175 | 0.624 | 0.028 | 0.006 | 0.167 | 0.000 | ||
| 4 spectra, AANSLEAFIFETQDK | 0.000 | 0.100 | 0.119 | 0.490 | 0.083 | 0.085 | 0.123 | 0.000 | ||
| 12 spectra, EAGTQPQLQIR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 11 spectra, YFQHLLGK | 0.000 | 0.040 | 0.000 | 0.960 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, DAVITVPAFFNQAER | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EEISGK | 0.000 | 0.097 | 0.159 | 0.420 | 0.000 | 0.210 | 0.114 | 0.000 | ||
| 6 spectra, LFNEQR | 0.000 | 0.128 | 0.033 | 0.742 | 0.000 | 0.073 | 0.024 | 0.000 | ||
| 1 spectrum, LGNTISSLFGGGTSSDAK | 0.000 | 0.033 | 0.000 | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, YPDYESK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EGETPDEK | 0.000 | 0.000 | 0.019 | 0.943 | 0.000 | 0.000 | 0.038 | 0.000 | ||
| 11 spectra, EVQYLLNK | 0.000 | 0.000 | 0.000 | 0.951 | 0.000 | 0.049 | 0.000 | 0.000 | ||
| 18 spectra, VITFNR | 0.000 | 0.027 | 0.025 | 0.886 | 0.000 | 0.000 | 0.062 | 0.000 | ||
| 5 spectra, DAVIYPILVEFTR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, DEPAEQGELK | 0.000 | 0.000 | 0.155 | 0.600 | 0.000 | 0.098 | 0.138 | 0.009 | ||
| 21 spectra, MGPYPQR | 0.000 | 0.006 | 0.000 | 0.994 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, GVGFDR | 0.000 | 0.044 | 0.000 | 0.956 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, FLGDSAAGMAIK | 0.000 | 0.045 | 0.000 | 0.903 | 0.000 | 0.052 | 0.000 | 0.000 | ||
| 1 spectrum, SLAEDFAEQPIK | 0.051 | 0.000 | 0.000 | 0.949 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, SEAQKPNEK | 0.000 | 0.000 | 0.000 | 0.988 | 0.000 | 0.000 | 0.000 | 0.012 | ||
| 2 spectra, VEFEELCADLFDR | 0.010 | 0.000 | 0.000 | 0.983 | 0.000 | 0.000 | 0.000 | 0.007 | ||
| 7 spectra, LEDLTLR | 0.000 | 0.024 | 0.018 | 0.958 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LIPEMDQIFTDVEMTTLEK | 0.000 | 0.074 | 0.001 | 0.925 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, AHFNLDESGVLSLDR | 0.000 | 0.080 | 0.090 | 0.684 | 0.000 | 0.000 | 0.146 | 0.000 | ||
| 9 spectra, LCQGLFFR | 0.038 | 0.000 | 0.000 | 0.950 | 0.000 | 0.000 | 0.000 | 0.012 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
109 spectra |
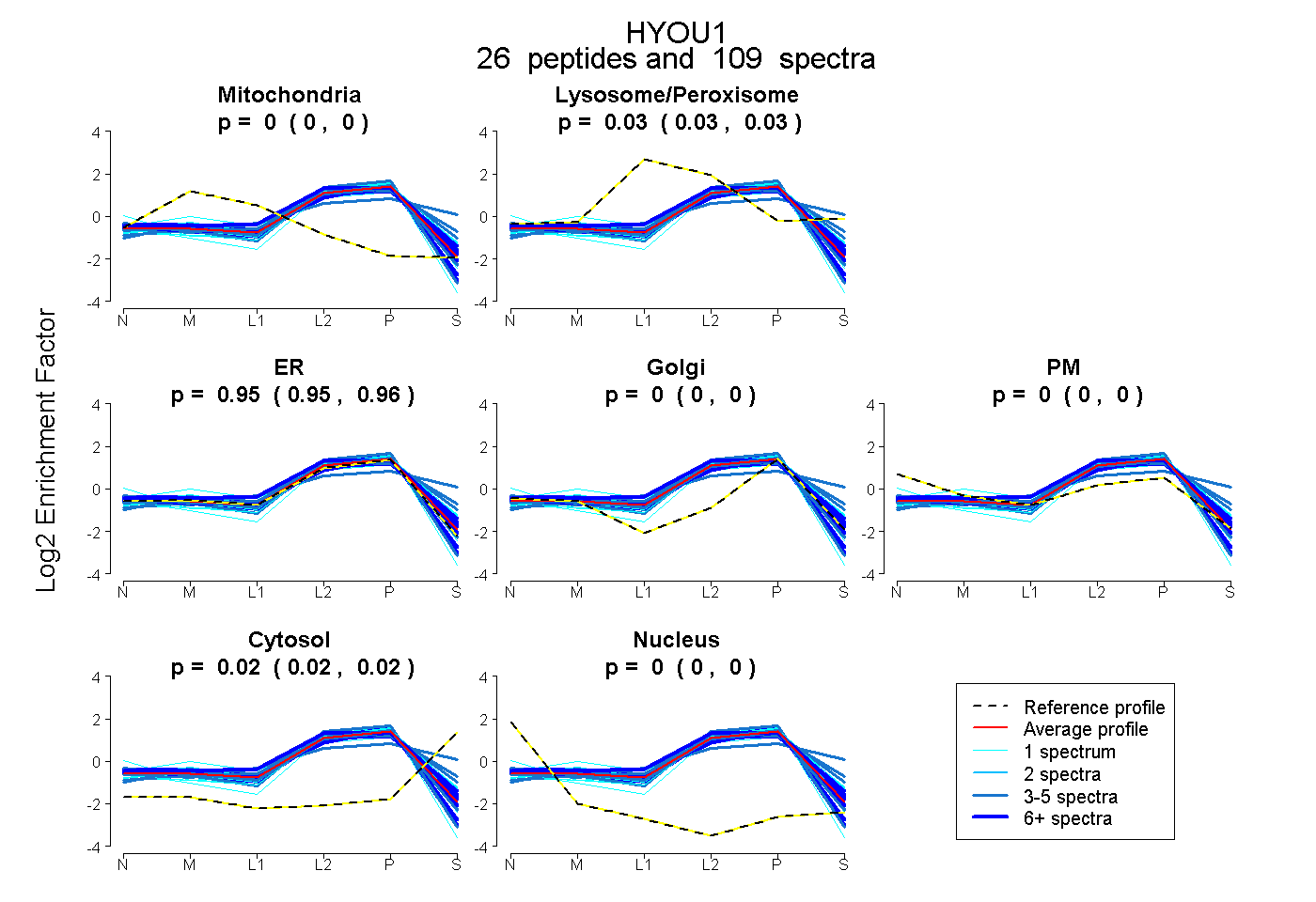 |
0.000 0.000 | 0.000 |
0.031 0.028 | 0.034 |
0.951 0.946 | 0.956 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.018 0.015 | 0.020 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
368 spectra |
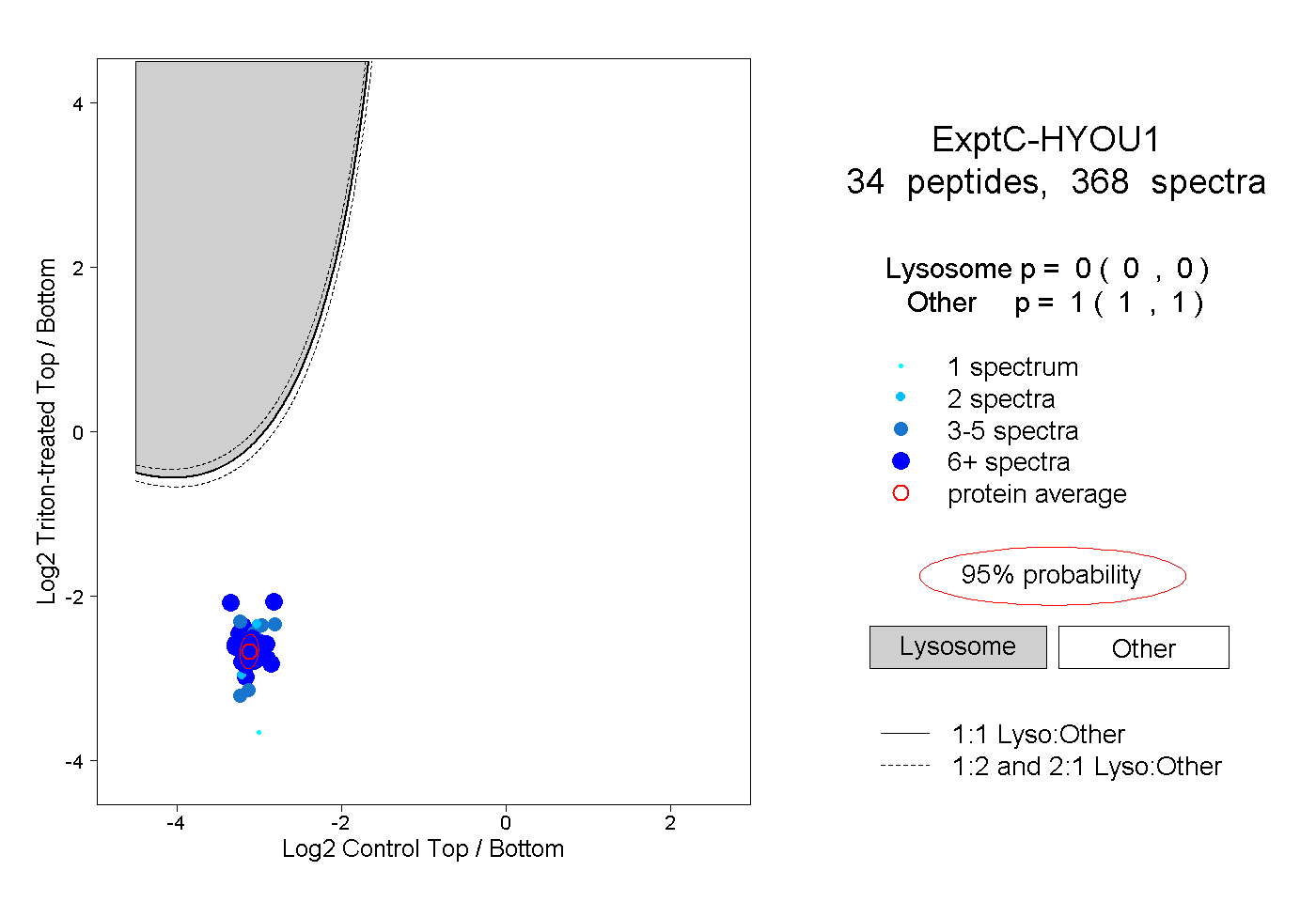 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
51 spectra |
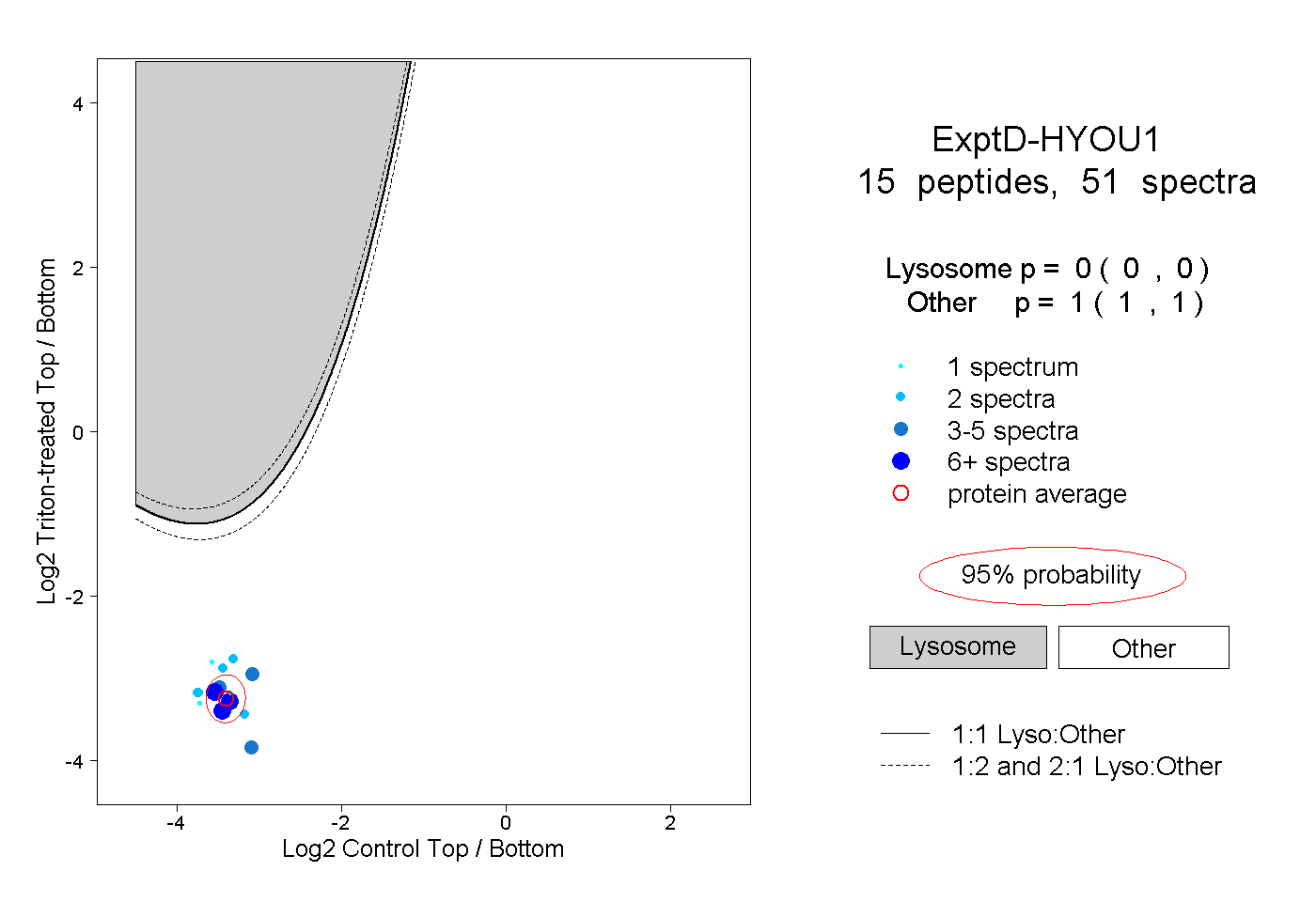 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |