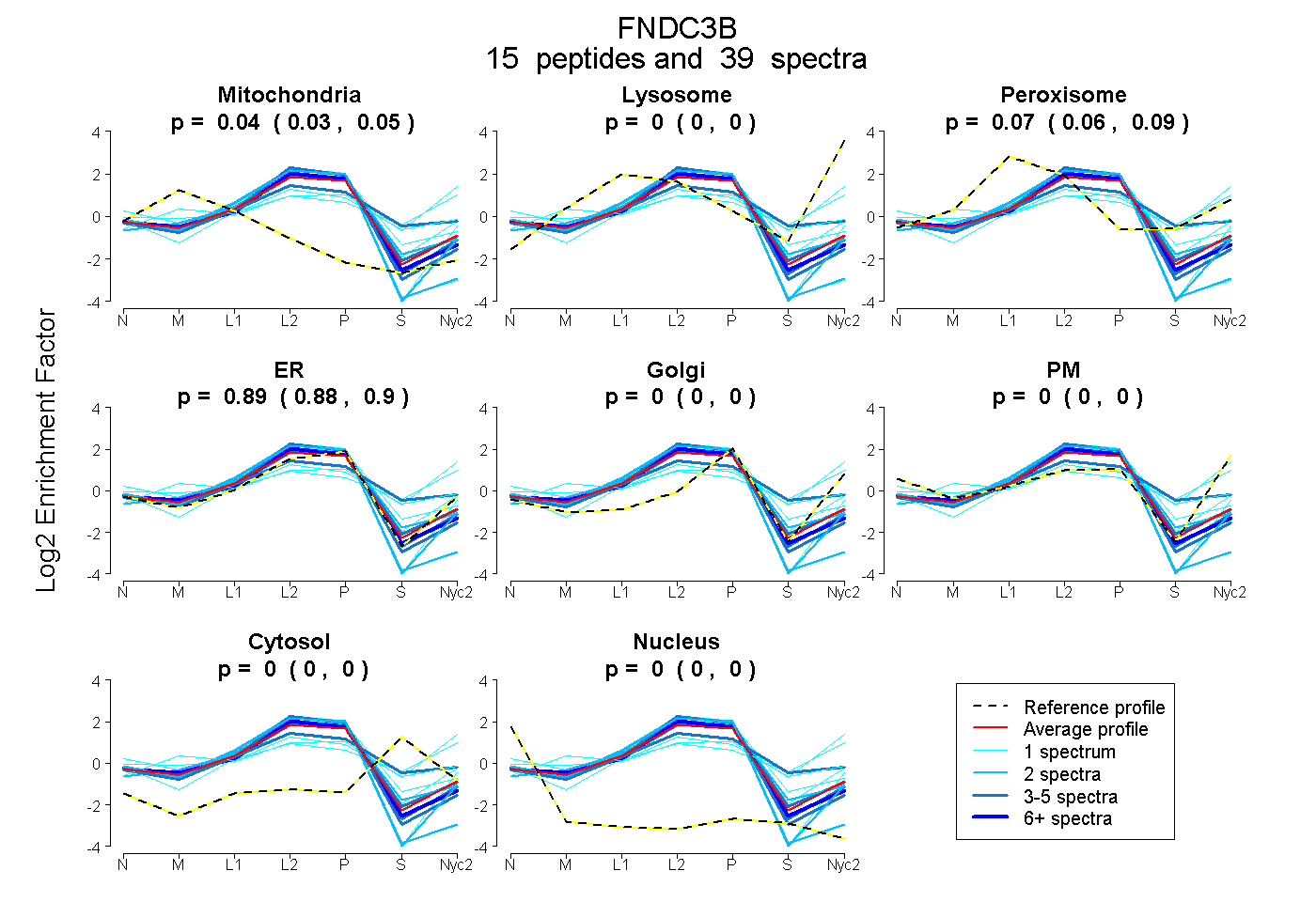
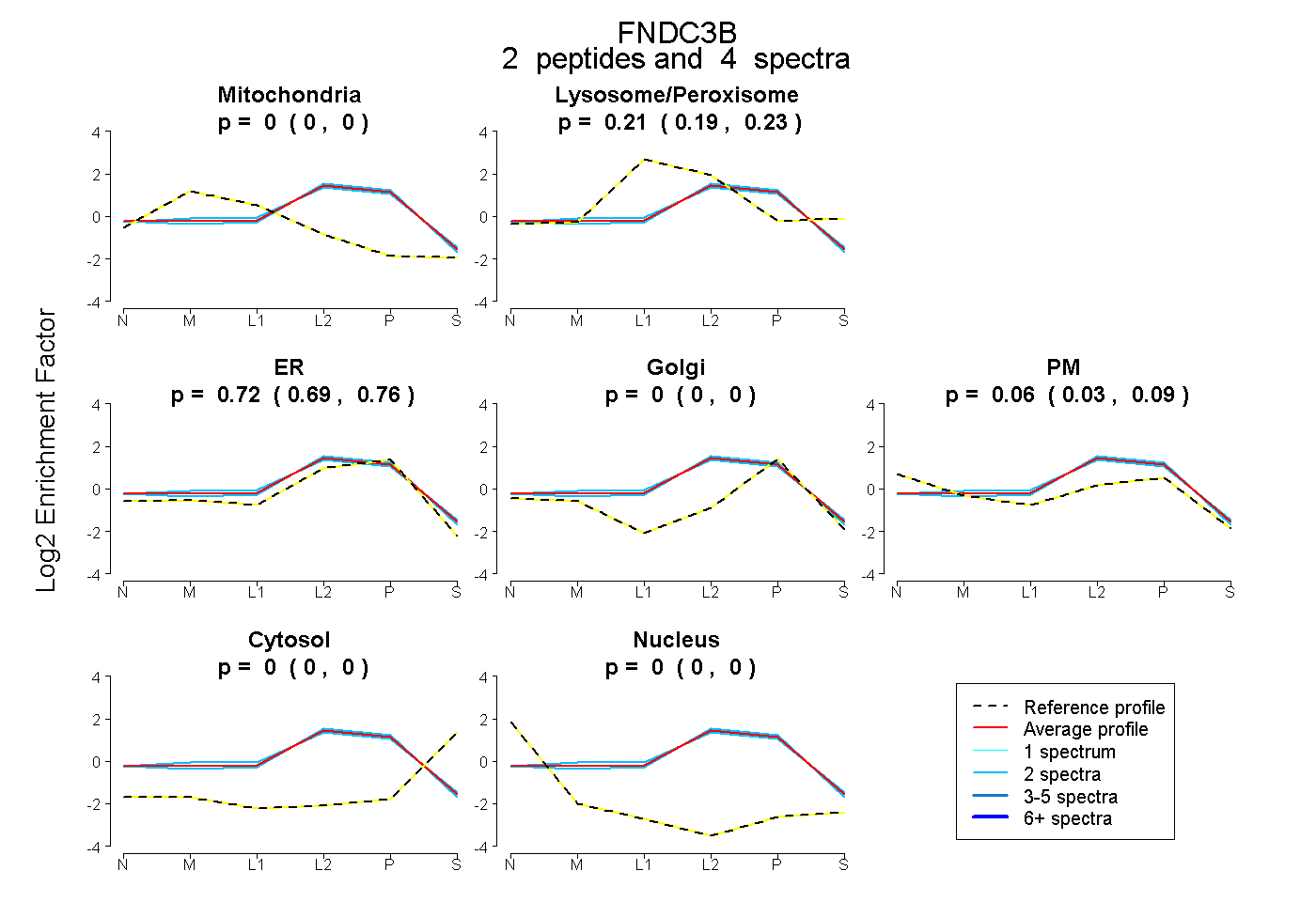
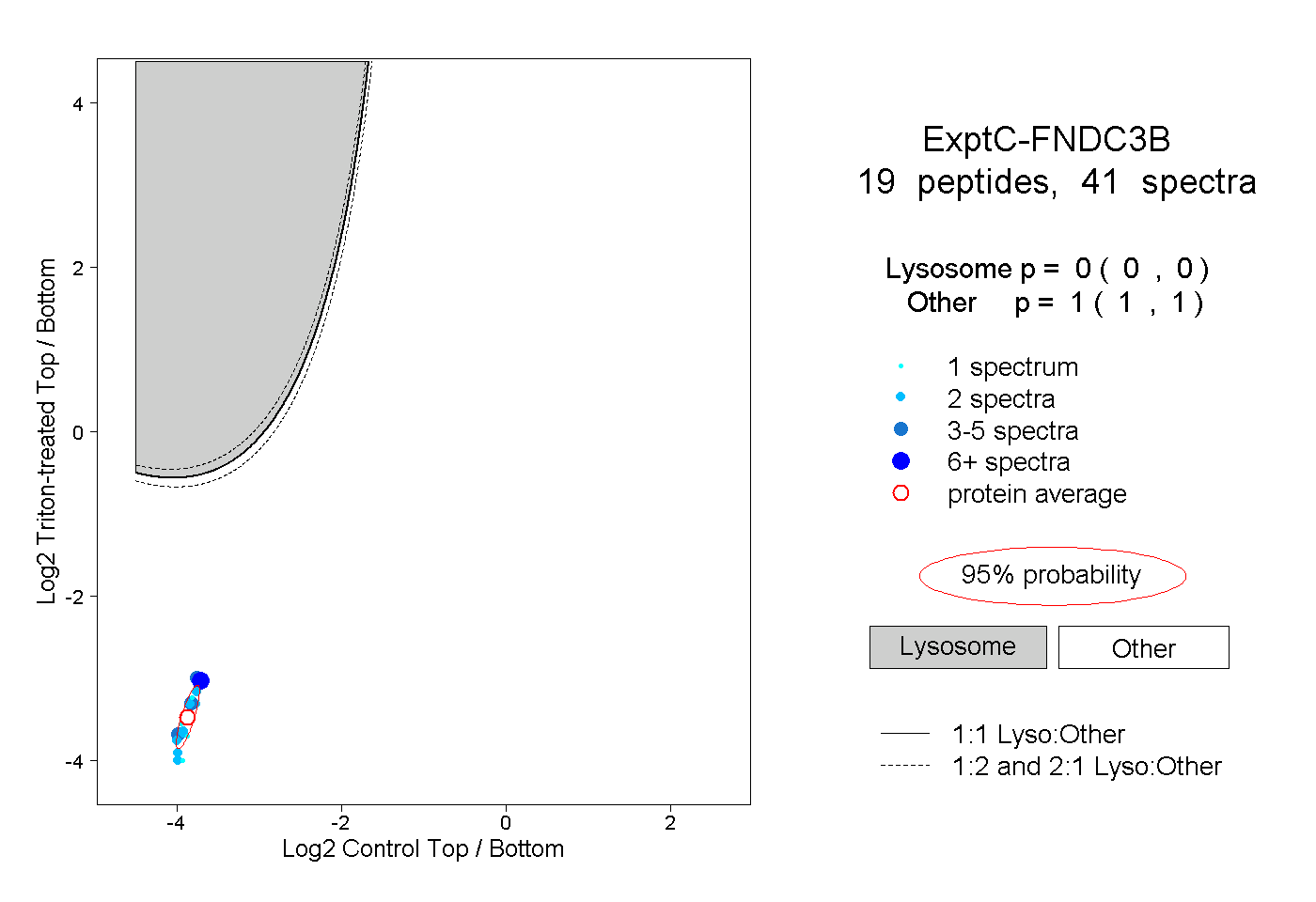
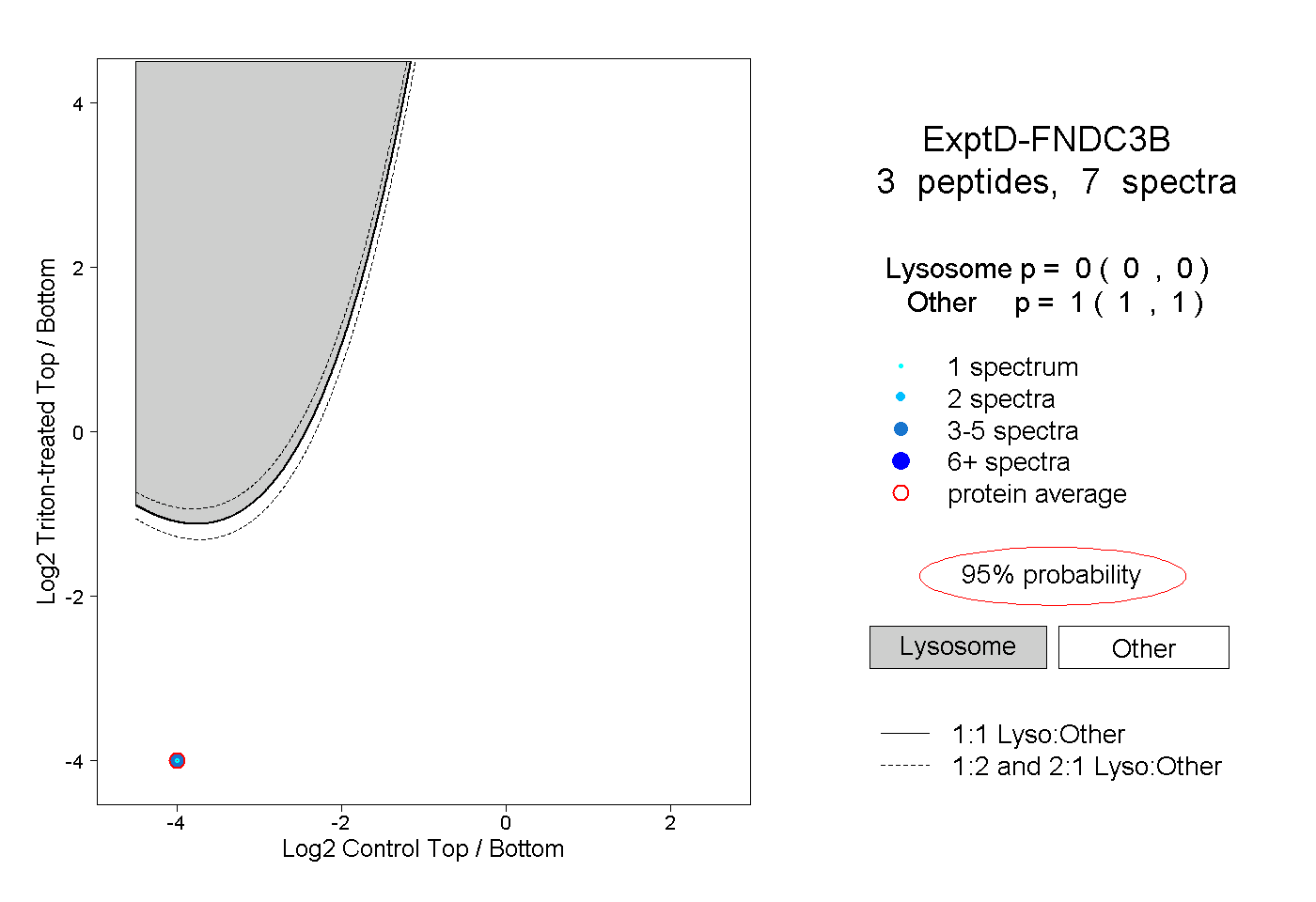
| 2 spectra, LTEFTCYSFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LECAASGPQSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LCPAMGYTFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YTGEDLTCTVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, FISIYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VQDILSGIEKPQVSNIQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SSDSDLQEYELEVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IIYSGEELECNLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NLLPETTYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TRPLPPSPPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TLSLAPGQCRPPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GPSHTYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DNGGSEILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QCFFGGQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DLLPAAQYCCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SSLTLQWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, WGDSNSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LTASNTEGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, APIDNGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |