peptides
spectra
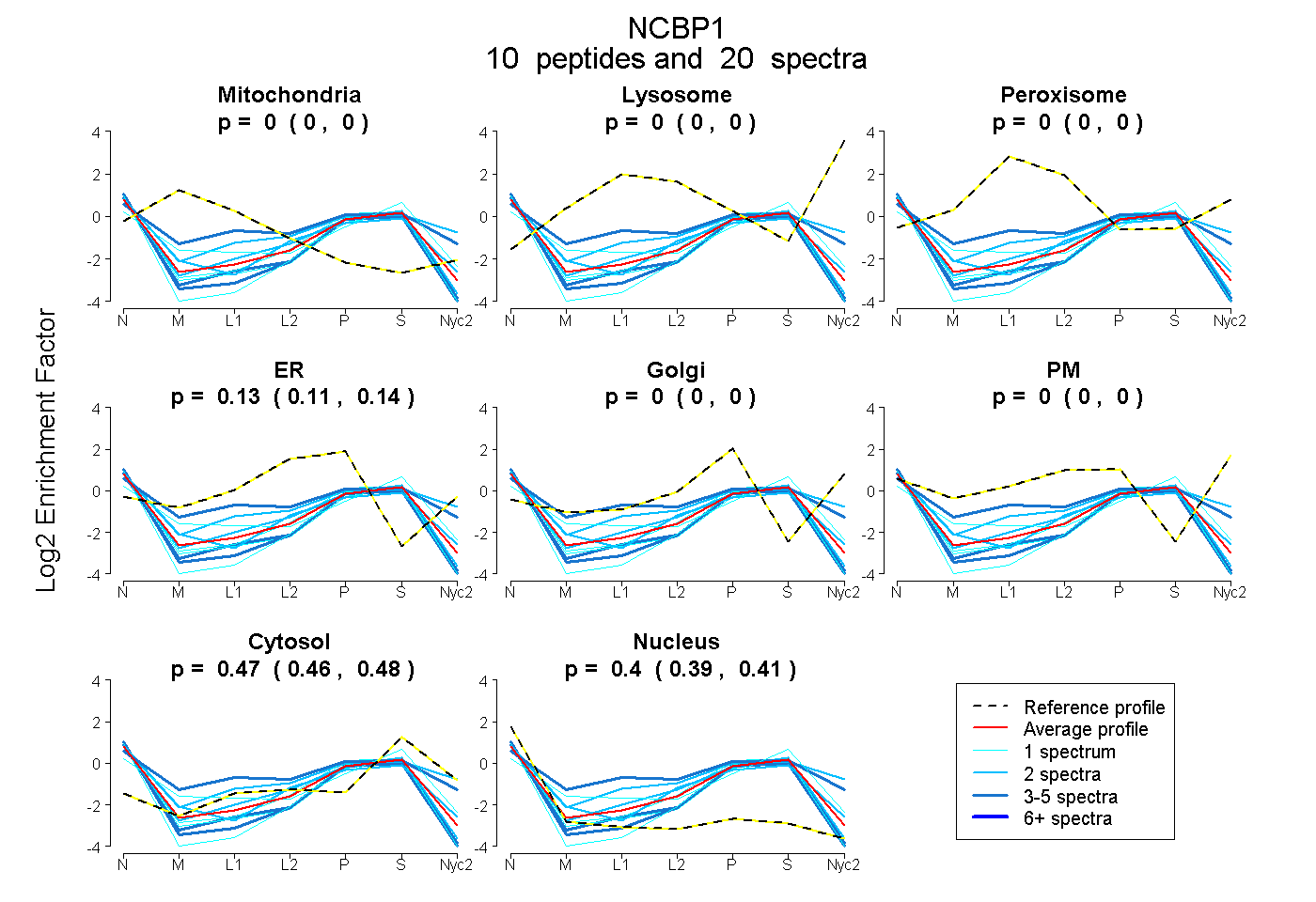
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.114 | 0.135
0.000 | 0.000
0.000 | 0.000
0.461 | 0.481
0.388 | 0.414
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.126 0.114 | 0.135 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.472 0.461 | 0.481 |
0.402 0.388 | 0.414 |
| 2 spectra, MFDYTDDPEGPVMPGSHSVER | 0.000 | 0.000 | 0.000 | 0.176 | 0.000 | 0.000 | 0.422 | 0.401 | ||
| 1 spectrum, LDTMSTTCVDR | 0.000 | 0.000 | 0.000 | 0.098 | 0.000 | 0.000 | 0.431 | 0.470 | ||
| 4 spectra, DGALEEQIER | 0.000 | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | 0.419 | 0.579 | ||
| 3 spectra, ANNYNEAVYLVR | 0.000 | 0.000 | 0.000 | 0.025 | 0.000 | 0.000 | 0.463 | 0.512 | ||
| 2 spectra, LLCTVAR | 0.000 | 0.000 | 0.000 | 0.127 | 0.000 | 0.000 | 0.461 | 0.412 | ||
| 1 spectrum, VMFEVWR | 0.033 | 0.000 | 0.000 | 0.097 | 0.000 | 0.000 | 0.625 | 0.245 | ||
| 3 spectra, TLAESDK | 0.000 | 0.000 | 0.146 | 0.200 | 0.039 | 0.019 | 0.414 | 0.181 | ||
| 1 spectrum, DVPNPNQVDDDDEGFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.426 | 0.574 | ||
| 2 spectra, HSYENDGGQPHK | 0.000 | 0.000 | 0.000 | 0.008 | 0.051 | 0.269 | 0.496 | 0.175 | ||
| 1 spectrum, ATNDEIFSILK | 0.000 | 0.000 | 0.000 | 0.016 | 0.000 | 0.000 | 0.433 | 0.551 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
5 spectra |
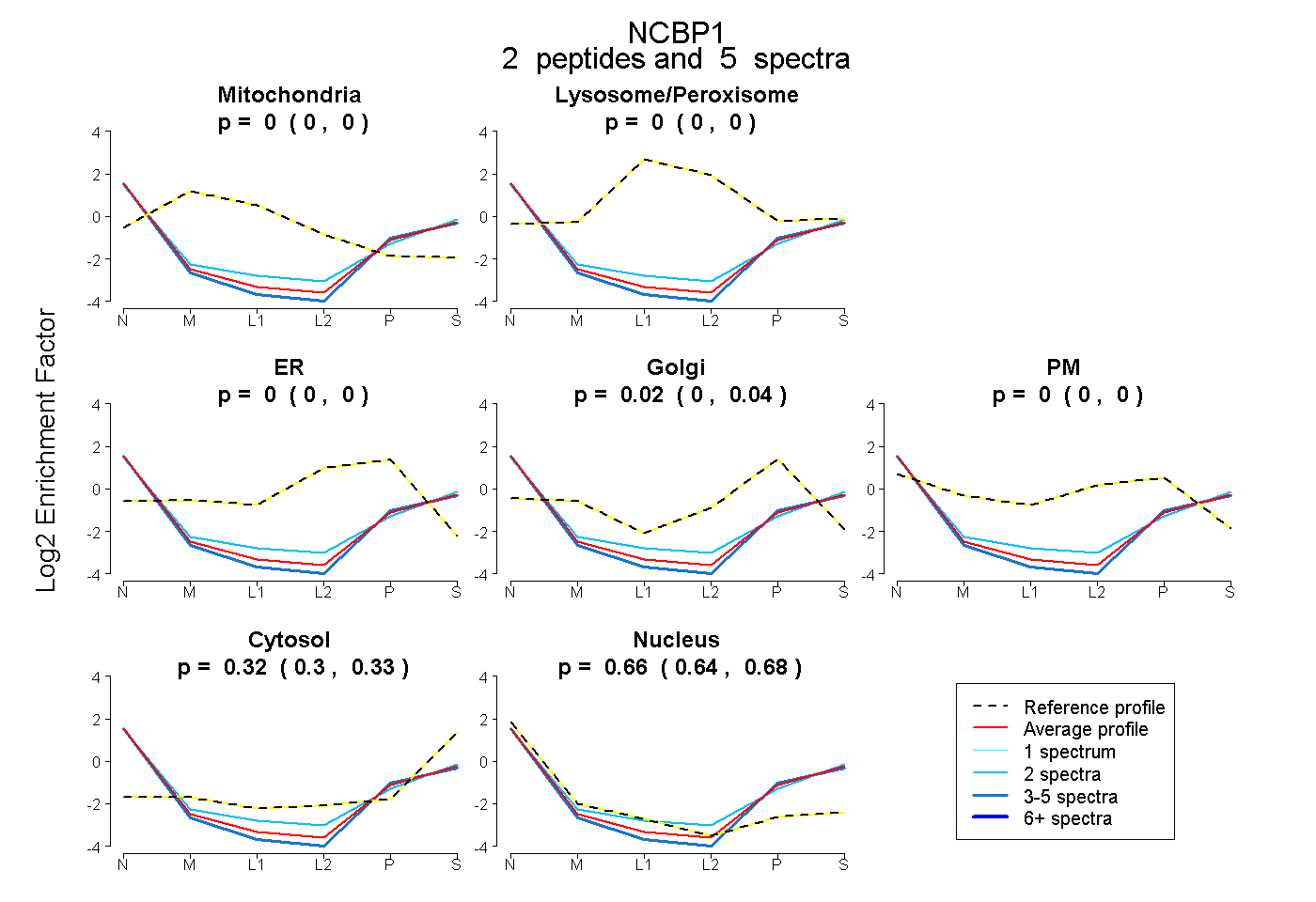 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.024 0.001 | 0.044 |
0.000 0.000 | 0.000 |
0.315 0.301 | 0.326 |
0.661 0.639 | 0.679 |