peptides
spectra
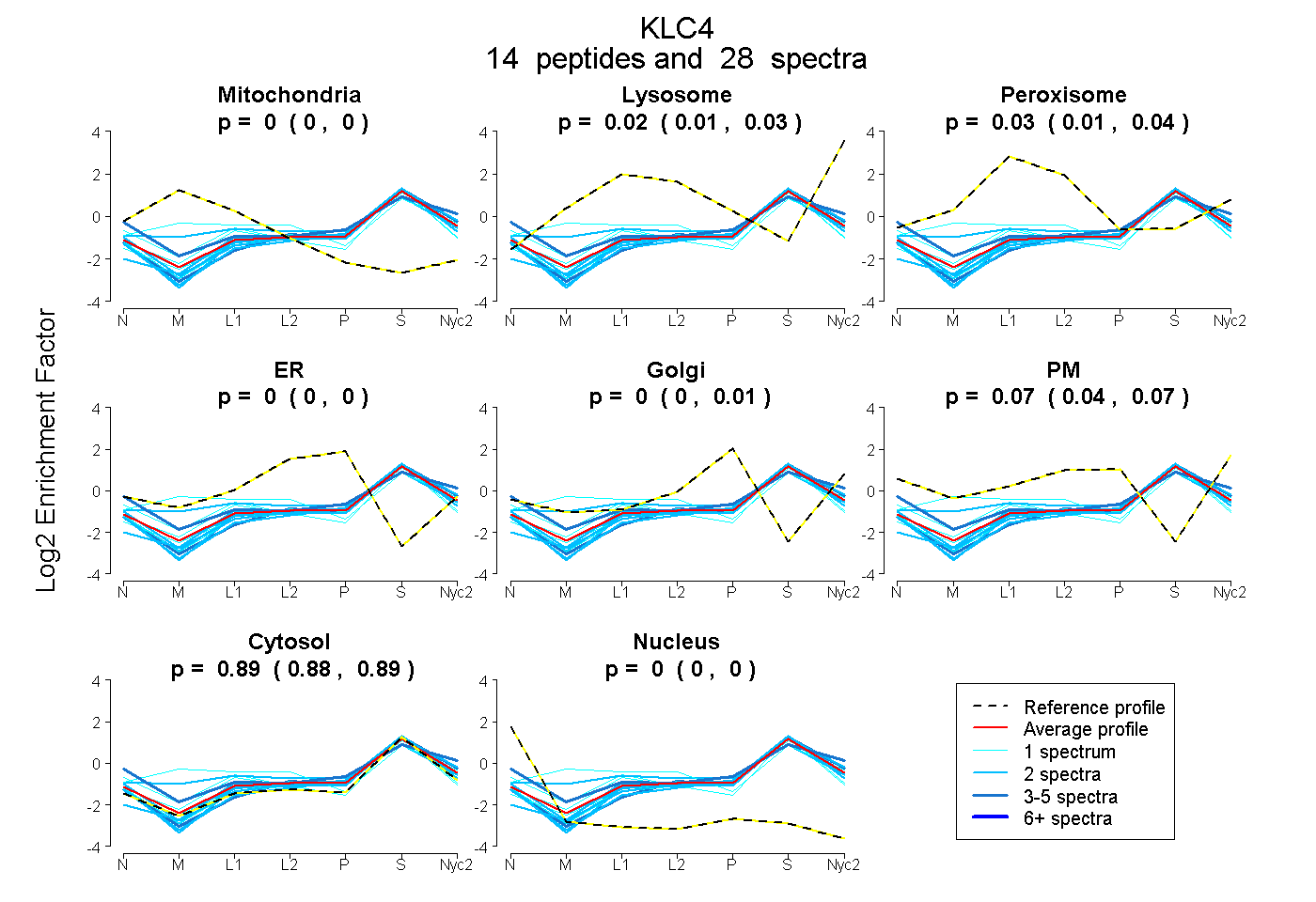
0.000 | 0.000
0.006 | 0.030
0.012 | 0.038
0.000 | 0.000
0.000 | 0.012
0.041 | 0.074
0.881 | 0.894
0.000 | 0.000
peptides
spectra
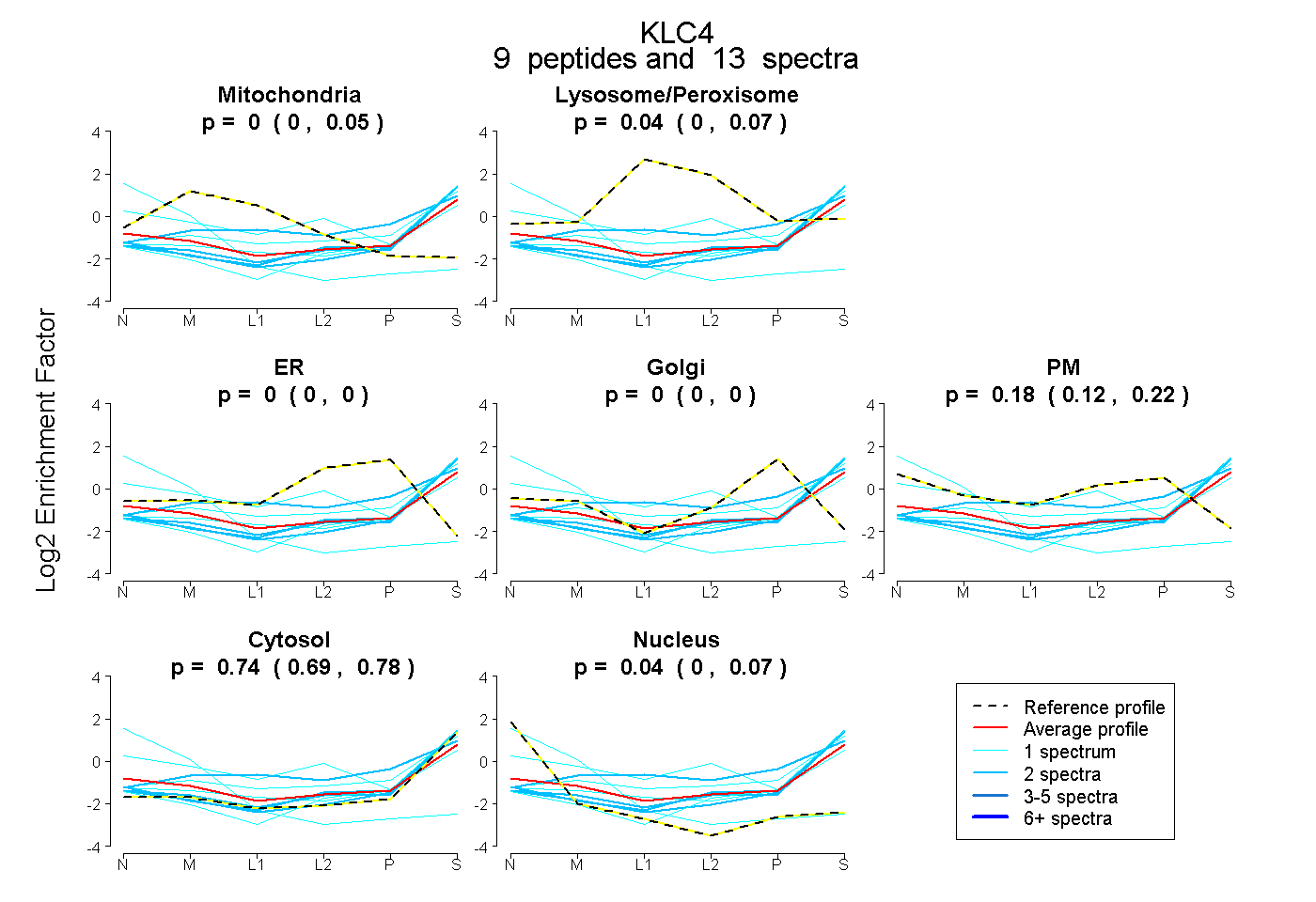
0.000 | 0.050
0.000 | 0.072
0.000 | 0.000
0.000 | 0.000
0.120 | 0.221
0.695 | 0.776
0.000 | 0.070
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.020 0.006 | 0.030 |
0.026 0.012 | 0.038 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.012 |
0.066 0.041 | 0.074 |
0.889 0.881 | 0.894 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
 |
0.003 0.000 | 0.050 |
0.040 0.000 | 0.072 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.179 0.120 | 0.221 |
0.738 0.695 | 0.776 |
0.040 0.000 | 0.070 |
| 2 spectra, LSQEEILGSTR | 0.000 | 0.008 | 0.002 | 0.000 | 0.088 | 0.901 | 0.000 | |||
| 1 spectrum, VSSPTVNTTLR | 0.000 | 0.000 | 0.000 | 0.058 | 0.000 | 0.942 | 0.000 | |||
| 2 spectra, QALEDLER | 0.000 | 0.000 | 0.000 | 0.036 | 0.000 | 0.951 | 0.012 | |||
| 1 spectrum, EAEPLCQR | 0.283 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.717 | |||
| 1 spectrum, DHPAVAATLNNLAVLYGK | 0.000 | 0.077 | 0.000 | 0.000 | 0.042 | 0.880 | 0.001 | |||
| 2 spectra, TLHNLVIQYAAQGR | 0.000 | 0.304 | 0.000 | 0.135 | 0.000 | 0.562 | 0.000 | |||
| 1 spectrum, HLEFLR | 0.000 | 0.204 | 0.000 | 0.090 | 0.000 | 0.706 | 0.000 | |||
| 2 spectra, NLGALYR | 0.000 | 0.035 | 0.000 | 0.000 | 0.043 | 0.922 | 0.000 | |||
| 1 spectrum, GQGAAAAQQGGYEIPAR | 0.039 | 0.293 | 0.000 | 0.000 | 0.198 | 0.391 | 0.078 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
30 spectra |
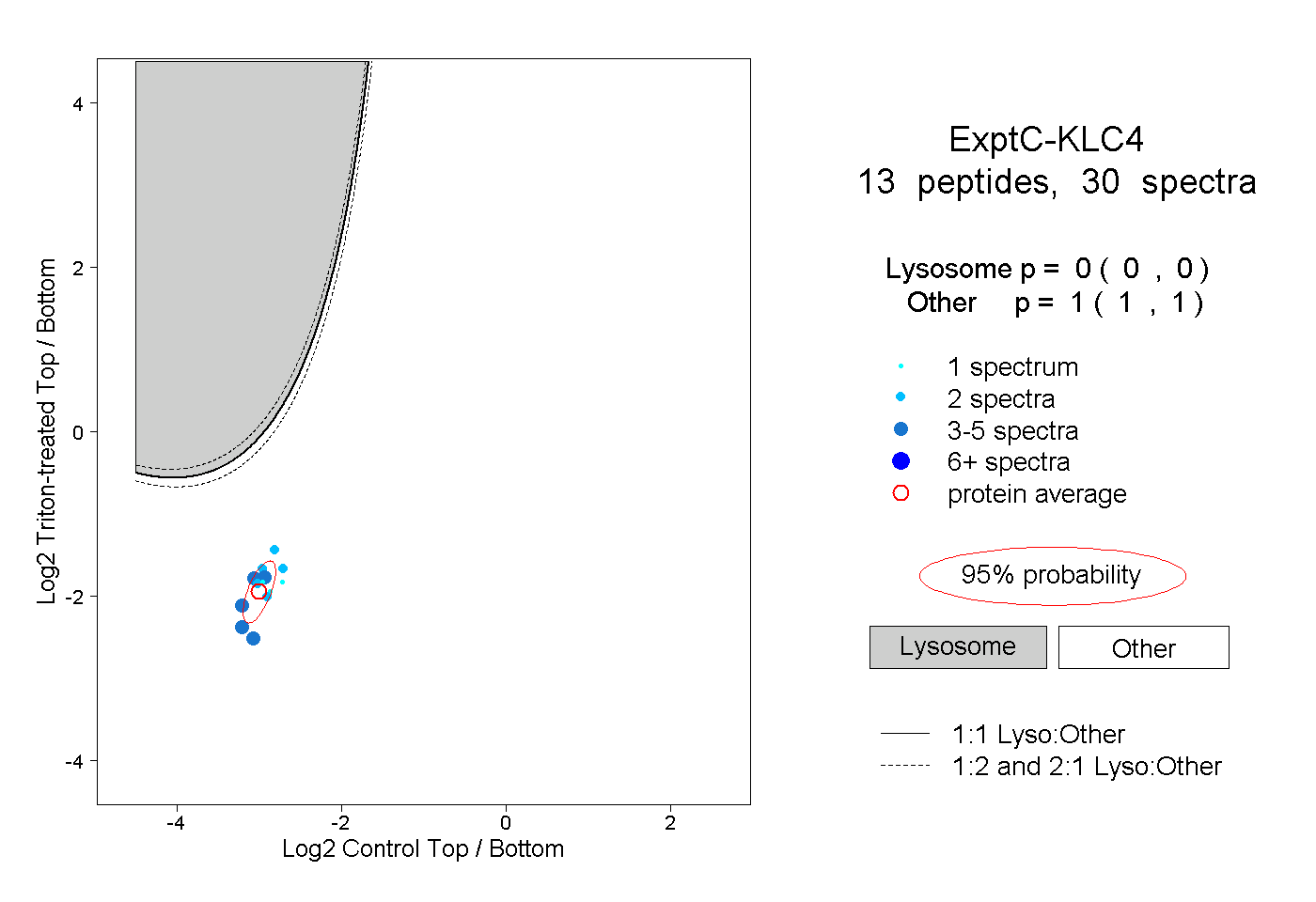 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
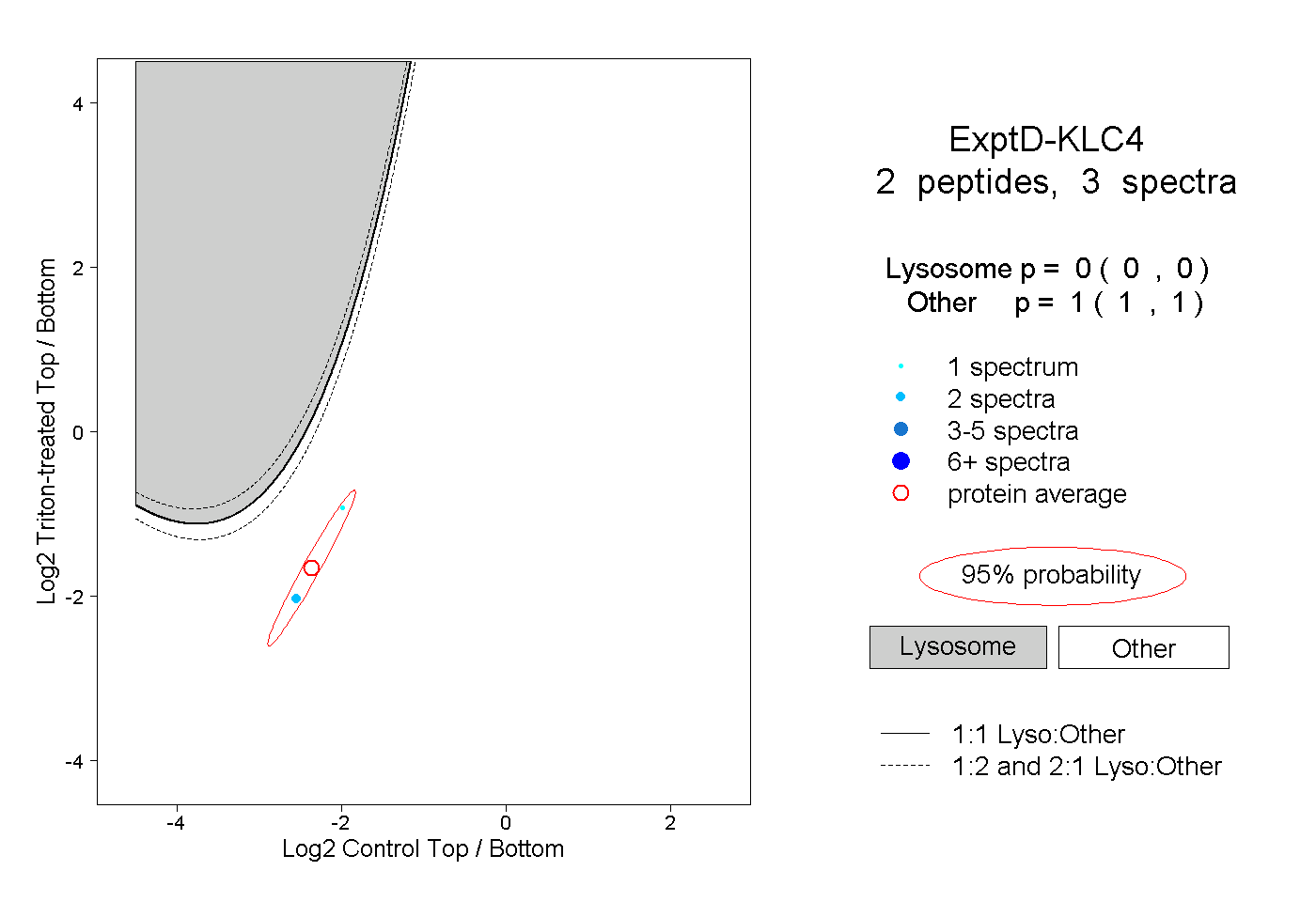 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |