peptides
spectra
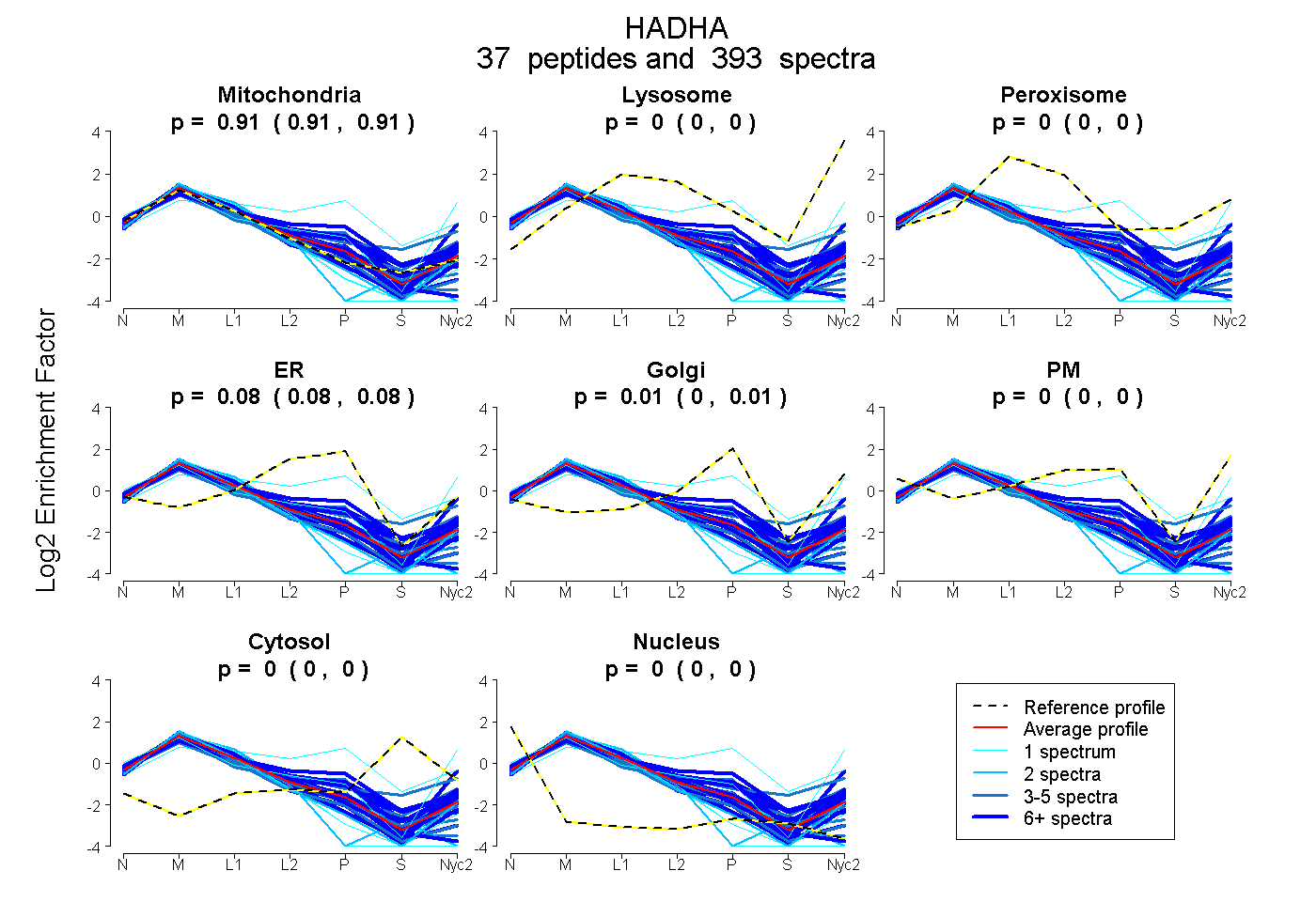
0.910 | 0.913
0.000 | 0.000
0.000 | 0.000
0.079 | 0.084
0.003 | 0.009
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
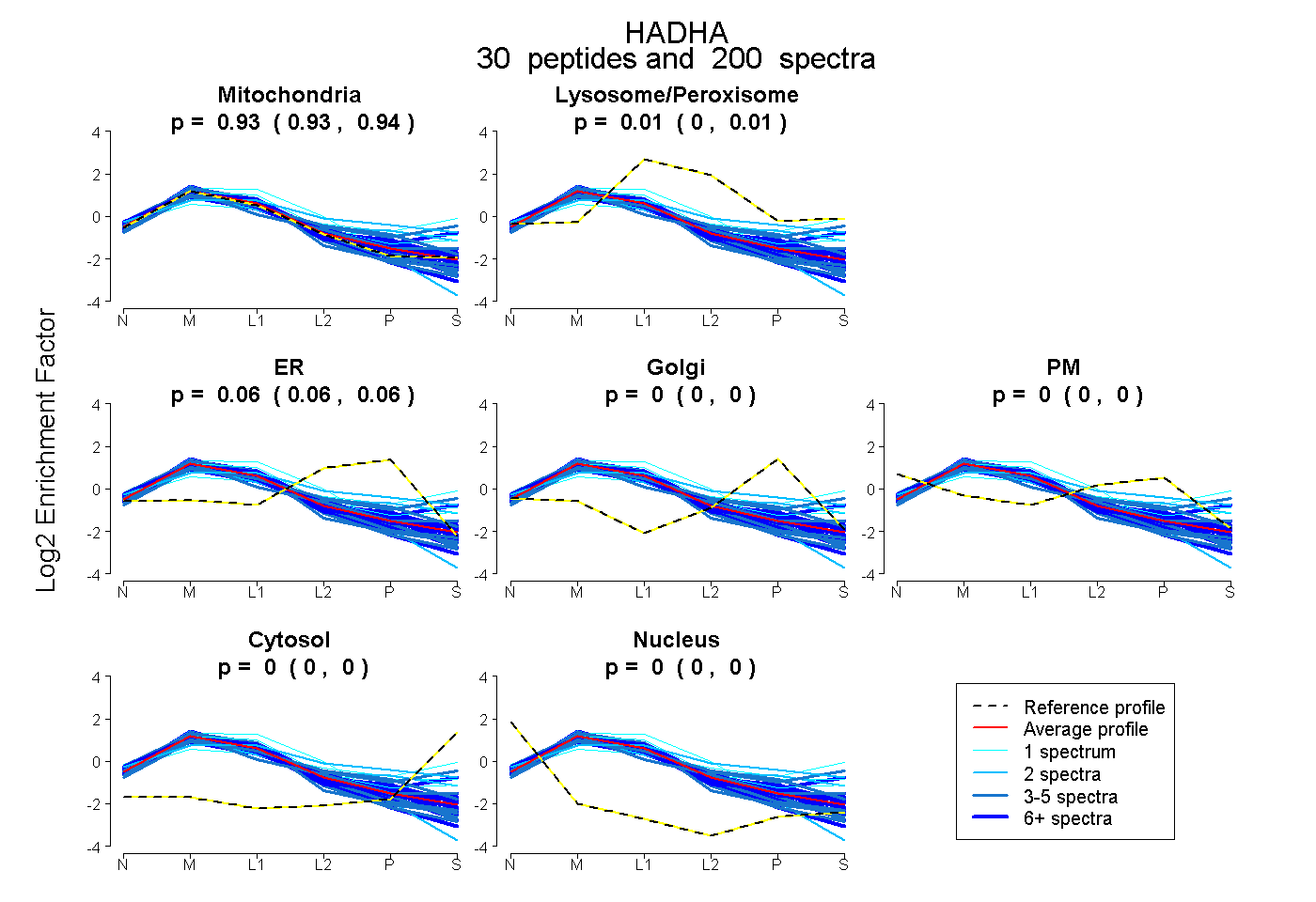
0.933 | 0.937
0.004 | 0.008
0.057 | 0.061
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
393 spectra |
 |
0.912 0.910 | 0.913 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.082 0.079 | 0.084 |
0.006 0.003 | 0.009 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
200 spectra |
 |
0.935 0.933 | 0.937 |
0.006 0.004 | 0.008 |
0.059 0.057 | 0.061 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, GFYIYQSGSK | 0.605 | 0.171 | 0.000 | 0.196 | 0.000 | 0.029 | 0.000 | |||
| 26 spectra, MQLLEIITTDK | 0.853 | 0.093 | 0.000 | 0.019 | 0.000 | 0.035 | 0.000 | |||
| 2 spectra, DLANNSSK | 0.992 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.008 | |||
| 8 spectra, ADMVIEAVFEDLAVK | 0.973 | 0.000 | 0.027 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, THINYGVK | 0.547 | 0.253 | 0.000 | 0.033 | 0.000 | 0.167 | 0.000 | |||
| 7 spectra, NLNSEIDNILVNLR | 0.879 | 0.069 | 0.000 | 0.025 | 0.017 | 0.000 | 0.010 | |||
| 9 spectra, DSIFSNLIGQLDYK | 0.657 | 0.145 | 0.000 | 0.000 | 0.045 | 0.152 | 0.000 | |||
| 7 spectra, LPAKPEVSSDEDIQYR | 0.936 | 0.010 | 0.000 | 0.048 | 0.000 | 0.005 | 0.000 | |||
| 18 spectra, DGPGFYTTR | 0.864 | 0.048 | 0.000 | 0.088 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, LLDAVK | 0.987 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.013 | |||
| 1 spectrum, CLAPMMSEVIR | 0.882 | 0.118 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VNTLNK | 0.426 | 0.358 | 0.000 | 0.186 | 0.000 | 0.029 | 0.000 | |||
| 14 spectra, TIEYLEEVAVNFAK | 0.854 | 0.050 | 0.000 | 0.000 | 0.096 | 0.000 | 0.000 | |||
| 3 spectra, GQQQVFK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, GFLGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ISQEGQK | 0.865 | 0.029 | 0.000 | 0.000 | 0.106 | 0.000 | 0.000 | |||
| 3 spectra, ALMGLYNGQVLCK | 0.861 | 0.000 | 0.139 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, FVDLYGAQK | 0.993 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.007 | |||
| 5 spectra, ILQEGVDPK | 0.969 | 0.000 | 0.031 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LTSYAMTIPFVR | 0.761 | 0.194 | 0.000 | 0.000 | 0.000 | 0.045 | 0.000 | |||
| 1 spectrum, ALTEYAR | 0.352 | 0.312 | 0.000 | 0.043 | 0.071 | 0.221 | 0.000 | |||
| 16 spectra, DTTVTGLGR | 0.935 | 0.000 | 0.065 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FGAPQK | 0.586 | 0.172 | 0.000 | 0.058 | 0.095 | 0.089 | 0.000 | |||
| 8 spectra, ALTSFER | 0.992 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.008 | |||
| 3 spectra, VIIVVK | 0.709 | 0.101 | 0.083 | 0.091 | 0.015 | 0.000 | 0.000 | |||
| 6 spectra, GDVAVIR | 0.953 | 0.000 | 0.000 | 0.047 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VIGMHYFSPVDK | 0.839 | 0.002 | 0.088 | 0.000 | 0.000 | 0.071 | 0.000 | |||
| 14 spectra, FGELALTK | 0.982 | 0.000 | 0.018 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, DTTASAVAVGLK | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.016 | |||
| 6 spectra, FGGGSVELLK | 0.833 | 0.030 | 0.048 | 0.089 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1701 spectra |
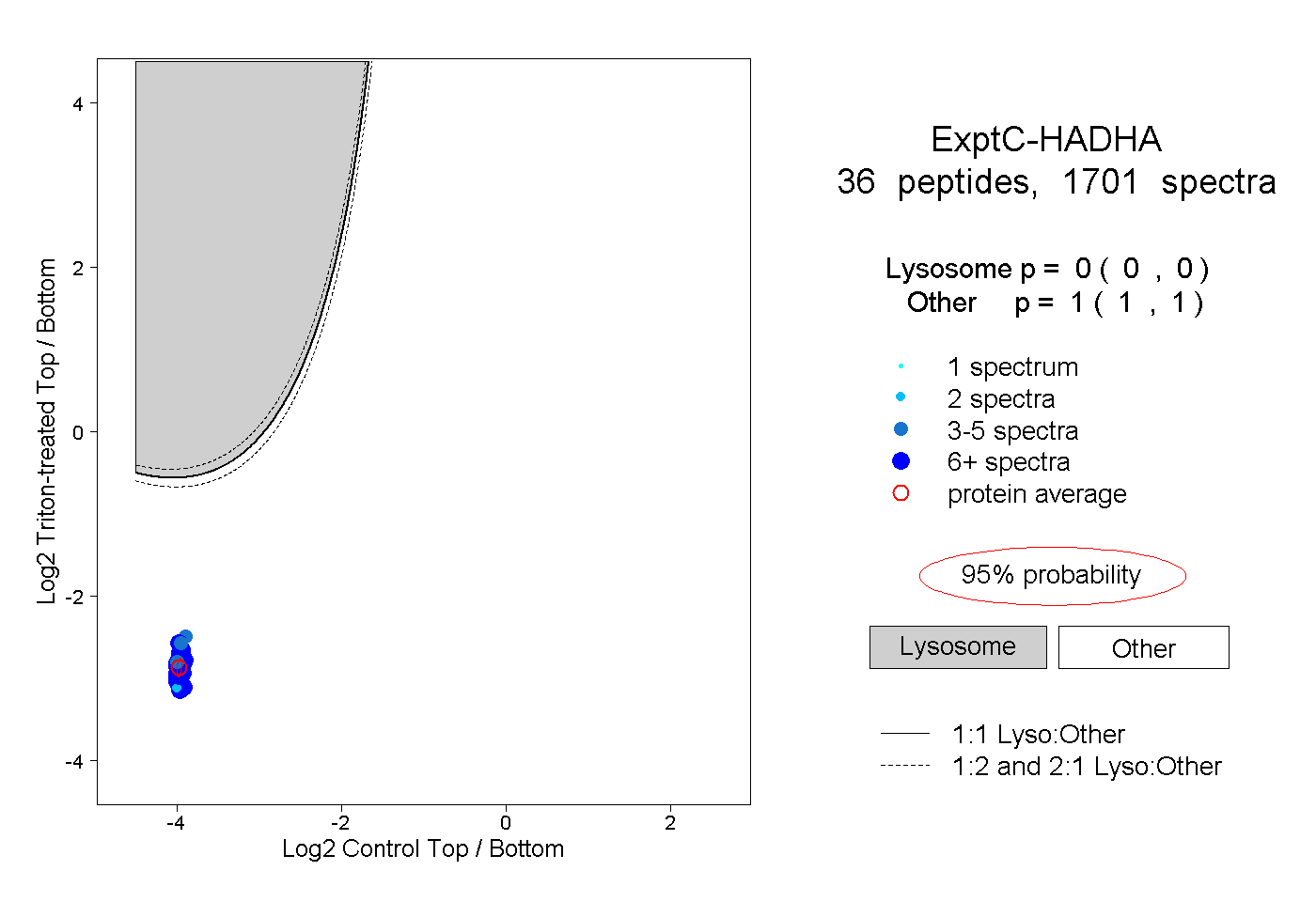 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
108 spectra |
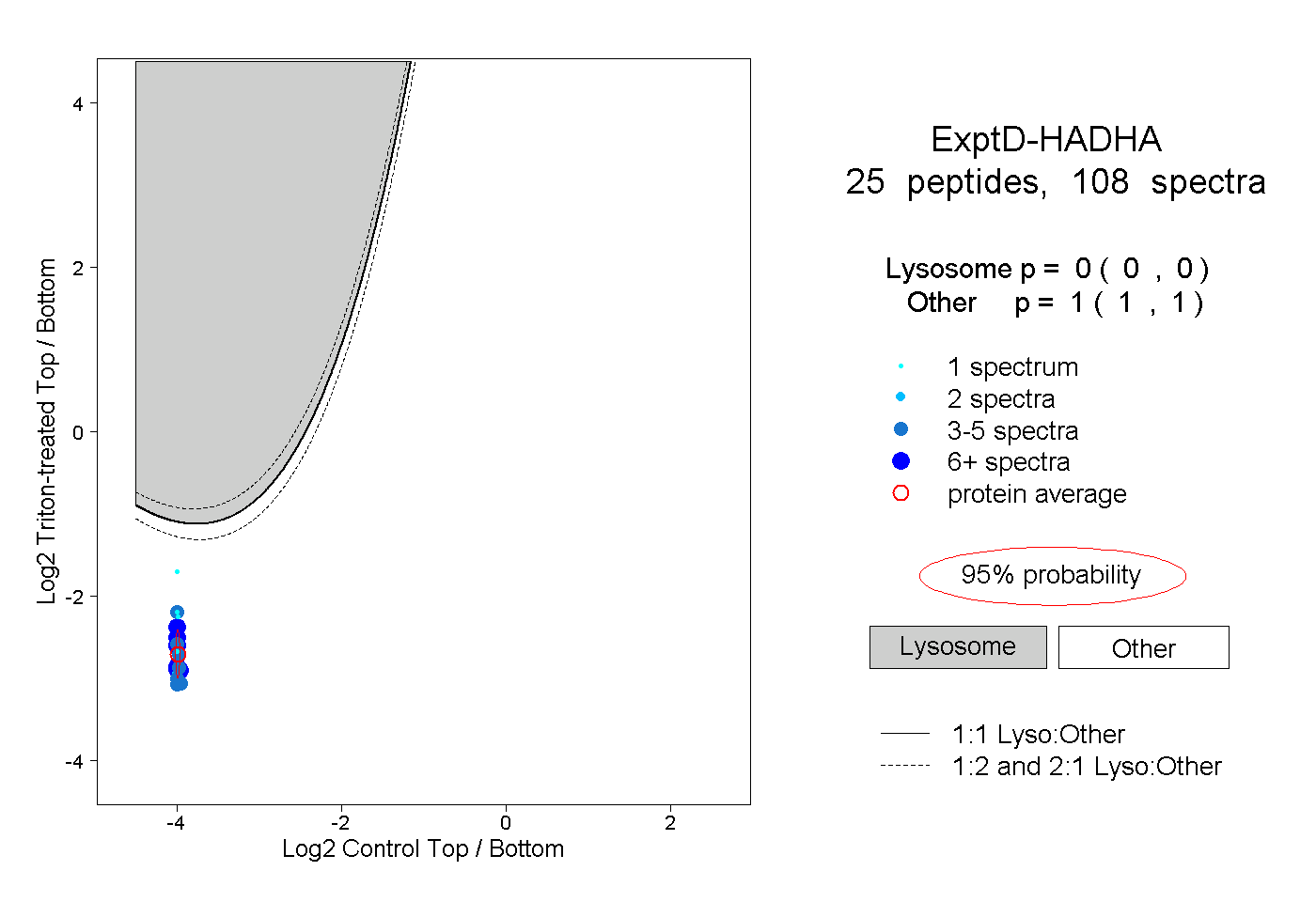 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |