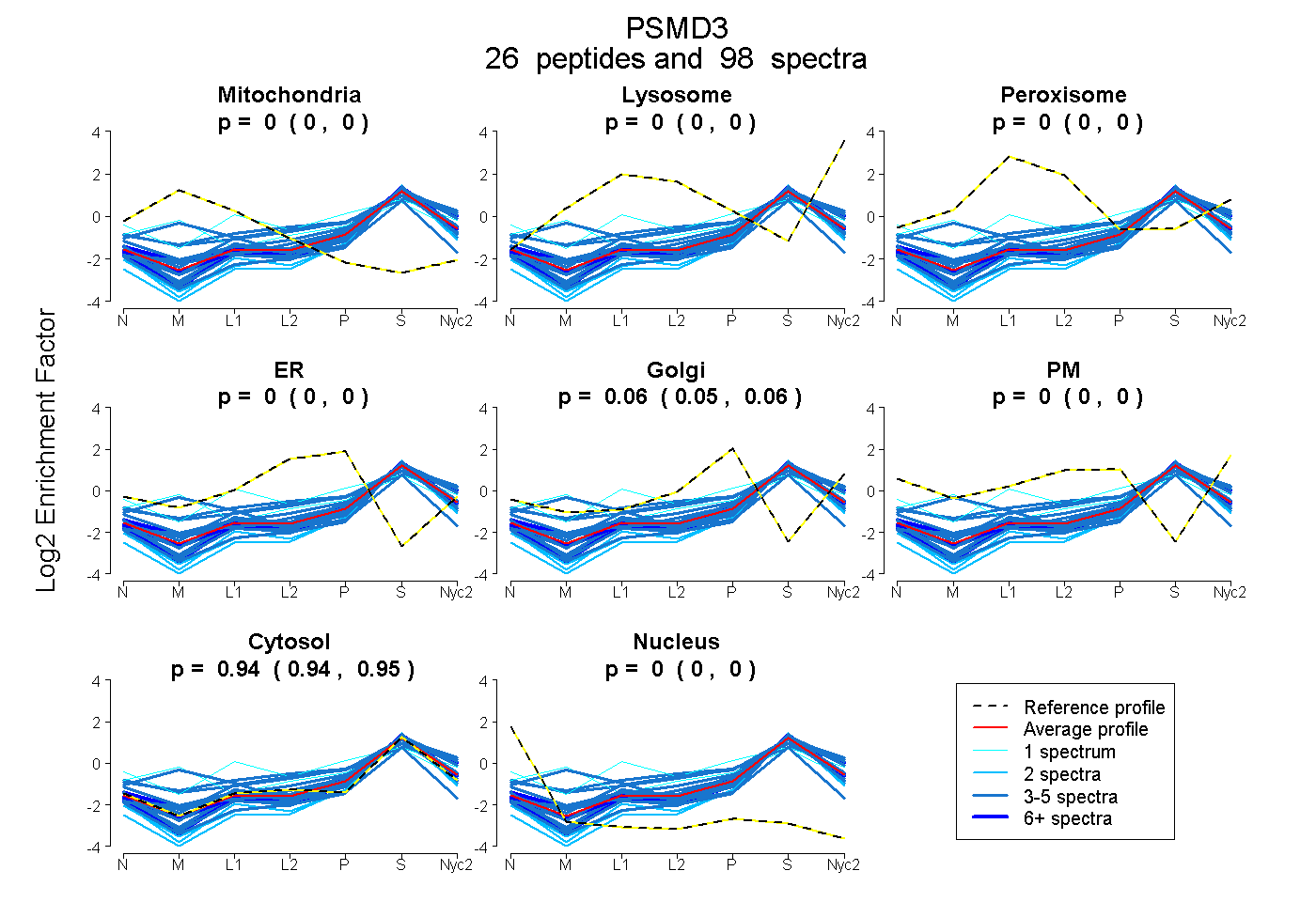
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.054 | 0.058
0.000 | 0.000
0.941 | 0.946
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
98 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.056 0.054 | 0.058 |
0.000 0.000 | 0.000 |
0.944 0.941 | 0.946 |
0.000 0.000 | 0.000 |
| 3 spectra, SVFPEQANNNEWAR | 0.000 | 0.003 | 0.000 | 0.000 | 0.029 | 0.000 | 0.968 | 0.000 | ||
| 1 spectrum, DGVIEASINHEK | 0.000 | 0.000 | 0.252 | 0.000 | 0.193 | 0.000 | 0.555 | 0.000 | ||
| 3 spectra, AIQLEYSEAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.981 | 0.019 | ||
| 3 spectra, SFLHAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.112 | 0.000 | 0.888 | 0.000 | ||
| 3 spectra, HDADGQATLLNLLLR | 0.347 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.653 | 0.000 | ||
| 2 spectra, DLESAEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, ISLADIAQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 5 spectra, EMIDIYSTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, EQQDLEFAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 4 spectra, CYYYHAR | 0.000 | 0.000 | 0.108 | 0.000 | 0.186 | 0.000 | 0.706 | 0.000 | ||
| 4 spectra, AVHGFFTSNNATR | 0.000 | 0.127 | 0.041 | 0.000 | 0.102 | 0.073 | 0.657 | 0.000 | ||
| 5 spectra, ISDDLMQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 | 0.000 | 0.998 | 0.000 | ||
| 3 spectra, VYEFLDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.980 | 0.020 | ||
| 4 spectra, EPQLAFHQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.070 | 0.000 | 0.930 | 0.000 | ||
| 3 spectra, LNHYVLYK | 0.000 | 0.138 | 0.000 | 0.000 | 0.083 | 0.000 | 0.779 | 0.000 | ||
| 2 spectra, ALDLVAAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.974 | 0.026 | ||
| 2 spectra, ELDTVTLEDIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.998 | 0.002 | ||
| 3 spectra, SLMPYFLLTQAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | 0.957 | 0.000 | ||
| 4 spectra, FQTDGTYTLIIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.008 | 0.000 | 0.992 | 0.000 | ||
| 7 spectra, MISLSYSR | 0.000 | 0.055 | 0.000 | 0.000 | 0.057 | 0.000 | 0.888 | 0.000 | ||
| 2 spectra, DFLLPFLEEPMDTEADLQFRPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 12 spectra, MLPSTSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.041 | 0.000 | 0.959 | 0.000 | ||
| 4 spectra, TMTNALR | 0.000 | 0.041 | 0.000 | 0.000 | 0.052 | 0.000 | 0.907 | 0.000 | ||
| 5 spectra, AAATEHSQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.107 | 0.000 | 0.893 | 0.000 | ||
| 1 spectrum, FNQVLDQFGEK | 0.203 | 0.045 | 0.000 | 0.000 | 0.157 | 0.000 | 0.595 | 0.000 | ||
| 4 spectra, YLYYTGR | 0.000 | 0.011 | 0.000 | 0.000 | 0.049 | 0.000 | 0.940 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
38 spectra |
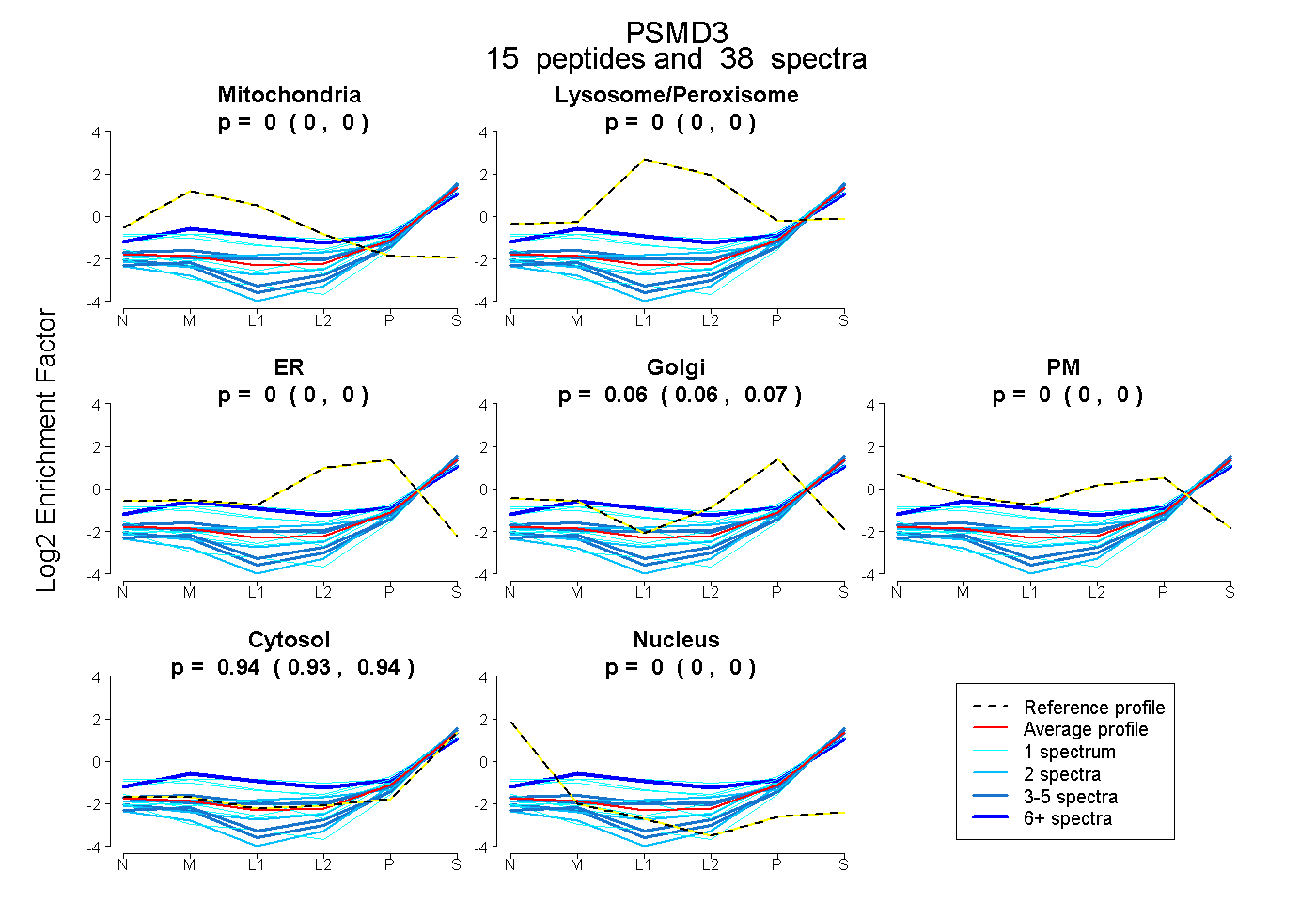 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.063 0.057 | 0.068 |
0.000 0.000 | 0.000 |
0.937 0.931 | 0.942 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
69 spectra |
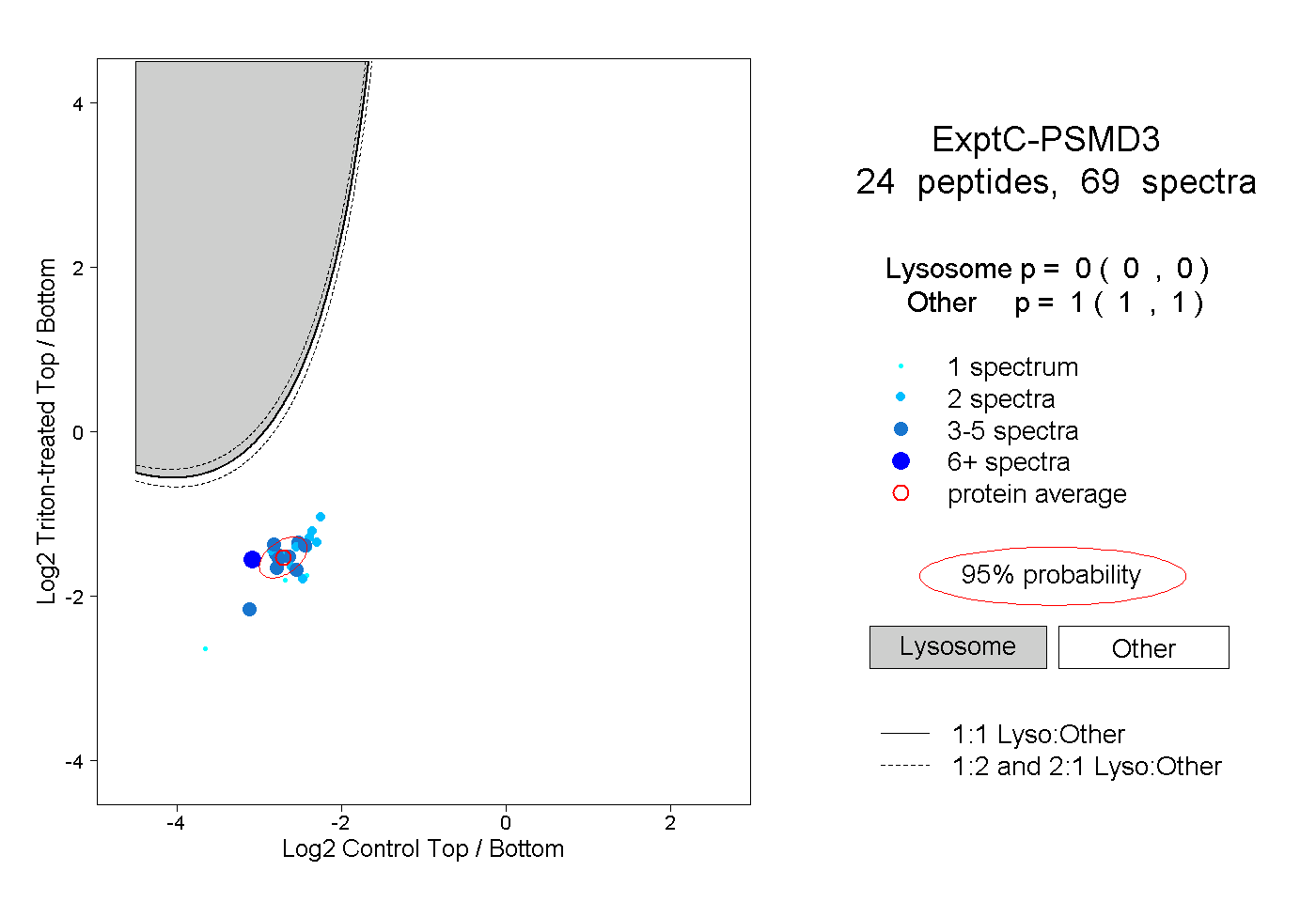 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
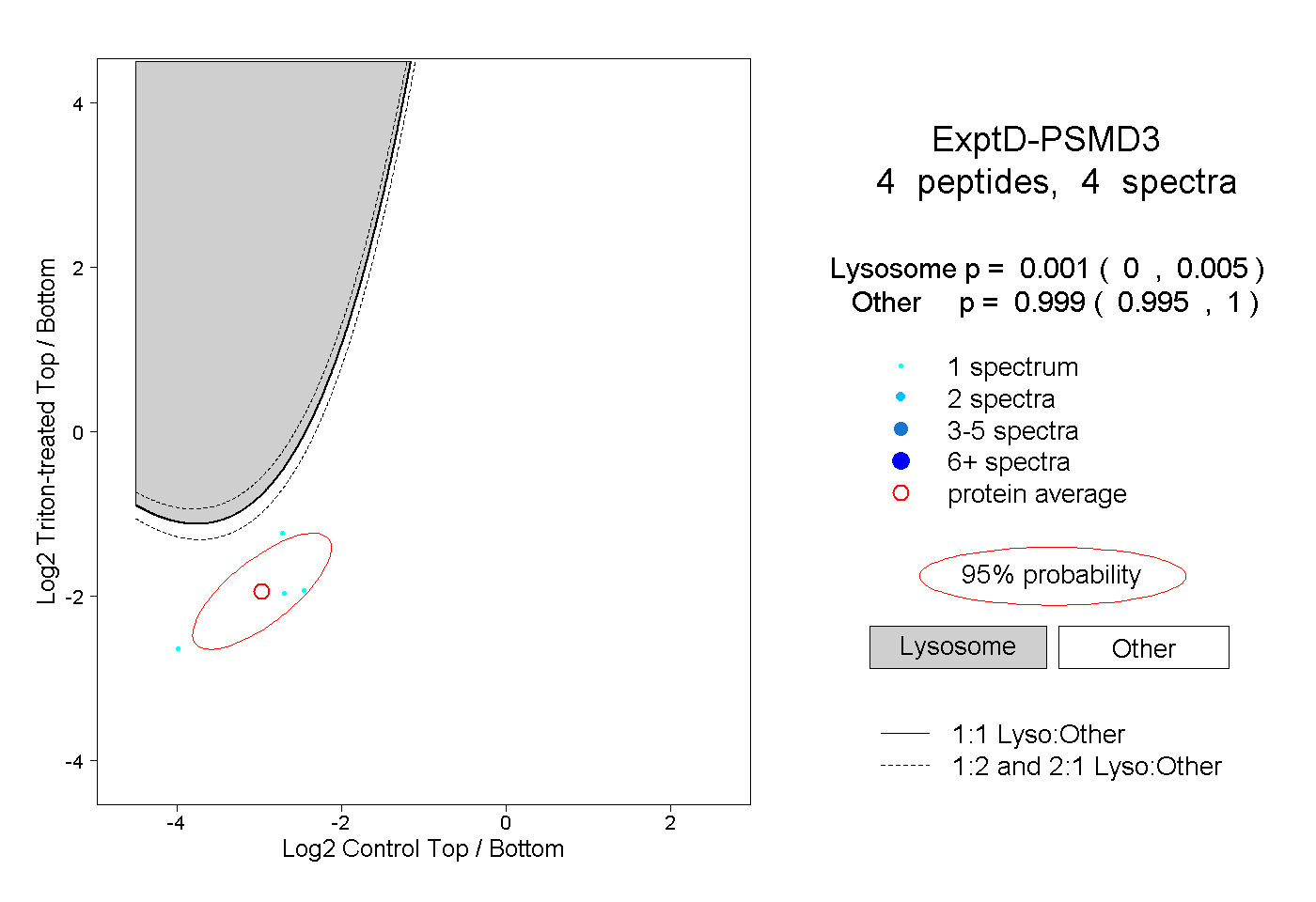 |
0.001 0.000 | 0.005 |
0.999 0.995 | 1.000 |