peptides
spectra
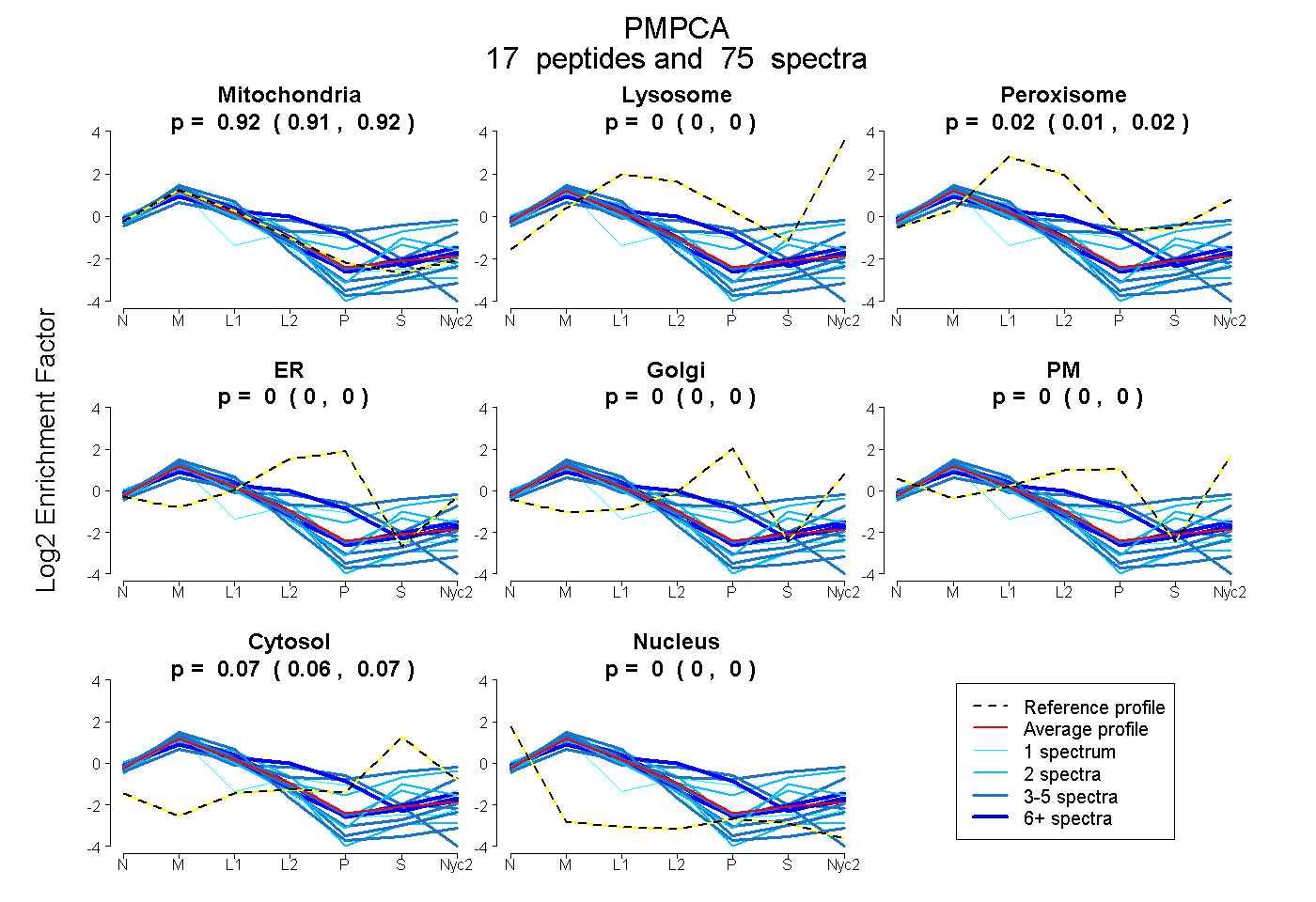
0.907 | 0.923
0.000 | 0.000
0.009 | 0.022
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.063 | 0.072
0.000 | 0.000
peptides
spectra
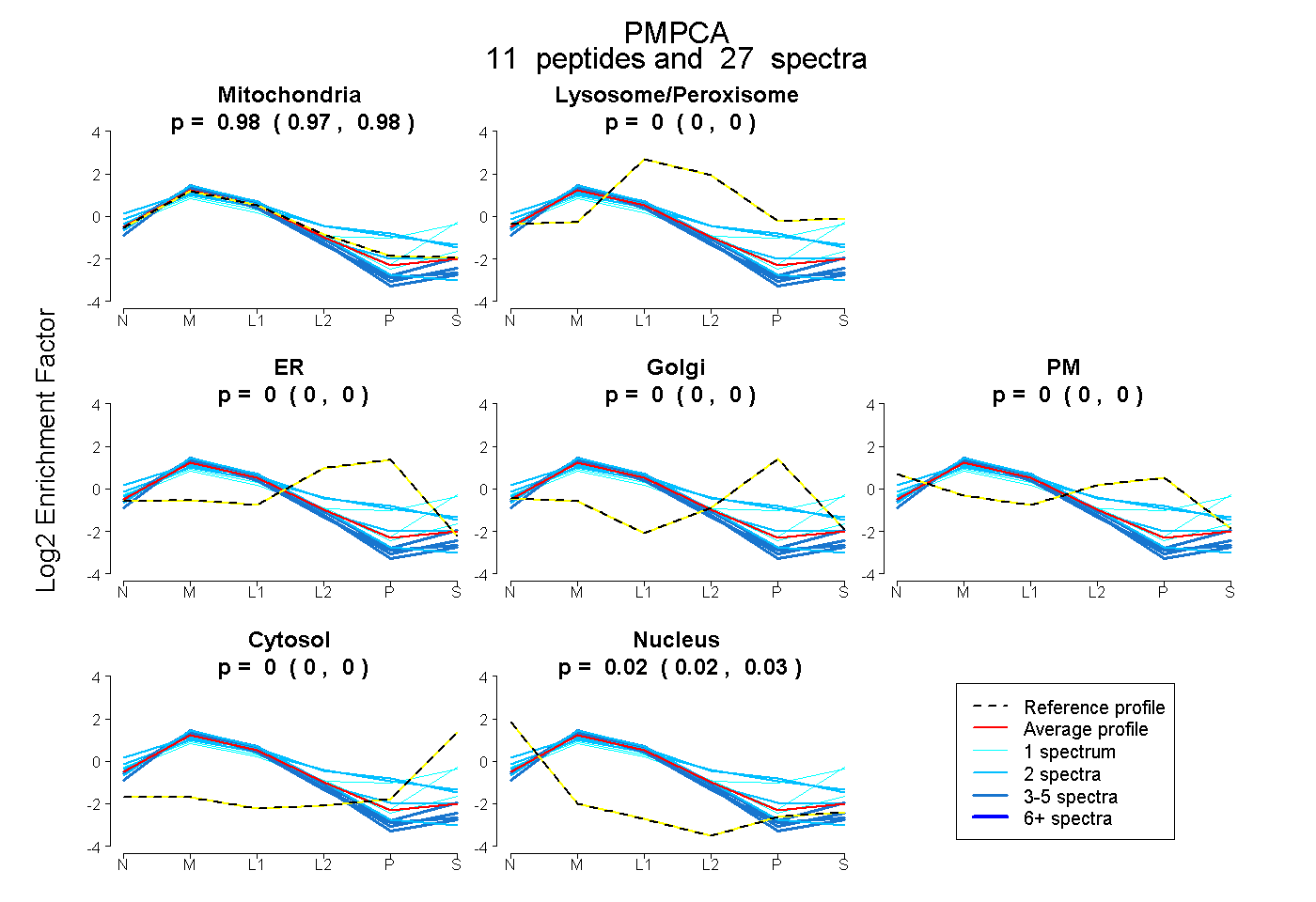
0.970 | 0.980
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.019 | 0.028
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
75 spectra |
 |
0.916 0.907 | 0.923 |
0.000 0.000 | 0.000 |
0.016 0.009 | 0.022 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.068 0.063 | 0.072 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
 |
0.976 0.970 | 0.980 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.024 0.019 | 0.028 |
| 2 spectra, VTTLDNGLR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, TVDLVELER | 0.991 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.009 | |||
| 1 spectrum, EVLHSYLK | 0.674 | 0.100 | 0.000 | 0.000 | 0.000 | 0.226 | 0.000 | |||
| 2 spectra, NYYTPDR | 0.923 | 0.008 | 0.000 | 0.000 | 0.000 | 0.000 | 0.068 | |||
| 2 spectra, QVLATHSR | 0.673 | 0.180 | 0.000 | 0.147 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, LAFSSTAR | 0.943 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.057 | |||
| 2 spectra, ENTVGLHR | 0.644 | 0.133 | 0.000 | 0.044 | 0.166 | 0.013 | 0.000 | |||
| 1 spectrum, HGGICDCQTSR | 0.555 | 0.169 | 0.000 | 0.057 | 0.000 | 0.219 | 0.000 | |||
| 4 spectra, LTDEEIEMTR | 0.989 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.011 | |||
| 3 spectra, LYLNVLNR | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | |||
| 1 spectrum, EFILMGR | 0.954 | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
254 spectra |
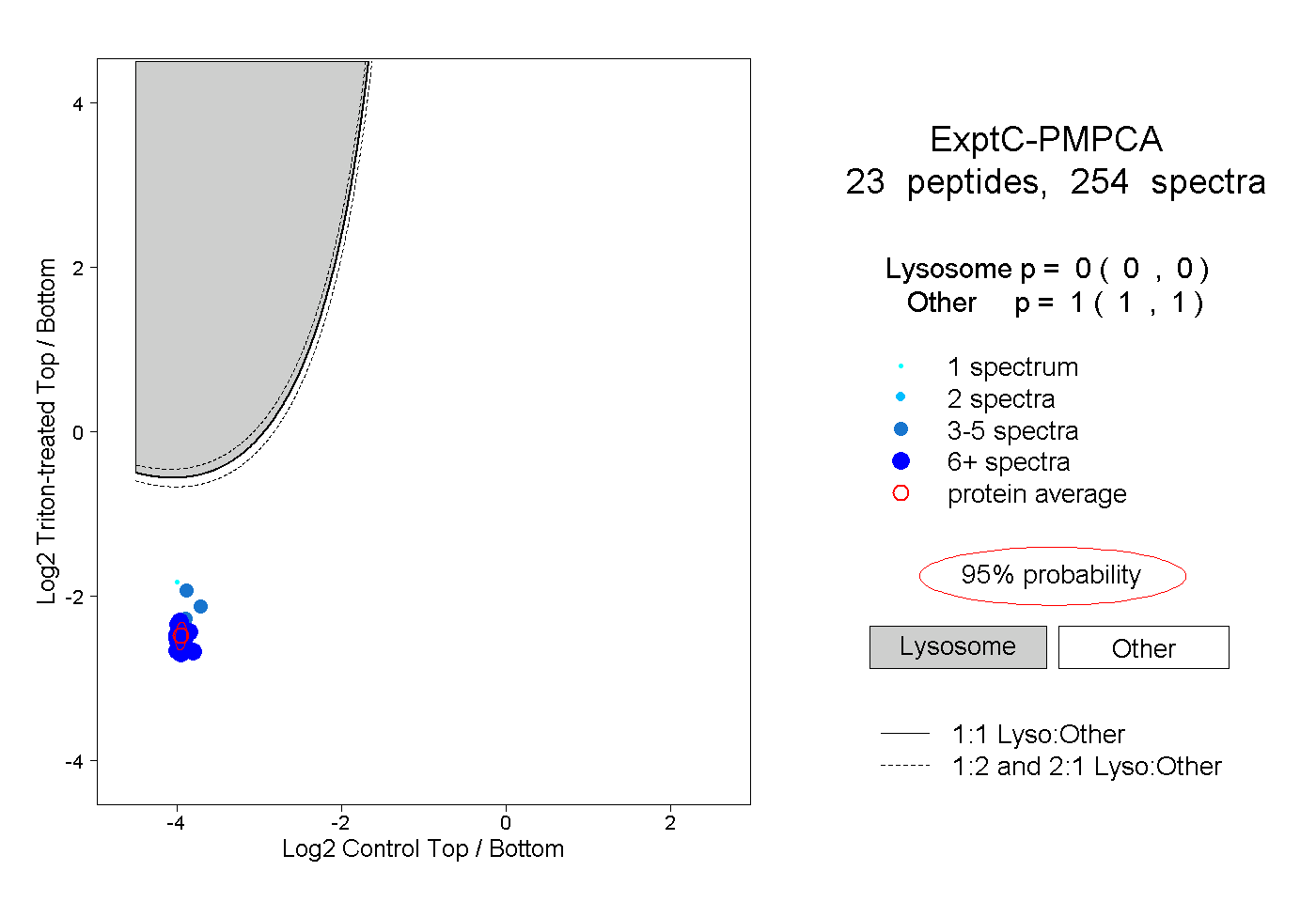 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
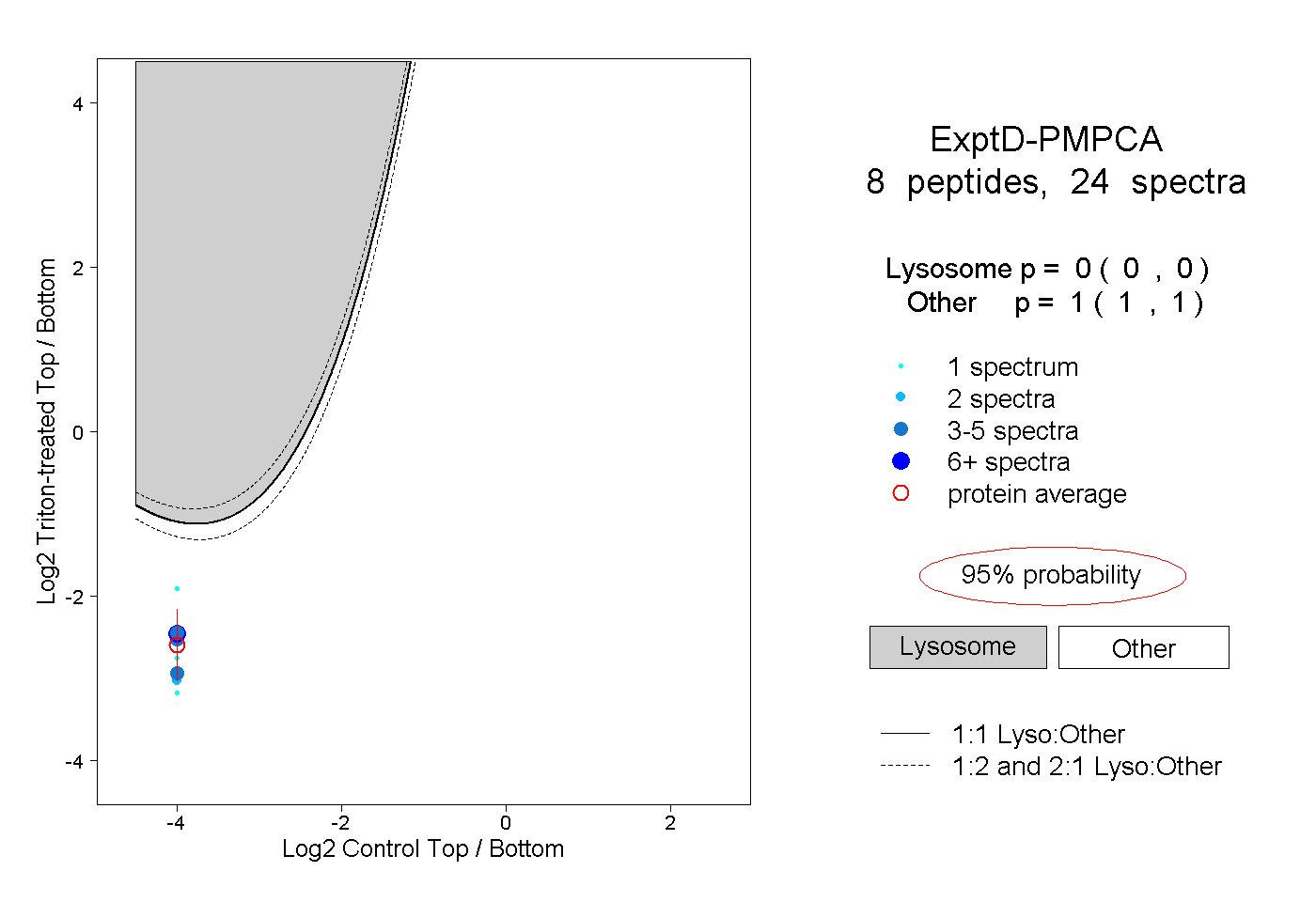 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |