peptides
spectra
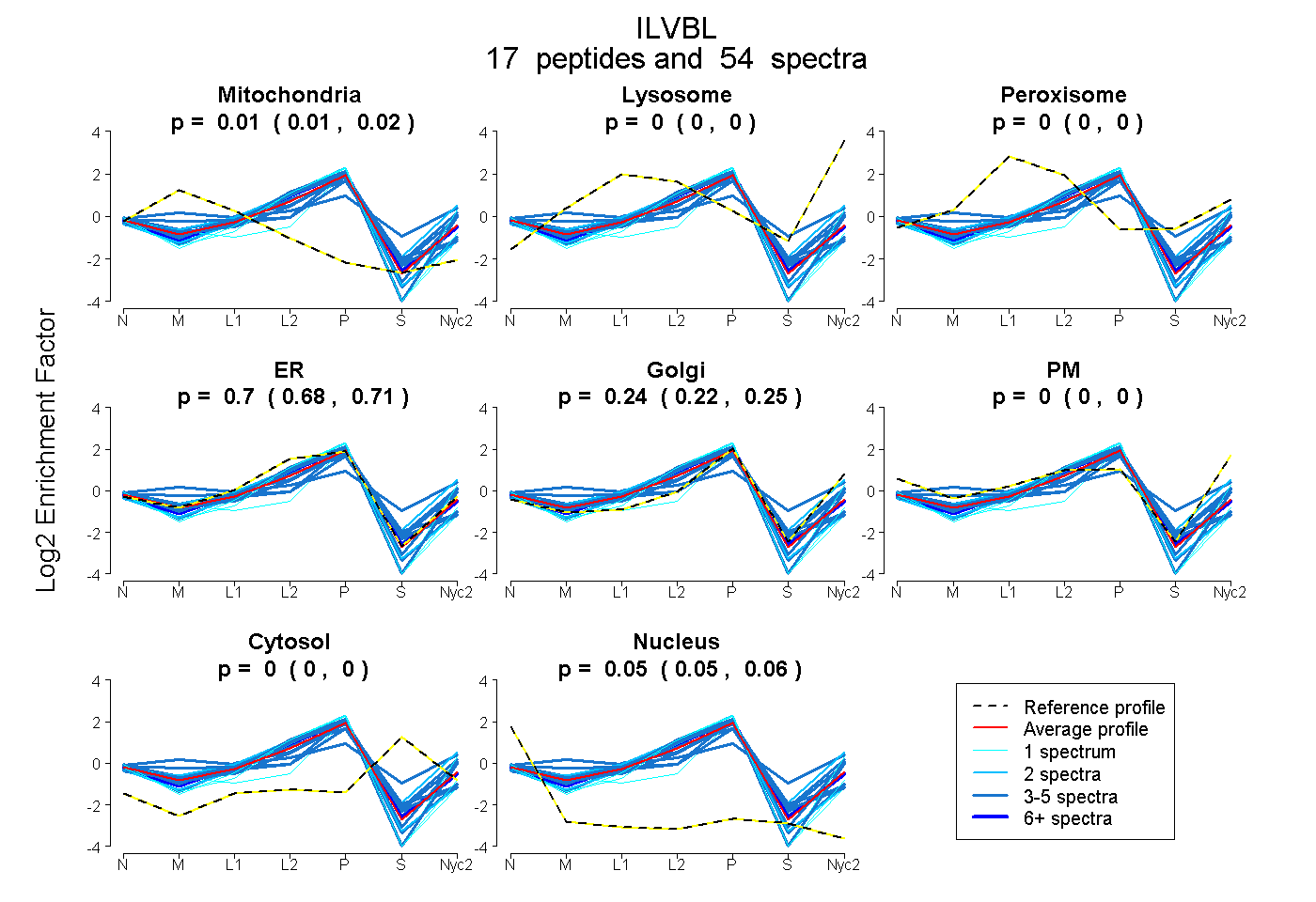
0.006 | 0.017
0.000 | 0.000
0.000 | 0.000
0.682 | 0.715
0.219 | 0.249
0.000 | 0.000
0.000 | 0.000
0.047 | 0.056
peptides
spectra
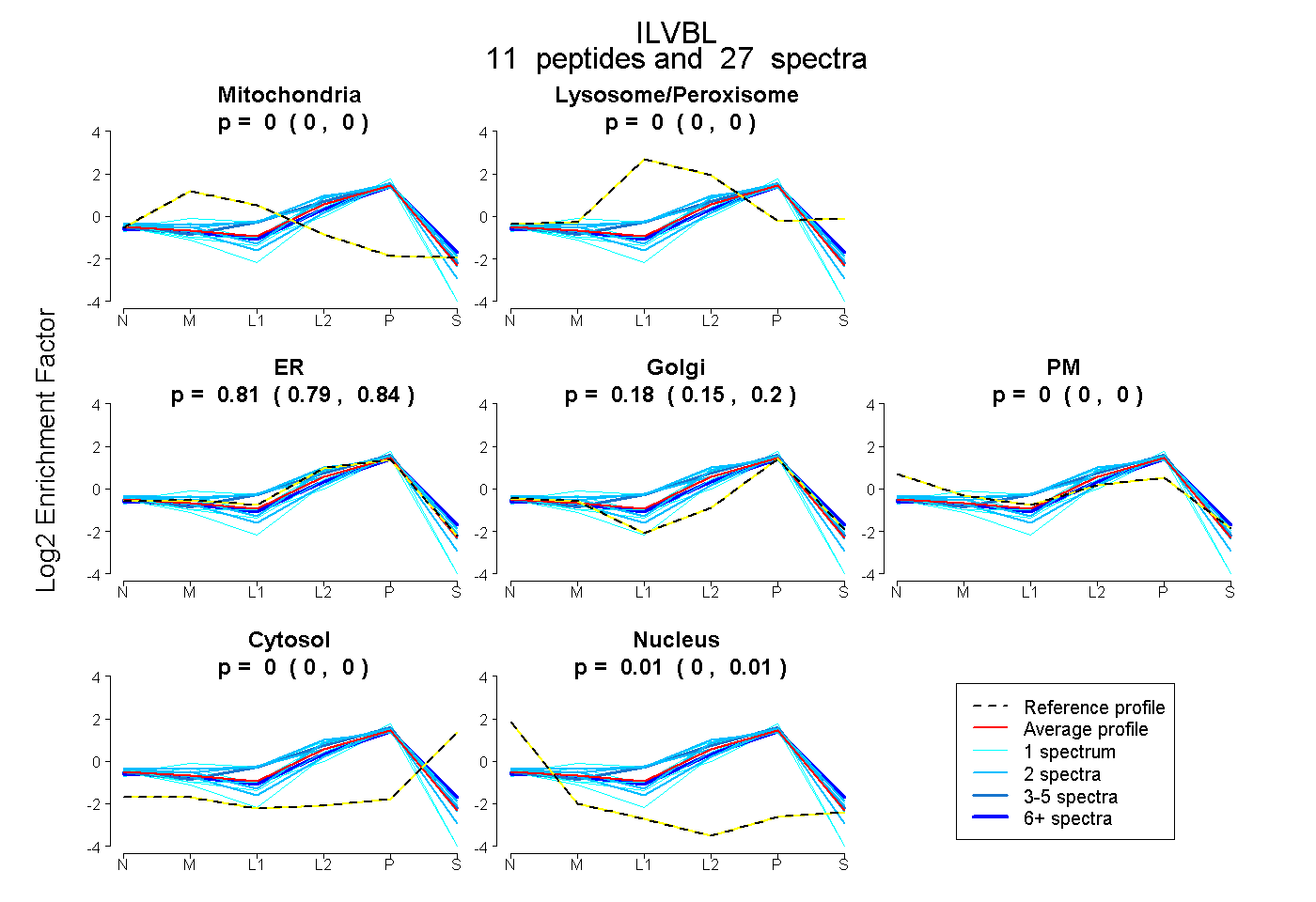
0.000 | 0.000
0.000 | 0.000
0.789 | 0.837
0.152 | 0.204
0.000 | 0.000
0.000 | 0.000
0.000 | 0.010
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
54 spectra |
 |
0.012 0.006 | 0.017 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.700 0.682 | 0.715 |
0.236 0.219 | 0.249 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.052 0.047 | 0.056 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.815 0.789 | 0.837 |
0.180 0.152 | 0.204 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.005 0.000 | 0.010 |
| 2 spectra, NHPLHIR | 0.000 | 0.164 | 0.603 | 0.201 | 0.032 | 0.000 | 0.000 | |||
| 1 spectrum, AAMGLGAQGLILSR | 0.024 | 0.000 | 0.597 | 0.380 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DNEDQVVK | 0.000 | 0.000 | 0.478 | 0.518 | 0.000 | 0.000 | 0.005 | |||
| 2 spectra, SSIIIVNR | 0.000 | 0.000 | 0.862 | 0.138 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, ALLPVPQHLNPVR | 0.000 | 0.061 | 0.560 | 0.350 | 0.000 | 0.029 | 0.000 | |||
| 1 spectrum, LGLFYQLMHK | 0.000 | 0.000 | 0.883 | 0.108 | 0.000 | 0.009 | 0.000 | |||
| 2 spectra, HGGESVAAVLR | 0.000 | 0.099 | 0.824 | 0.000 | 0.078 | 0.000 | 0.000 | |||
| 2 spectra, LCQEGHAVVVNILIGR | 0.000 | 0.000 | 0.520 | 0.480 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DIVPTLR | 0.000 | 0.000 | 0.633 | 0.349 | 0.000 | 0.018 | 0.000 | |||
| 3 spectra, FCASVR | 0.000 | 0.070 | 0.877 | 0.052 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GALQAIDQMSLFRPLCK | 0.035 | 0.000 | 0.965 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
52 spectra |
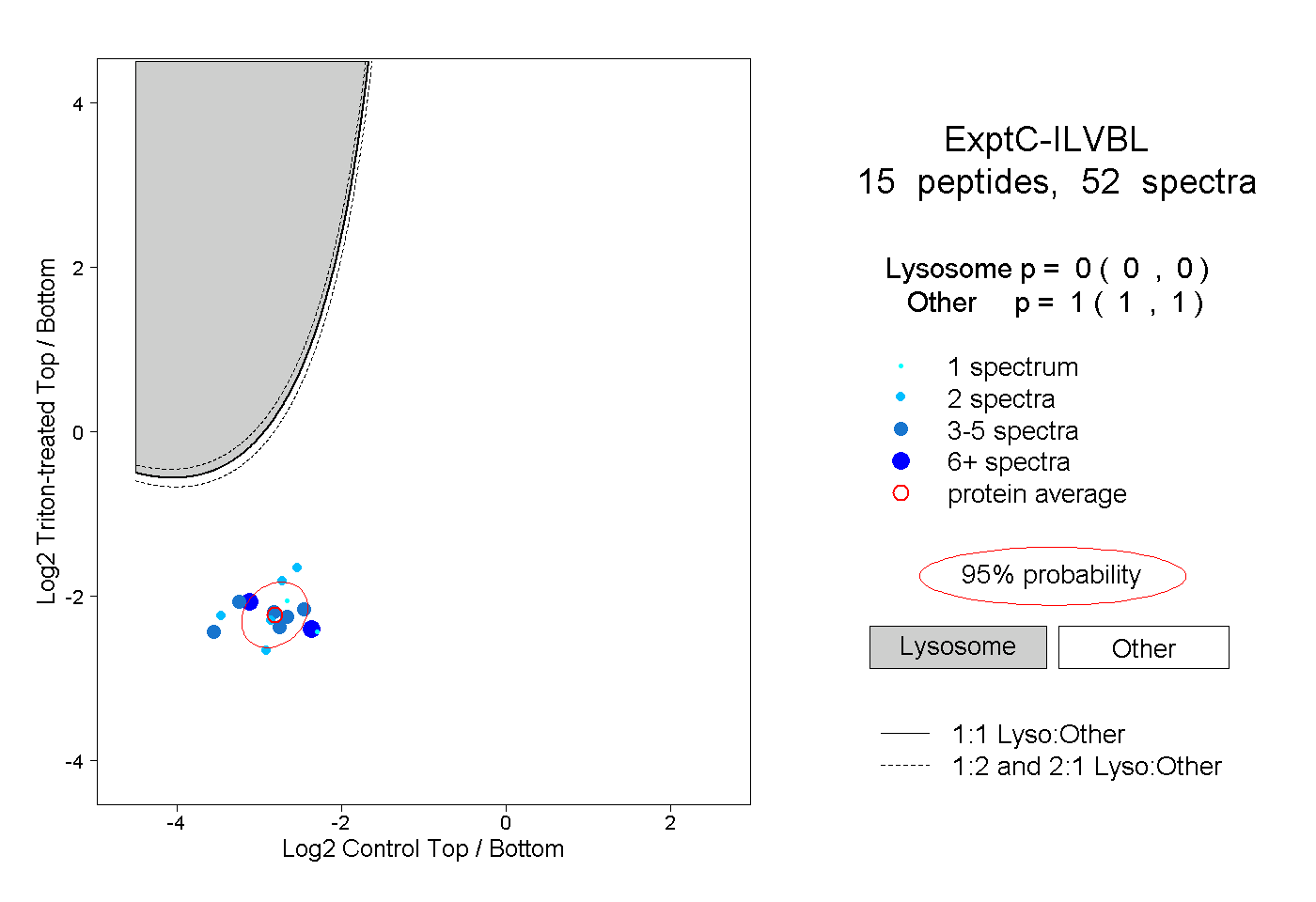 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
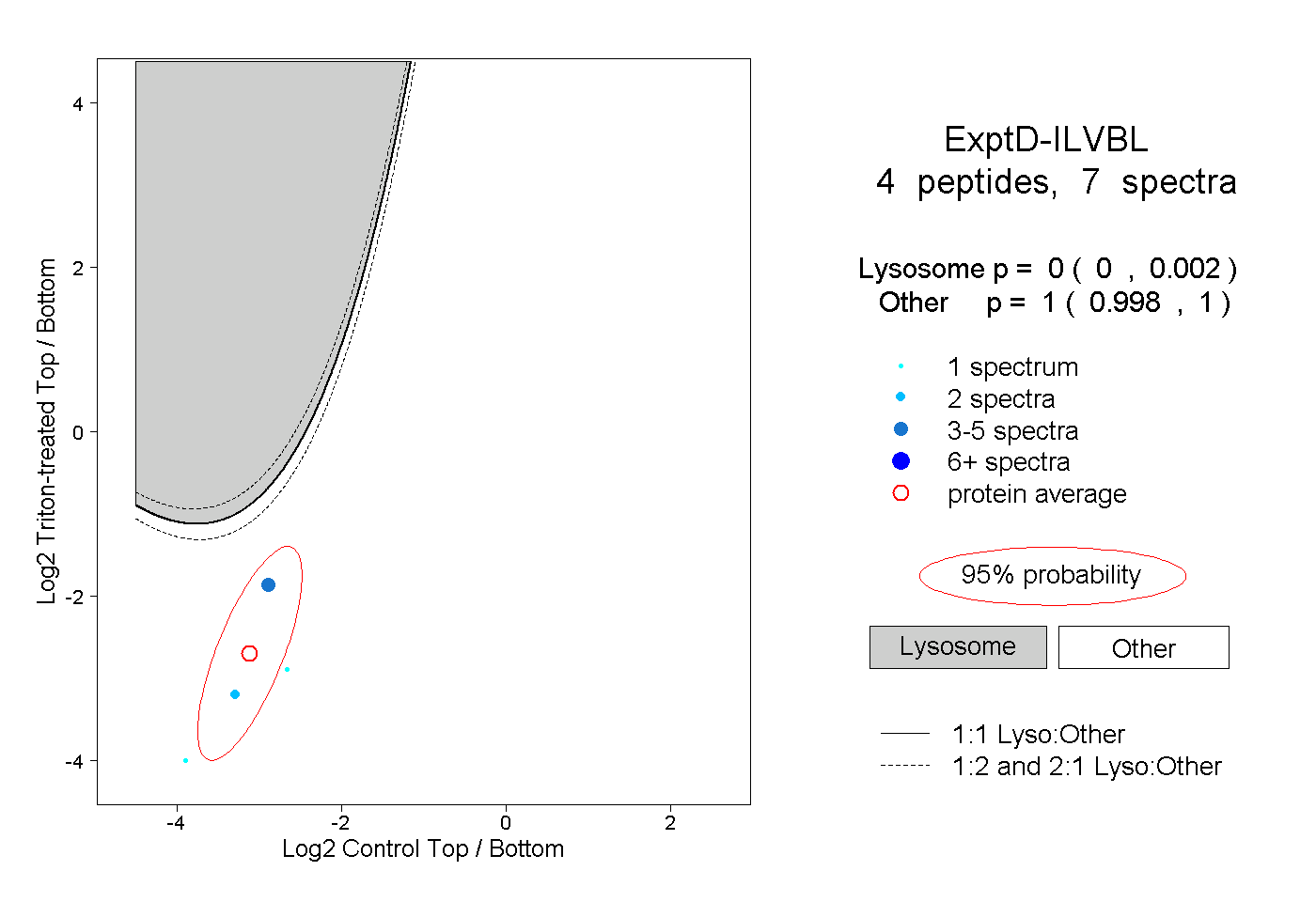 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |