peptides
spectra
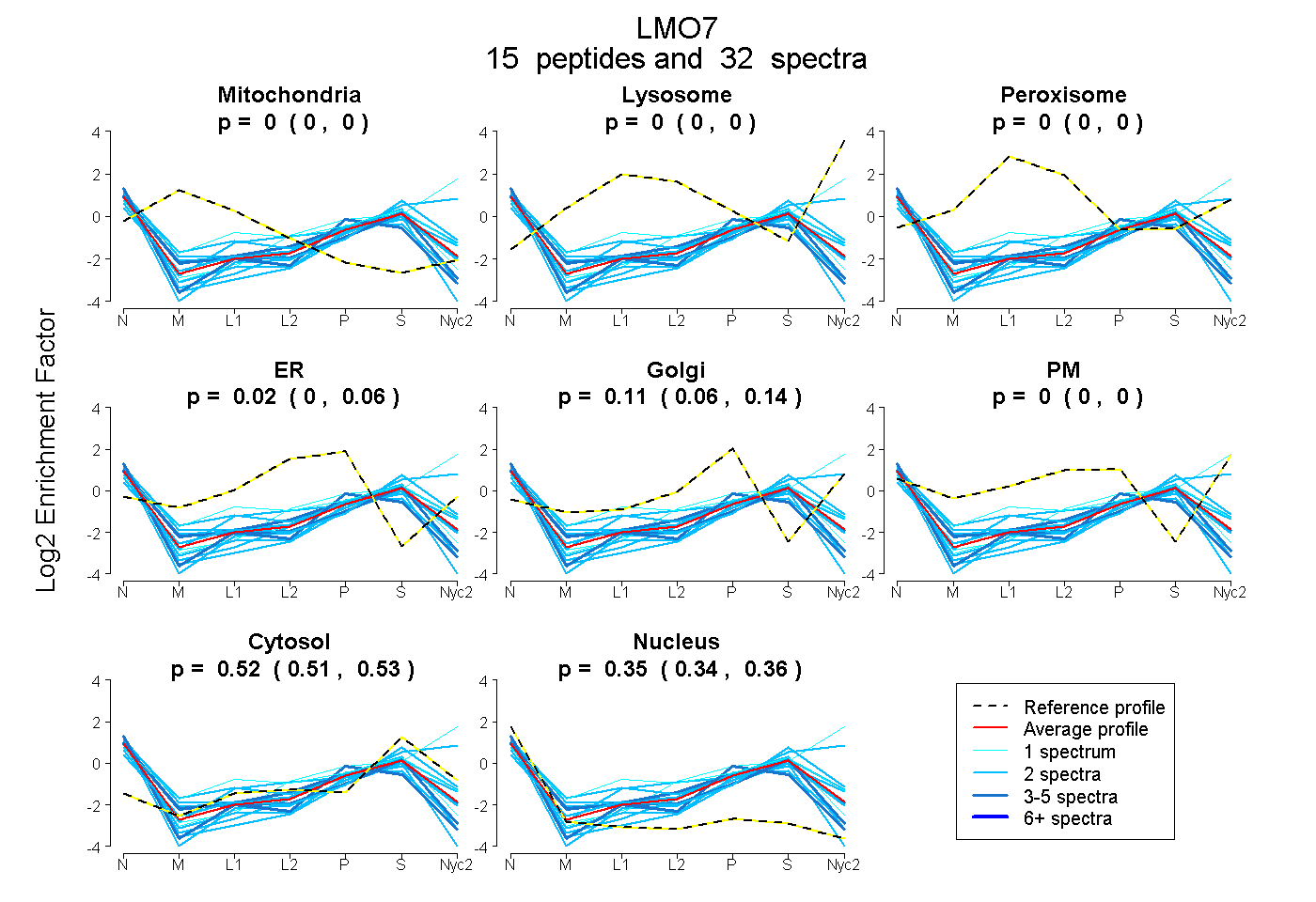
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.055
0.061 | 0.135
0.000 | 0.003
0.515 | 0.527
0.339 | 0.358
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
32 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.024 0.000 | 0.055 |
0.106 0.061 | 0.135 |
0.000 0.000 | 0.003 |
0.521 0.515 | 0.527 |
0.349 0.339 | 0.358 |
| 2 spectra, STTELNDPLIEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | 0.540 | 0.417 | ||
| 3 spectra, GISSLPR | 0.000 | 0.000 | 0.000 | 0.159 | 0.011 | 0.006 | 0.502 | 0.322 | ||
| 2 spectra, WQDDLAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.053 | 0.711 | 0.235 | ||
| 2 spectra, IGTTSFSQR | 0.000 | 0.000 | 0.081 | 0.000 | 0.000 | 0.189 | 0.405 | 0.325 | ||
| 2 spectra, SALPFNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.096 | 0.000 | 0.480 | 0.424 | ||
| 2 spectra, DLGGSSSGAEVR | 0.000 | 0.000 | 0.000 | 0.196 | 0.000 | 0.000 | 0.351 | 0.454 | ||
| 1 spectrum, YEEMQK | 0.000 | 0.000 | 0.145 | 0.078 | 0.000 | 0.083 | 0.471 | 0.222 | ||
| 3 spectra, TSPGSPSPR | 0.000 | 0.000 | 0.000 | 0.101 | 0.000 | 0.000 | 0.353 | 0.546 | ||
| 2 spectra, AEAQAQAEAEAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.380 | 0.620 | ||
| 1 spectrum, EDSTTFASR | 0.000 | 0.000 | 0.000 | 0.000 | 0.060 | 0.351 | 0.526 | 0.064 | ||
| 2 spectra, DQGPSEAELER | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 | 0.000 | 0.583 | 0.358 | ||
| 2 spectra, ISASLPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.307 | 0.651 | 0.042 | ||
| 5 spectra, WAWDQEEER | 0.000 | 0.000 | 0.000 | 0.059 | 0.000 | 0.000 | 0.496 | 0.445 | ||
| 1 spectrum, AEAEAQAR | 0.000 | 0.000 | 0.000 | 0.057 | 0.000 | 0.000 | 0.552 | 0.391 | ||
| 2 spectra, RPIDSYDLPK | 0.000 | 0.000 | 0.000 | 0.108 | 0.000 | 0.000 | 0.500 | 0.391 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
6 spectra |
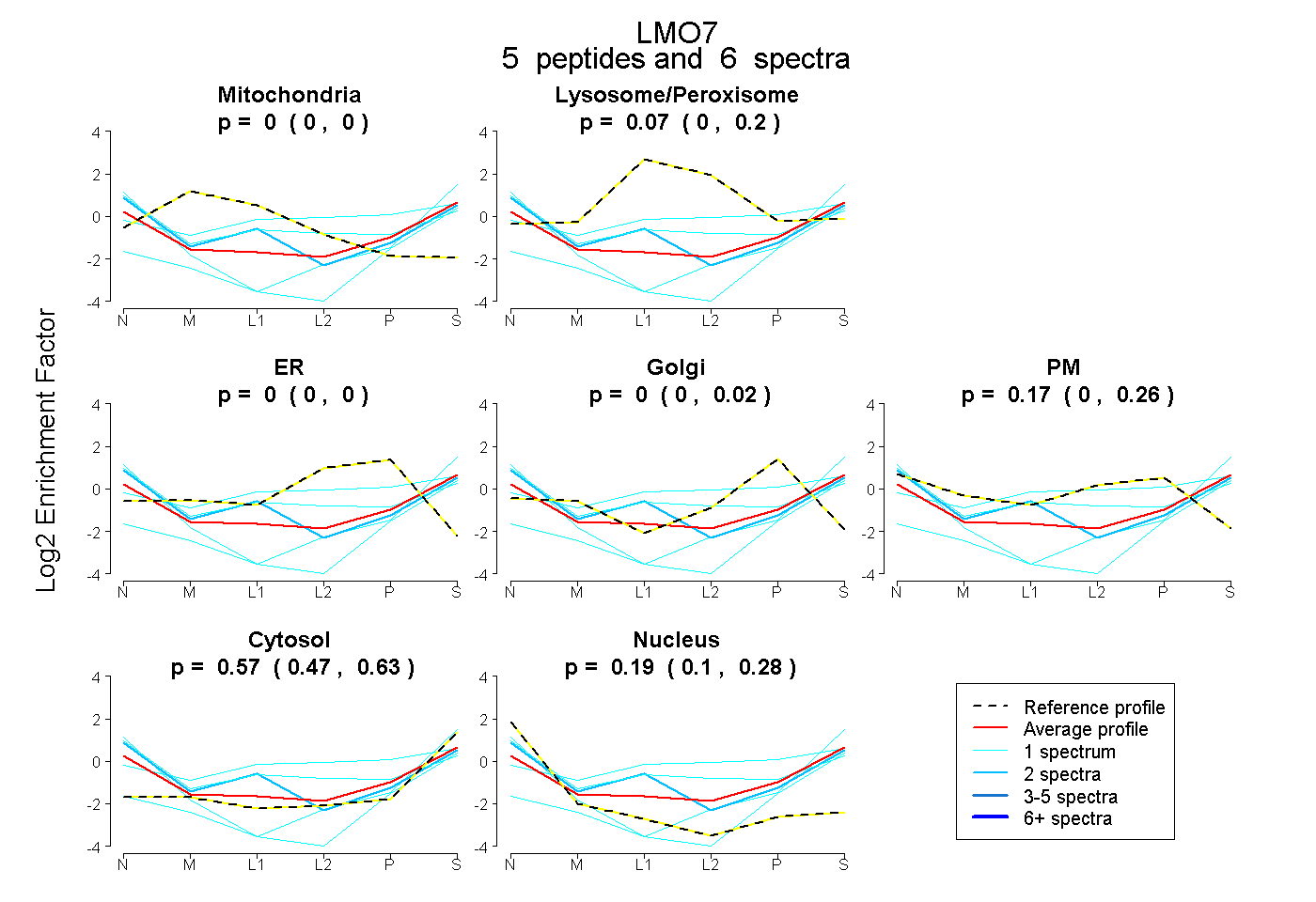 |
0.000 0.000 | 0.000 |
0.068 0.000 | 0.196 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.024 |
0.174 0.000 | 0.261 |
0.566 0.475 | 0.632 |
0.193 0.104 | 0.285 |