peptides
spectra
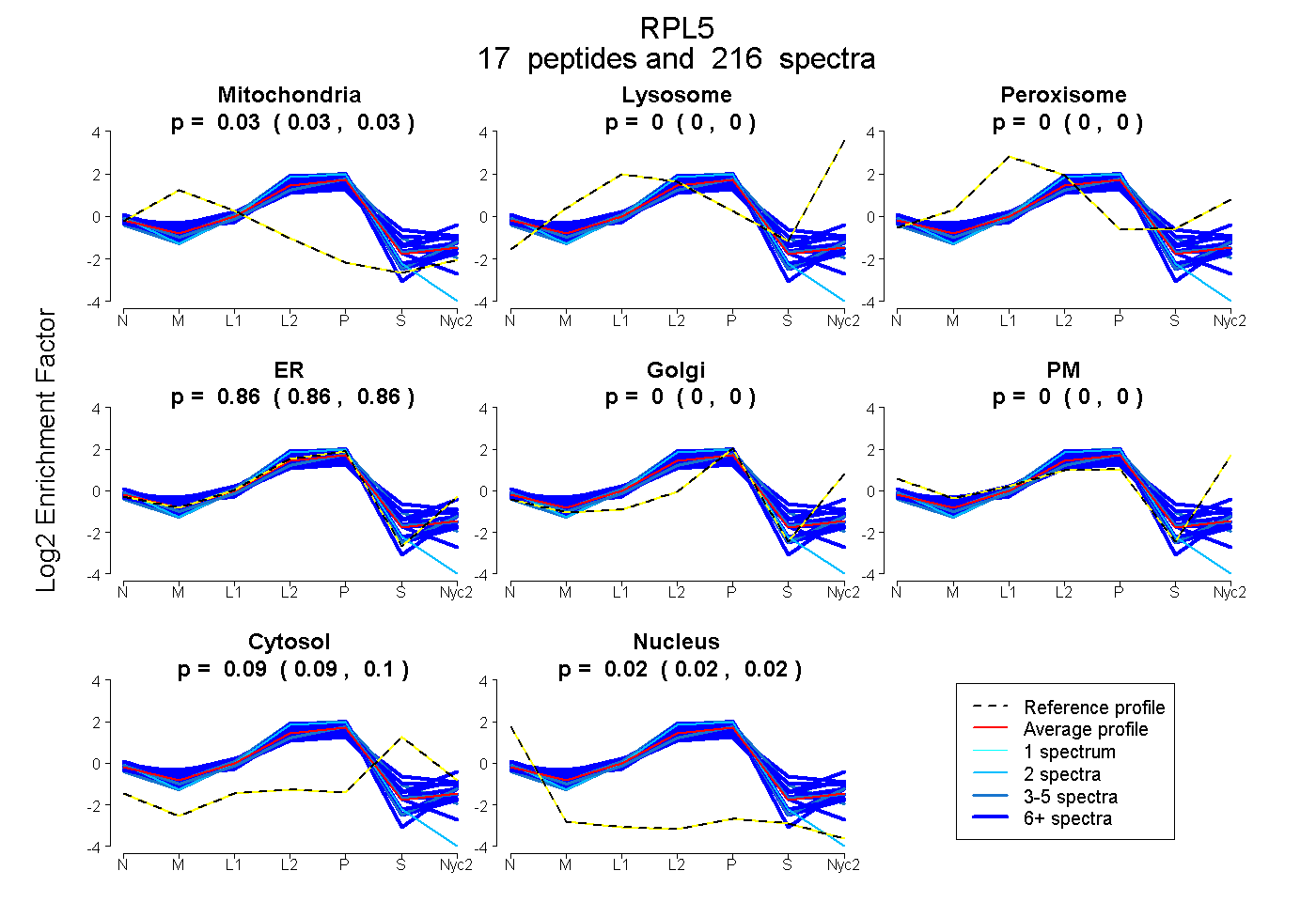
0.026 | 0.029
0.000 | 0.000
0.000 | 0.000
0.856 | 0.860
0.000 | 0.000
0.000 | 0.000
0.091 | 0.098
0.017 | 0.021
peptides
spectra
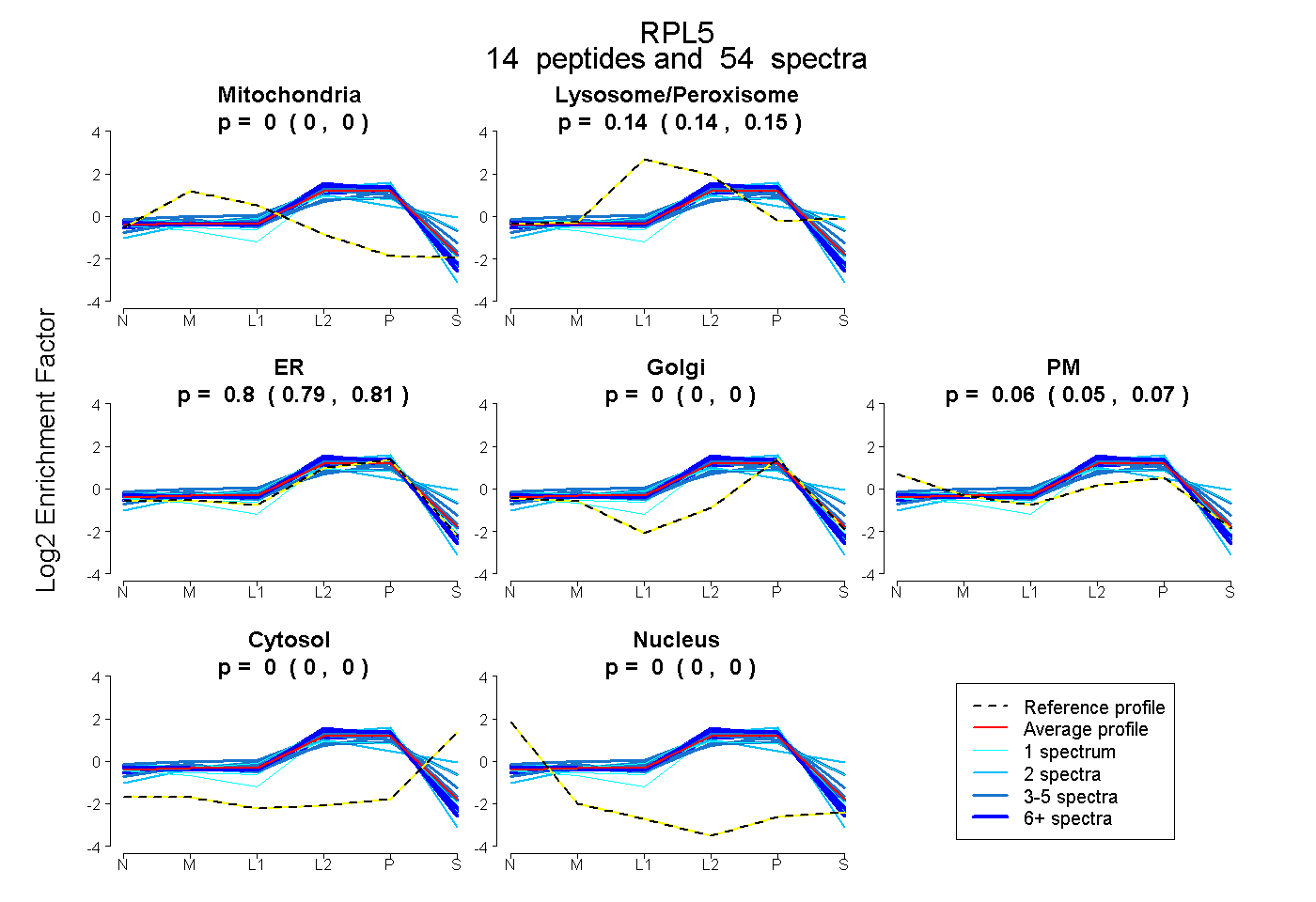
0.000 | 0.000
0.137 | 0.150
0.786 | 0.811
0.000 | 0.000
0.045 | 0.066
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
216 spectra |
 |
0.028 0.026 | 0.029 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.858 0.856 | 0.860 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.095 0.091 | 0.098 |
0.019 0.017 | 0.021 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
54 spectra |
 |
0.000 0.000 | 0.000 |
0.144 0.137 | 0.150 |
0.800 0.786 | 0.811 |
0.000 0.000 | 0.000 |
0.057 0.045 | 0.066 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 10 spectra, VFGALK | 0.000 | 0.064 | 0.936 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, TDYYAR | 0.000 | 0.213 | 0.787 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, QFSQYIK | 0.001 | 0.220 | 0.605 | 0.000 | 0.173 | 0.000 | 0.000 | |||
| 4 spectra, IEGDMIVCAAYAHELPK | 0.000 | 0.289 | 0.397 | 0.313 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FPGYDSESK | 0.000 | 0.000 | 0.950 | 0.042 | 0.000 | 0.008 | 0.000 | |||
| 1 spectrum, ENPVYEK | 0.000 | 0.010 | 0.990 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LVIQDK | 0.000 | 0.088 | 0.912 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, DIICQIAYAR | 0.000 | 0.091 | 0.909 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, HIMGQNVADYMR | 0.000 | 0.328 | 0.278 | 0.312 | 0.010 | 0.072 | 0.000 | |||
| 1 spectrum, TTTGNK | 0.000 | 0.165 | 0.835 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AHAAIR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, EFNAEVHR | 0.000 | 0.129 | 0.835 | 0.035 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, MSLAQK | 0.000 | 0.438 | 0.085 | 0.348 | 0.115 | 0.014 | 0.000 | |||
| 2 spectra, GAVDGGLSIPHSTK | 0.000 | 0.381 | 0.201 | 0.048 | 0.212 | 0.158 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
339 spectra |
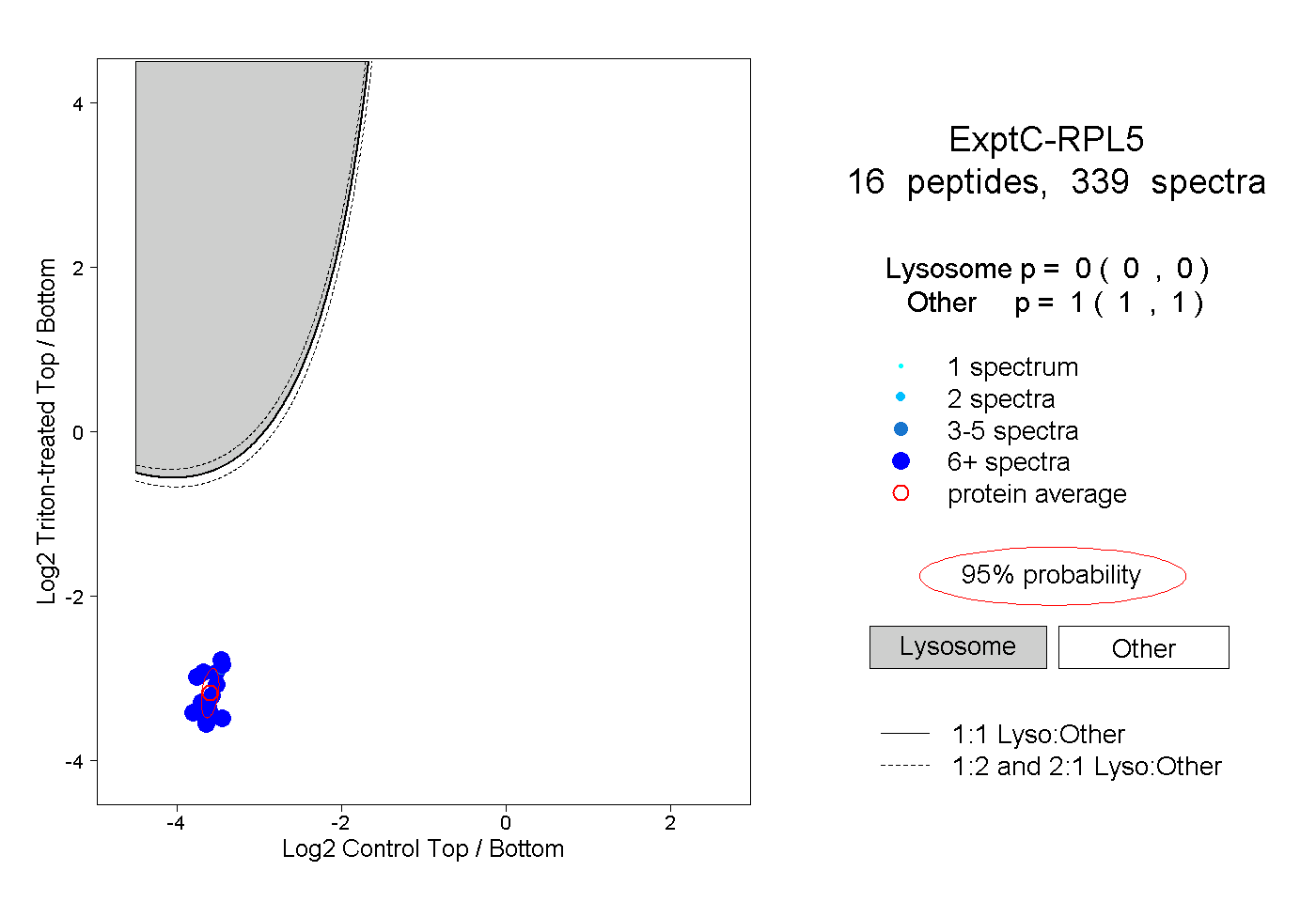 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
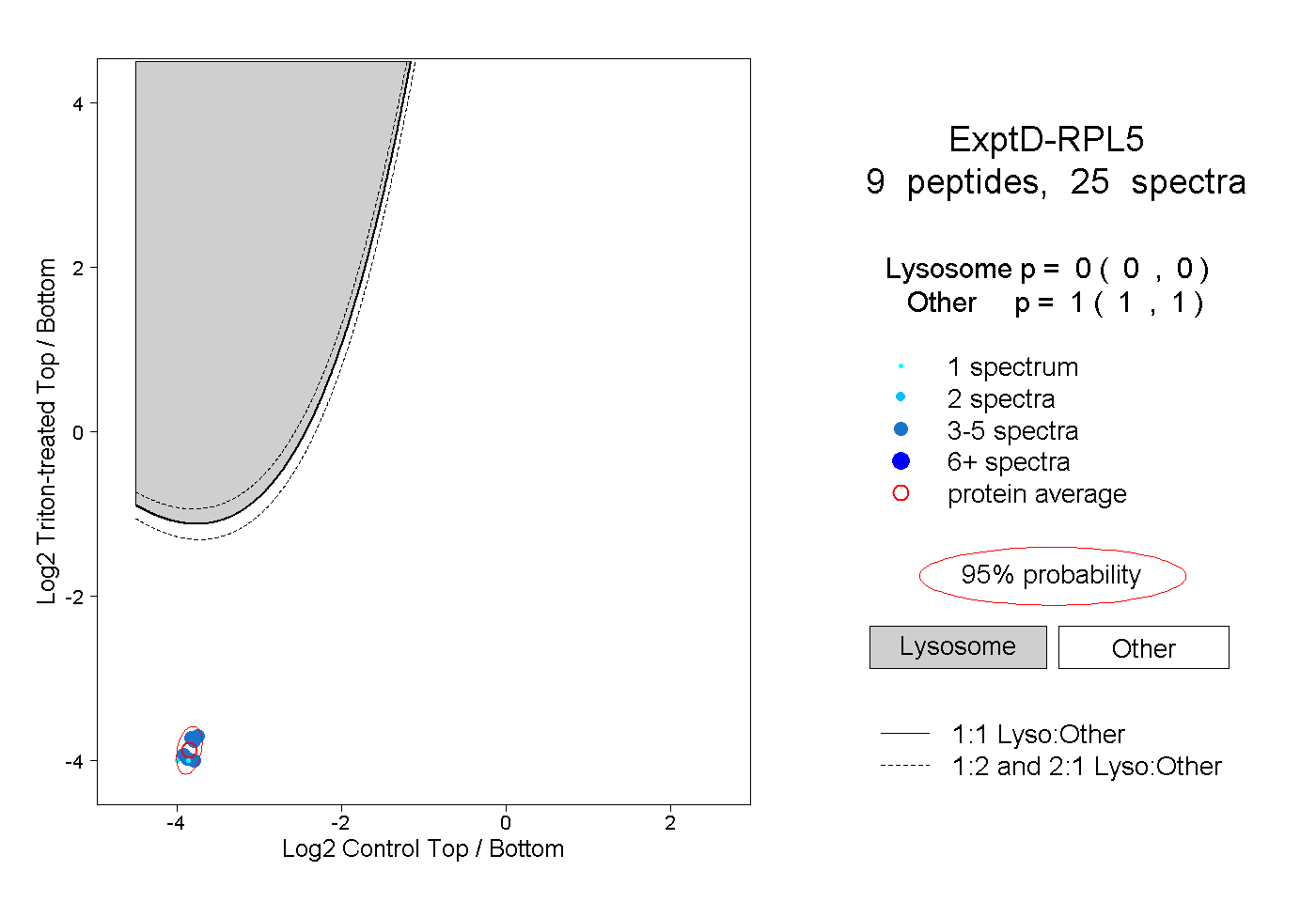 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |