peptides
spectra
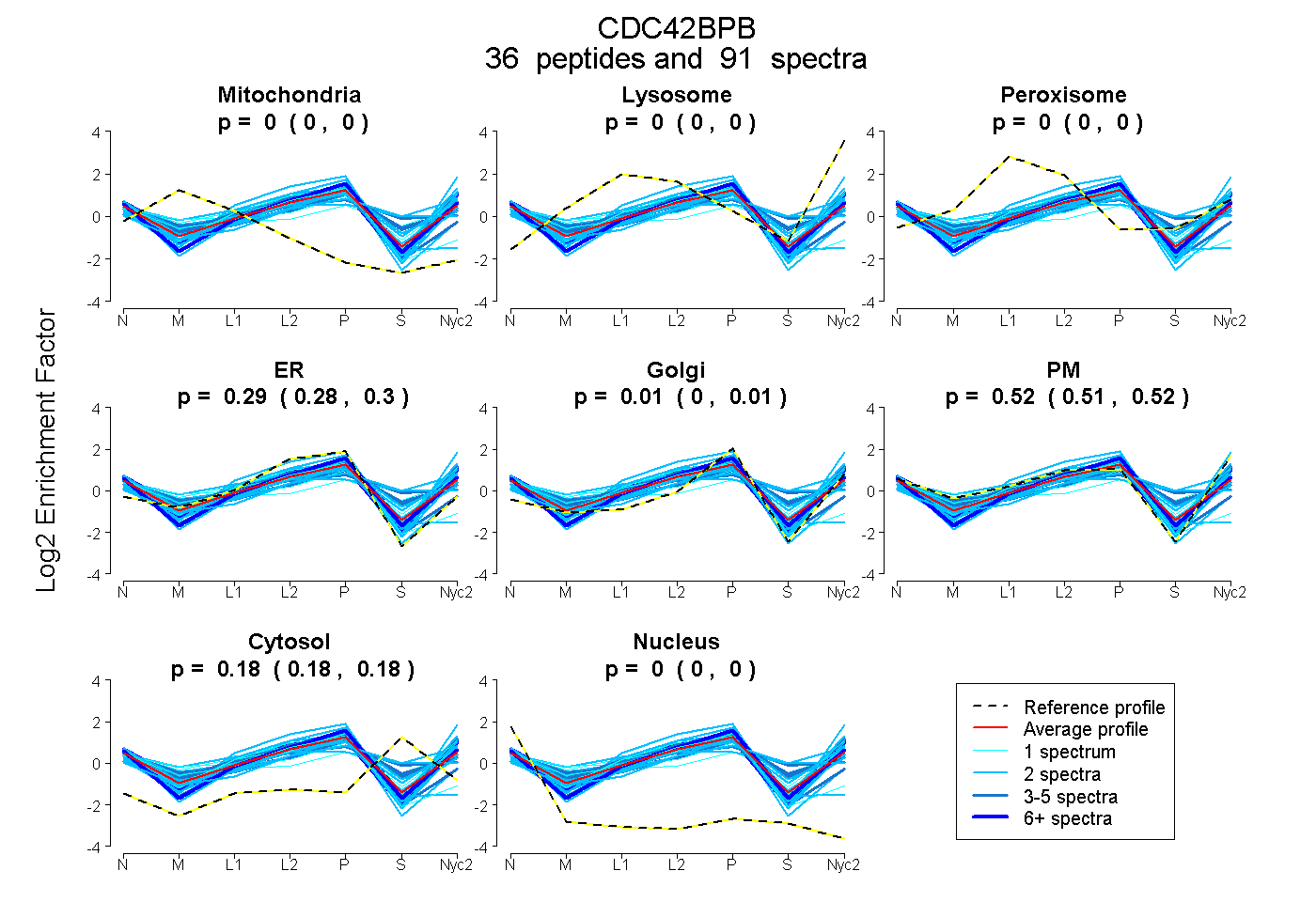
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.285 | 0.300
0.000 | 0.011
0.512 | 0.525
0.179 | 0.185
0.000 | 0.000
peptides
spectra
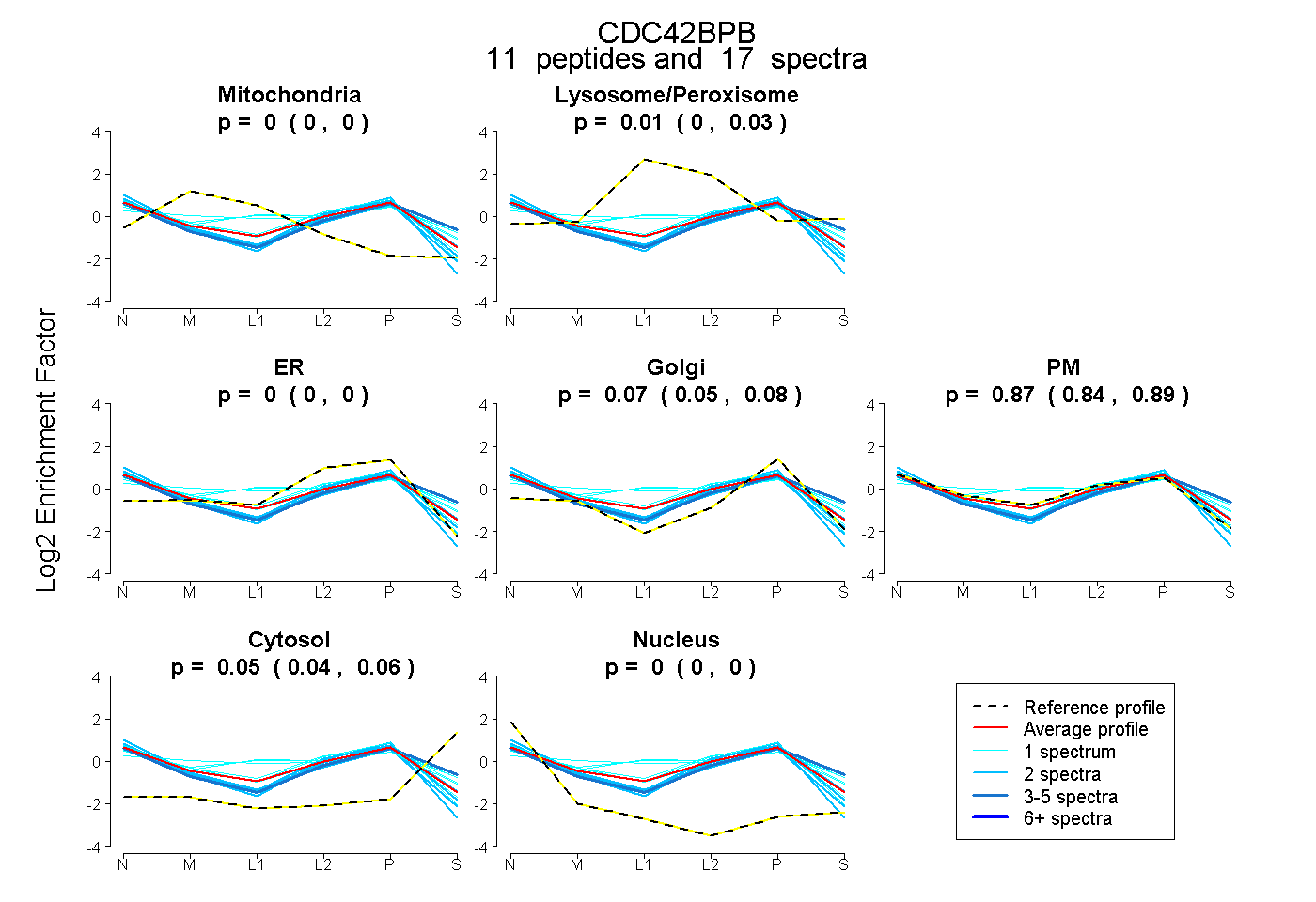
0.000 | 0.000
0.000 | 0.028
0.000 | 0.000
0.050 | 0.083
0.843 | 0.890
0.038 | 0.060
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
91 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.294 0.285 | 0.300 |
0.005 0.000 | 0.011 |
0.519 0.512 | 0.525 |
0.182 0.179 | 0.185 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.013 0.000 | 0.028 |
0.000 0.000 | 0.000 |
0.068 0.050 | 0.083 |
0.869 0.843 | 0.890 |
0.050 0.038 | 0.060 |
0.000 0.000 | 0.000 |
| 1 spectrum, EDFEILK | 0.000 | 0.101 | 0.000 | 0.081 | 0.742 | 0.077 | 0.000 | |||
| 2 spectra, ALQEFSELNER | 0.000 | 0.000 | 0.245 | 0.170 | 0.484 | 0.000 | 0.101 | |||
| 2 spectra, QLVEASER | 0.000 | 0.000 | 0.000 | 0.207 | 0.738 | 0.051 | 0.003 | |||
| 1 spectrum, HAFFEGLNWENIR | 0.049 | 0.249 | 0.000 | 0.152 | 0.465 | 0.084 | 0.000 | |||
| 2 spectra, DIPCIFR | 0.000 | 0.000 | 0.000 | 0.137 | 0.768 | 0.000 | 0.095 | |||
| 3 spectra, TVLAAAIVDGDR | 0.000 | 0.000 | 0.000 | 0.090 | 0.713 | 0.198 | 0.000 | |||
| 1 spectrum, RPLGVDVQR | 0.000 | 0.249 | 0.000 | 0.001 | 0.671 | 0.027 | 0.053 | |||
| 1 spectrum, VLFYEEELVR | 0.000 | 0.000 | 0.111 | 0.082 | 0.807 | 0.000 | 0.000 | |||
| 2 spectra, LFLYDLPEGK | 0.000 | 0.000 | 0.000 | 0.179 | 0.798 | 0.000 | 0.023 | |||
| 1 spectrum, DIKPDNVLLDVNGHIR | 0.000 | 0.256 | 0.000 | 0.065 | 0.591 | 0.088 | 0.000 | |||
| 1 spectrum, EASHVLEVK | 0.000 | 0.000 | 0.000 | 0.141 | 0.846 | 0.013 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
124 spectra |
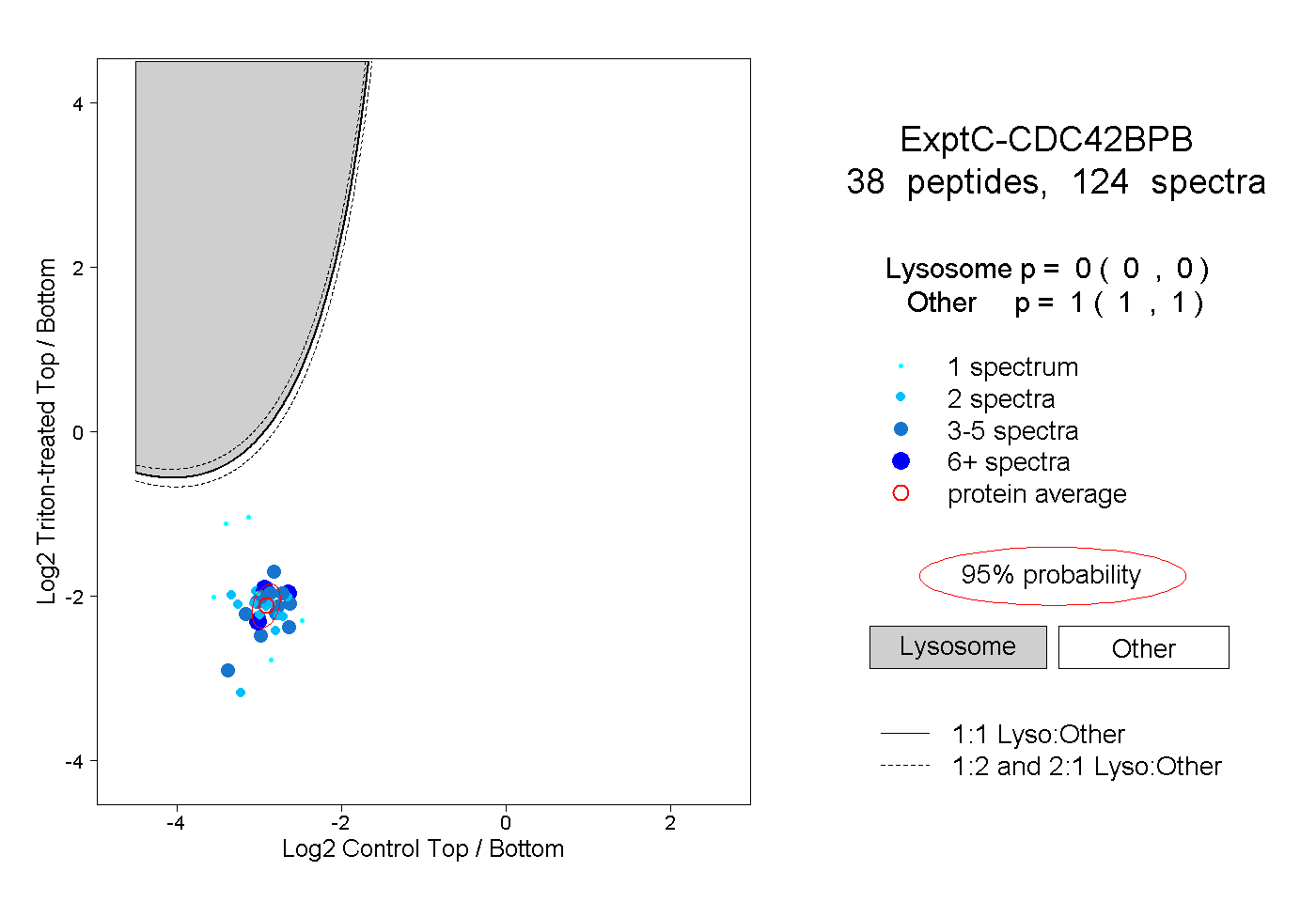 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
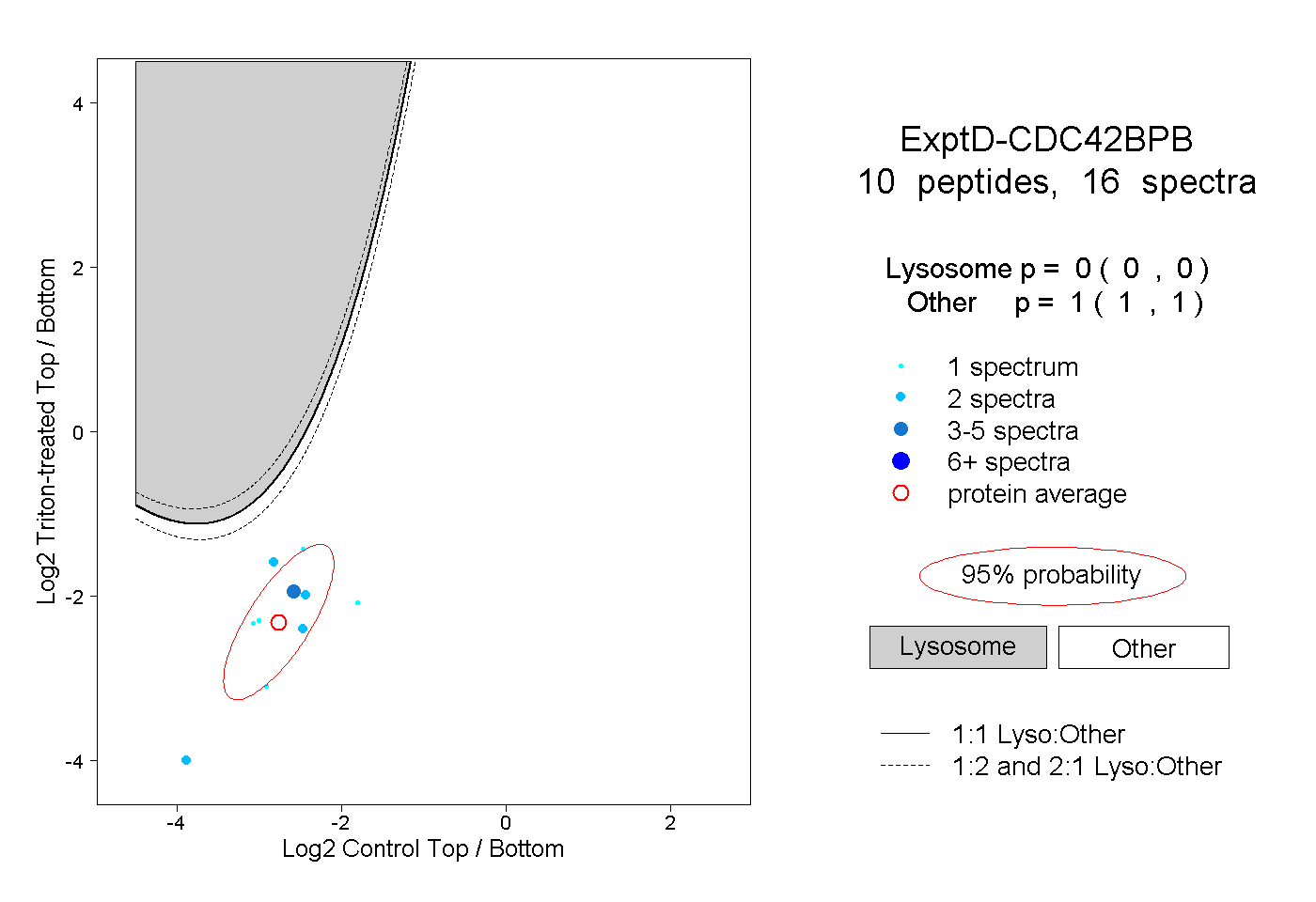 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |