peptides
spectra
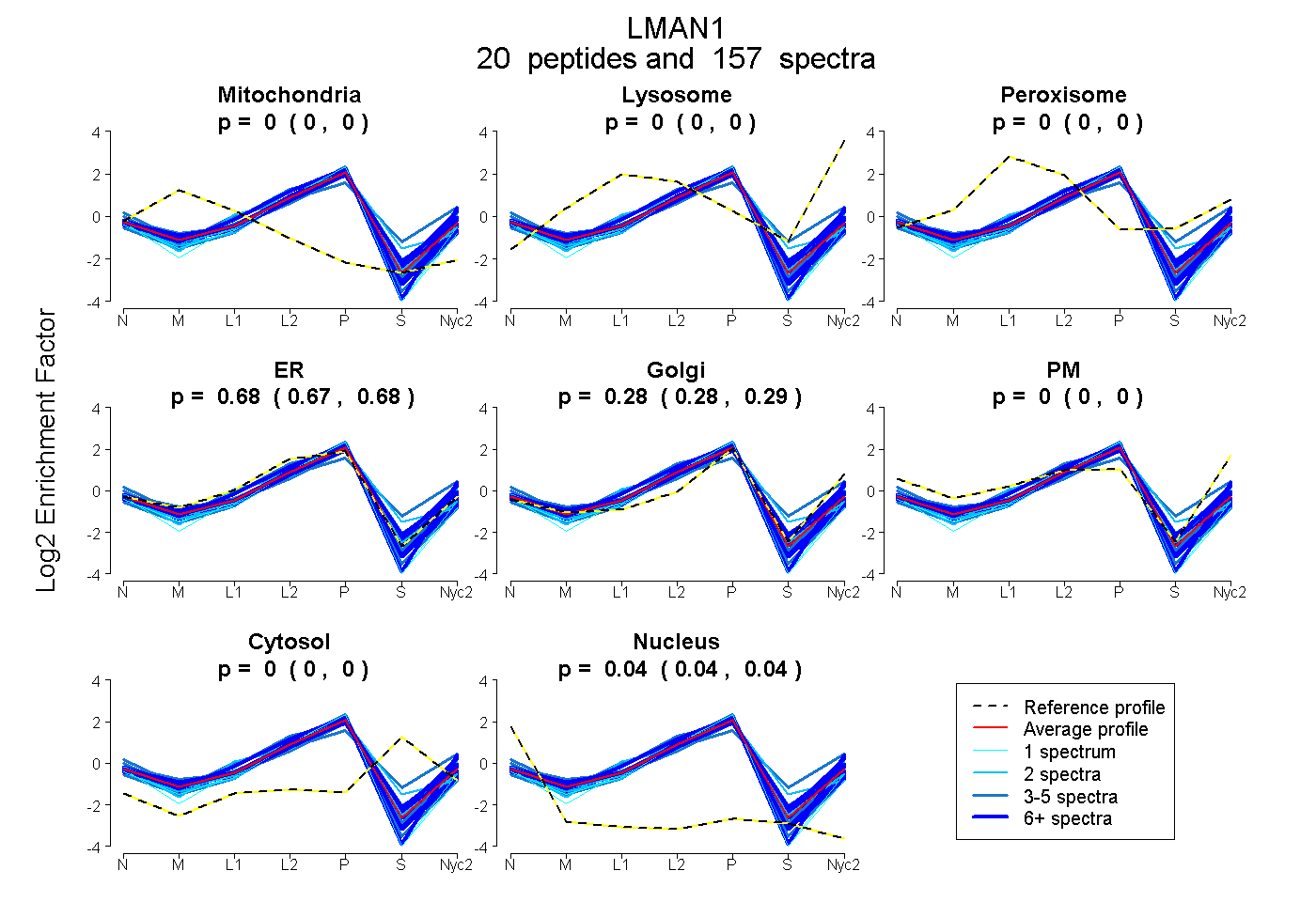
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.673 | 0.680
0.278 | 0.287
0.000 | 0.000
0.000 | 0.000
0.039 | 0.041
peptides
spectra
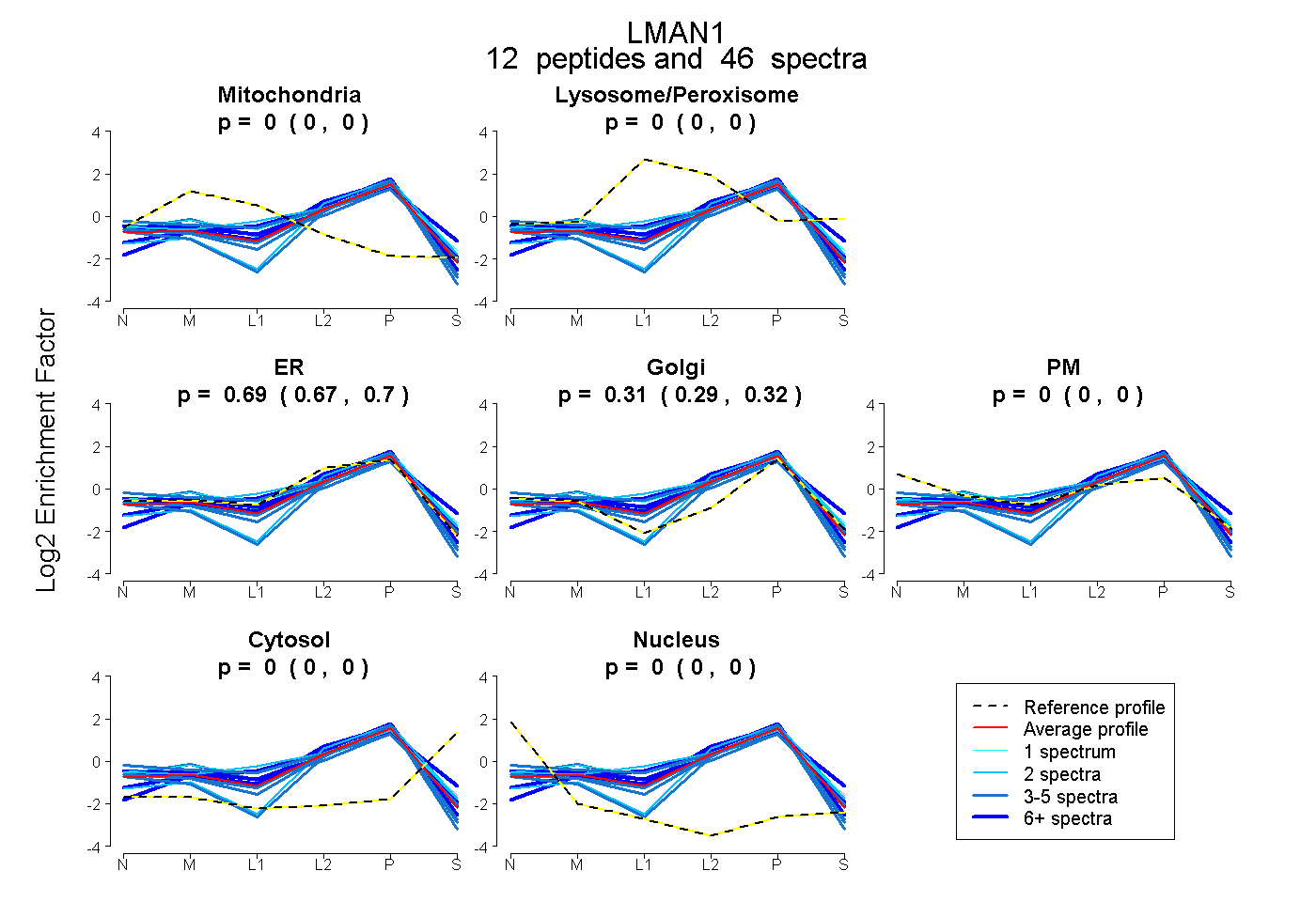
0.000 | 0.000
0.000 | 0.000
0.673 | 0.704
0.294 | 0.324
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
157 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.677 0.673 | 0.680 |
0.283 0.278 | 0.287 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.040 0.039 | 0.041 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
46 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.690 0.673 | 0.704 |
0.310 0.294 | 0.324 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 4 spectra, QVFEGQNR | 0.000 | 0.000 | 0.601 | 0.399 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, YVSSLTEEISR | 0.000 | 0.000 | 0.311 | 0.689 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, TQQEILR | 0.000 | 0.000 | 0.664 | 0.336 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QLDMILDEQR | 0.000 | 0.000 | 0.446 | 0.525 | 0.000 | 0.029 | 0.000 | |||
| 6 spectra, EHLHIVK | 0.000 | 0.000 | 0.830 | 0.134 | 0.000 | 0.036 | 0.000 | |||
| 6 spectra, IHLELK | 0.000 | 0.000 | 0.800 | 0.200 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QVNEMK | 0.008 | 0.200 | 0.329 | 0.462 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DIDSLAQR | 0.098 | 0.000 | 0.565 | 0.337 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, GHPDLQGQPADDIFESIGDR | 0.000 | 0.283 | 0.215 | 0.503 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, ITYYQK | 0.000 | 0.053 | 0.599 | 0.316 | 0.032 | 0.000 | 0.000 | |||
| 2 spectra, NKPYPVR | 0.000 | 0.192 | 0.502 | 0.305 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, TQQEAAAK | 0.000 | 0.082 | 0.505 | 0.194 | 0.219 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
281 spectra |
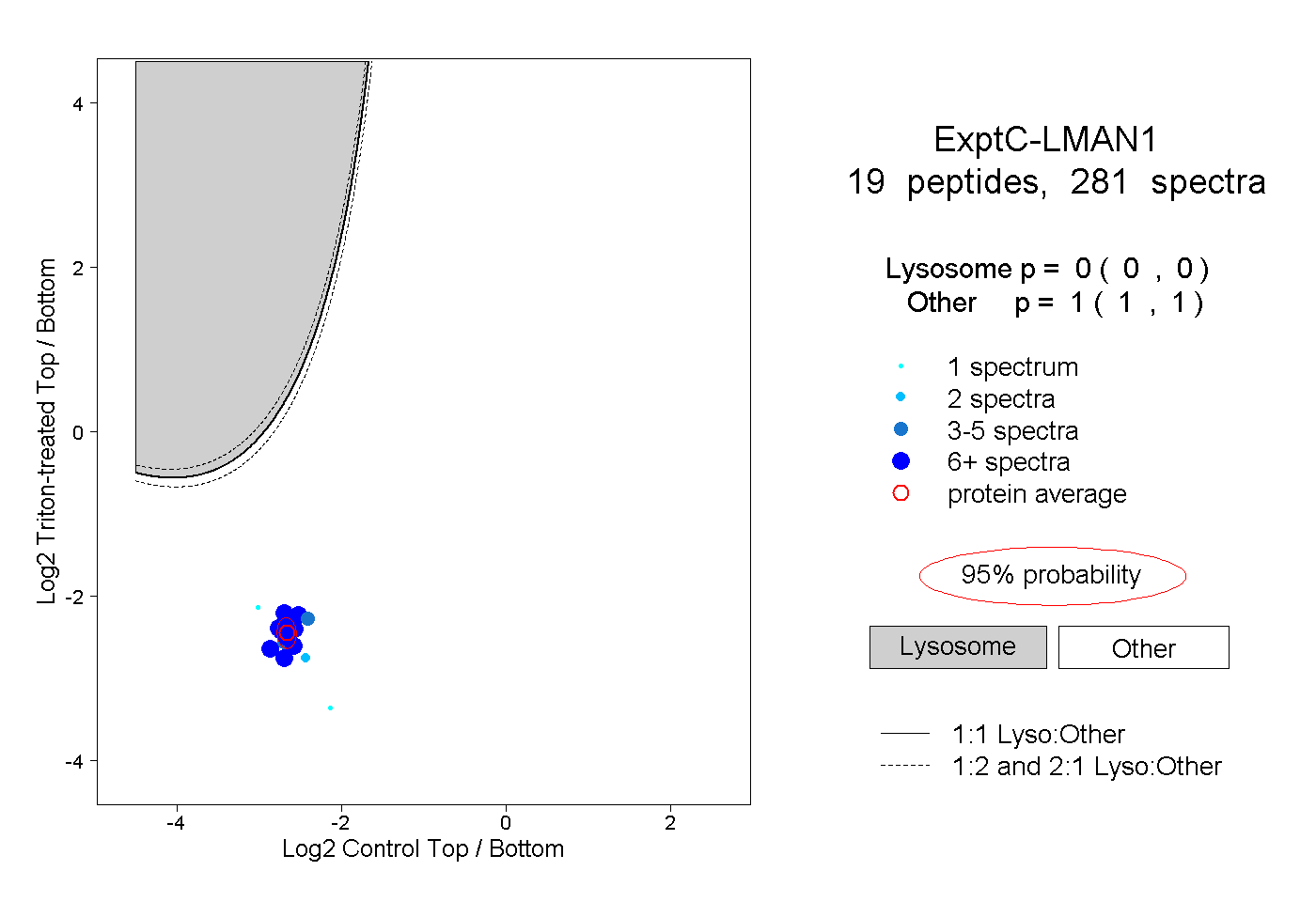 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
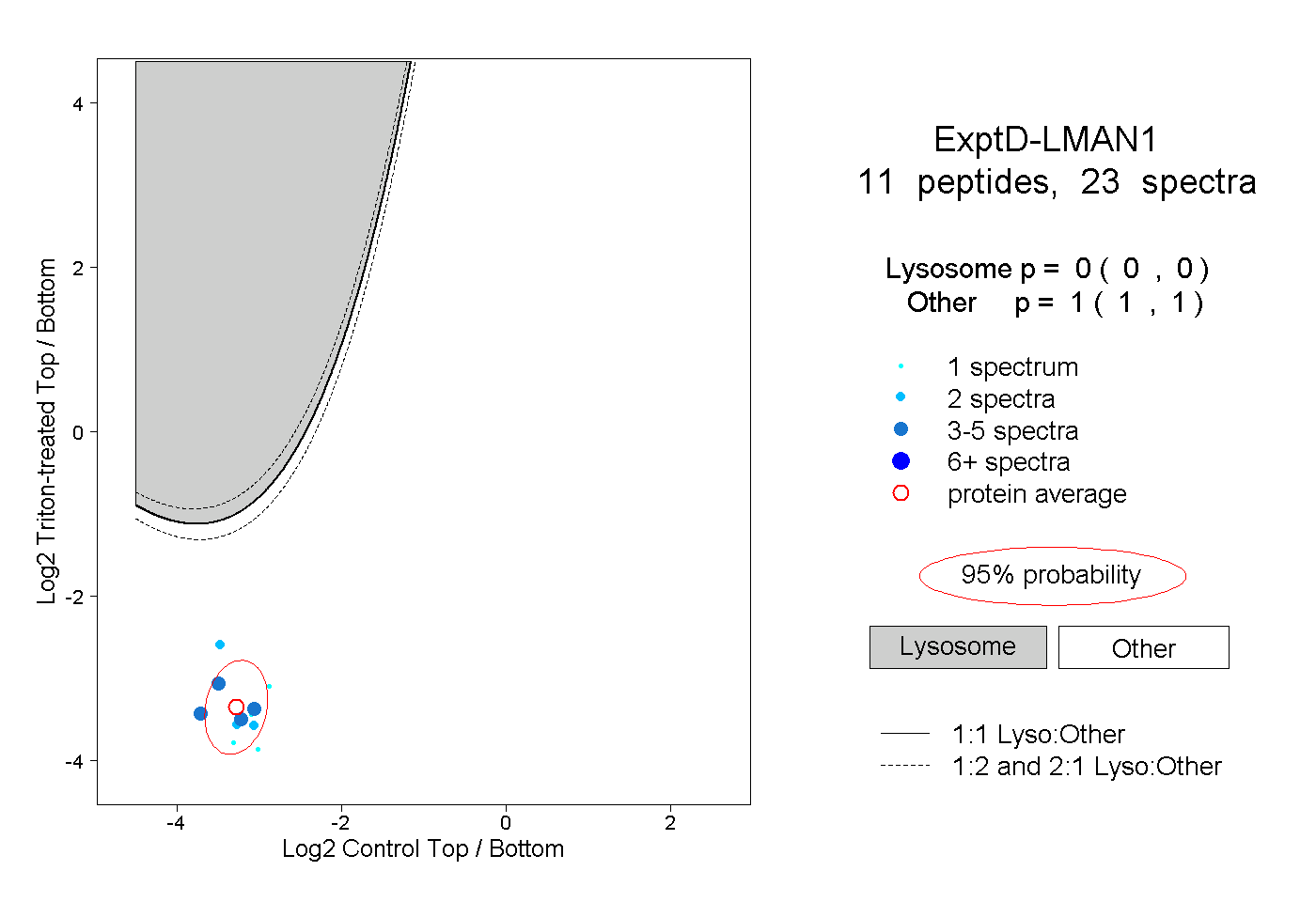 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |