peptides
spectra
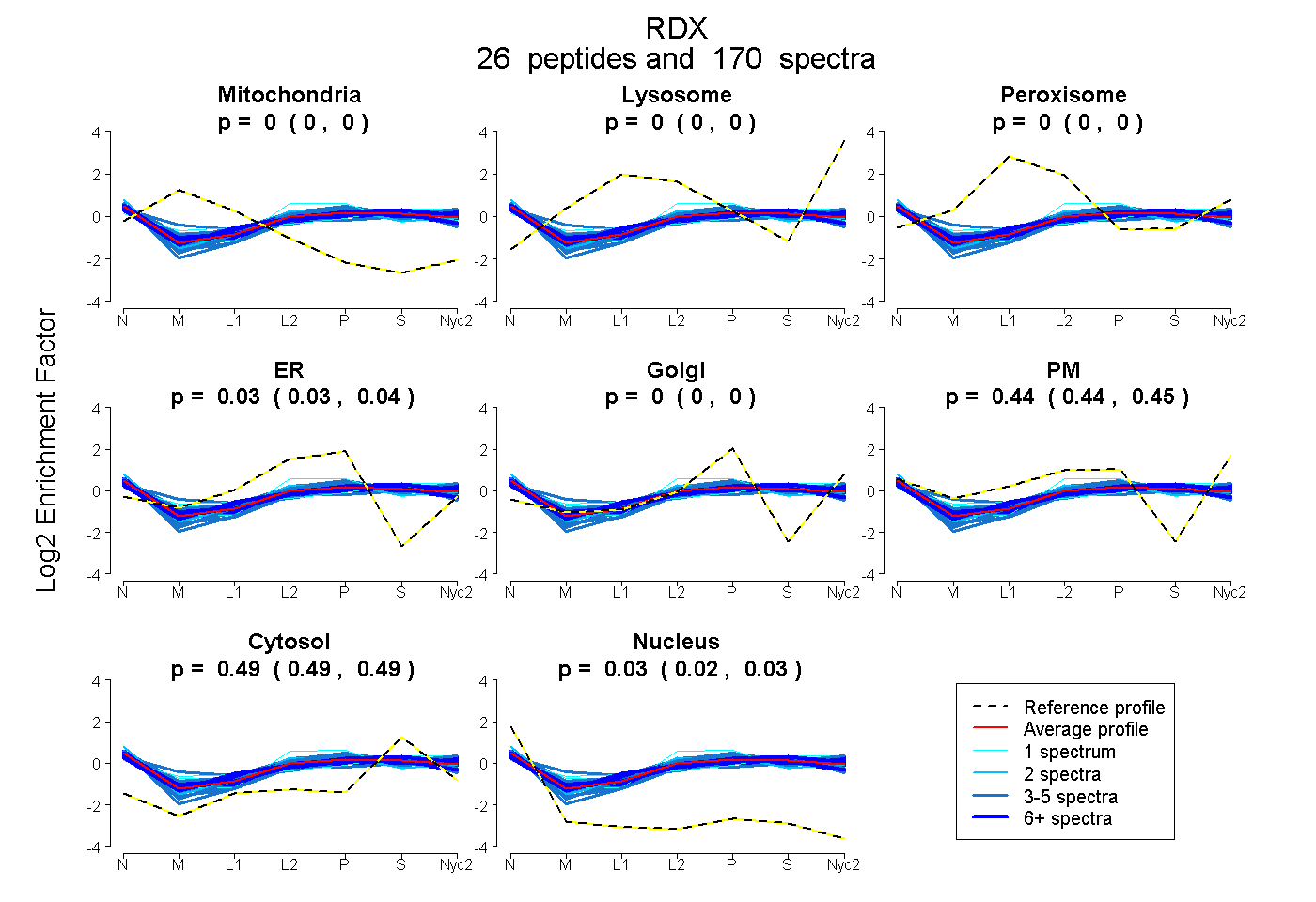
0.000 | 0.000
0.000 | 0.000
0.001 | 0.004
0.032 | 0.037
0.000 | 0.000
0.440 | 0.445
0.493 | 0.495
0.024 | 0.026
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
170 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.003 0.001 | 0.004 |
0.035 0.032 | 0.037 |
0.000 0.000 | 0.000 |
0.443 0.440 | 0.445 |
0.494 0.493 | 0.495 |
0.025 0.024 | 0.026 |
| 4 spectra, AAEEAK | 0.000 | 0.000 | 0.000 | 0.088 | 0.000 | 0.446 | 0.466 | 0.000 | ||
| 4 spectra, VTETQK | 0.000 | 0.000 | 0.000 | 0.124 | 0.000 | 0.281 | 0.524 | 0.070 | ||
| 13 spectra, QIEEQTMK | 0.000 | 0.000 | 0.014 | 0.000 | 0.000 | 0.502 | 0.464 | 0.020 | ||
| 3 spectra, IAQDLEMYGVNYFEIK | 0.000 | 0.000 | 0.000 | 0.120 | 0.000 | 0.276 | 0.543 | 0.061 | ||
| 8 spectra, EIHKPGYLANDR | 0.000 | 0.000 | 0.000 | 0.017 | 0.000 | 0.436 | 0.513 | 0.034 | ||
| 2 spectra, QLQALSSELAQAR | 0.000 | 0.000 | 0.000 | 0.066 | 0.000 | 0.462 | 0.408 | 0.064 | ||
| 9 spectra, ELEEQTR | 0.000 | 0.000 | 0.000 | 0.052 | 0.000 | 0.414 | 0.516 | 0.018 | ||
| 27 spectra, EDSMMEYLK | 0.000 | 0.000 | 0.019 | 0.000 | 0.000 | 0.492 | 0.489 | 0.000 | ||
| 6 spectra, EVWFFGLQYVDSK | 0.000 | 0.000 | 0.026 | 0.060 | 0.000 | 0.356 | 0.494 | 0.063 | ||
| 8 spectra, EQWEER | 0.000 | 0.000 | 0.000 | 0.028 | 0.000 | 0.476 | 0.485 | 0.011 | ||
| 3 spectra, EEEATEWQHK | 0.000 | 0.000 | 0.000 | 0.130 | 0.000 | 0.315 | 0.505 | 0.050 | ||
| 1 spectrum, FFPEDVSEELIQEITQR | 0.000 | 0.000 | 0.000 | 0.051 | 0.000 | 0.375 | 0.512 | 0.062 | ||
| 10 spectra, VTQQDVK | 0.000 | 0.000 | 0.049 | 0.025 | 0.000 | 0.405 | 0.521 | 0.000 | ||
| 3 spectra, ENPLQFK | 0.108 | 0.000 | 0.017 | 0.000 | 0.000 | 0.446 | 0.428 | 0.000 | ||
| 19 spectra, QAADQMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.488 | 0.492 | 0.020 | ||
| 1 spectrum, EELMER | 0.007 | 0.000 | 0.052 | 0.008 | 0.000 | 0.464 | 0.468 | 0.001 | ||
| 4 spectra, IQNWHEEHR | 0.000 | 0.000 | 0.000 | 0.020 | 0.000 | 0.513 | 0.467 | 0.000 | ||
| 16 spectra, AFAAQEDLEK | 0.000 | 0.000 | 0.069 | 0.078 | 0.000 | 0.347 | 0.438 | 0.068 | ||
| 1 spectrum, IDEFEAM | 0.006 | 0.000 | 0.098 | 0.000 | 0.000 | 0.392 | 0.504 | 0.000 | ||
| 12 spectra, YGDYNK | 0.000 | 0.000 | 0.036 | 0.054 | 0.000 | 0.373 | 0.478 | 0.059 | ||
| 1 spectrum, GYSTWLK | 0.000 | 0.000 | 0.000 | 0.072 | 0.000 | 0.377 | 0.516 | 0.035 | ||
| 4 spectra, AQLENEK | 0.000 | 0.000 | 0.000 | 0.013 | 0.000 | 0.441 | 0.497 | 0.050 | ||
| 3 spectra, TQNDVLHAENVK | 0.000 | 0.000 | 0.000 | 0.151 | 0.000 | 0.318 | 0.506 | 0.025 | ||
| 5 spectra, IALLEEAK | 0.000 | 0.000 | 0.101 | 0.000 | 0.000 | 0.409 | 0.422 | 0.069 | ||
| 2 spectra, NQEQLAAELAEFTAK | 0.000 | 0.000 | 0.010 | 0.045 | 0.000 | 0.444 | 0.481 | 0.020 | ||
| 1 spectrum, PKPINVR | 0.000 | 0.000 | 0.000 | 0.185 | 0.000 | 0.408 | 0.388 | 0.019 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
38 spectra |
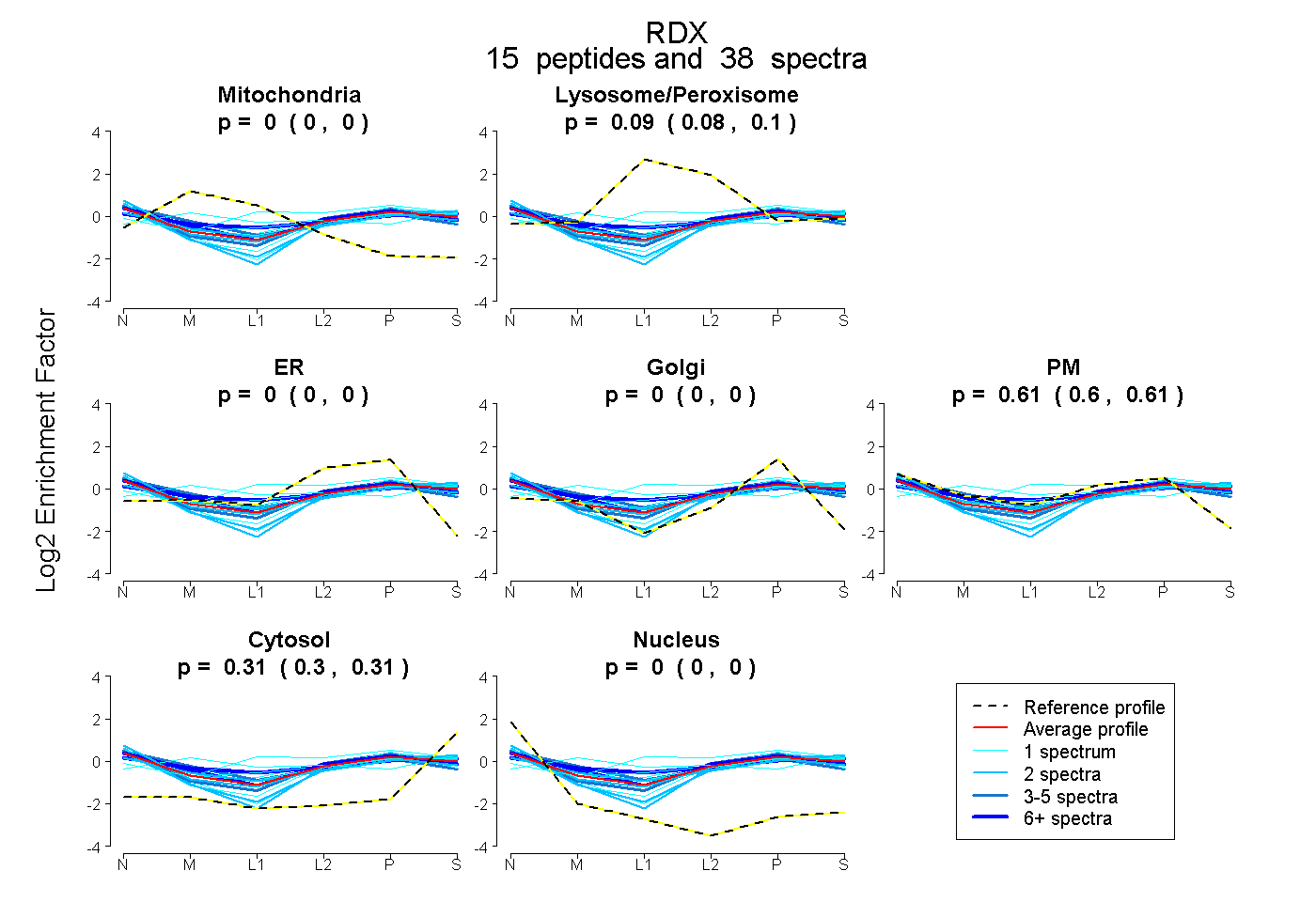 |
0.000 0.000 | 0.000 |
0.089 0.080 | 0.096 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.605 0.598 | 0.612 |
0.306 0.302 | 0.310 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
232 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
31 spectra |
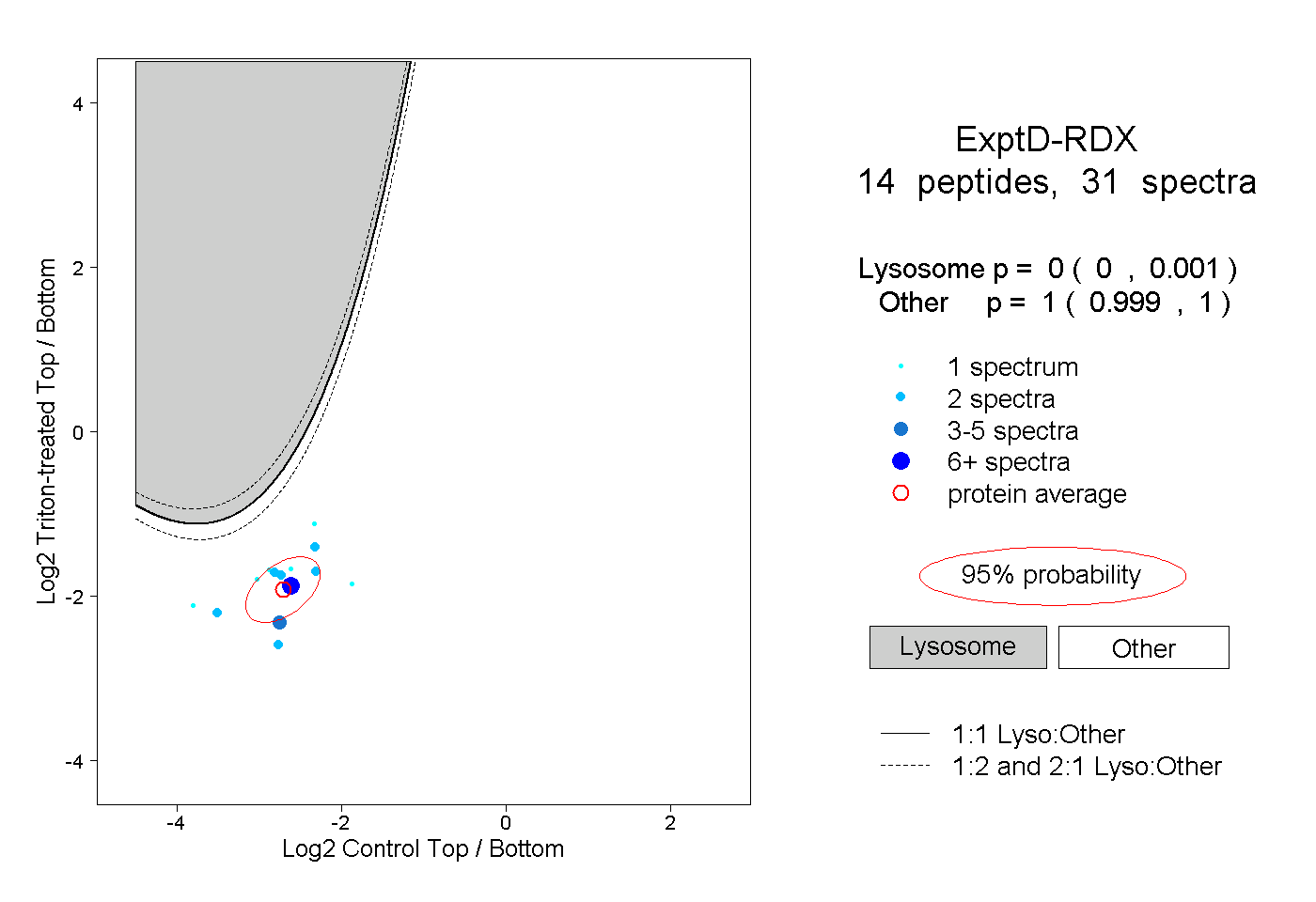 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |