peptides
spectra
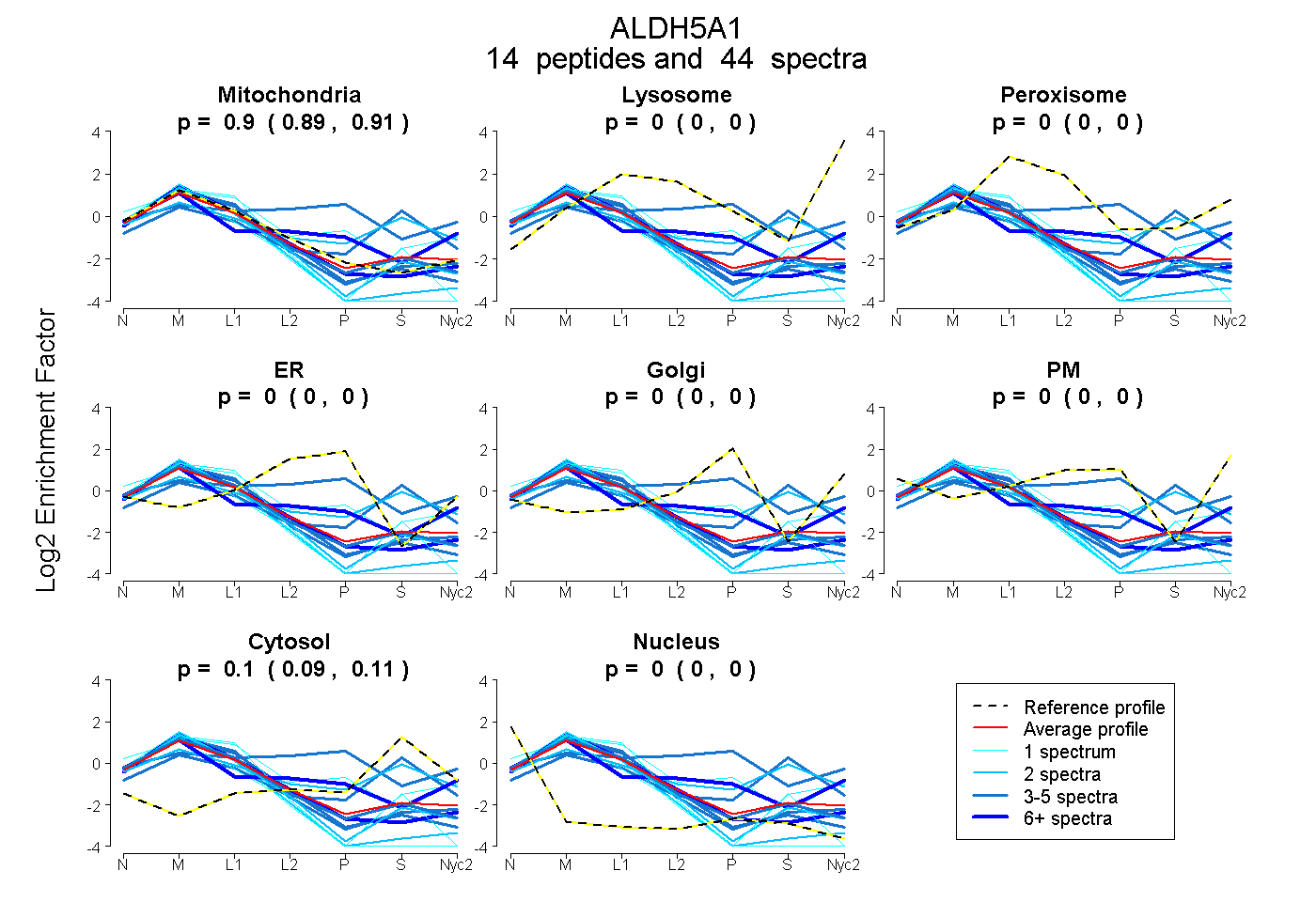
0.890 | 0.911
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.087 | 0.108
0.000 | 0.000
peptides
spectra
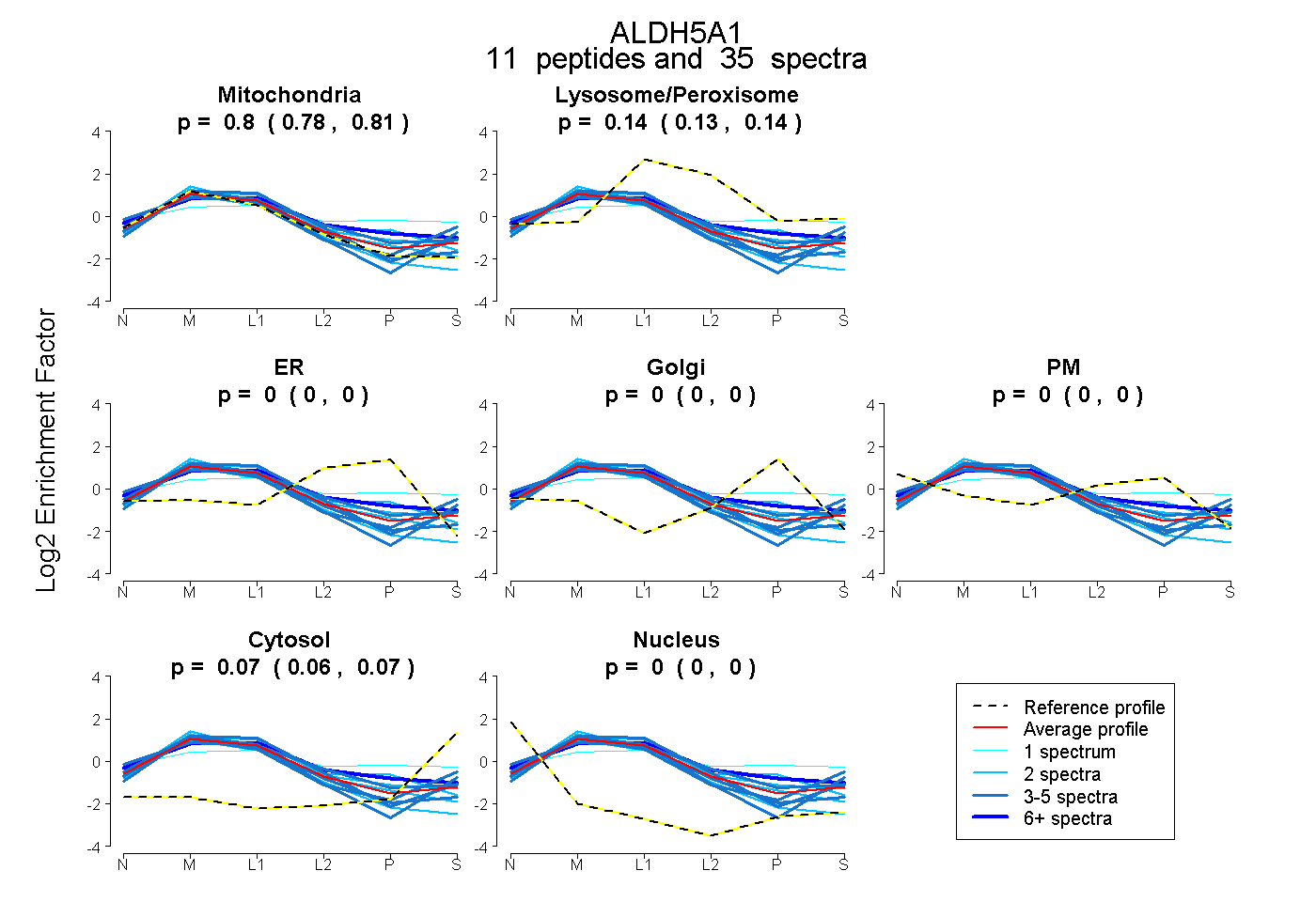
0.783 | 0.808
0.128 | 0.145
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.059 | 0.073
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
44 spectra |
 |
0.901 0.890 | 0.911 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.099 0.087 | 0.108 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.796 0.783 | 0.808 |
0.138 0.128 | 0.145 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.067 0.059 | 0.073 |
0.000 0.000 | 0.000 |
| 5 spectra, LGTVADCGVPEAR | 0.715 | 0.101 | 0.000 | 0.000 | 0.000 | 0.185 | 0.000 | |||
| 3 spectra, NAGQTCVCSNR | 0.663 | 0.202 | 0.000 | 0.000 | 0.085 | 0.050 | 0.000 | |||
| 2 spectra, AAYDAFSSWK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GIHDSFVTK | 0.767 | 0.185 | 0.000 | 0.029 | 0.000 | 0.019 | 0.000 | |||
| 3 spectra, VGNGFEEGTTQGPLINEK | 0.801 | 0.151 | 0.000 | 0.000 | 0.000 | 0.047 | 0.000 | |||
| 3 spectra, VYGDIIYTSAK | 0.846 | 0.031 | 0.000 | 0.000 | 0.000 | 0.123 | 0.000 | |||
| 8 spectra, ILLHHAANSVK | 0.582 | 0.280 | 0.000 | 0.111 | 0.000 | 0.027 | 0.000 | |||
| 2 spectra, HVNDAVAK | 0.656 | 0.147 | 0.000 | 0.197 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YGIDEYLEVK | 0.952 | 0.037 | 0.000 | 0.000 | 0.000 | 0.011 | 0.000 | |||
| 2 spectra, GATVVTGGK | 0.919 | 0.007 | 0.073 | 0.001 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, HQSGGNFFEPTLLSNVTR | 0.269 | 0.388 | 0.000 | 0.202 | 0.016 | 0.124 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
295 spectra |
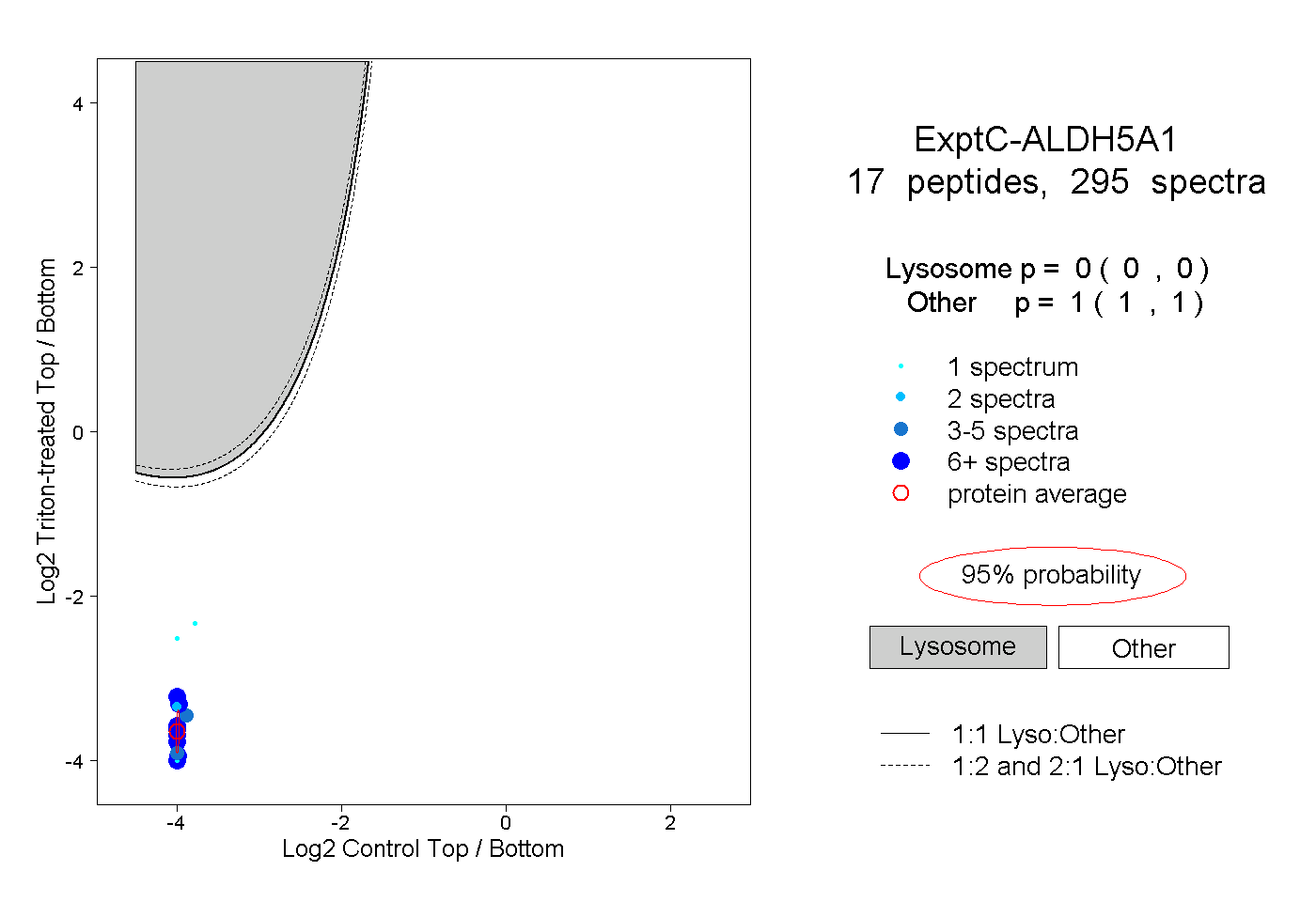 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
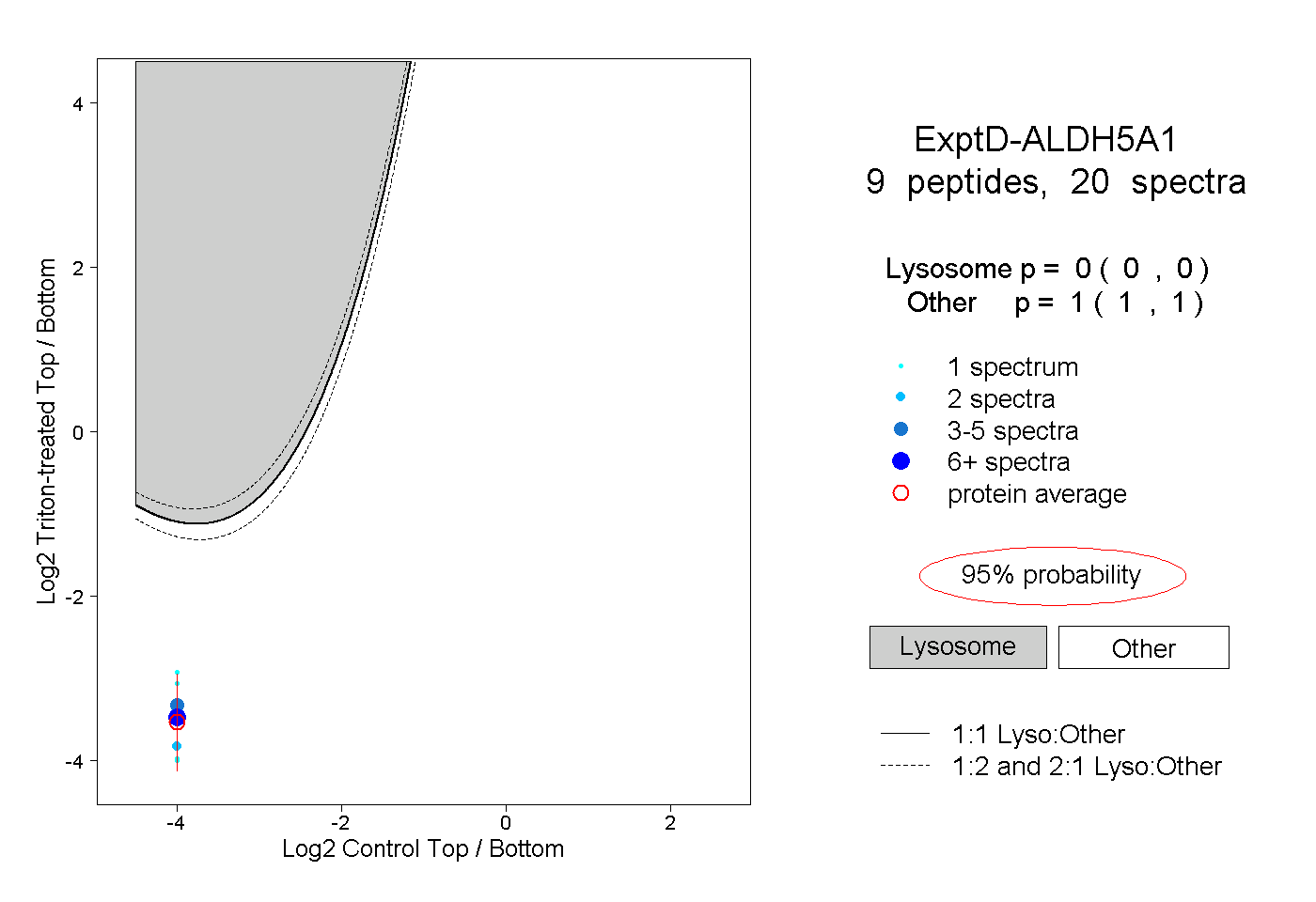 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |