peptides
spectra
0.000 | 0.062
0.175 | 0.246
0.404 | 0.481
0.000 | 0.000
0.000 | 0.000
0.222 | 0.299
0.018 | 0.066
0.000 | 0.000
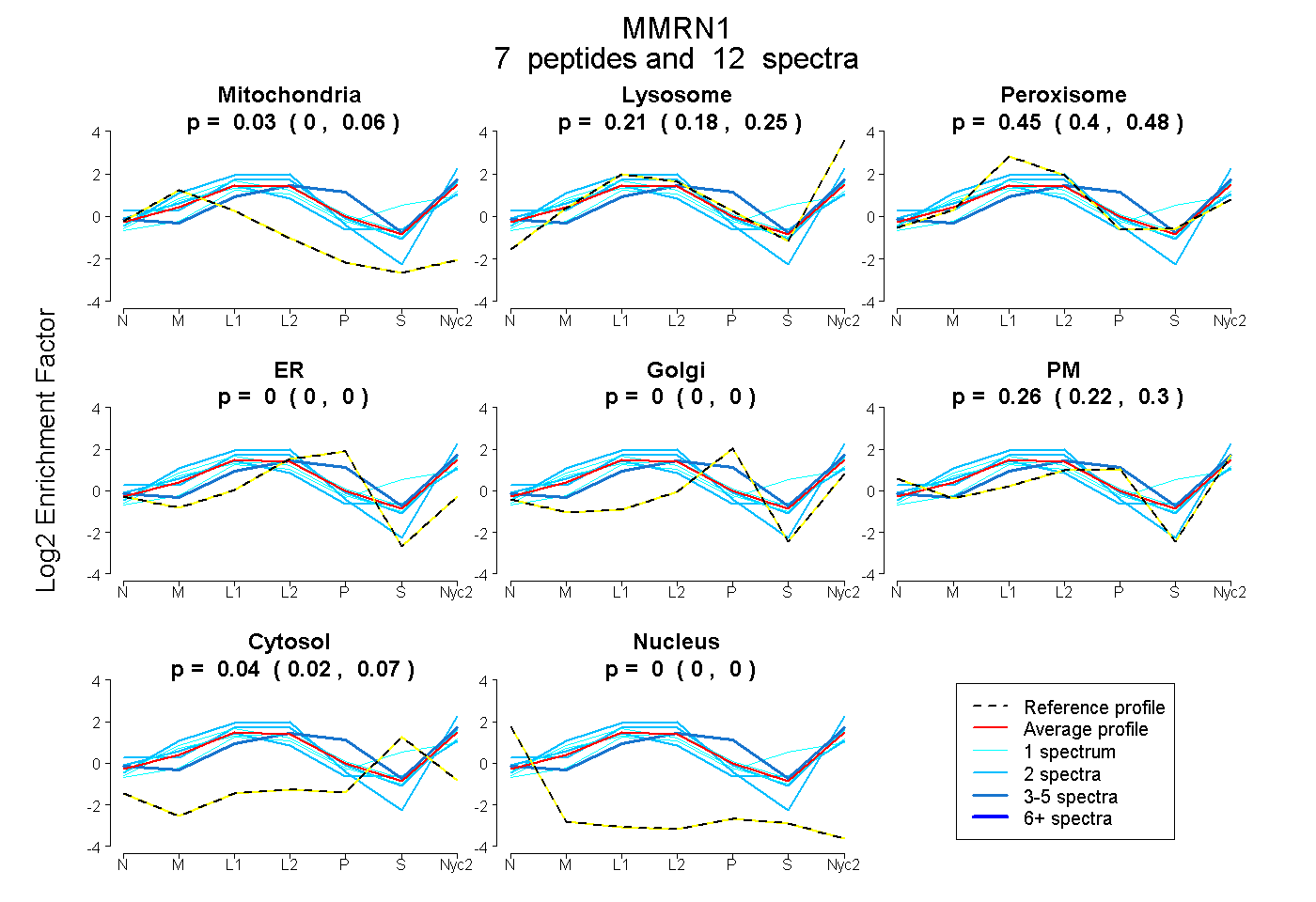
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
12 spectra |
 |
0.034 0.000 | 0.062 |
0.212 0.175 | 0.246 |
0.447 0.404 | 0.481 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.264 0.222 | 0.299 |
0.044 0.018 | 0.066 |
0.000 0.000 | 0.000 |
| 1 spectrum, SLLQQQIIHEPK | 0.144 | 0.356 | 0.371 | 0.000 | 0.000 | 0.129 | 0.000 | 0.000 | ||
| 1 spectrum, LSQLNFQK | 0.081 | 0.258 | 0.439 | 0.047 | 0.044 | 0.092 | 0.038 | 0.000 | ||
| 2 spectra, MAEQLSQQER | 0.117 | 0.528 | 0.216 | 0.000 | 0.000 | 0.140 | 0.000 | 0.000 | ||
| 2 spectra, IVEENALAPDFSK | 0.160 | 0.186 | 0.450 | 0.000 | 0.000 | 0.125 | 0.080 | 0.000 | ||
| 2 spectra, FESENTDSEIHCDR | 0.000 | 0.089 | 0.551 | 0.000 | 0.000 | 0.360 | 0.000 | 0.000 | ||
| 3 spectra, QDSGDPAMIHK | 0.000 | 0.289 | 0.160 | 0.142 | 0.010 | 0.325 | 0.075 | 0.000 | ||
| 1 spectrum, GECEEMLSK | 0.000 | 0.201 | 0.506 | 0.000 | 0.000 | 0.000 | 0.293 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
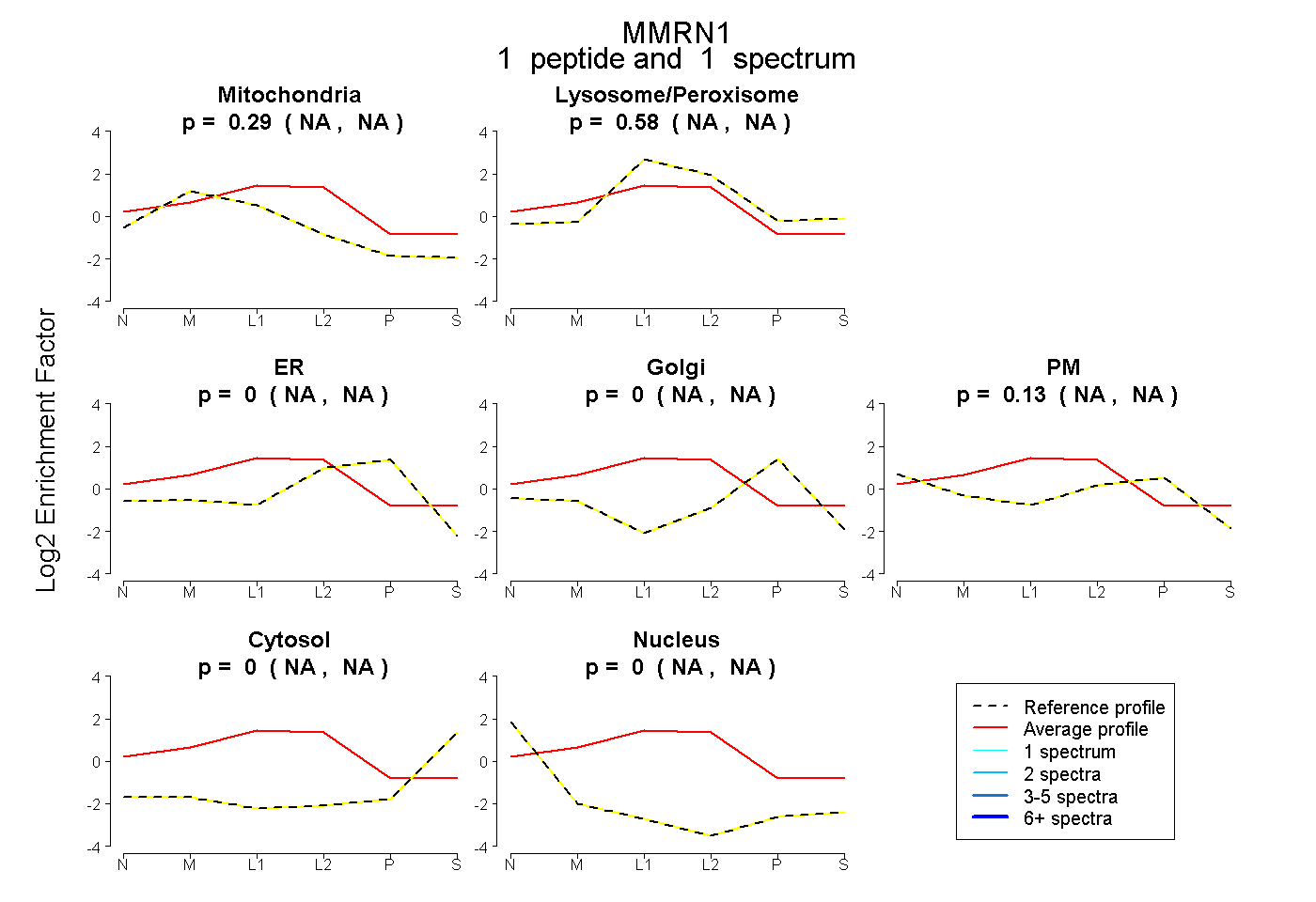 |
0.289 NA | NA |
0.582 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.128 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
59 spectra |
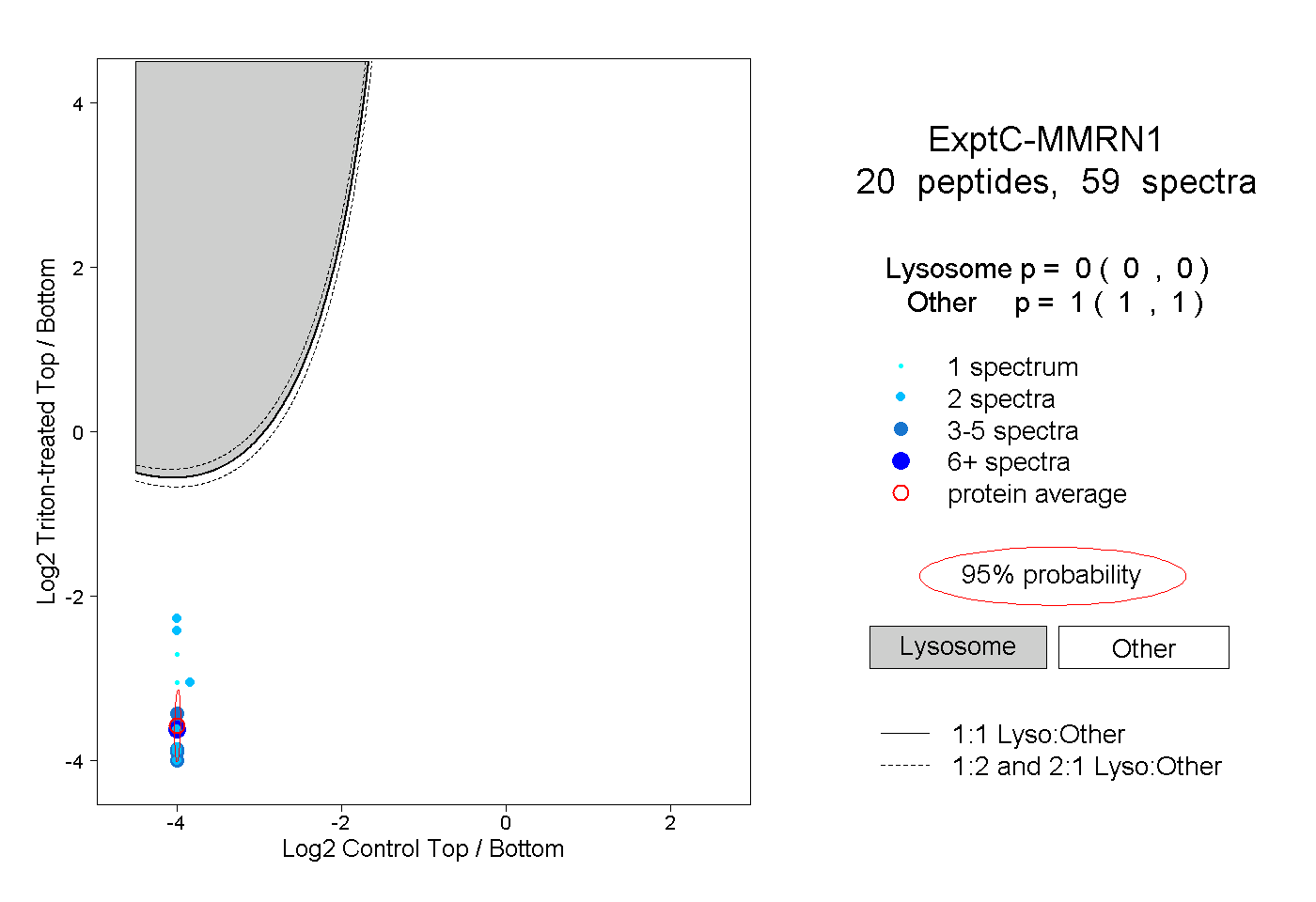 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |