peptides
spectra
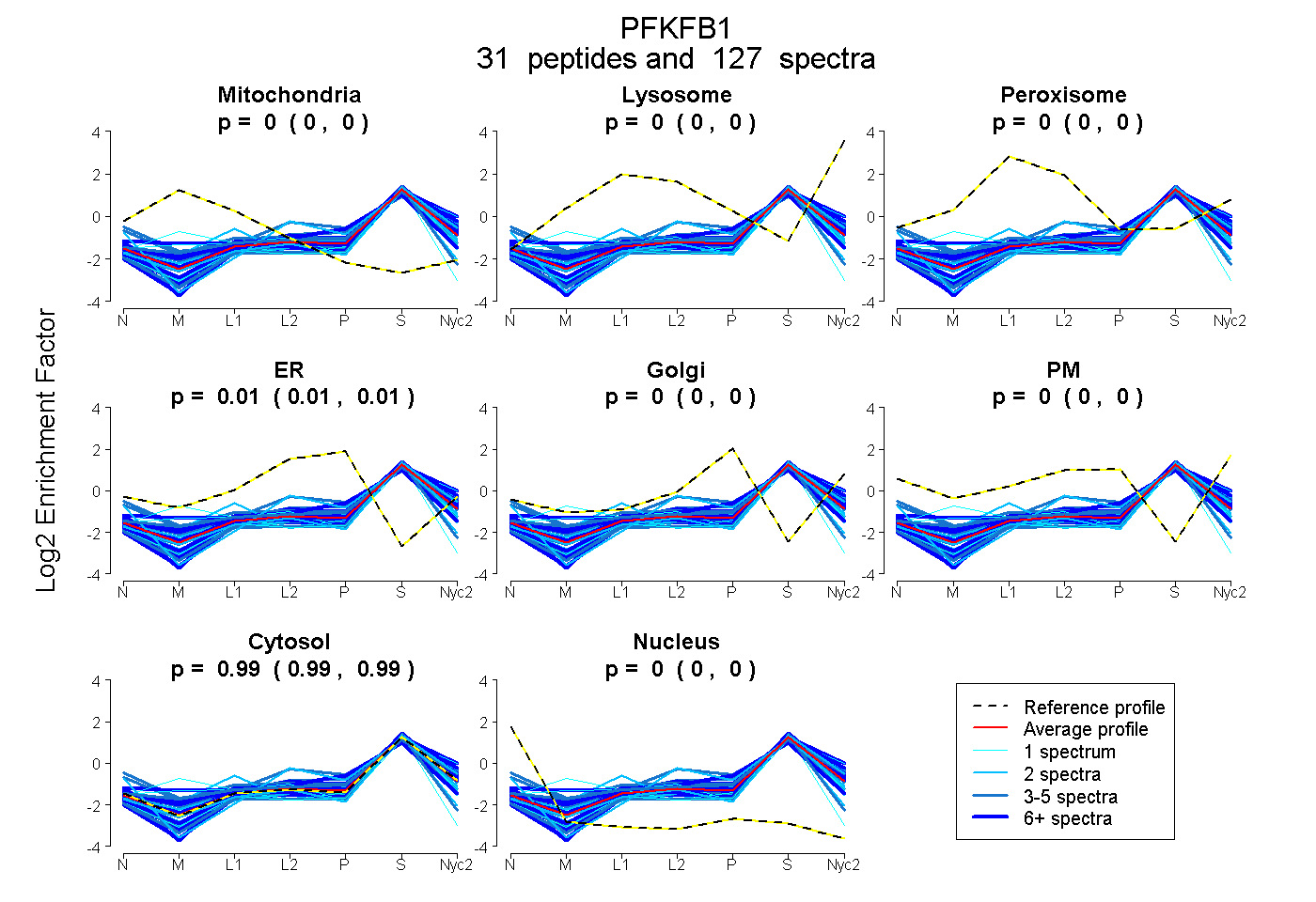
0.000 | 0.000
0.000 | 0.000
0.000 | 0.002
0.009 | 0.012
0.000 | 0.000
0.000 | 0.000
0.987 | 0.990
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
127 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.011 0.009 | 0.012 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.989 0.987 | 0.990 |
0.000 0.000 | 0.000 |
| 3 spectra, LGSPDYIDCDQEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.974 | 0.026 | ||
| 3 spectra, EEGHVAVFDATNTTR | 0.000 | 0.000 | 0.019 | 0.027 | 0.000 | 0.213 | 0.741 | 0.000 | ||
| 1 spectrum, CLLAYFLDK | 0.028 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.865 | 0.106 | ||
| 1 spectrum, TIQTAEALGVPYEQWK | 0.114 | 0.137 | 0.000 | 0.000 | 0.000 | 0.000 | 0.749 | 0.000 | ||
| 2 spectra, VQDHVQSR | 0.000 | 0.000 | 0.000 | 0.072 | 0.000 | 0.000 | 0.900 | 0.028 | ||
| 9 spectra, VLEDFLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, EAEEALDTVPAHY | 0.000 | 0.029 | 0.001 | 0.038 | 0.000 | 0.004 | 0.928 | 0.000 | ||
| 1 spectrum, VFFIESICNDPEIIAENIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.976 | 0.024 | ||
| 6 spectra, QENVLVICHQAVMR | 0.117 | 0.000 | 0.000 | 0.097 | 0.000 | 0.000 | 0.786 | 0.000 | ||
| 2 spectra, YLNWIGTPTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 7 spectra, LEPVIMELER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 9 spectra, SSDELPYLK | 0.000 | 0.002 | 0.000 | 0.000 | 0.000 | 0.000 | 0.998 | 0.000 | ||
| 9 spectra, EMGELTQTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, IGGDSGLSAR | 0.019 | 0.008 | 0.000 | 0.000 | 0.000 | 0.000 | 0.973 | 0.000 | ||
| 2 spectra, SQGISSLK | 0.000 | 0.024 | 0.000 | 0.000 | 0.000 | 0.000 | 0.976 | 0.000 | ||
| 4 spectra, DKPENVDITR | 0.000 | 0.000 | 0.000 | 0.104 | 0.000 | 0.000 | 0.896 | 0.000 | ||
| 2 spectra, IWIPHSSSSSVLQR | 0.145 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.855 | 0.000 | ||
| 4 spectra, SLILQFAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, NYEFFRPDNTEAQLIR | 0.000 | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 | 0.985 | 0.000 | ||
| 1 spectrum, TAYYLMNIHVTPR | 0.149 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.851 | 0.000 | ||
| 6 spectra, VFNLGQYR | 0.003 | 0.097 | 0.000 | 0.000 | 0.000 | 0.000 | 0.901 | 0.000 | ||
| 6 spectra, EAVSYR | 0.000 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | 0.896 | 0.000 | ||
| 2 spectra, CPLHTVLK | 0.059 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.941 | 0.000 | ||
| 4 spectra, IFDVGTR | 0.000 | 0.058 | 0.000 | 0.000 | 0.000 | 0.000 | 0.942 | 0.000 | ||
| 2 spectra, QCALAALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | ||
| 3 spectra, SIYLCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.871 | 0.129 | ||
| 5 spectra, VWTSHMK | 0.039 | 0.082 | 0.000 | 0.000 | 0.009 | 0.000 | 0.870 | 0.000 | ||
| 3 spectra, HGESELNLR | 0.031 | 0.000 | 0.097 | 0.002 | 0.000 | 0.042 | 0.793 | 0.035 | ||
| 6 spectra, GESYEDLVQR | 0.000 | 0.019 | 0.000 | 0.000 | 0.000 | 0.000 | 0.981 | 0.000 | ||
| 4 spectra, TYISTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 9 spectra, QYAYALANFIR | 0.017 | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.916 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
60 spectra |
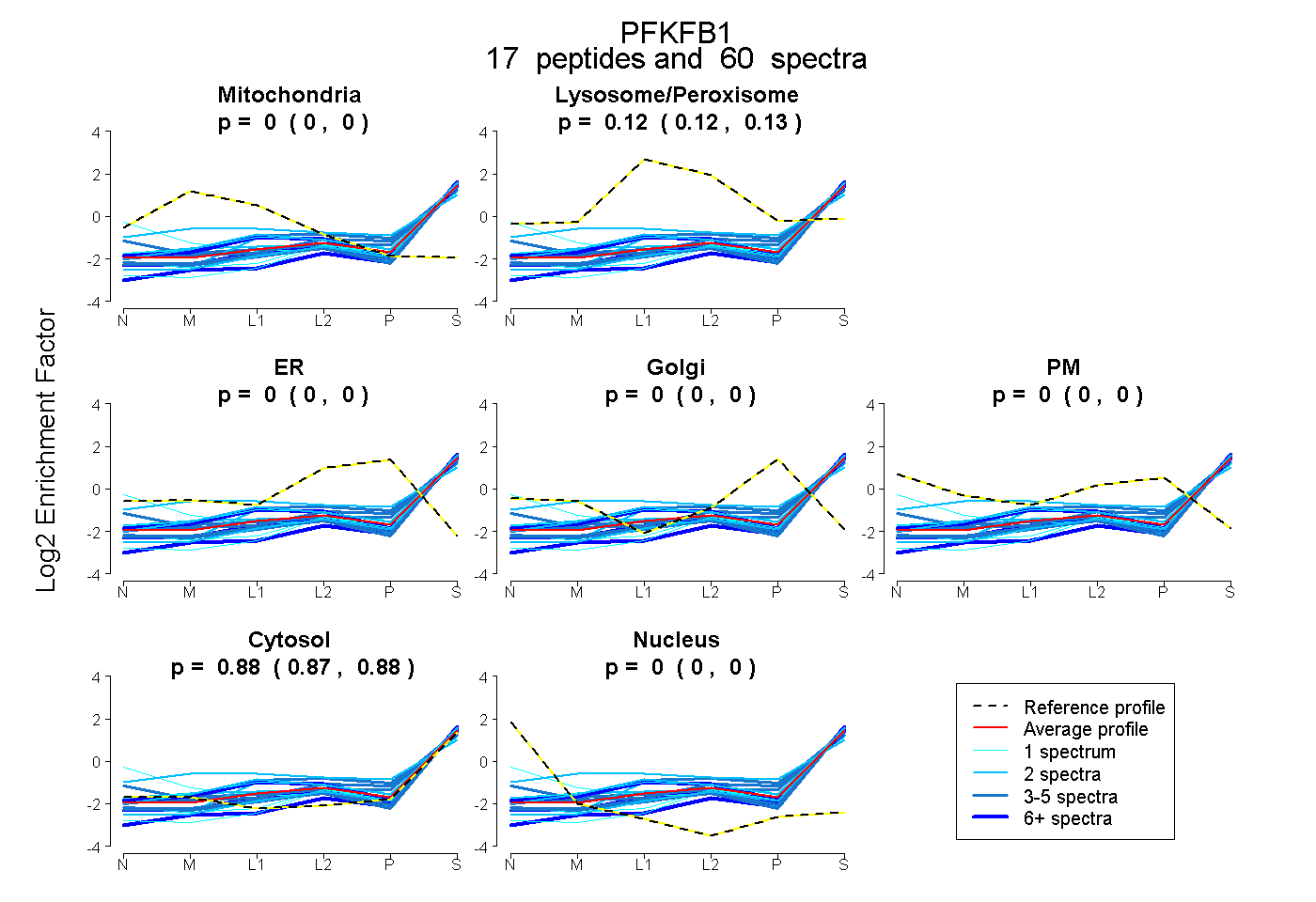 |
0.000 0.000 | 0.000 |
0.123 0.118 | 0.126 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.877 0.873 | 0.881 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
108 spectra |
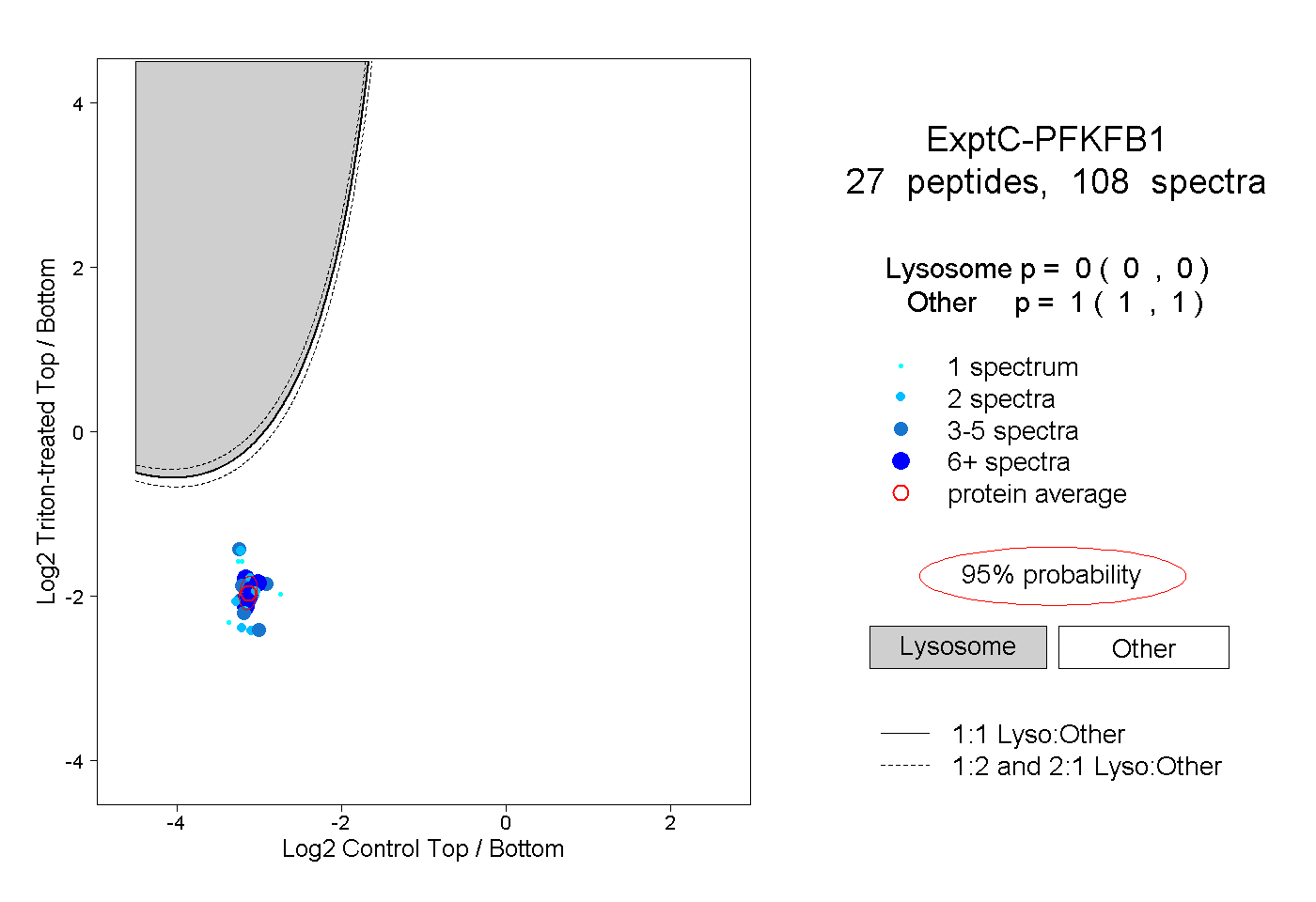 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
22 spectra |
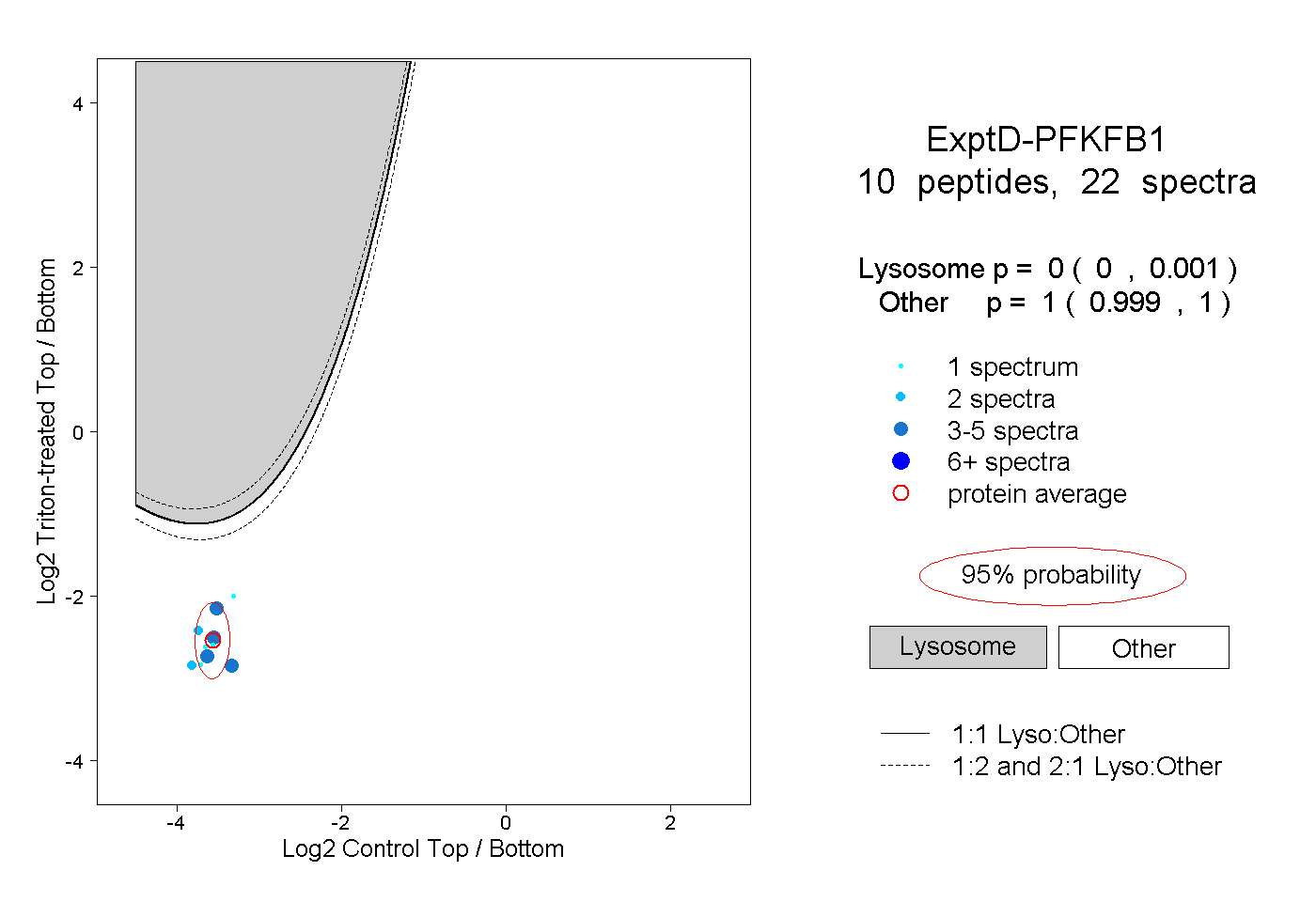 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |