peptides
spectra
0.000 | 0.000
0.000 | 0.006
0.010 | 0.050
0.000 | 0.095
0.124 | 0.217
0.000 | 0.000
0.726 | 0.755
0.000 | 0.000
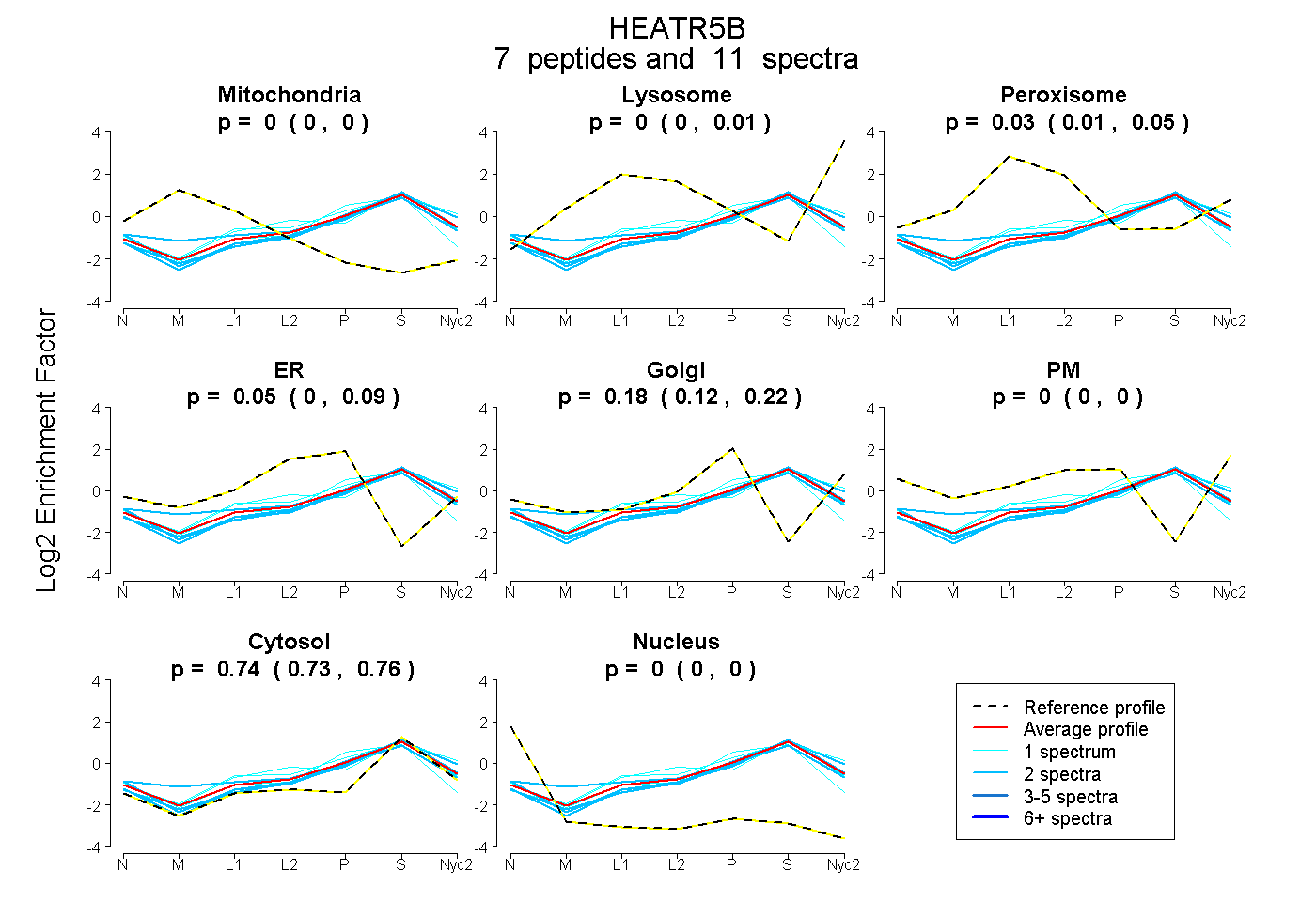
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
11 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.006 |
0.033 0.010 | 0.050 |
0.045 0.000 | 0.095 |
0.180 0.124 | 0.217 |
0.000 0.000 | 0.000 |
0.741 0.726 | 0.755 |
0.000 0.000 | 0.000 |
| 1 spectrum, AAVACLR | 0.000 | 0.000 | 0.000 | 0.250 | 0.000 | 0.000 | 0.750 | 0.000 | ||
| 2 spectra, MVVSIAEDLLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.216 | 0.000 | 0.784 | 0.000 | ||
| 1 spectrum, MAGLQALEDIIK | 0.000 | 0.130 | 0.026 | 0.000 | 0.192 | 0.000 | 0.652 | 0.000 | ||
| 1 spectrum, LAAVACVGAFYEK | 0.000 | 0.000 | 0.125 | 0.132 | 0.000 | 0.000 | 0.743 | 0.000 | ||
| 2 spectra, LAAAWCLR | 0.013 | 0.000 | 0.109 | 0.047 | 0.170 | 0.000 | 0.662 | 0.000 | ||
| 2 spectra, AHGAHLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.192 | 0.000 | 0.808 | 0.000 | ||
| 2 spectra, LWLAALK | 0.000 | 0.028 | 0.000 | 0.000 | 0.206 | 0.000 | 0.766 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
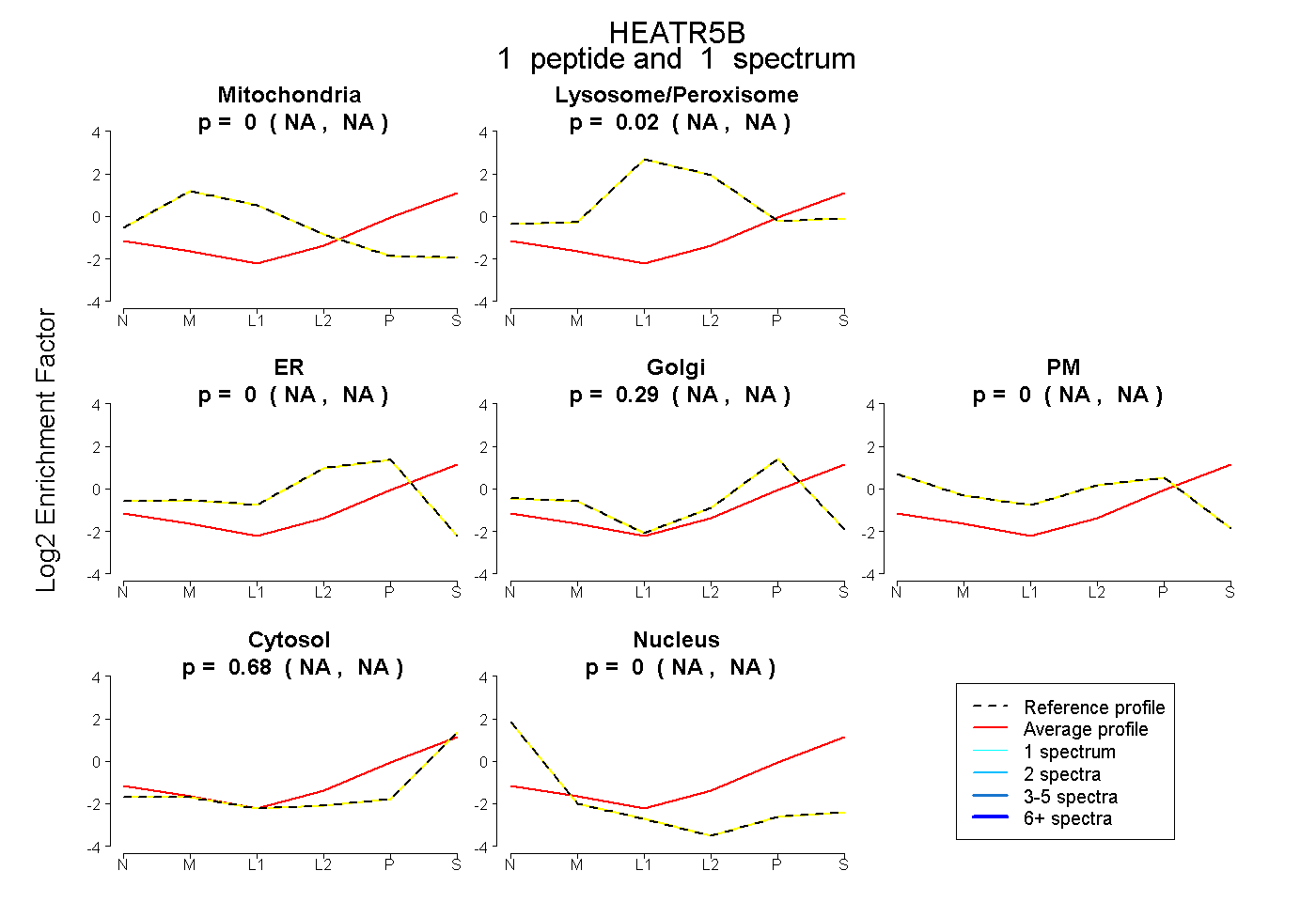 |
0.000 NA | NA |
0.025 NA | NA |
0.000 NA | NA |
0.293 NA | NA |
0.000 NA | NA |
0.683 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
14 spectra |
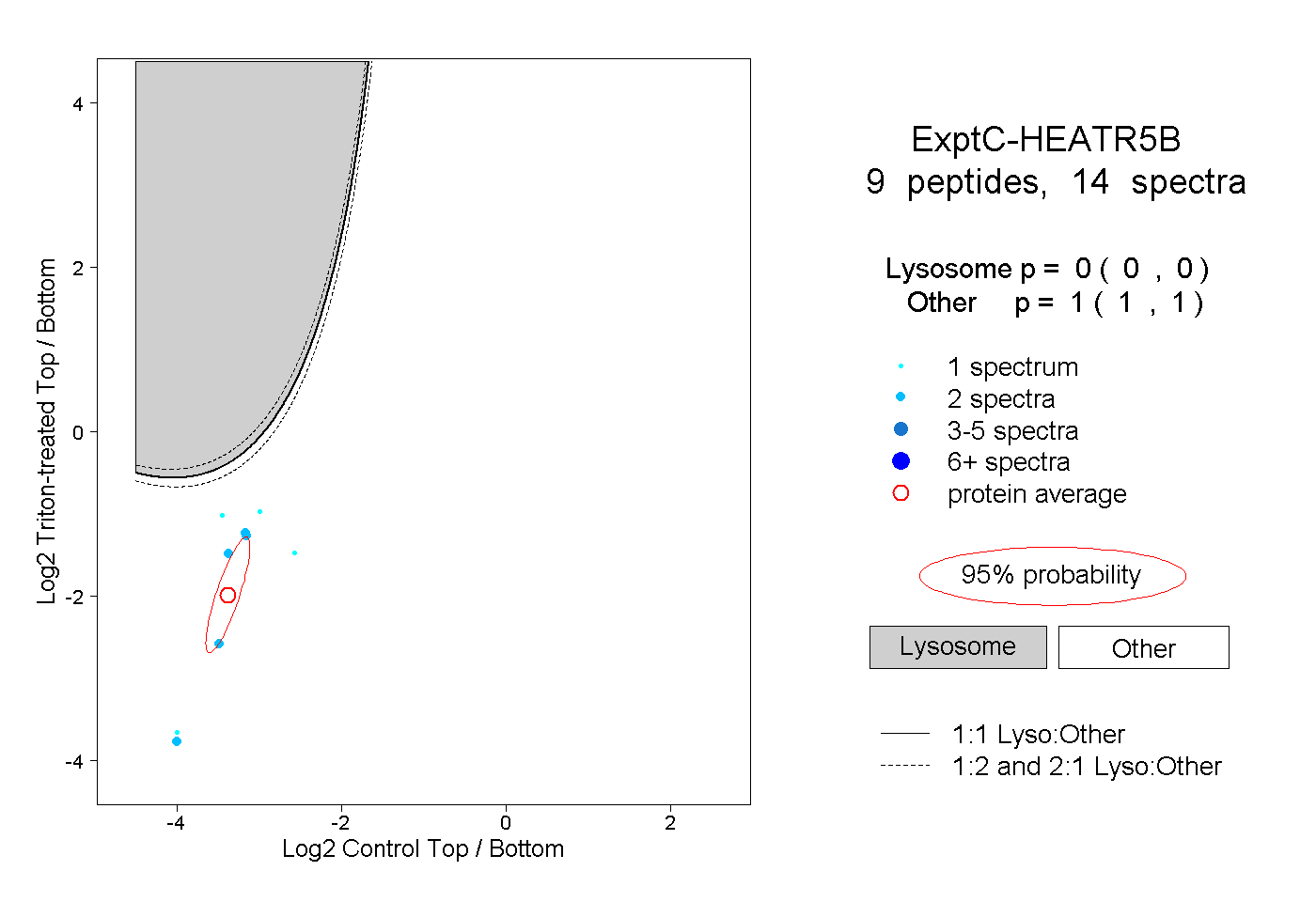 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |