peptides
spectra
0.026 | 0.034
0.000 | 0.000
0.000 | 0.003
0.964 | 0.973
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.089 | 0.108
0.890 | 0.909
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
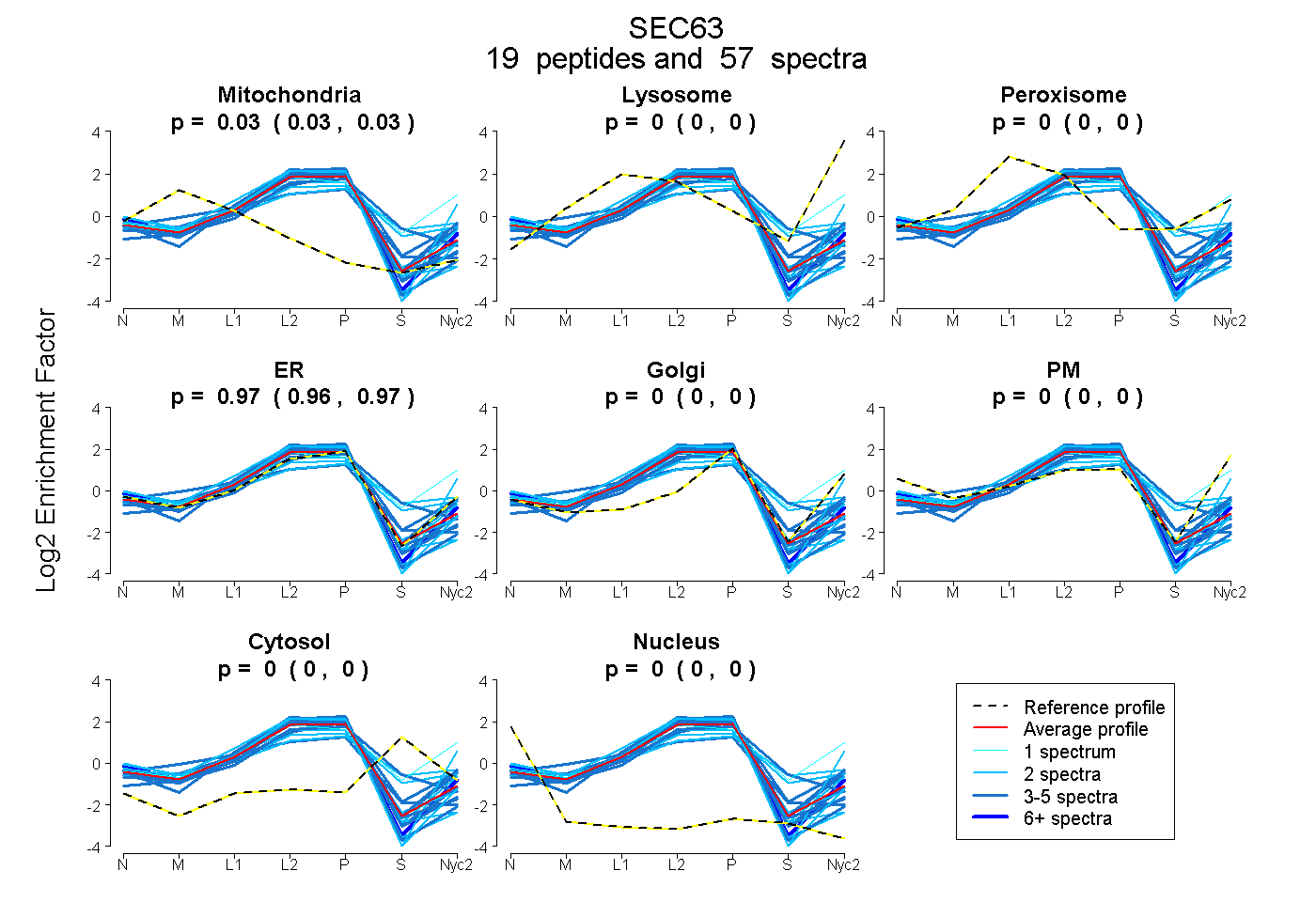
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
57 spectra |
 |
0.031 0.026 | 0.034 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.003 |
0.969 0.964 | 0.973 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
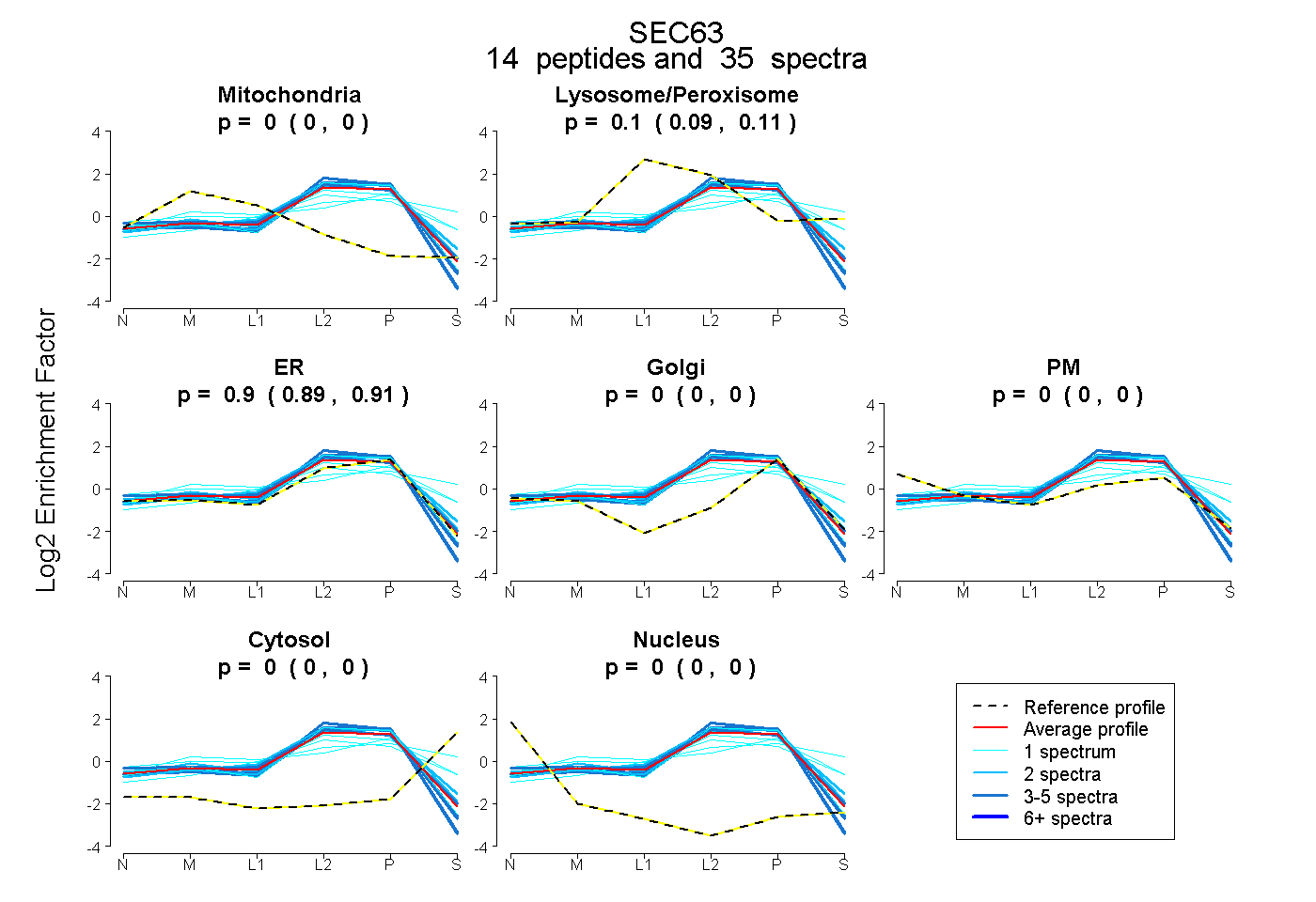
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.000 0.000 | 0.000 |
0.099 0.089 | 0.108 |
0.901 0.890 | 0.909 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, EIGSINLK | 0.000 | 0.398 | 0.258 | 0.123 | 0.000 | 0.221 | 0.000 | |||
| 1 spectrum, ALIETK | 0.195 | 0.087 | 0.680 | 0.038 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, YSGDQILIR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TTQIYTYFVYK | 0.000 | 0.218 | 0.782 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LSQMAVQGLQQFK | 0.000 | 0.158 | 0.837 | 0.000 | 0.000 | 0.004 | 0.000 | |||
| 2 spectra, SPLLQLPHIEEDNLR | 0.000 | 0.077 | 0.923 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DQNAEQIR | 0.000 | 0.070 | 0.930 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, VLLLSHLAR | 0.000 | 0.134 | 0.866 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, SIQDLVSLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, NEPPLTCPYSLK | 0.000 | 0.277 | 0.595 | 0.027 | 0.000 | 0.100 | 0.000 | |||
| 1 spectrum, APTLASLENCMK | 0.000 | 0.411 | 0.200 | 0.258 | 0.090 | 0.041 | 0.000 | |||
| 4 spectra, DATSRPTDNVLIPQLIR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, FPAPGRPGNHQYTVFLR | 0.000 | 0.016 | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, AYAALTDEESR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
135 spectra |
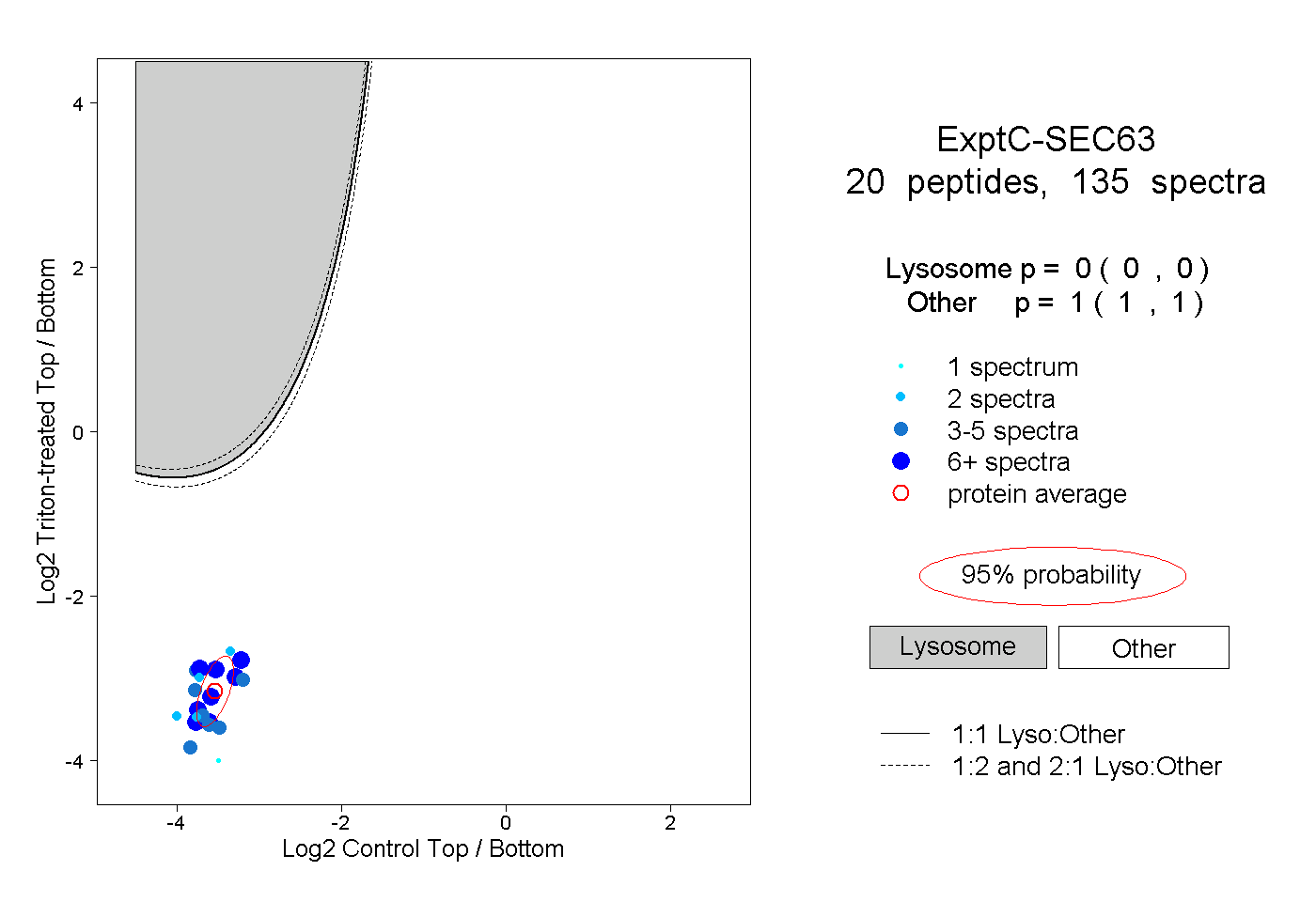 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
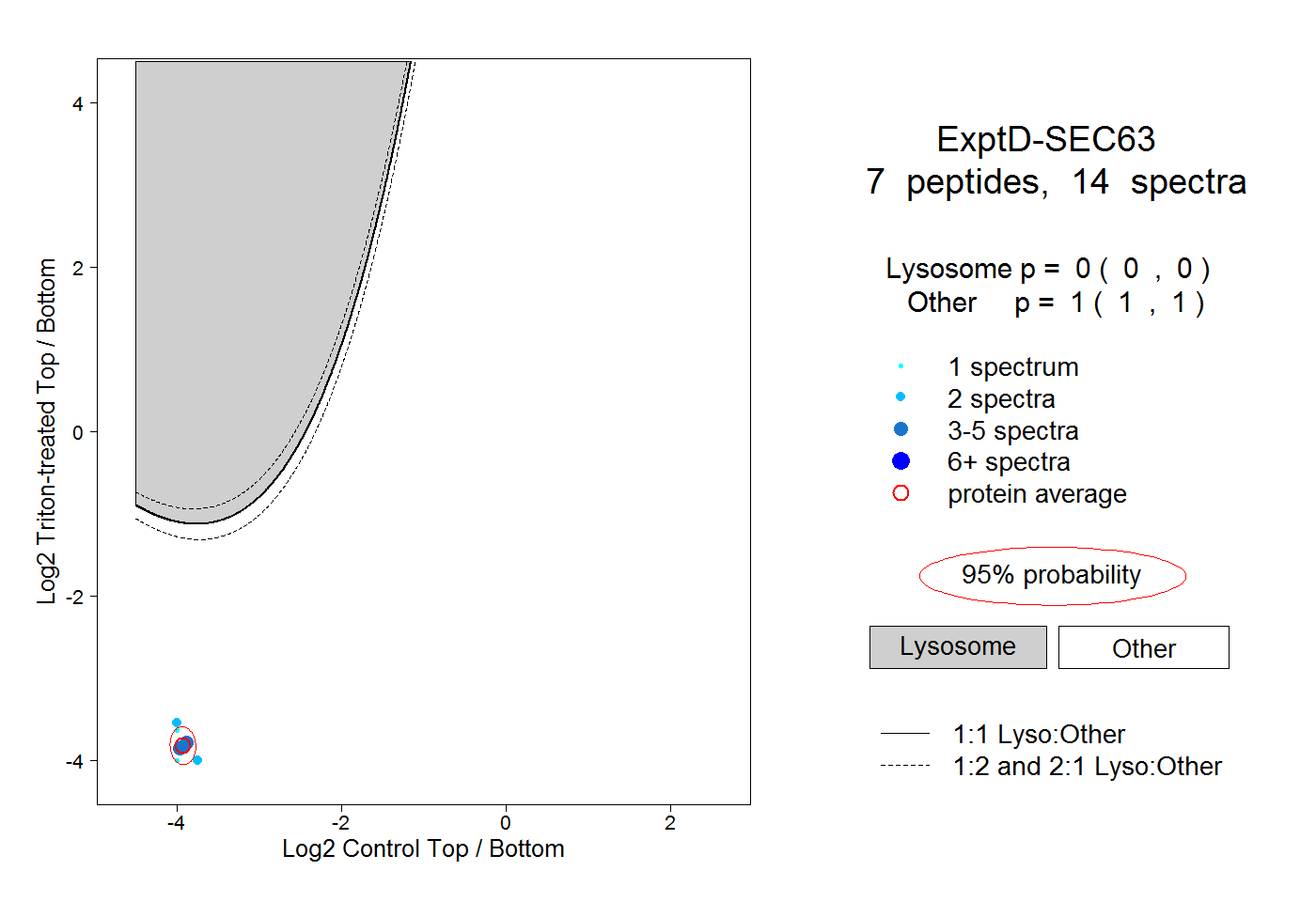 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |