peptides
spectra
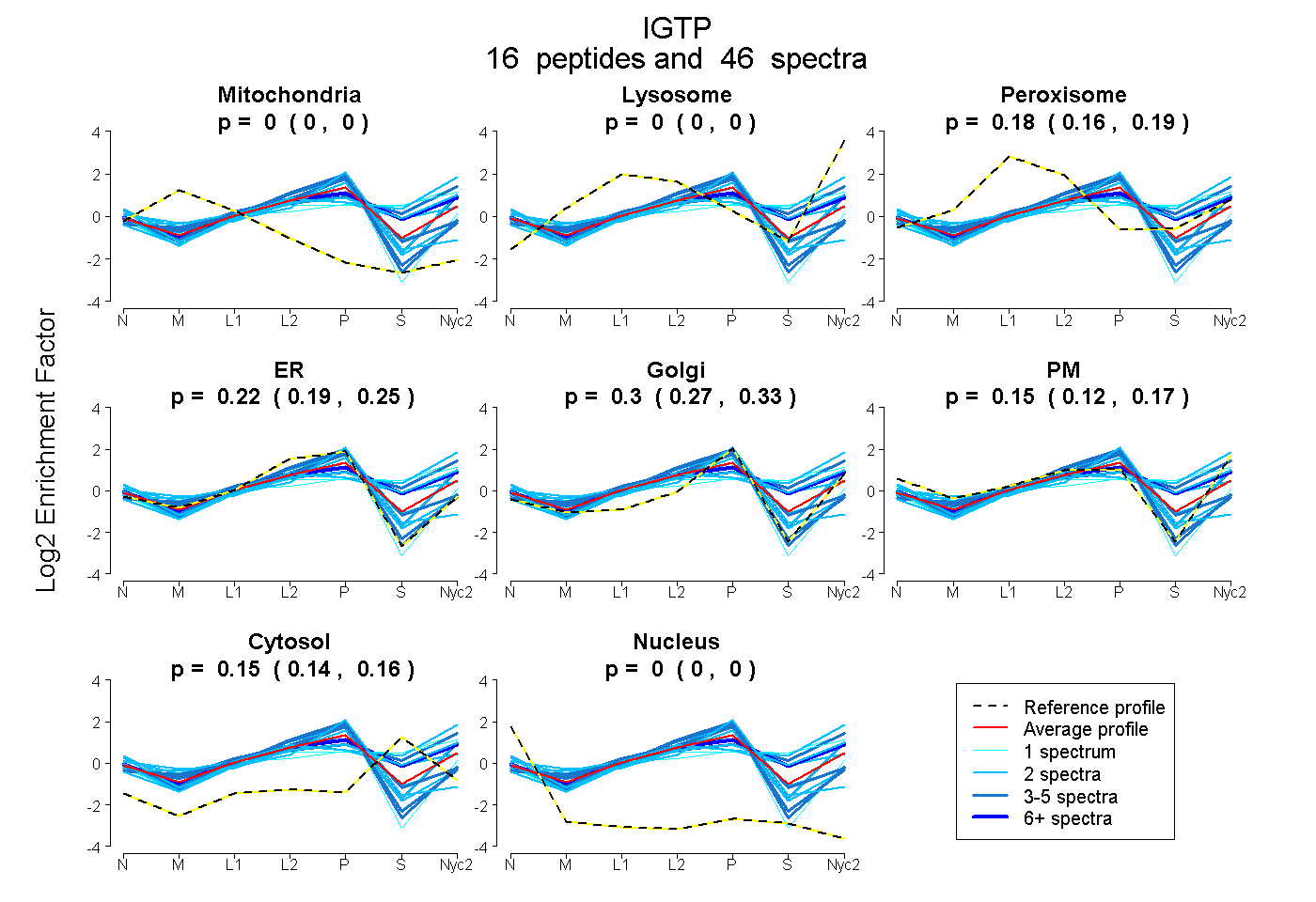
0.000 | 0.000
0.000 | 0.000
0.162 | 0.185
0.195 | 0.250
0.272 | 0.325
0.121 | 0.166
0.143 | 0.162
0.000 | 0.000
peptides
spectra
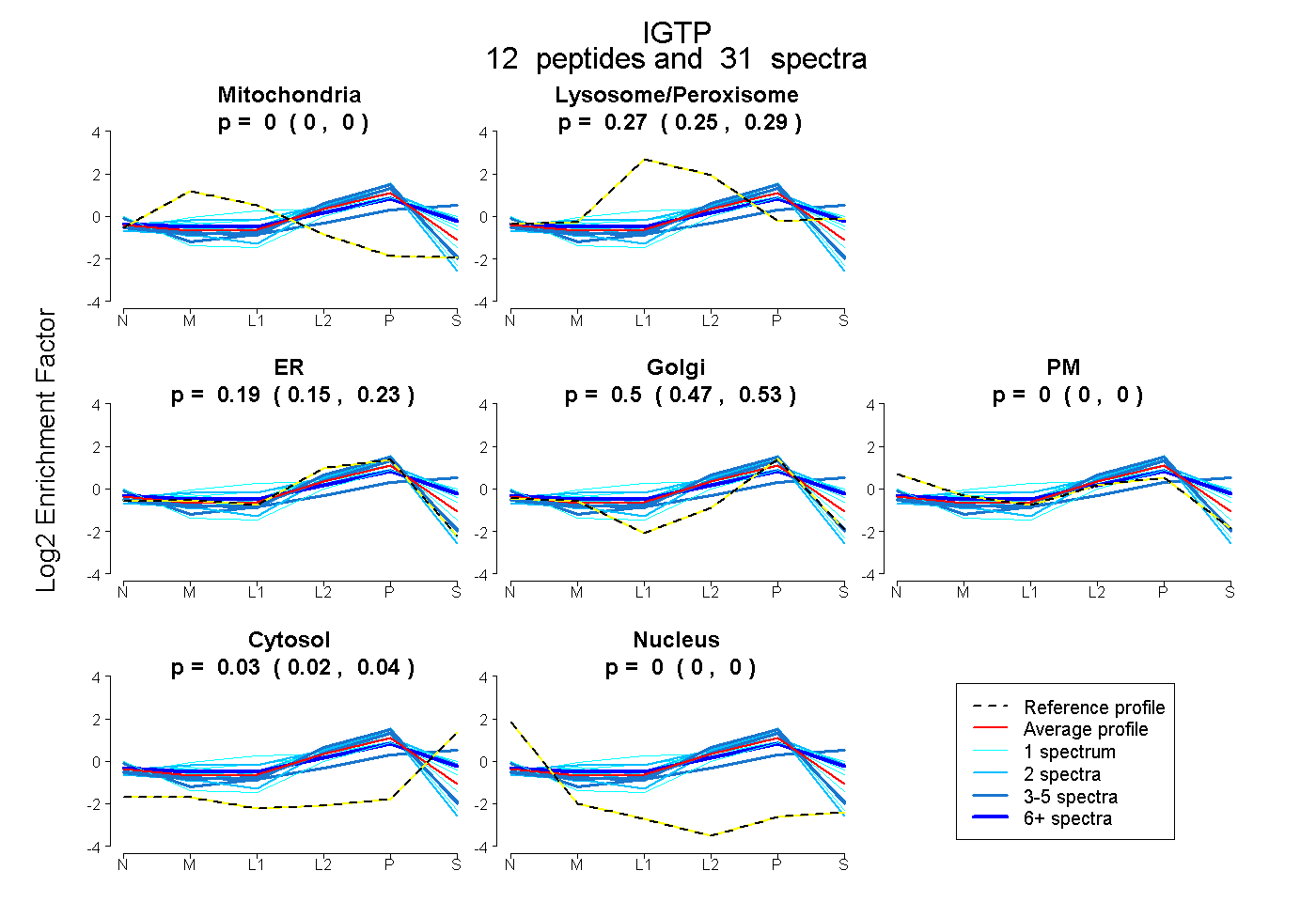
0.000 | 0.000
0.252 | 0.286
0.154 | 0.226
0.474 | 0.528
0.000 | 0.000
0.019 | 0.043
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
46 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.175 0.162 | 0.185 |
0.225 0.195 | 0.250 |
0.301 0.272 | 0.325 |
0.145 0.121 | 0.166 |
0.154 0.143 | 0.162 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
31 spectra |
 |
0.000 0.000 | 0.000 |
0.271 0.252 | 0.286 |
0.193 0.154 | 0.226 |
0.504 0.474 | 0.528 |
0.000 0.000 | 0.000 |
0.032 0.019 | 0.043 |
0.000 0.000 | 0.000 |
| 3 spectra, IIDENNLQR | 0.000 | 0.253 | 0.000 | 0.208 | 0.170 | 0.370 | 0.000 | |||
| 3 spectra, VAQSTGRPEMSTR | 0.000 | 0.102 | 0.565 | 0.327 | 0.000 | 0.005 | 0.000 | |||
| 2 spectra, IIEIVAK | 0.117 | 0.000 | 0.883 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SLDTYQK | 0.000 | 0.122 | 0.132 | 0.307 | 0.170 | 0.269 | 0.000 | |||
| 3 spectra, LFGVDNESLR | 0.000 | 0.028 | 0.765 | 0.207 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LAEAMQR | 0.000 | 0.091 | 0.552 | 0.090 | 0.000 | 0.267 | 0.000 | |||
| 1 spectrum, DIHNIR | 0.000 | 0.215 | 0.339 | 0.445 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ALQFQDLIK | 0.000 | 0.093 | 0.685 | 0.196 | 0.025 | 0.000 | 0.000 | |||
| 11 spectra, LIGHEEEDSAPTGVVR | 0.000 | 0.373 | 0.000 | 0.504 | 0.000 | 0.123 | 0.000 | |||
| 1 spectrum, DFYFVR | 0.000 | 0.482 | 0.000 | 0.503 | 0.000 | 0.015 | 0.000 | |||
| 1 spectrum, AVAEGDLQK | 0.000 | 0.015 | 0.777 | 0.080 | 0.128 | 0.000 | 0.000 | |||
| 1 spectrum, FYVVWTK | 0.000 | 0.423 | 0.000 | 0.511 | 0.000 | 0.066 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
125 spectra |
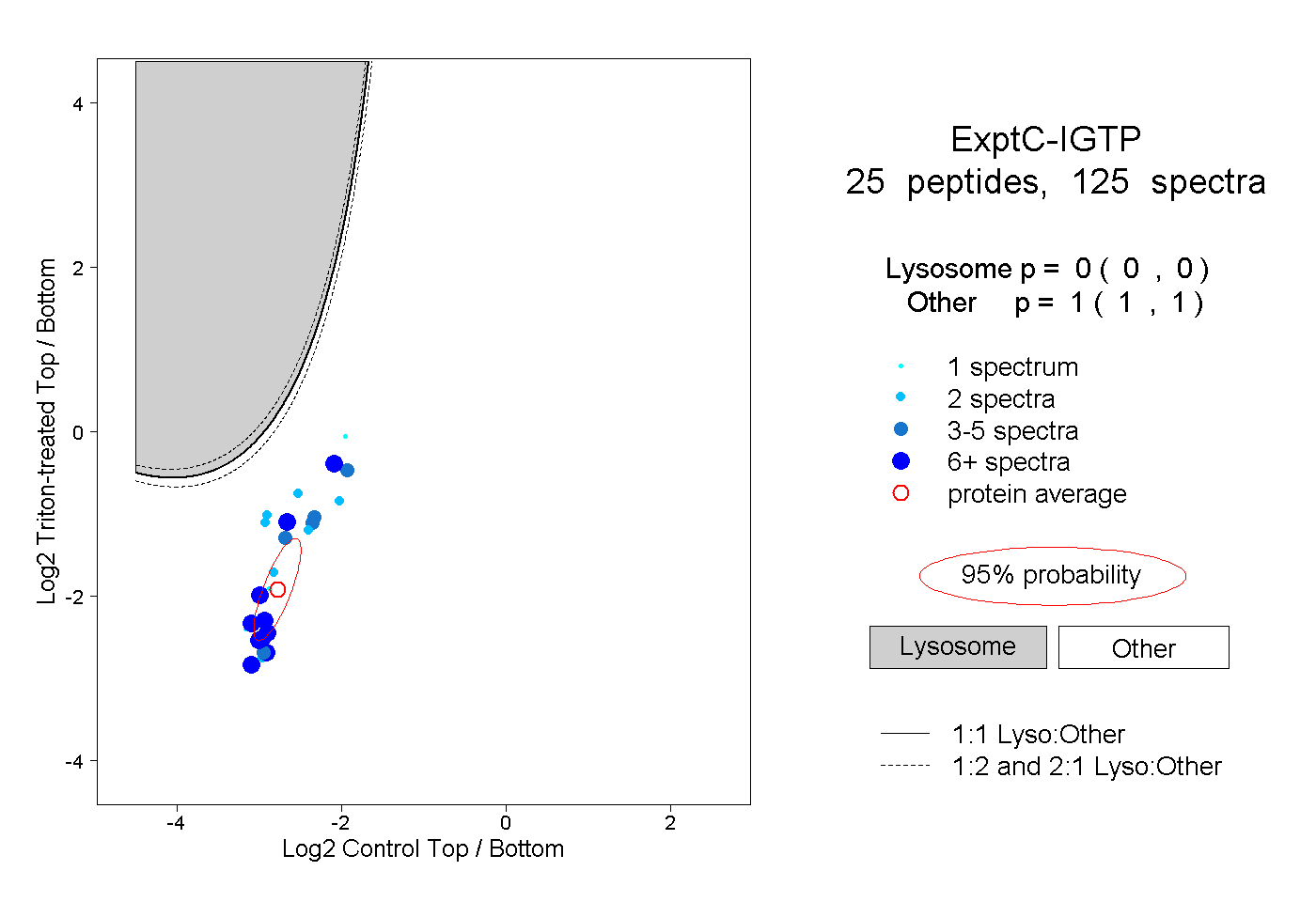 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
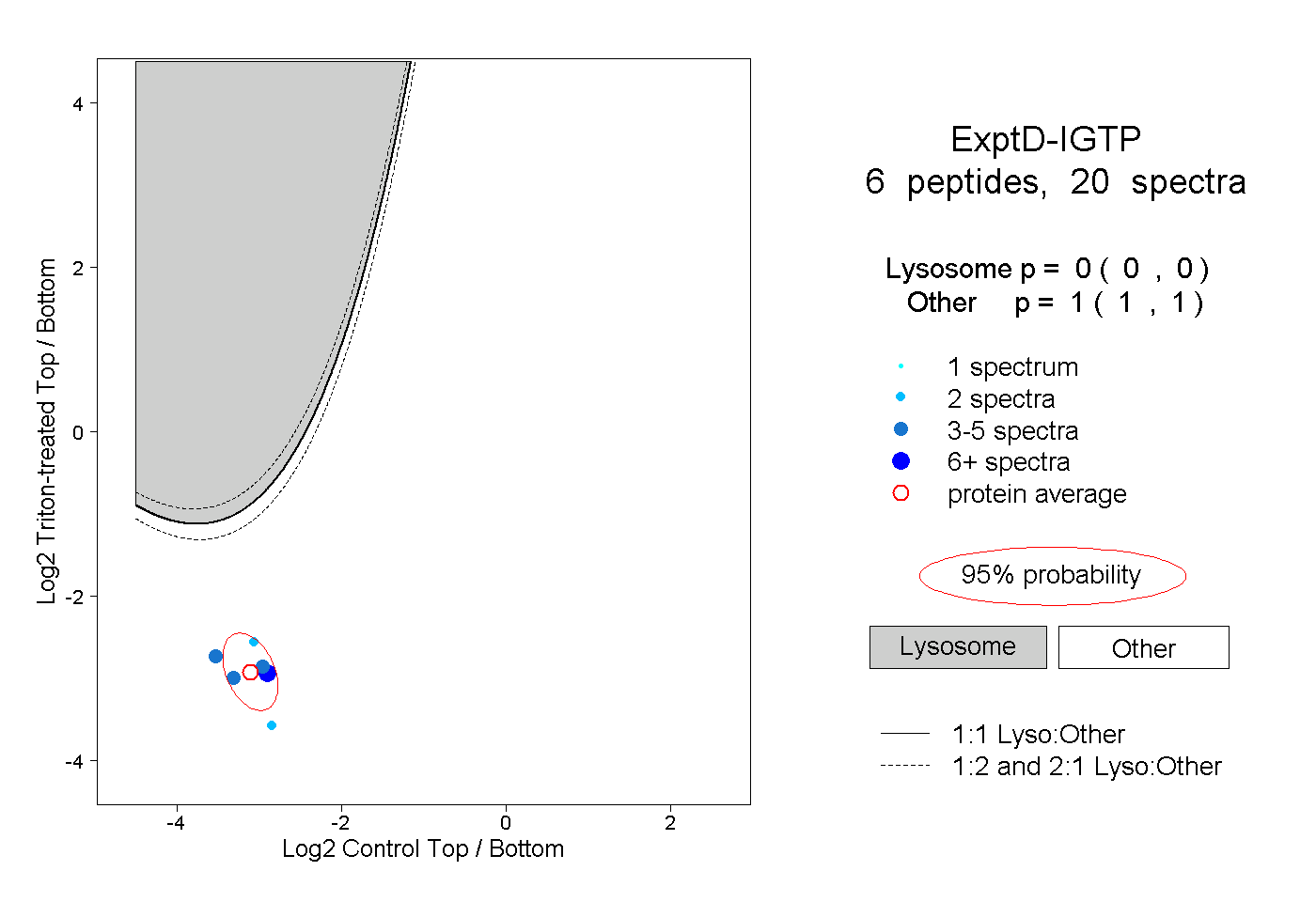 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |