peptides
spectra
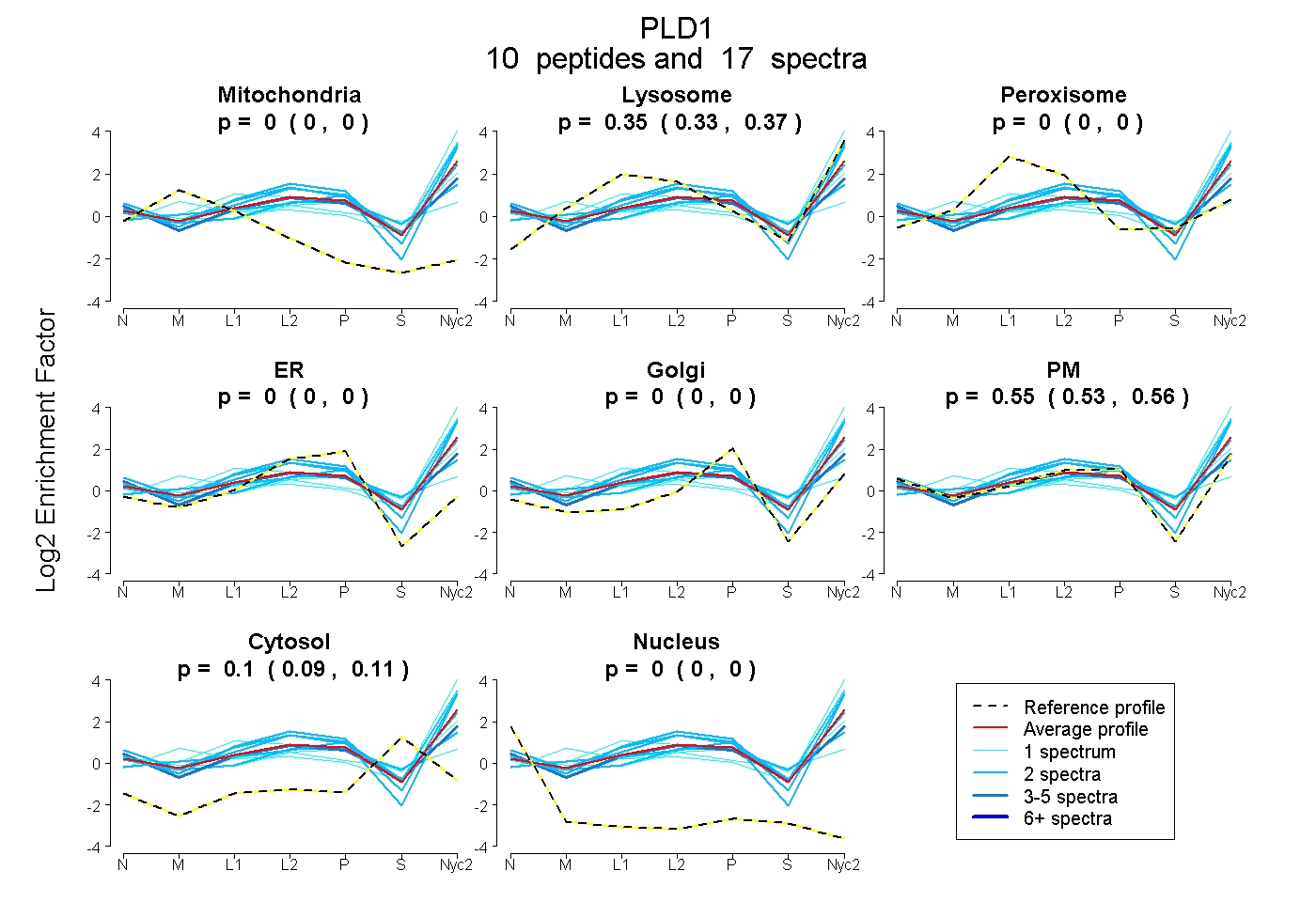
0.000 | 0.000
0.328 | 0.371
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.526 | 0.565
0.089 | 0.114
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.351 0.328 | 0.371 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.547 0.526 | 0.565 |
0.102 0.089 | 0.114 |
0.000 0.000 | 0.000 |
| 1 spectrum, DYCNFVFK | 0.013 | 0.000 | 0.207 | 0.000 | 0.000 | 0.478 | 0.301 | 0.000 | ||
| 3 spectra, SSENAIQEEQFFGR | 0.000 | 0.144 | 0.076 | 0.000 | 0.000 | 0.605 | 0.174 | 0.000 | ||
| 2 spectra, VGNAIAQR | 0.000 | 0.300 | 0.000 | 0.000 | 0.000 | 0.700 | 0.000 | 0.000 | ||
| 1 spectrum, QLEDYLTK | 0.000 | 0.569 | 0.000 | 0.000 | 0.000 | 0.420 | 0.011 | 0.000 | ||
| 2 spectra, YQVPGAVHAK | 0.000 | 0.405 | 0.000 | 0.000 | 0.120 | 0.367 | 0.108 | 0.000 | ||
| 2 spectra, WDDNEHR | 0.000 | 0.433 | 0.000 | 0.000 | 0.000 | 0.567 | 0.000 | 0.000 | ||
| 1 spectrum, MPWHDIGSVVHGK | 0.000 | 0.671 | 0.000 | 0.000 | 0.000 | 0.251 | 0.055 | 0.022 | ||
| 2 spectra, FAQGLR | 0.000 | 0.525 | 0.000 | 0.000 | 0.000 | 0.463 | 0.011 | 0.000 | ||
| 1 spectrum, RPVVEGNR | 0.000 | 0.228 | 0.000 | 0.000 | 0.000 | 0.549 | 0.223 | 0.000 | ||
| 2 spectra, SQATAHELR | 0.000 | 0.178 | 0.019 | 0.000 | 0.000 | 0.542 | 0.260 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
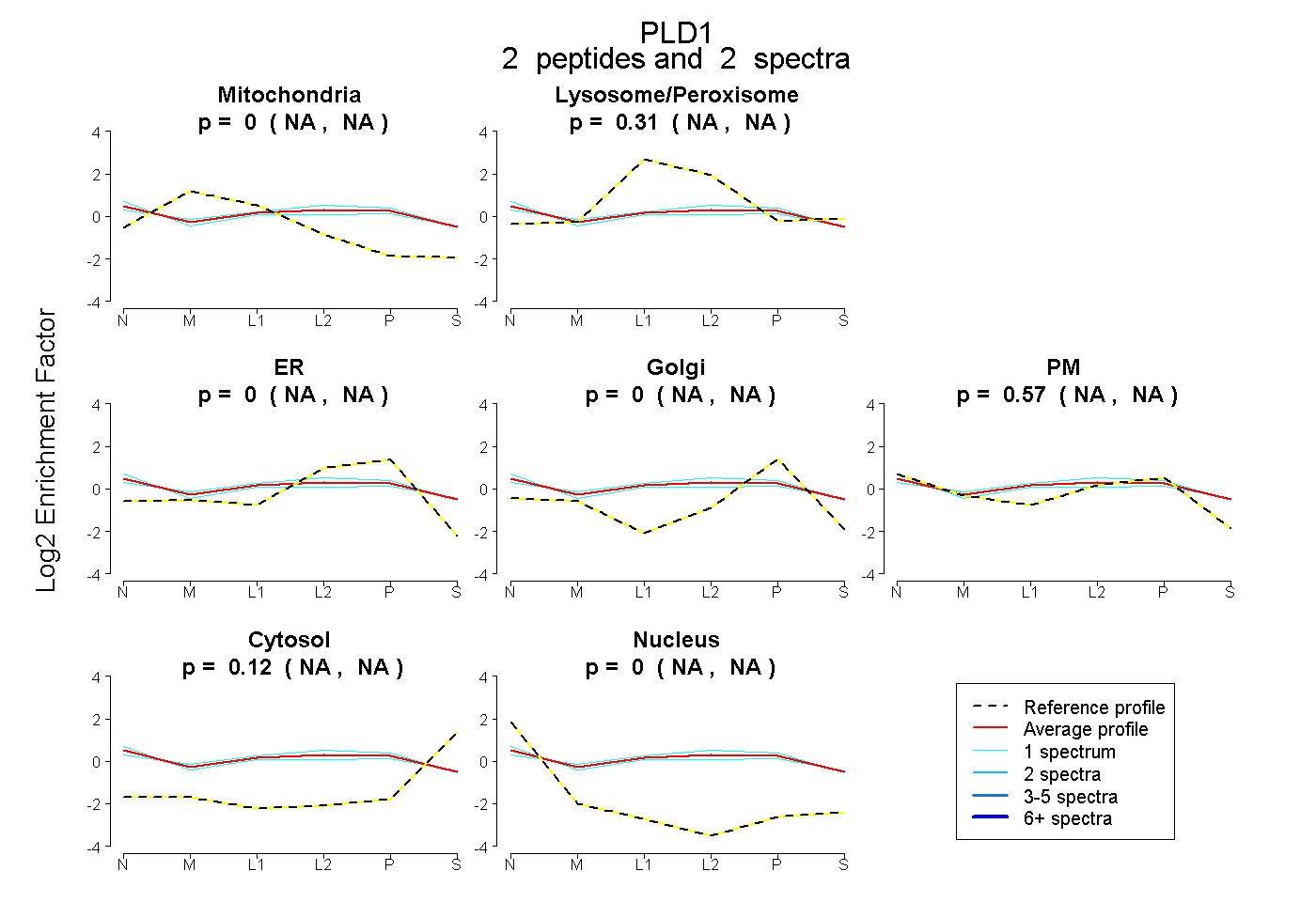 |
0.000 NA | NA |
0.312 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.570 NA | NA |
0.118 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
31 spectra |
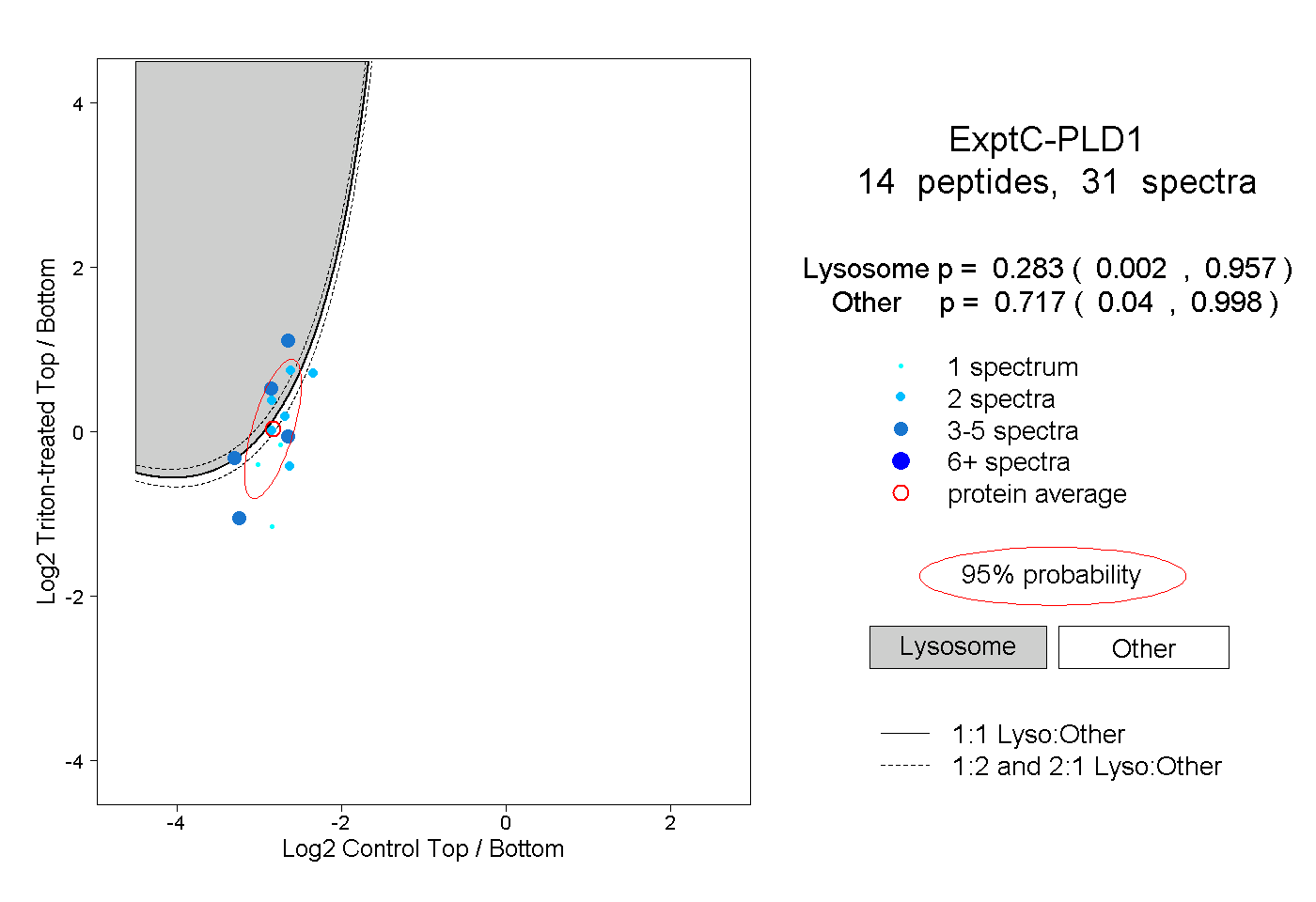 |
0.283 0.002 | 0.957 |
0.717 0.040 | 0.998 |