peptides
spectra
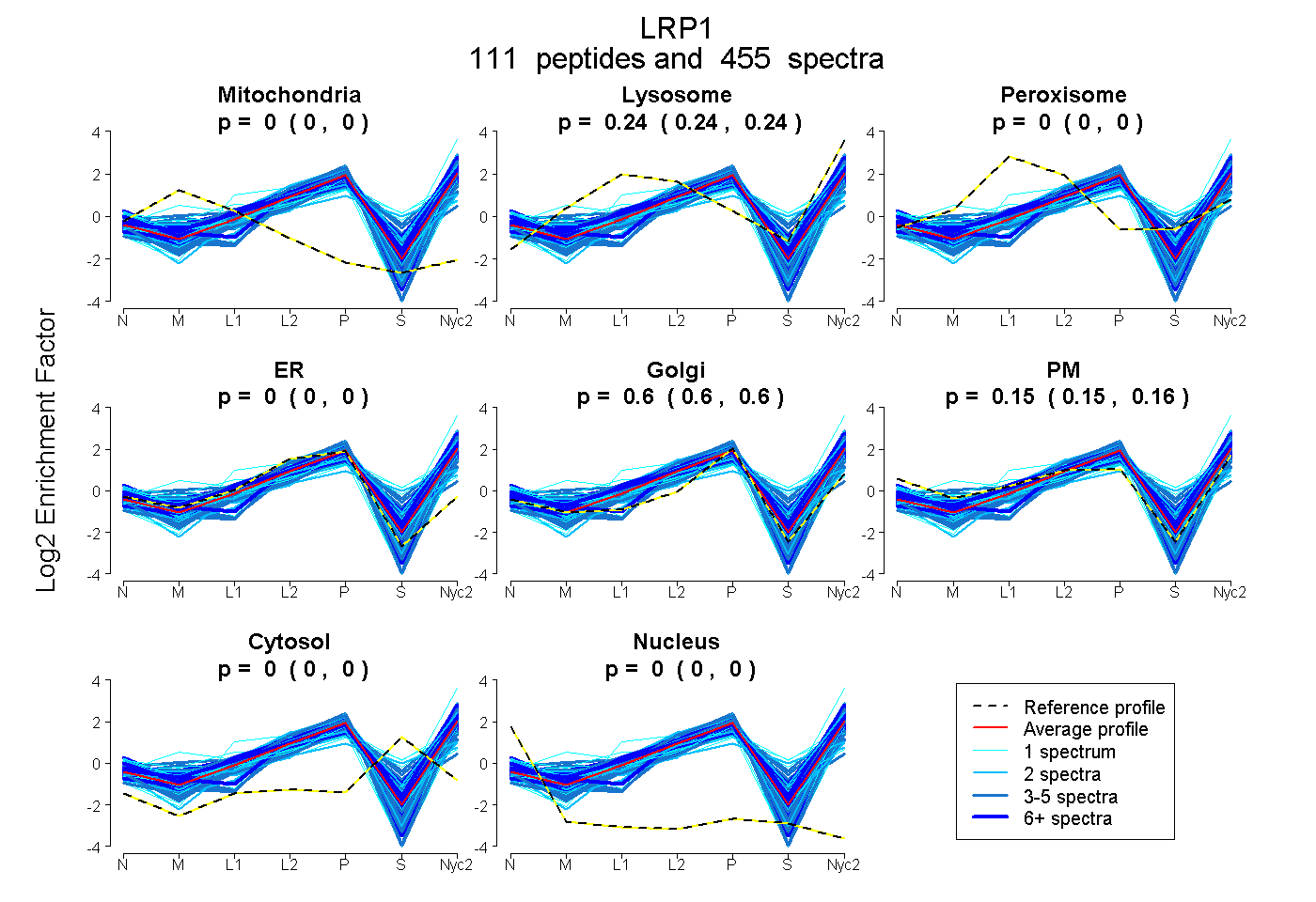
0.000 | 0.000
0.242 | 0.244
0.000 | 0.000
0.000 | 0.000
0.602 | 0.604
0.152 | 0.155
0.000 | 0.000
0.000 | 0.000
peptides
spectra
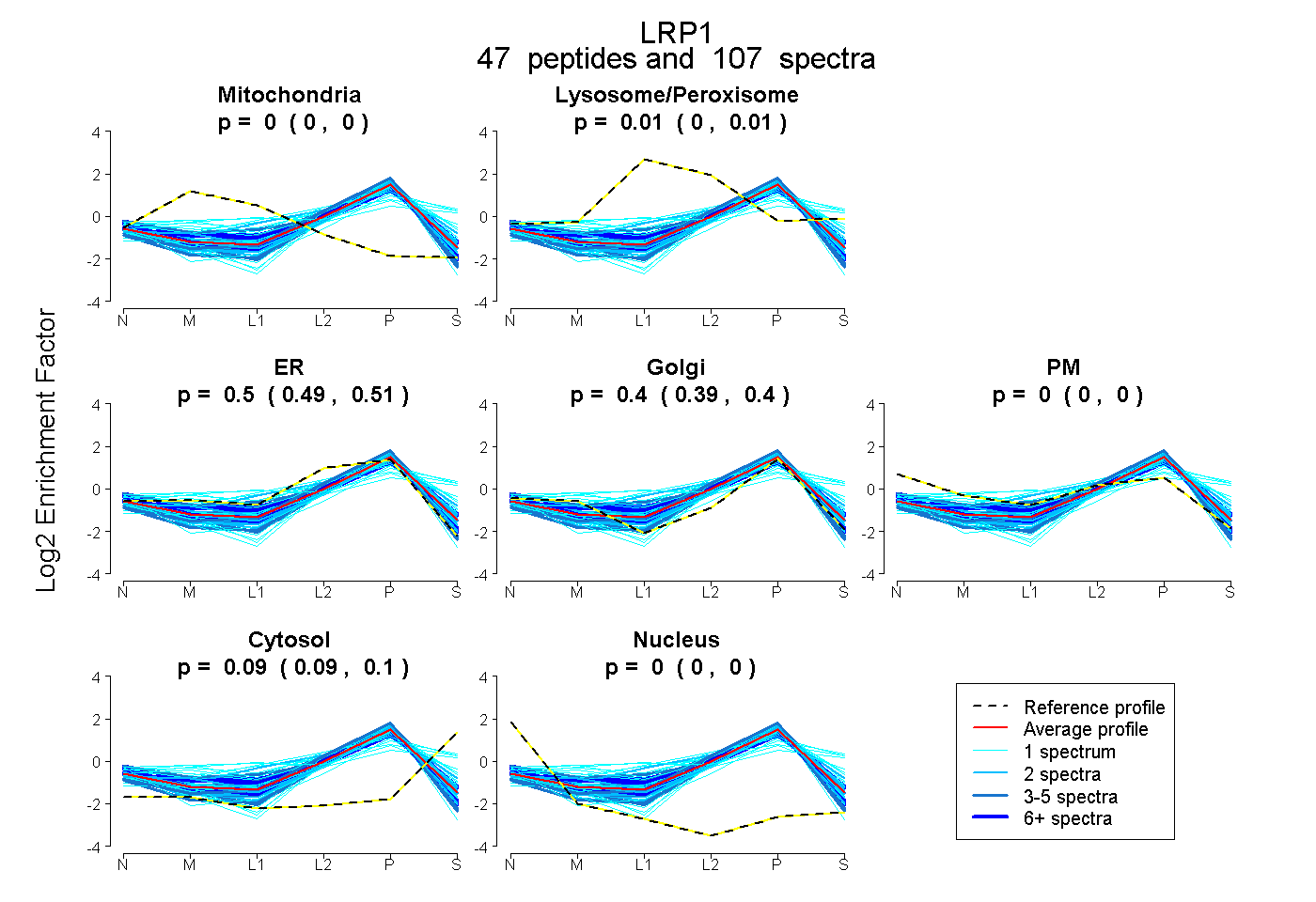
0.000 | 0.000
0.004 | 0.012
0.491 | 0.509
0.391 | 0.405
0.000 | 0.000
0.090 | 0.095
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
455 spectra |
 |
0.000 0.000 | 0.000 |
0.243 0.242 | 0.244 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.603 0.602 | 0.604 |
0.154 0.152 | 0.155 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
107 spectra |
 |
0.000 0.000 | 0.000 |
0.008 0.004 | 0.012 |
0.501 0.491 | 0.509 |
0.398 0.391 | 0.405 |
0.000 0.000 | 0.000 |
0.093 0.090 | 0.095 |
0.000 0.000 | 0.000 |
| 1 spectrum, SGFSLGSDGK | 0.000 | 0.000 | 0.149 | 0.851 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, NVIALAFDYR | 0.000 | 0.000 | 0.431 | 0.339 | 0.000 | 0.231 | 0.000 | |||
| 2 spectra, ILQEDFTCR | 0.000 | 0.000 | 0.327 | 0.655 | 0.000 | 0.019 | 0.000 | |||
| 1 spectrum, VFFTDYGQIPK | 0.000 | 0.000 | 0.327 | 0.442 | 0.000 | 0.231 | 0.000 | |||
| 1 spectrum, CININWR | 0.000 | 0.255 | 0.000 | 0.717 | 0.000 | 0.027 | 0.000 | |||
| 2 spectra, CPTGFTGPR | 0.000 | 0.000 | 0.394 | 0.575 | 0.000 | 0.032 | 0.000 | |||
| 5 spectra, AGTSPGTPNR | 0.000 | 0.000 | 0.275 | 0.725 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LWWADQVSEK | 0.000 | 0.033 | 0.585 | 0.268 | 0.000 | 0.114 | 0.000 | |||
| 3 spectra, GRPGIIR | 0.000 | 0.062 | 0.553 | 0.319 | 0.000 | 0.066 | 0.000 | |||
| 6 spectra, SDAIYSAR | 0.000 | 0.000 | 0.456 | 0.520 | 0.000 | 0.017 | 0.006 | |||
| 1 spectrum, TTIVENVGSVEGLAYHR | 0.000 | 0.280 | 0.165 | 0.549 | 0.000 | 0.005 | 0.000 | |||
| 1 spectrum, SIIVDTK | 0.000 | 0.148 | 0.302 | 0.550 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LYWCDAR | 0.000 | 0.068 | 0.300 | 0.554 | 0.000 | 0.077 | 0.000 | |||
| 2 spectra, GVLFQPCER | 0.000 | 0.000 | 0.259 | 0.733 | 0.000 | 0.007 | 0.000 | |||
| 2 spectra, CLPGFLGDR | 0.000 | 0.020 | 0.526 | 0.405 | 0.000 | 0.049 | 0.000 | |||
| 1 spectrum, TLLFSGQK | 0.000 | 0.141 | 0.238 | 0.447 | 0.000 | 0.174 | 0.000 | |||
| 2 spectra, TTLLAGDIEHPR | 0.000 | 0.024 | 0.441 | 0.478 | 0.000 | 0.057 | 0.000 | |||
| 3 spectra, IFVCNR | 0.000 | 0.000 | 0.304 | 0.609 | 0.000 | 0.087 | 0.000 | |||
| 1 spectrum, ADGSGSVVLR | 0.000 | 0.014 | 0.236 | 0.352 | 0.000 | 0.398 | 0.000 | |||
| 2 spectra, GPVGLAIDFPESK | 0.000 | 0.058 | 0.448 | 0.465 | 0.000 | 0.029 | 0.000 | |||
| 1 spectrum, LSVIGSIR | 0.000 | 0.000 | 0.207 | 0.793 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, IVFPHGITLDLVSR | 0.000 | 0.000 | 0.489 | 0.511 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SLDPFKPFIIFSNR | 0.000 | 0.160 | 0.169 | 0.318 | 0.000 | 0.353 | 0.000 | |||
| 2 spectra, VCLWIGR | 0.000 | 0.000 | 0.363 | 0.631 | 0.000 | 0.006 | 0.000 | |||
| 6 spectra, FLLYAR | 0.000 | 0.000 | 0.514 | 0.483 | 0.000 | 0.003 | 0.000 | |||
| 2 spectra, CLSSSLR | 0.000 | 0.014 | 0.447 | 0.476 | 0.000 | 0.063 | 0.000 | |||
| 1 spectrum, DVIEVAQMK | 0.000 | 0.234 | 0.301 | 0.465 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, YVVISQGLDKPR | 0.000 | 0.404 | 0.000 | 0.488 | 0.000 | 0.107 | 0.000 | |||
| 2 spectra, QPEVTNPCDR | 0.000 | 0.000 | 0.430 | 0.560 | 0.000 | 0.000 | 0.010 | |||
| 1 spectrum, QINVAR | 0.027 | 0.117 | 0.496 | 0.345 | 0.015 | 0.000 | 0.000 | |||
| 1 spectrum, NAVVQGLEQPHGLVVHPLR | 0.000 | 0.415 | 0.000 | 0.351 | 0.000 | 0.234 | 0.000 | |||
| 5 spectra, HTVDQTRPGAFER | 0.000 | 0.238 | 0.113 | 0.647 | 0.003 | 0.000 | 0.000 | |||
| 1 spectrum, IFFSDIHFGNIQQINDDGSGR | 0.000 | 0.000 | 0.311 | 0.689 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TLISGMIDEPHAIVVDPLR | 0.000 | 0.000 | 0.306 | 0.662 | 0.000 | 0.032 | 0.000 | |||
| 6 spectra, AITVHPEK | 0.000 | 0.257 | 0.000 | 0.735 | 0.000 | 0.009 | 0.000 | |||
| 1 spectrum, AVTDEEPFLIFANR | 0.000 | 0.334 | 0.107 | 0.316 | 0.000 | 0.242 | 0.000 | |||
| 2 spectra, QPDVPNHPCK | 0.000 | 0.279 | 0.227 | 0.494 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TACGVGEFR | 0.000 | 0.000 | 0.479 | 0.519 | 0.000 | 0.001 | 0.000 | |||
| 4 spectra, ILWIDAR | 0.000 | 0.000 | 0.499 | 0.501 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, TVLVSSGLR | 0.000 | 0.000 | 0.592 | 0.408 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IDAMDVHVK | 0.000 | 0.037 | 0.476 | 0.323 | 0.000 | 0.164 | 0.000 | |||
| 2 spectra, IETAAMDGTLR | 0.000 | 0.000 | 0.430 | 0.453 | 0.000 | 0.117 | 0.000 | |||
| 1 spectrum, SGQQACEGVGSFLLYSVHEGIR | 0.000 | 0.418 | 0.000 | 0.551 | 0.000 | 0.030 | 0.000 | |||
| 6 spectra, SERPPIFEIR | 0.000 | 0.084 | 0.385 | 0.531 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, FQCPPNRPFR | 0.000 | 0.054 | 0.348 | 0.498 | 0.000 | 0.100 | 0.000 | |||
| 2 spectra, IDLETGENR | 0.000 | 0.000 | 0.414 | 0.479 | 0.000 | 0.107 | 0.000 | |||
| 2 spectra, LDGLCIPLR | 0.000 | 0.000 | 0.468 | 0.513 | 0.000 | 0.019 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
735 spectra |
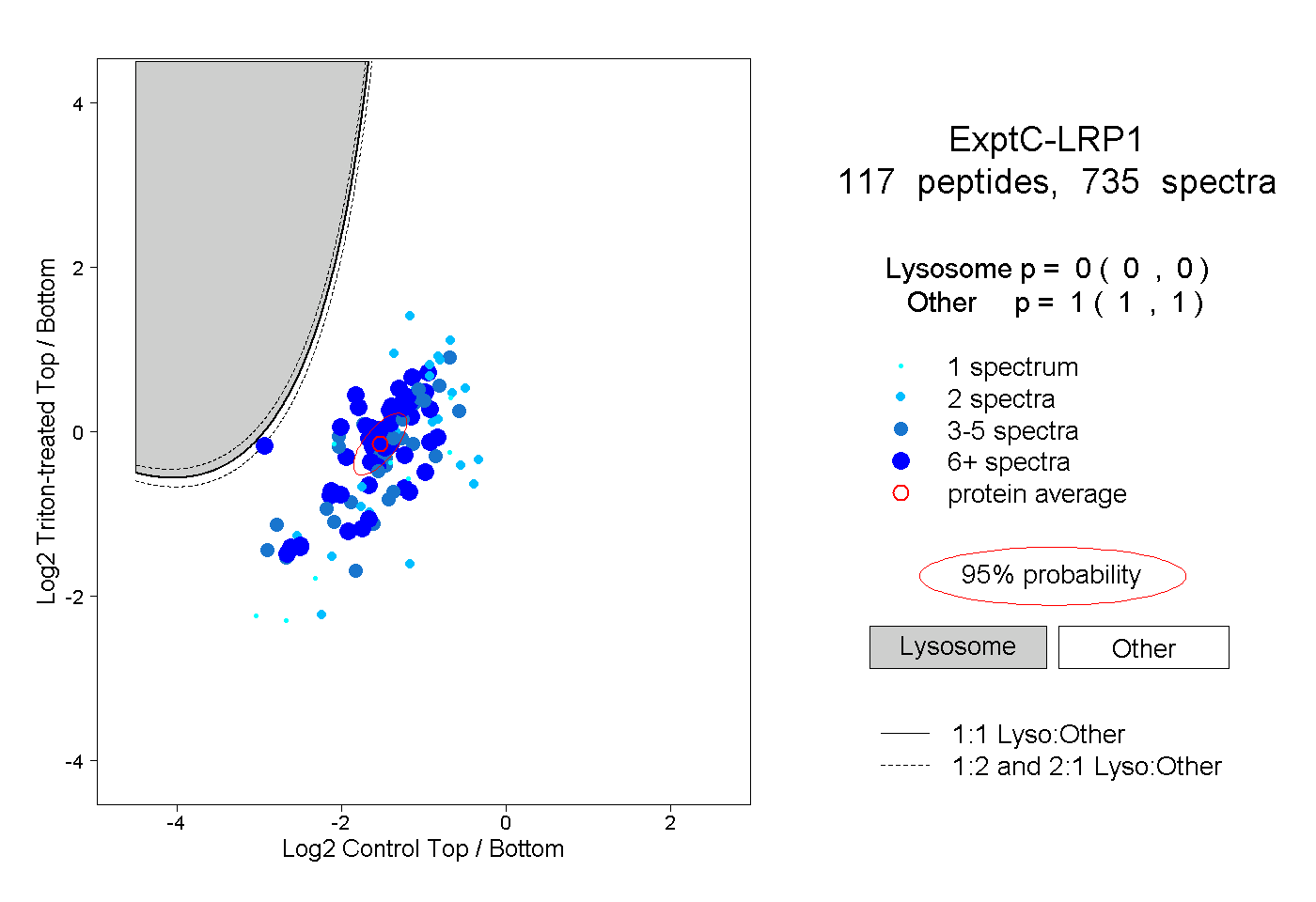 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
69 spectra |
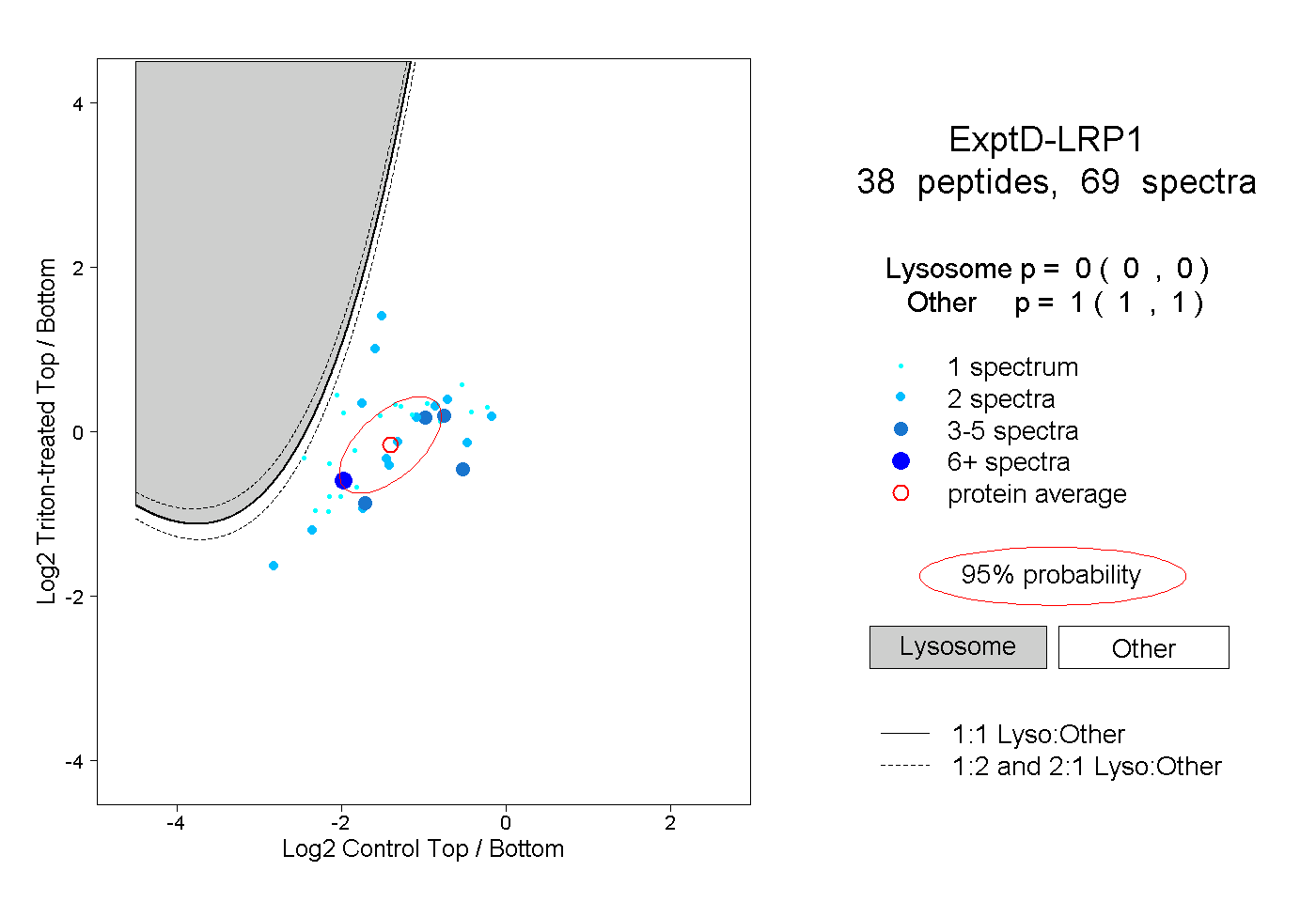 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |