peptides
spectra
0.002 | 0.007
0.014 | 0.018
0.000 | 0.000
0.000 | 0.000
0.000 | 0.002
0.000 | 0.000
0.976 | 0.980
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.000 | 0.016
0.000 | 0.008
0.000 | 0.028
0.000 | 0.000
0.965 | 0.984
0.000 | 0.008
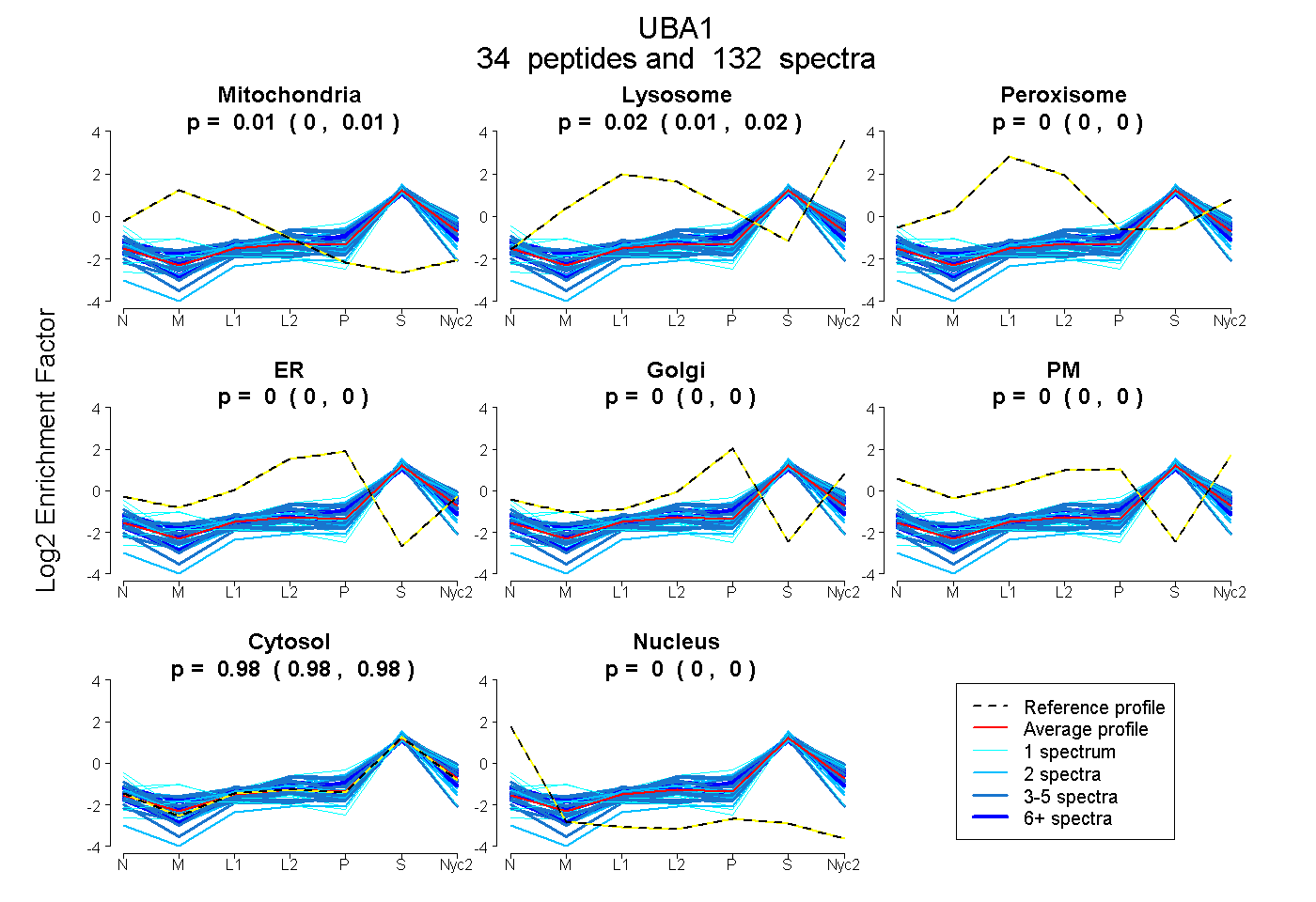
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
132 spectra |
 |
0.005 0.002 | 0.007 |
0.017 0.014 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.000 |
0.978 0.976 | 0.980 |
0.000 0.000 | 0.000 |
||
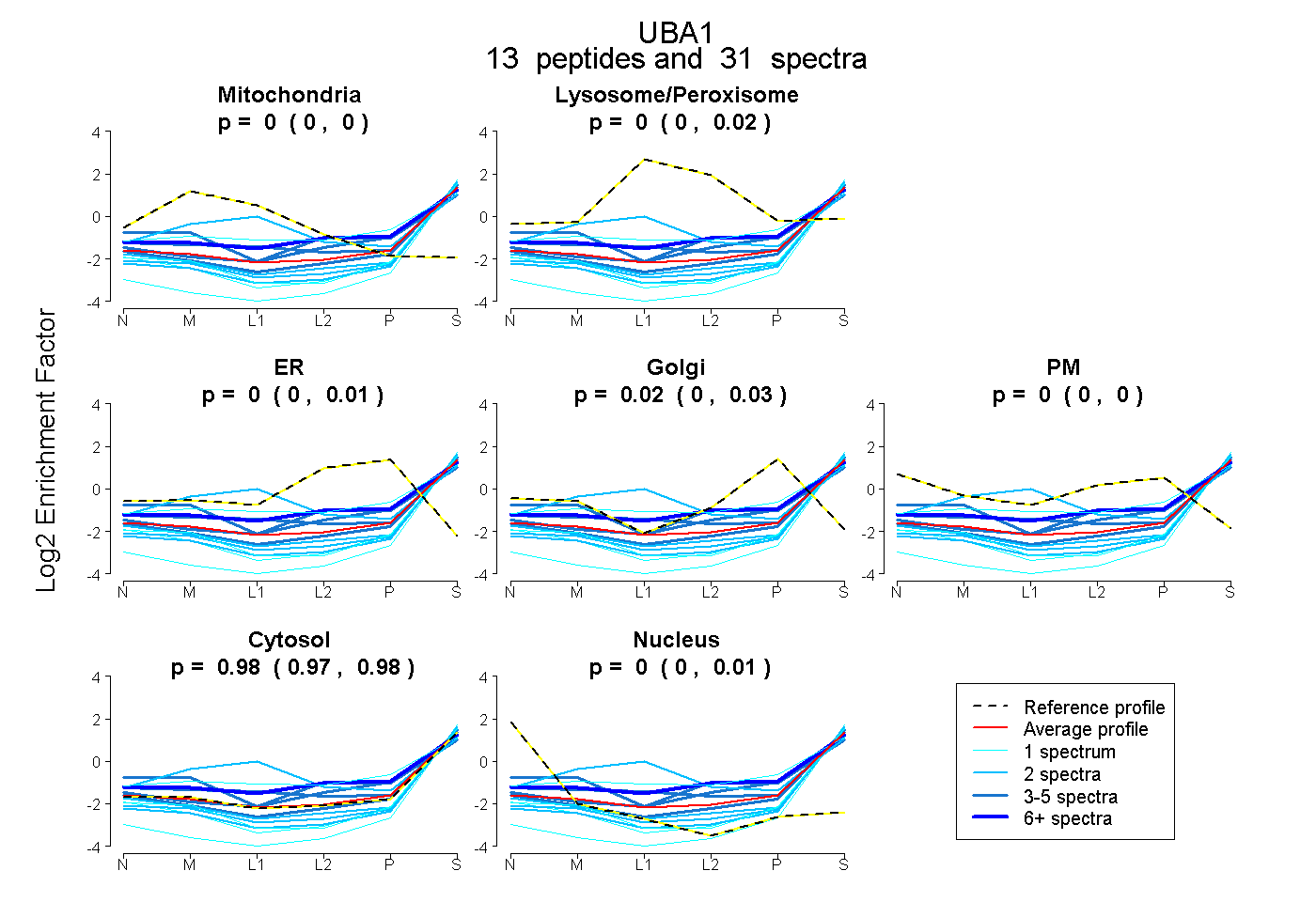
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
31 spectra |
 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.016 |
0.000 0.000 | 0.008 |
0.020 0.000 | 0.028 |
0.000 0.000 | 0.000 |
0.976 0.965 | 0.984 |
0.000 0.000 | 0.008 |
| 2 spectra, SDTAAAAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, QMNPYIQVTSHQNR | 0.149 | 0.277 | 0.000 | 0.000 | 0.000 | 0.574 | 0.000 | |||
| 2 spectra, LDQPMTEIVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.984 | 0.016 | |||
| 4 spectra, AEVSQPR | 0.000 | 0.000 | 0.132 | 0.000 | 0.000 | 0.868 | 0.000 | |||
| 3 spectra, DNPGVVTCLDEAR | 0.000 | 0.023 | 0.000 | 0.000 | 0.272 | 0.705 | 0.000 | |||
| 1 spectrum, VVQGHQQLDSYK | 0.000 | 0.227 | 0.000 | 0.122 | 0.000 | 0.651 | 0.000 | |||
| 1 spectrum, VGPDTER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.975 | 0.025 | |||
| 3 spectra, AENYDISPADR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.990 | 0.010 | |||
| 1 spectrum, LVVADTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.967 | 0.033 | |||
| 6 spectra, VGEFCHSR | 0.000 | 0.184 | 0.000 | 0.090 | 0.000 | 0.726 | 0.000 | |||
| 3 spectra, LAGTQPLEVLEAVQR | 0.000 | 0.145 | 0.000 | 0.000 | 0.000 | 0.841 | 0.013 | |||
| 2 spectra, QFLFRPWDVTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, DEFEGLFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
136 spectra |
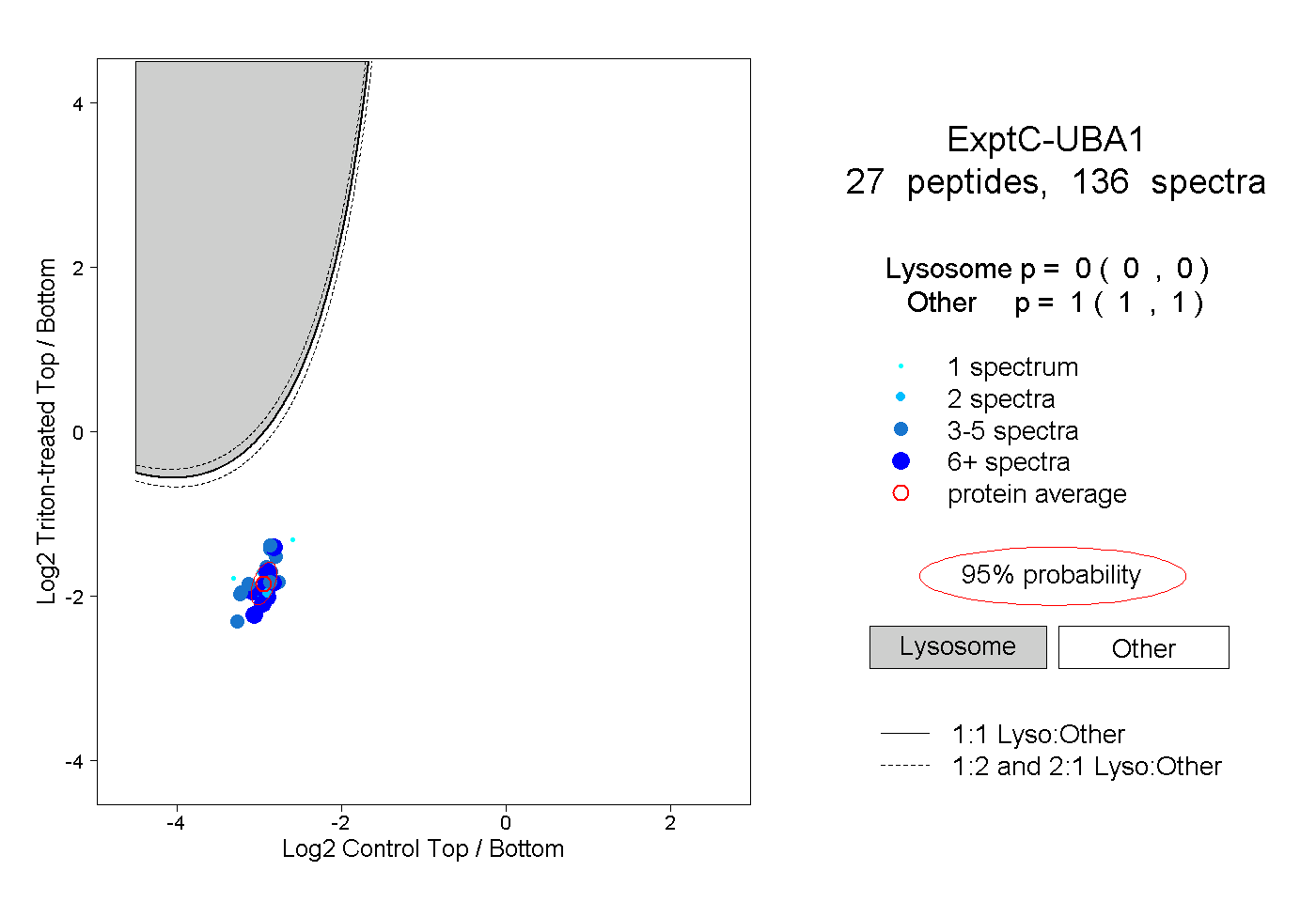 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
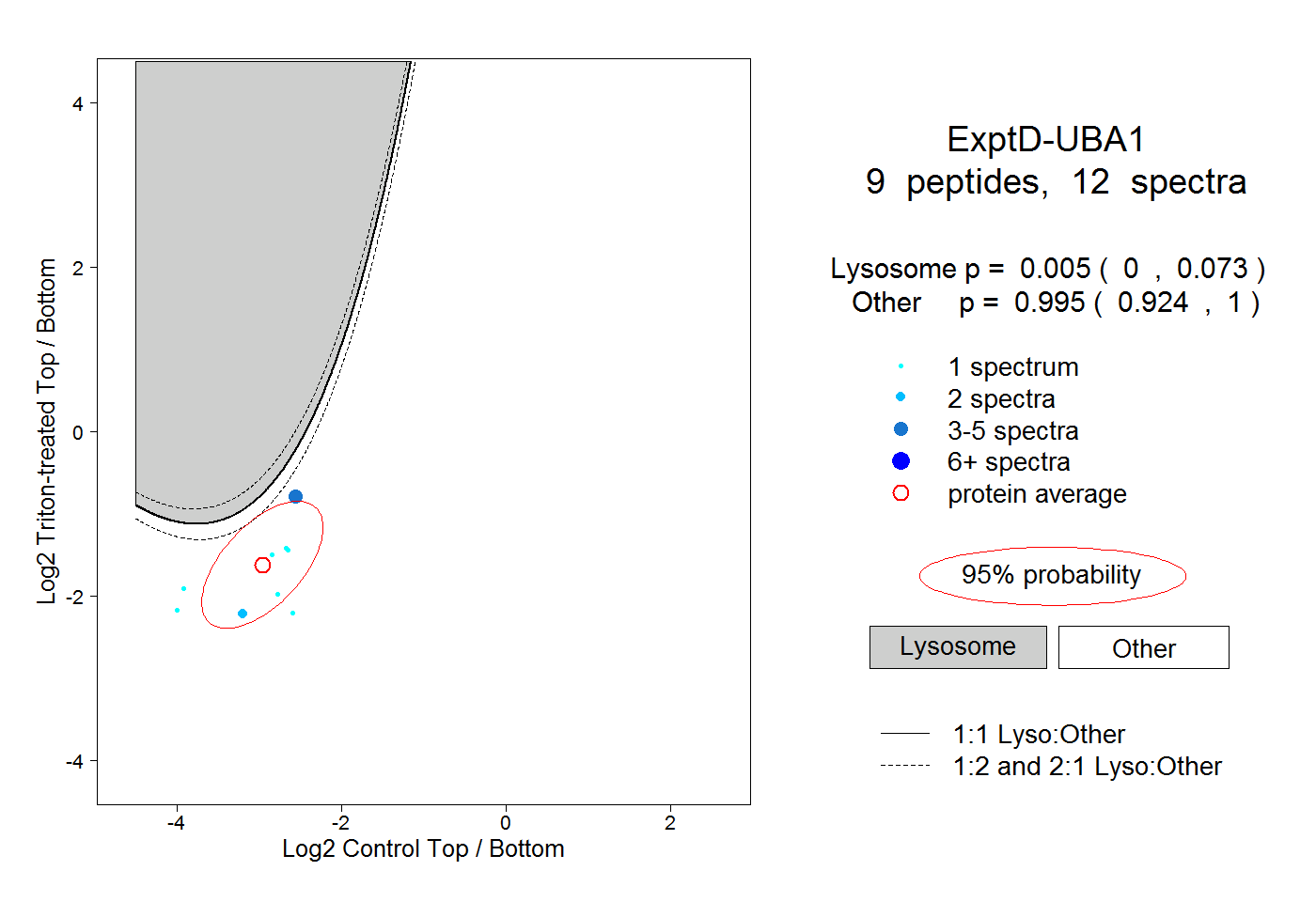 |
0.005 0.000 | 0.073 |
0.995 0.924 | 1.000 |