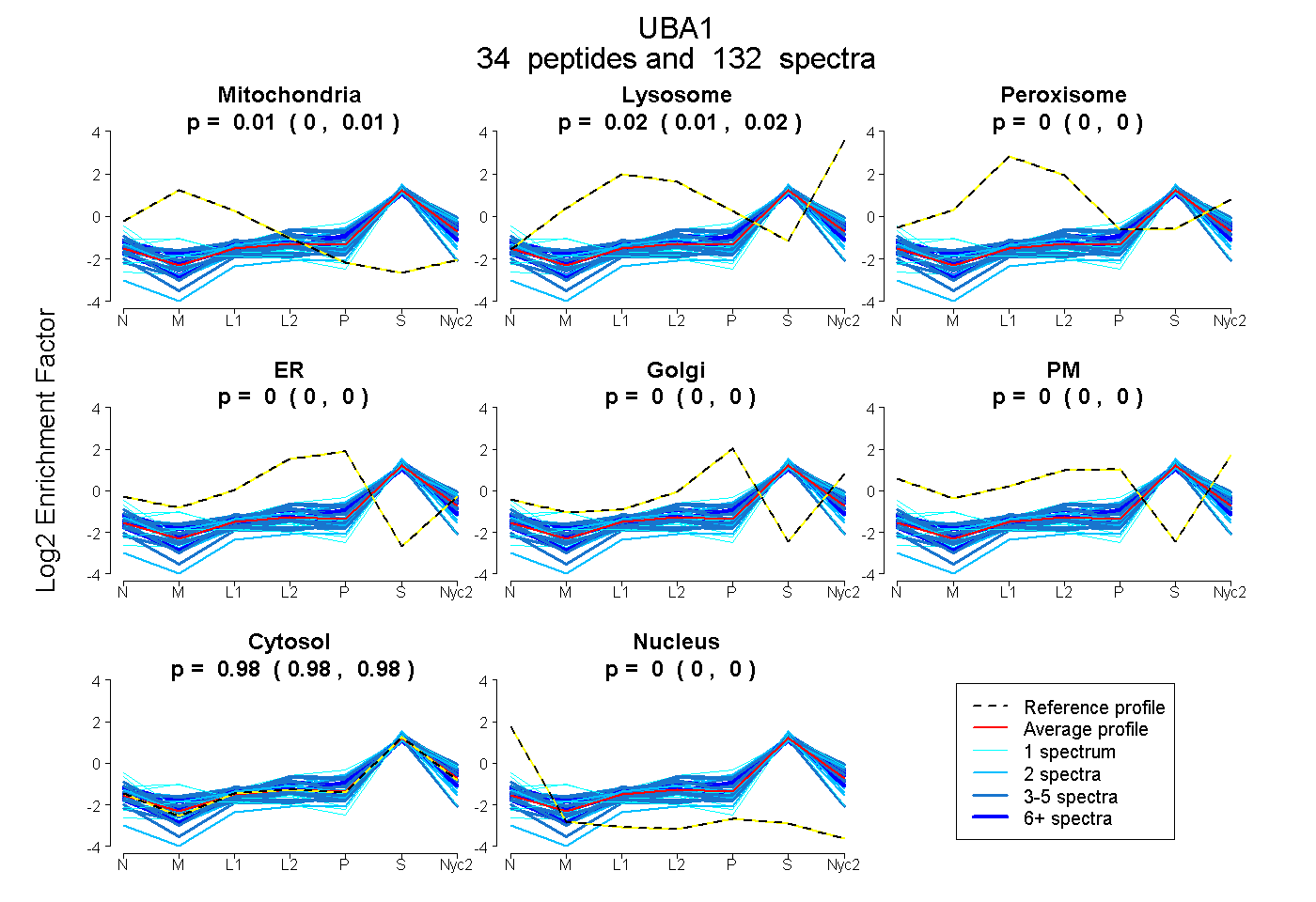
peptides
spectra
0.002 | 0.007
0.014 | 0.018
0.000 | 0.000
0.000 | 0.000
0.000 | 0.002
0.000 | 0.000
0.976 | 0.980
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
132 spectra |
 |
0.005 0.002 | 0.007 |
0.017 0.014 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.000 |
0.978 0.976 | 0.980 |
0.000 0.000 | 0.000 |
| 5 spectra, SDTAAAAVR | 0.000 | 0.003 | 0.000 | 0.136 | 0.000 | 0.000 | 0.861 | 0.000 | ||
| 1 spectrum, FEVQGLQPNGEEMTLK | 0.167 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.833 | 0.000 | ||
| 11 spectra, QMNPYIQVTSHQNR | 0.000 | 0.030 | 0.000 | 0.000 | 0.065 | 0.000 | 0.905 | 0.000 | ||
| 6 spectra, QFLDYFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, AVTLHDQGTTQWADLSSQFYLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 7 spectra, DNPGVVTCLDEAR | 0.059 | 0.000 | 0.027 | 0.057 | 0.000 | 0.000 | 0.857 | 0.000 | ||
| 4 spectra, VVQGHQQLDSYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.927 | 0.073 | ||
| 5 spectra, VGPDTER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 5 spectra, AENYDISPADR | 0.000 | 0.029 | 0.000 | 0.000 | 0.113 | 0.000 | 0.859 | 0.000 | ||
| 5 spectra, MLQTSSVLVSGLR | 0.000 | 0.151 | 0.000 | 0.000 | 0.000 | 0.000 | 0.849 | 0.000 | ||
| 2 spectra, GGIVSQVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 9 spectra, QLYVLGHEAMK | 0.013 | 0.000 | 0.000 | 0.018 | 0.011 | 0.000 | 0.958 | 0.000 | ||
| 1 spectrum, LVVADTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, ATLPSPDK | 0.000 | 0.046 | 0.038 | 0.000 | 0.110 | 0.000 | 0.806 | 0.000 | ||
| 3 spectra, SLPASLAEPDFVMTDFAK | 0.000 | 0.003 | 0.000 | 0.000 | 0.000 | 0.000 | 0.997 | 0.000 | ||
| 1 spectrum, MYMDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.064 | 0.862 | 0.074 | ||
| 3 spectra, QPAENVNQYLTDSK | 0.000 | 0.000 | 0.004 | 0.000 | 0.000 | 0.076 | 0.915 | 0.005 | ||
| 15 spectra, DEFEGLFK | 0.046 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.938 | 0.016 | ||
| 1 spectrum, QLLHNFPPDQLTSSGAPFWSGPK | 0.164 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.836 | 0.000 | ||
| 2 spectra, YDGQVAVFGSDLQEK | 0.000 | 0.080 | 0.000 | 0.000 | 0.000 | 0.000 | 0.913 | 0.007 | ||
| 8 spectra, LDQPMTEIVSR | 0.039 | 0.058 | 0.000 | 0.000 | 0.000 | 0.000 | 0.903 | 0.000 | ||
| 7 spectra, AEVSQPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, EEDIGK | 0.000 | 0.000 | 0.000 | 0.166 | 0.000 | 0.000 | 0.834 | 0.000 | ||
| 1 spectrum, NEEDATELVTLAQAVNAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, GLGVEIAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, YFLVGAGAIGCELLK | 0.036 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.901 | 0.063 | ||
| 3 spectra, VGEFCHSR | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.881 | 0.033 | ||
| 3 spectra, NIILGGVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 5 spectra, NFPNAIEHTLQWAR | 0.000 | 0.124 | 0.000 | 0.000 | 0.065 | 0.000 | 0.811 | 0.000 | ||
| 4 spectra, EALTEDK | 0.000 | 0.002 | 0.000 | 0.000 | 0.000 | 0.000 | 0.998 | 0.000 | ||
| 2 spectra, SPPAVQQDNVDEDLIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, SIPICTLK | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.913 | 0.000 | ||
| 1 spectrum, QFLFRPWDVTK | 0.000 | 0.030 | 0.000 | 0.000 | 0.000 | 0.000 | 0.970 | 0.000 | ||
| 2 spectra, HQYYNQEWTLWDR | 0.000 | 0.000 | 0.000 | 0.039 | 0.007 | 0.000 | 0.955 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
31 spectra |
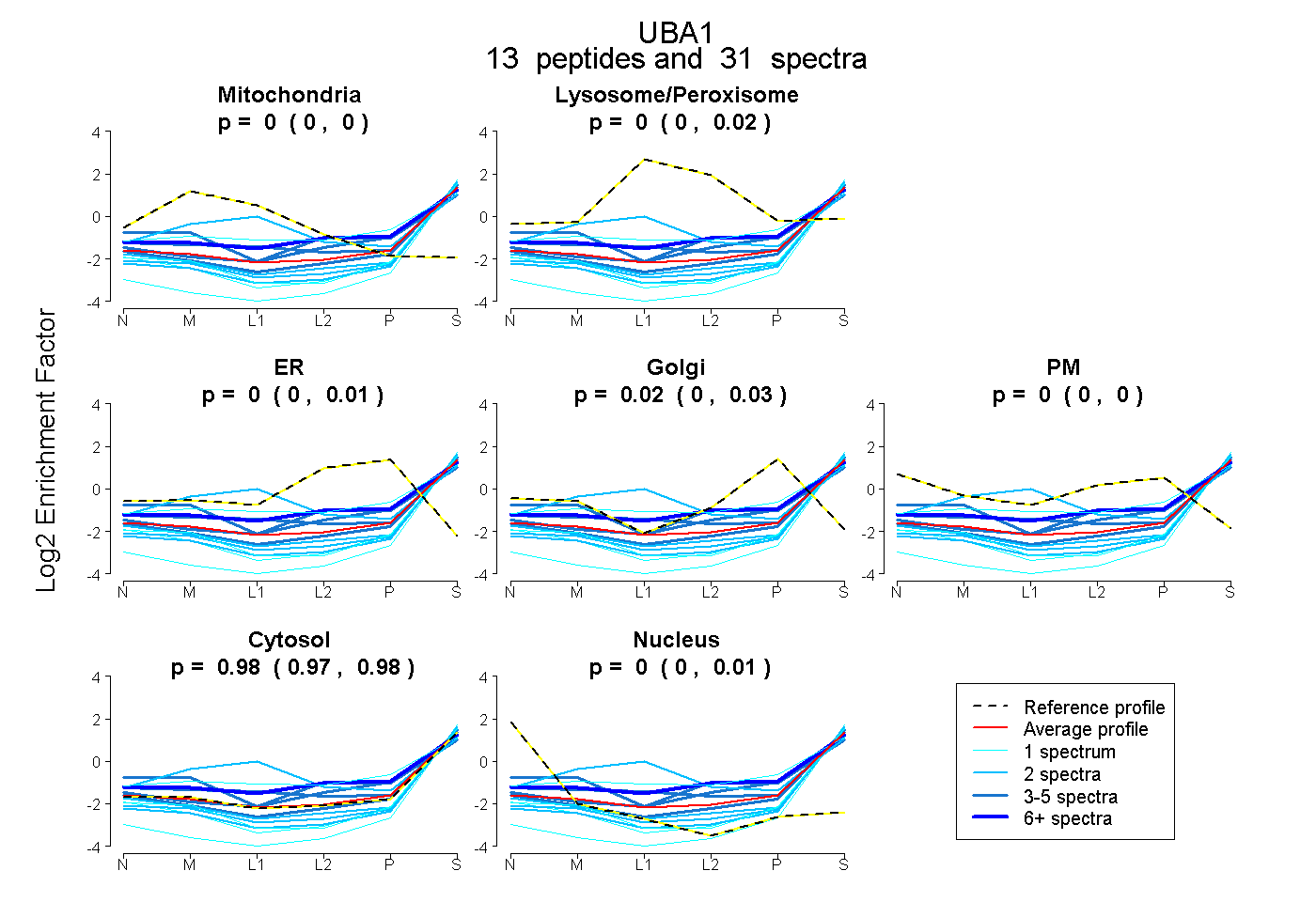 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.016 |
0.000 0.000 | 0.008 |
0.020 0.000 | 0.028 |
0.000 0.000 | 0.000 |
0.976 0.965 | 0.984 |
0.000 0.000 | 0.008 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
136 spectra |
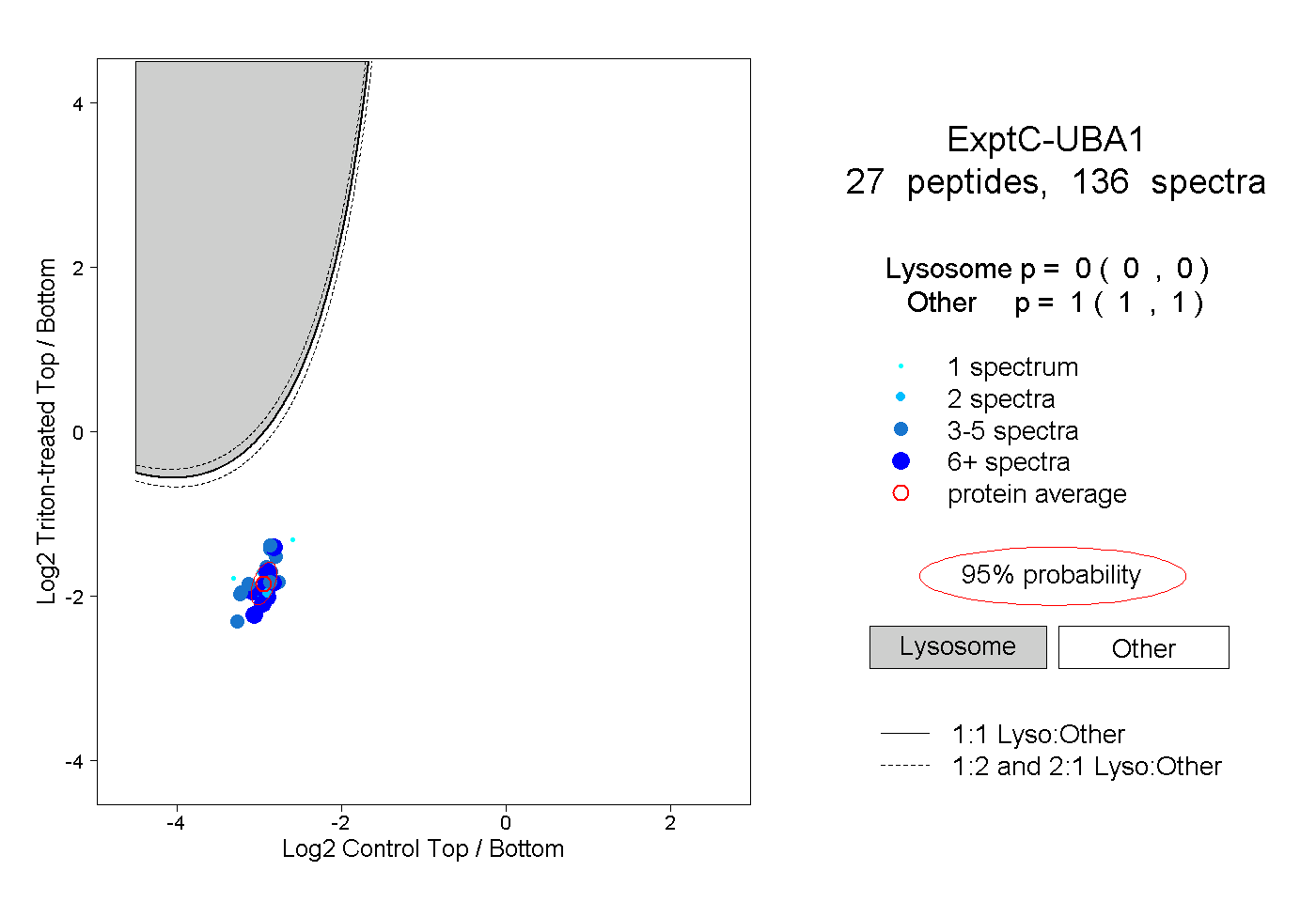 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
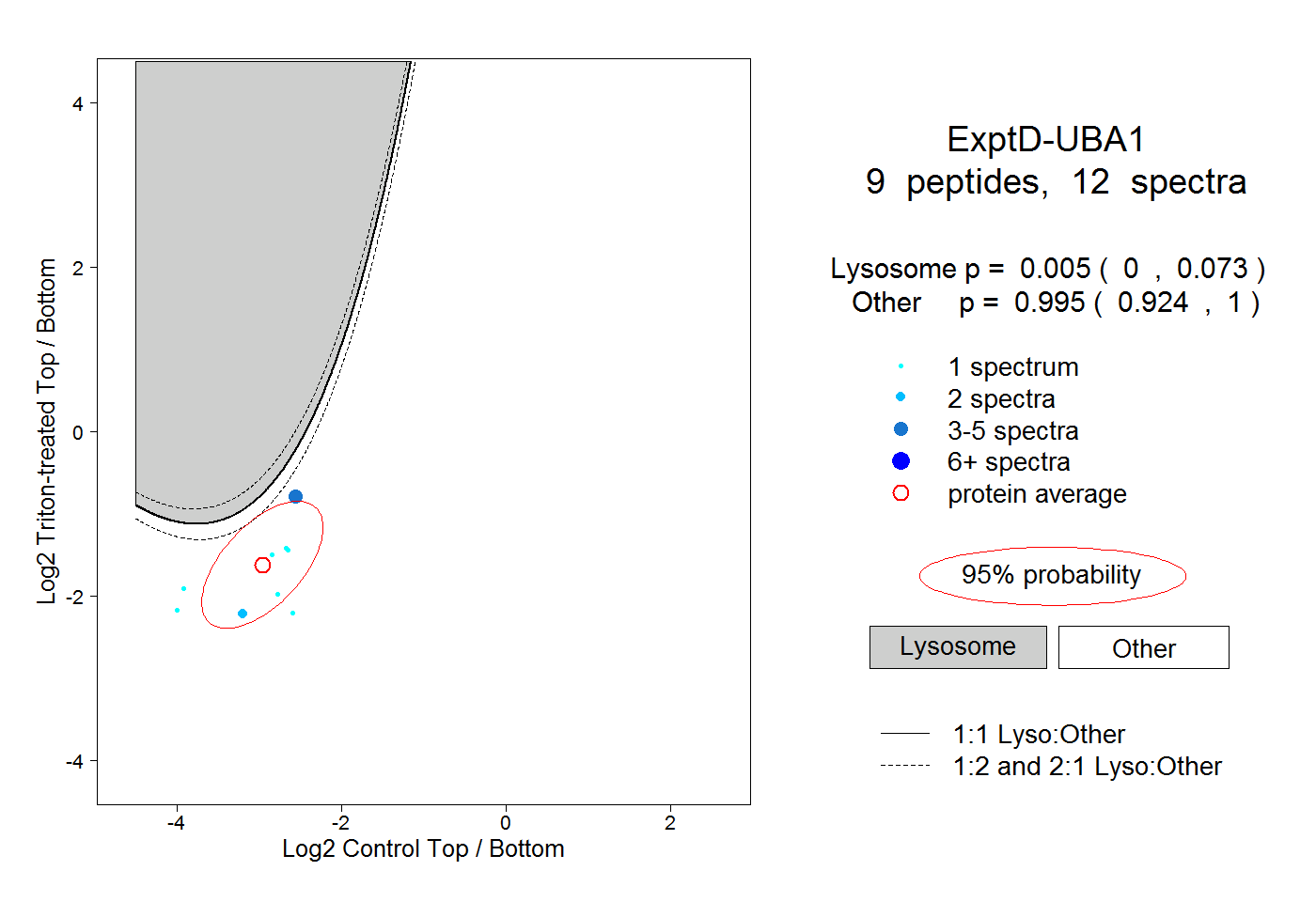 |
0.005 0.000 | 0.073 |
0.995 0.924 | 1.000 |