peptides
spectra
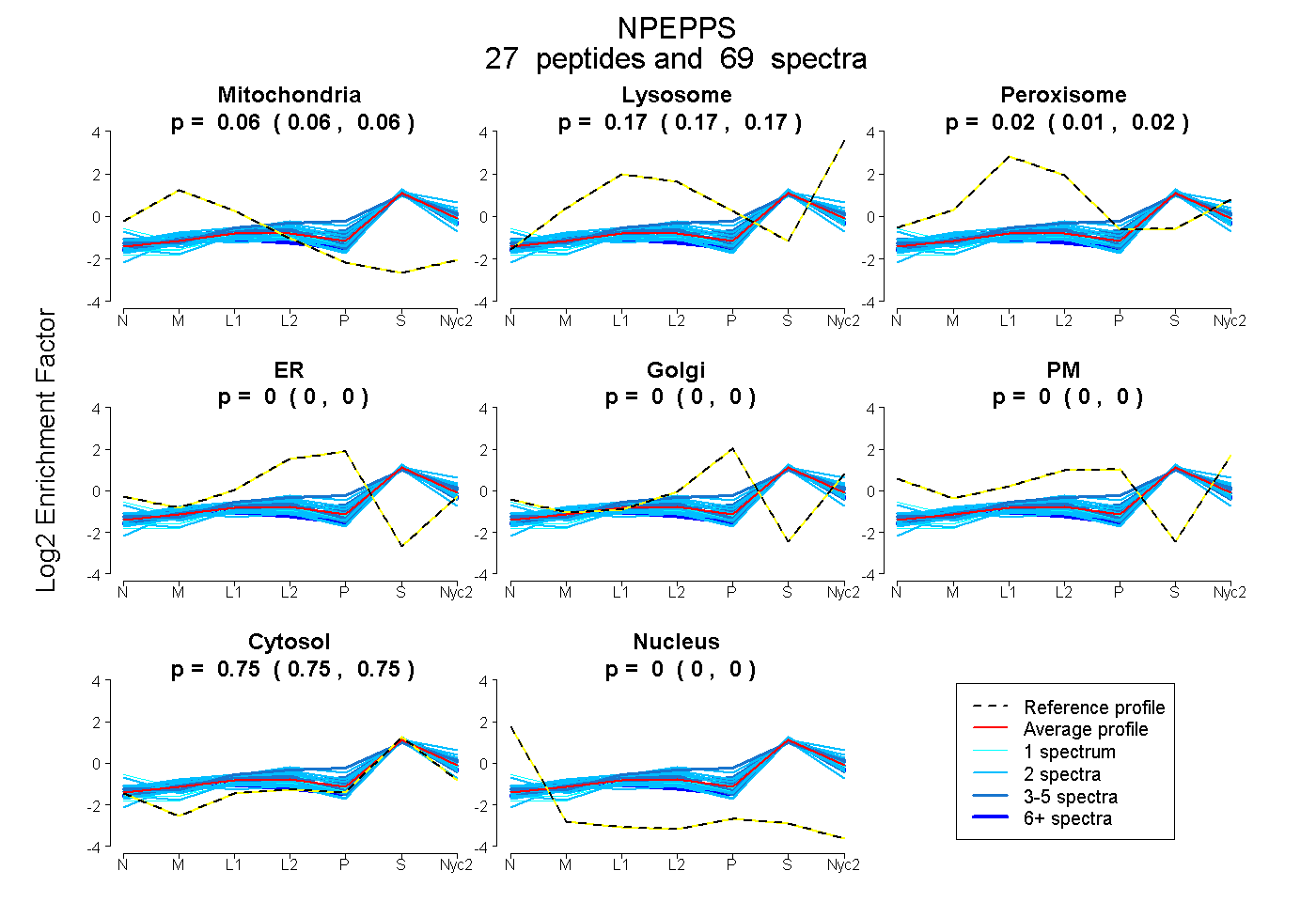
0.058 | 0.061
0.167 | 0.174
0.013 | 0.021
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.751 | 0.754
0.000 | 0.000
peptides
spectra
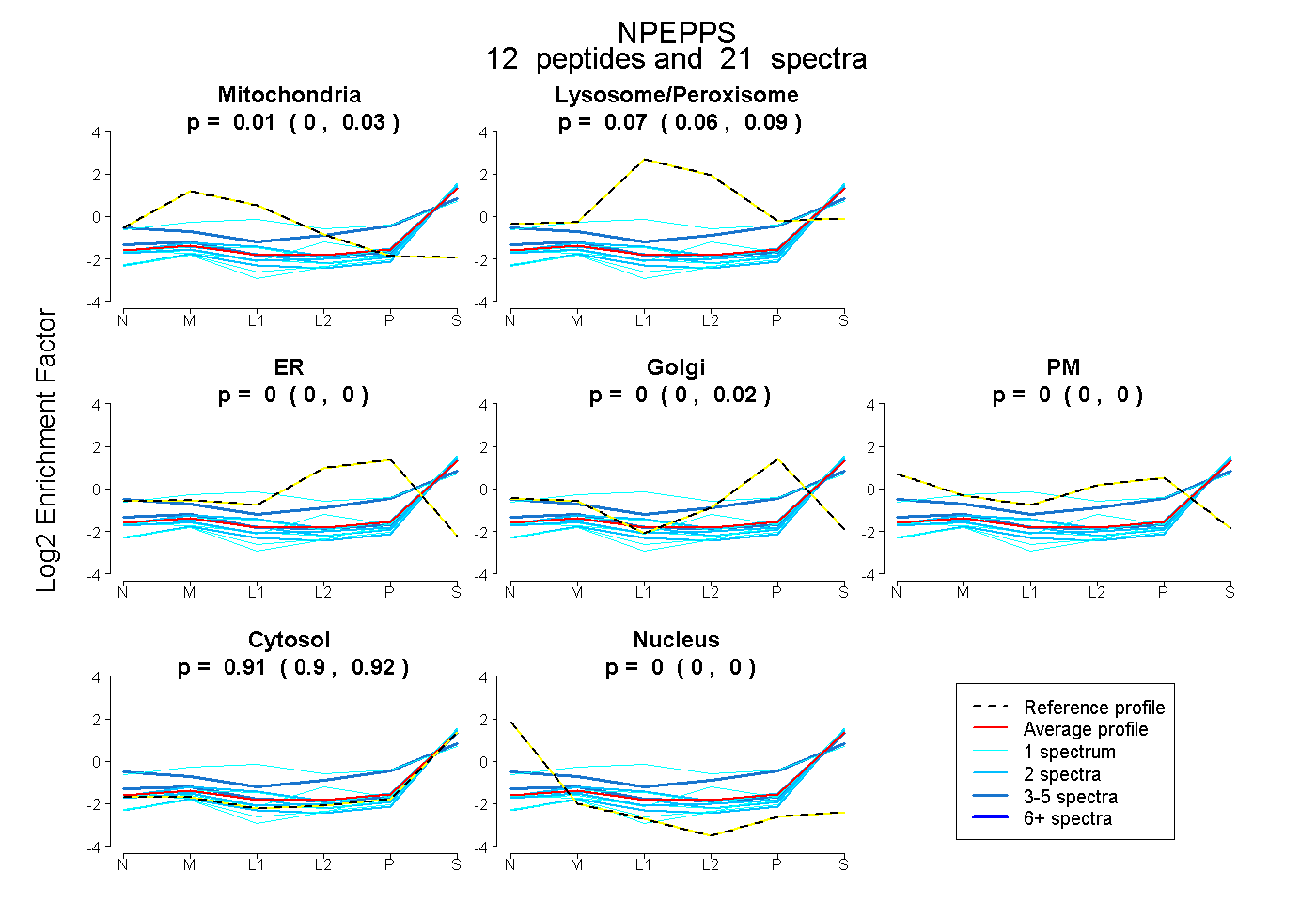
0.000 | 0.025
0.057 | 0.086
0.000 | 0.000
0.000 | 0.018
0.000 | 0.000
0.898 | 0.920
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
69 spectra |
 |
0.060 0.058 | 0.061 |
0.171 0.167 | 0.174 |
0.017 0.013 | 0.021 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.752 0.751 | 0.754 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
 |
0.013 0.000 | 0.025 |
0.072 0.057 | 0.086 |
0.000 0.000 | 0.000 |
0.003 0.000 | 0.018 |
0.000 0.000 | 0.000 |
0.912 0.898 | 0.920 |
0.000 0.000 | 0.000 |
| 1 spectrum, VALSNMNVIDR | 0.001 | 0.097 | 0.000 | 0.000 | 0.000 | 0.902 | 0.000 | |||
| 3 spectra, LGLQNDLFSLAR | 0.063 | 0.050 | 0.000 | 0.000 | 0.000 | 0.887 | 0.000 | |||
| 2 spectra, DVFSPIGER | 0.049 | 0.009 | 0.000 | 0.000 | 0.000 | 0.941 | 0.000 | |||
| 2 spectra, LGWDPKPGEGHLDALLR | 0.023 | 0.110 | 0.000 | 0.000 | 0.000 | 0.867 | 0.000 | |||
| 2 spectra, IDFVGELNDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, DADSIHQYLLQR | 0.049 | 0.377 | 0.000 | 0.126 | 0.020 | 0.428 | 0.000 | |||
| 1 spectrum, YAAVTQFEATDAR | 0.000 | 0.078 | 0.008 | 0.000 | 0.000 | 0.914 | 0.000 | |||
| 4 spectra, AFFESHPAPSAER | 0.000 | 0.160 | 0.000 | 0.045 | 0.235 | 0.560 | 0.000 | |||
| 1 spectrum, LSVEGFAVDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, YTTPAGEVR | 0.000 | 0.019 | 0.000 | 0.000 | 0.000 | 0.981 | 0.000 | |||
| 1 spectrum, YQGGFLISR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VLGATLSPELIQK | 0.000 | 0.003 | 0.000 | 0.000 | 0.000 | 0.994 | 0.003 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
98 spectra |
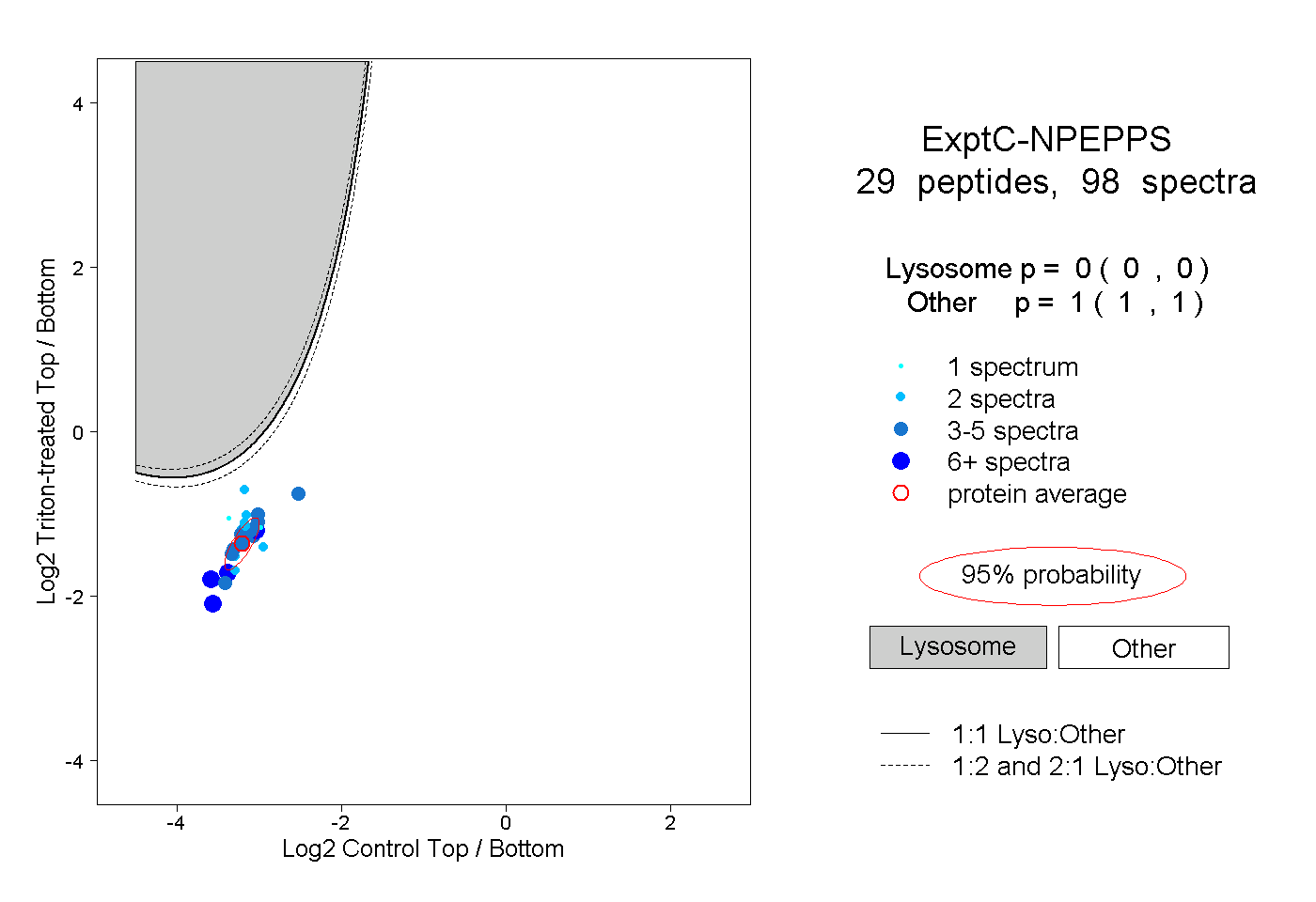 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
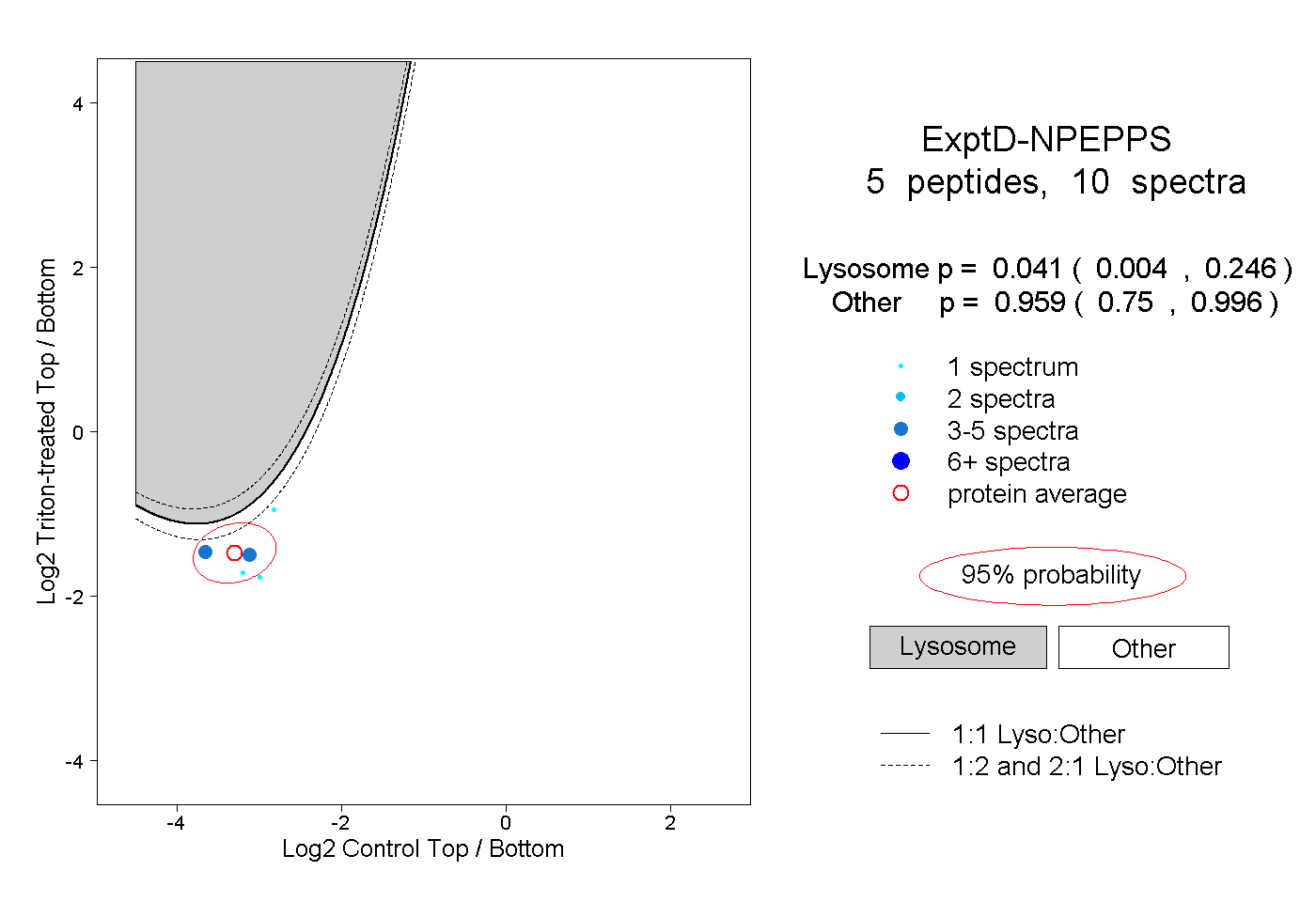 |
0.041 0.004 | 0.246 |
0.959 0.750 | 0.996 |