peptides
spectra
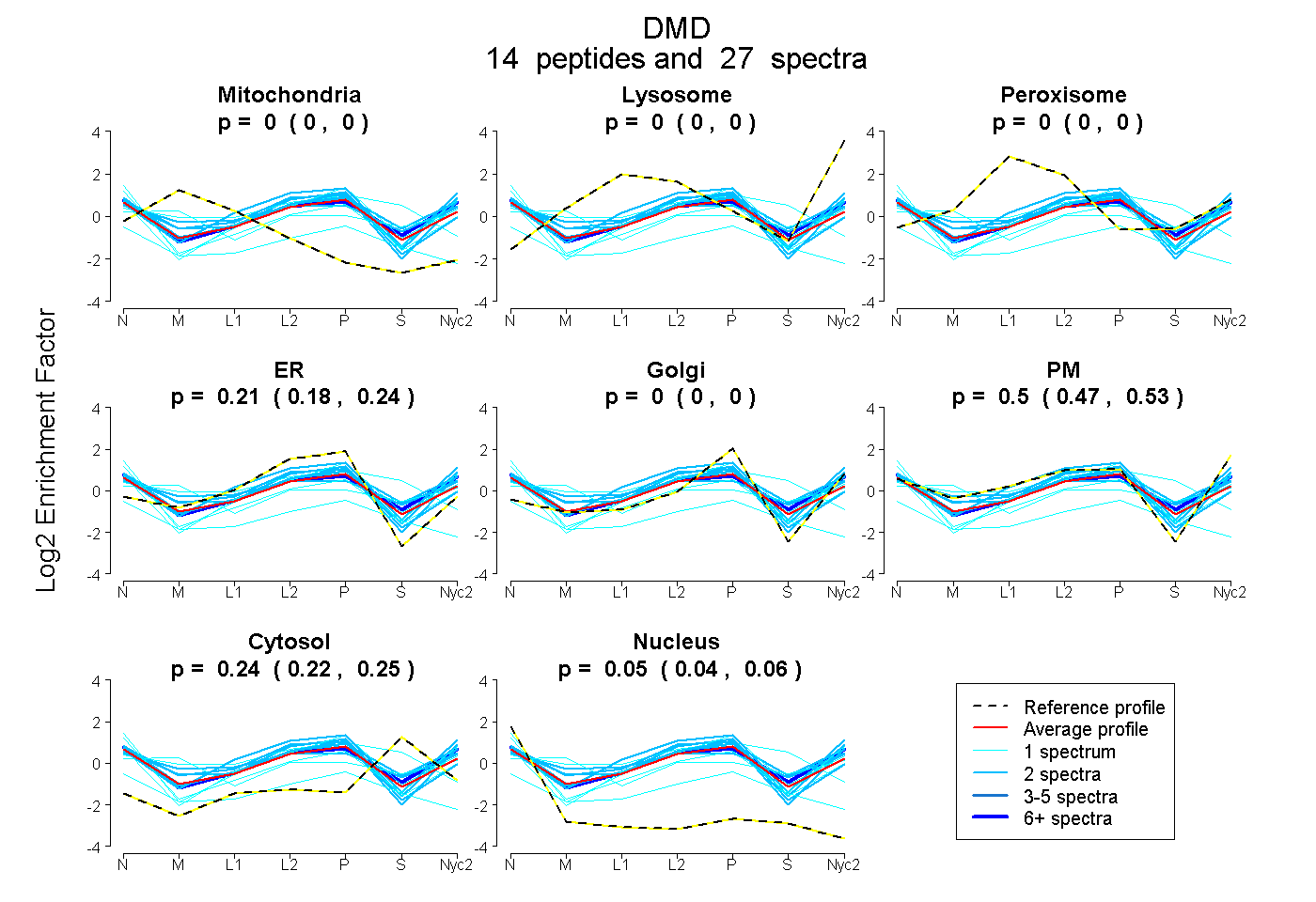
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.182 | 0.235
0.000 | 0.000
0.469 | 0.528
0.225 | 0.245
0.044 | 0.060
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.211 0.182 | 0.235 |
0.000 0.000 | 0.000 |
0.500 0.469 | 0.528 |
0.236 0.225 | 0.245 |
0.052 0.044 | 0.060 |
| 7 spectra, DAELIAEAK | 0.000 | 0.000 | 0.000 | 0.047 | 0.000 | 0.655 | 0.279 | 0.019 | ||
| 1 spectrum, QQHEHK | 0.000 | 0.000 | 0.000 | 0.260 | 0.145 | 0.327 | 0.250 | 0.018 | ||
| 1 spectrum, QLLEQPQAEAK | 0.174 | 0.000 | 0.000 | 0.000 | 0.003 | 0.497 | 0.326 | 0.000 | ||
| 1 spectrum, EHLK | 0.000 | 0.000 | 0.016 | 0.459 | 0.000 | 0.000 | 0.524 | 0.000 | ||
| 2 spectra, QVASSTGFCDQR | 0.000 | 0.000 | 0.000 | 0.372 | 0.000 | 0.422 | 0.085 | 0.121 | ||
| 2 spectra, MTELYQSLADLNNVR | 0.000 | 0.000 | 0.000 | 0.204 | 0.000 | 0.684 | 0.047 | 0.065 | ||
| 2 spectra, SDSSQPMLLR | 0.000 | 0.000 | 0.019 | 0.181 | 0.000 | 0.674 | 0.125 | 0.000 | ||
| 2 spectra, AHLEDK | 0.000 | 0.000 | 0.000 | 0.146 | 0.000 | 0.585 | 0.262 | 0.007 | ||
| 2 spectra, MQILEDHNK | 0.000 | 0.000 | 0.000 | 0.092 | 0.000 | 0.607 | 0.301 | 0.000 | ||
| 1 spectrum, SPAQILISLESEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.023 | 0.667 | 0.177 | 0.133 | ||
| 1 spectrum, VNGTTVSSPSTSLQR | 0.000 | 0.000 | 0.012 | 0.332 | 0.000 | 0.025 | 0.147 | 0.484 | ||
| 2 spectra, HFNYDICQSCFFSGR | 0.040 | 0.000 | 0.096 | 0.029 | 0.000 | 0.574 | 0.260 | 0.000 | ||
| 2 spectra, ILADLEEENR | 0.000 | 0.000 | 0.000 | 0.130 | 0.061 | 0.651 | 0.134 | 0.024 | ||
| 1 spectrum, LEPQSMVWLPVLHR | 0.131 | 0.000 | 0.030 | 0.363 | 0.000 | 0.376 | 0.100 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
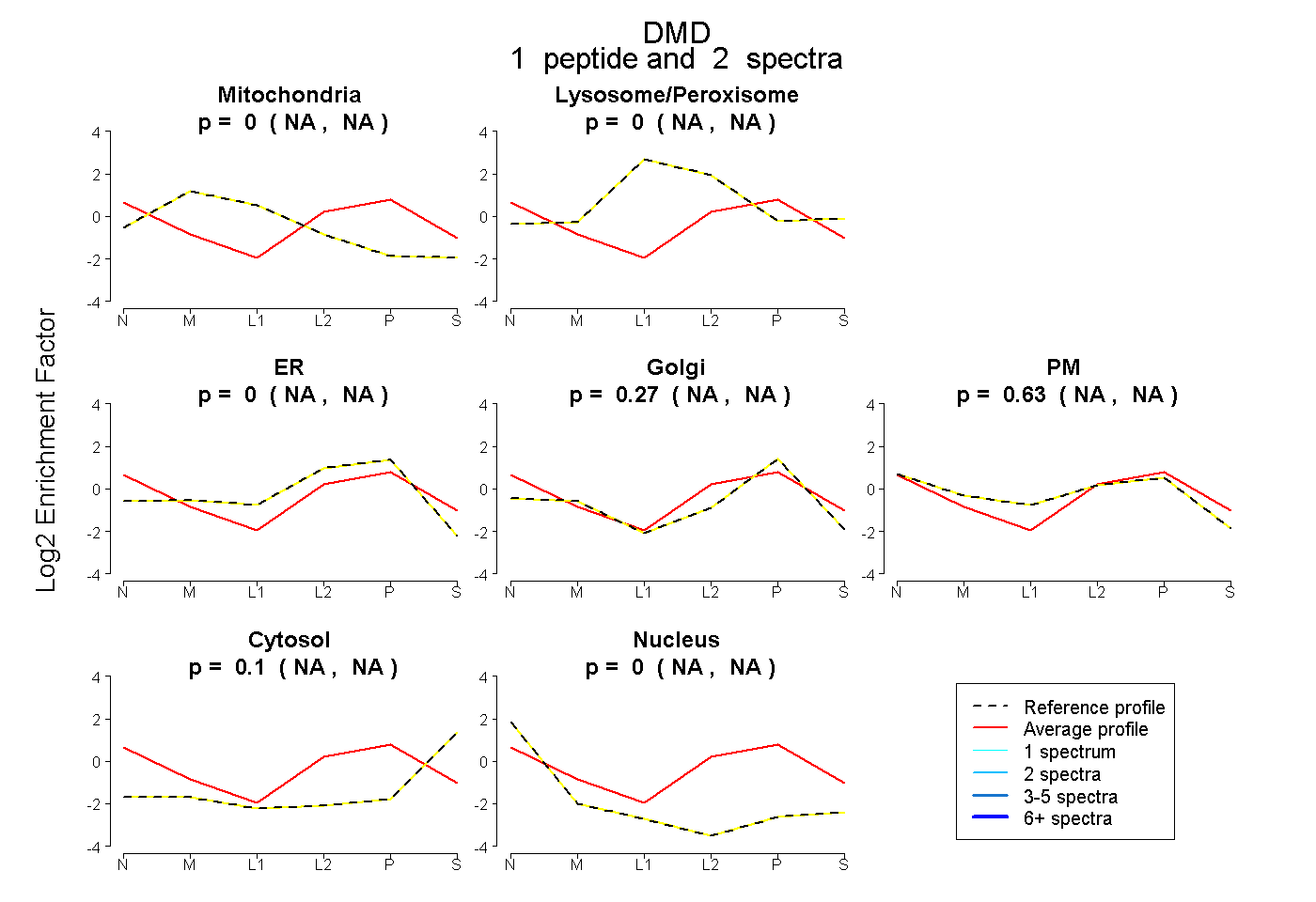 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.266 NA | NA |
0.632 NA | NA |
0.102 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
33 spectra |
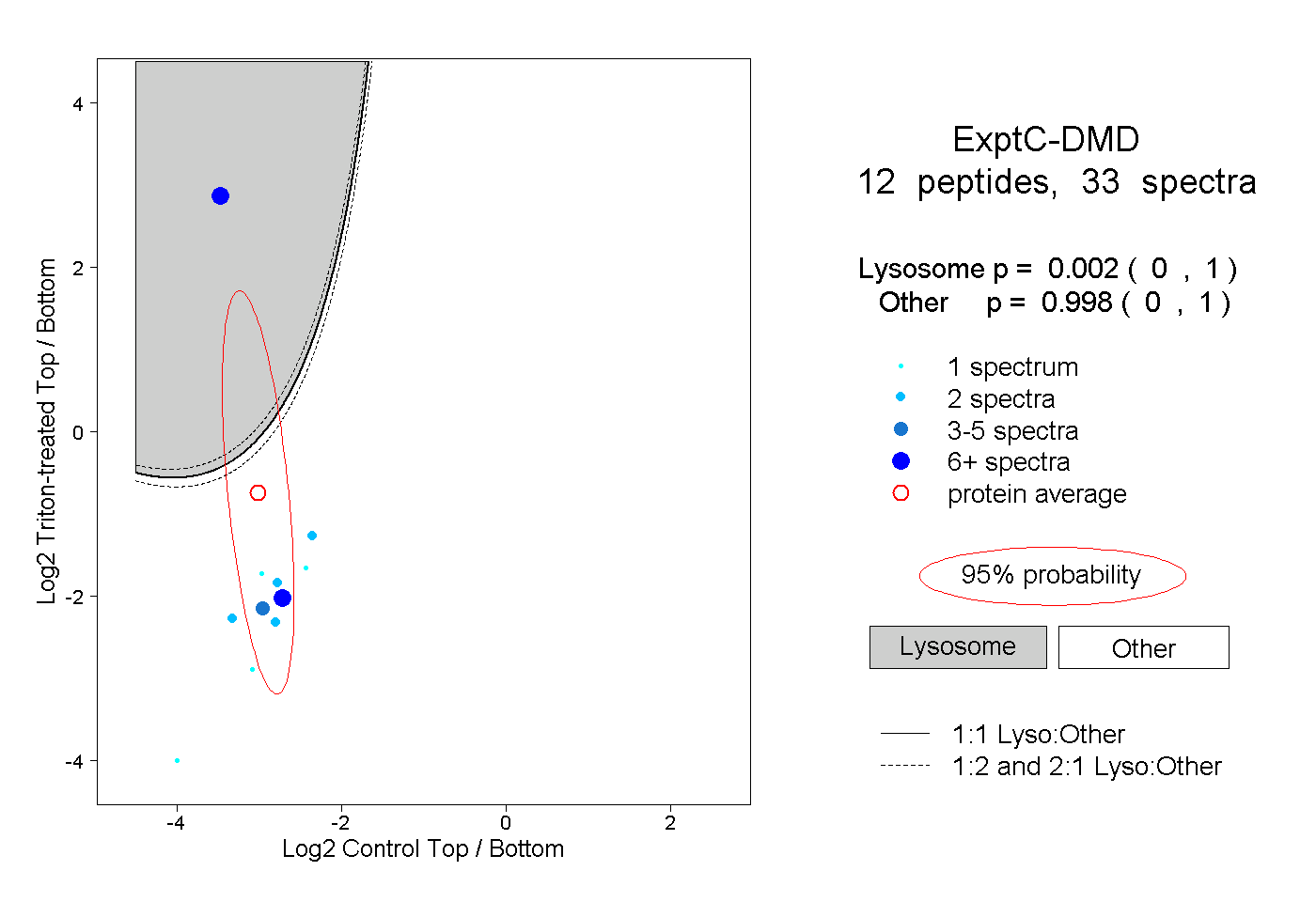 |
0.002 0.000 | 1.000 |
0.998 0.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
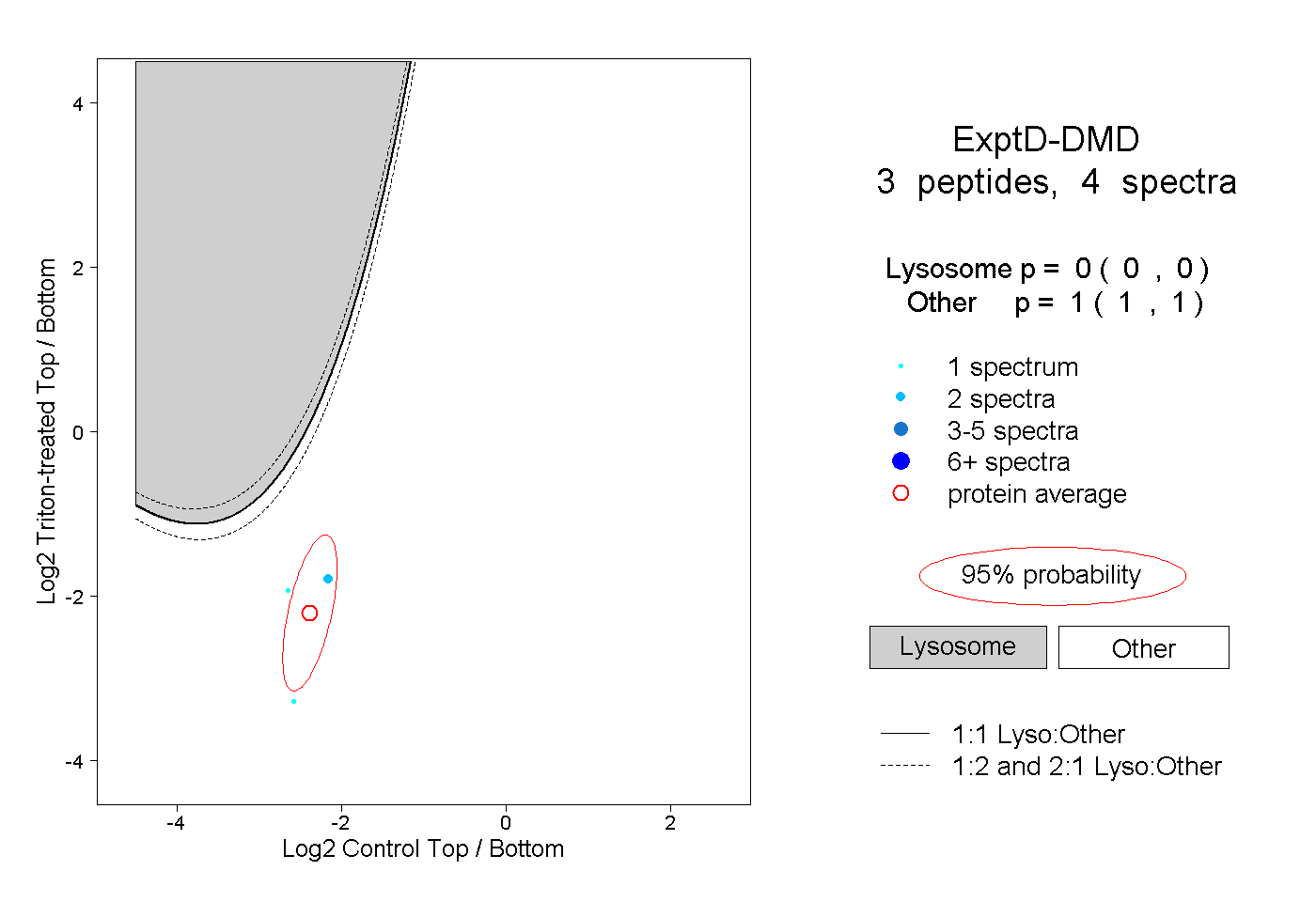 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |