peptides
spectra
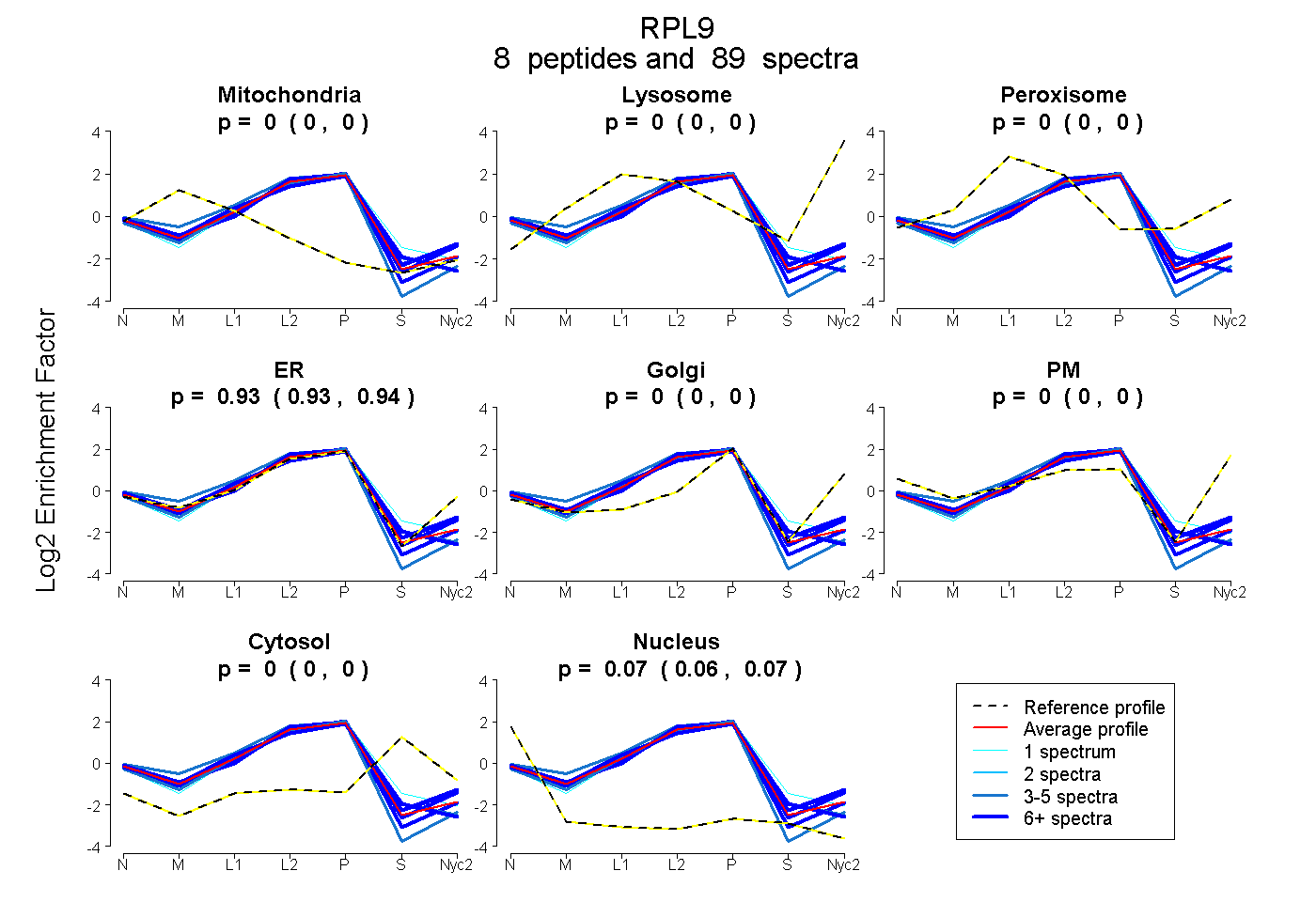
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.931 | 0.935
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.064 | 0.069
peptides
spectra
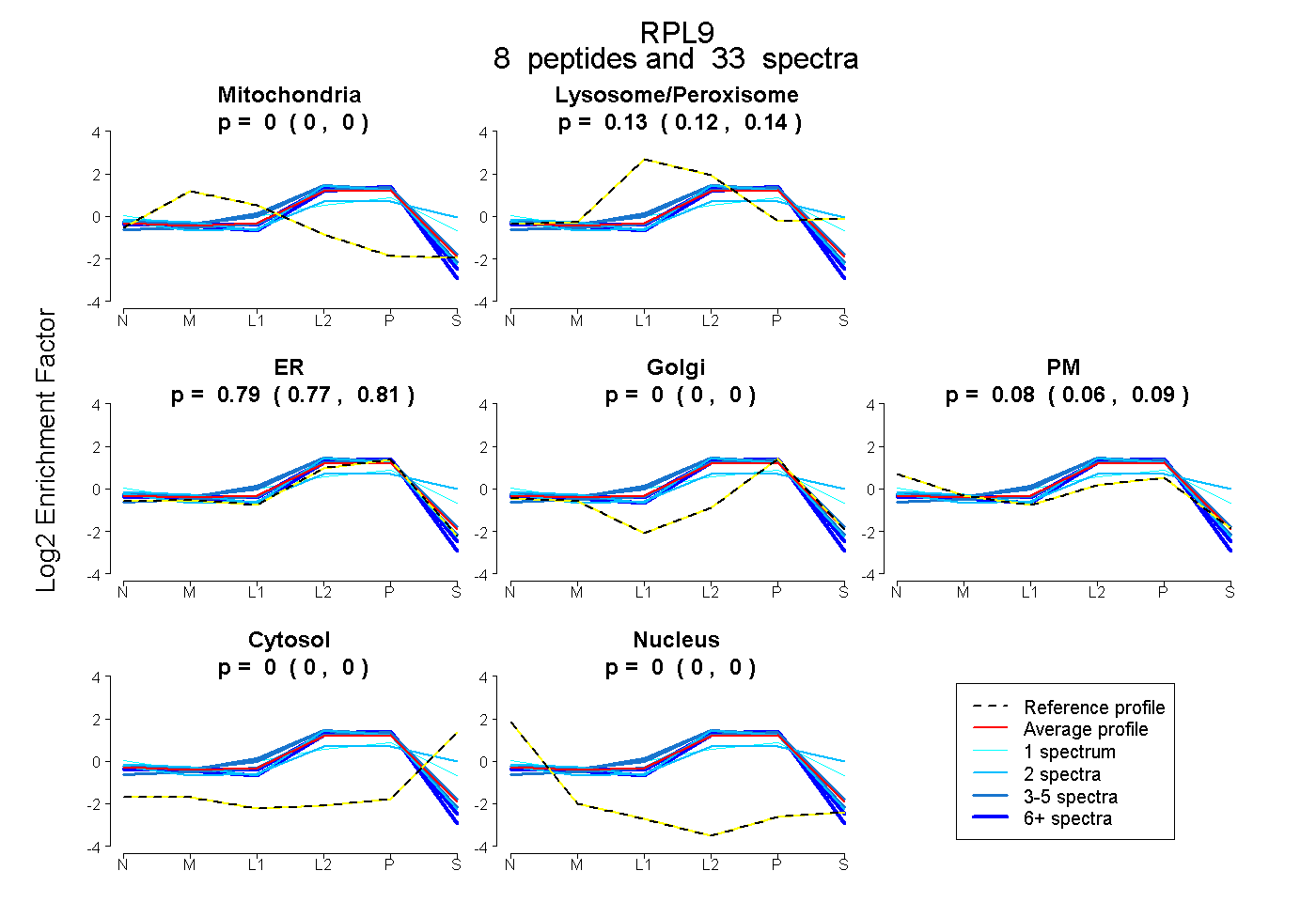
0.000 | 0.000
0.117 | 0.141
0.772 | 0.813
0.000 | 0.000
0.058 | 0.091
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
89 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.933 0.931 | 0.935 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.067 0.064 | 0.069 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
 |
0.000 0.000 | 0.000 |
0.130 0.117 | 0.141 |
0.794 0.772 | 0.813 |
0.000 0.000 | 0.000 |
0.076 0.058 | 0.091 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, TGVACSVSQAQK | 0.000 | 0.045 | 0.872 | 0.000 | 0.083 | 0.000 | 0.000 | |||
| 2 spectra, TILSNQTVDIPENVDITLK | 0.000 | 0.322 | 0.216 | 0.221 | 0.054 | 0.187 | 0.000 | |||
| 1 spectrum, DFNHINVELSLLGK | 0.000 | 0.420 | 0.000 | 0.413 | 0.153 | 0.013 | 0.000 | |||
| 3 spectra, NFLGEK | 0.000 | 0.241 | 0.759 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, GTVQQPDE | 0.000 | 0.131 | 0.869 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, ELATVR | 0.000 | 0.056 | 0.944 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, FLDGIYVSEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, GVTLGFR | 0.000 | 0.168 | 0.832 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
113 spectra |
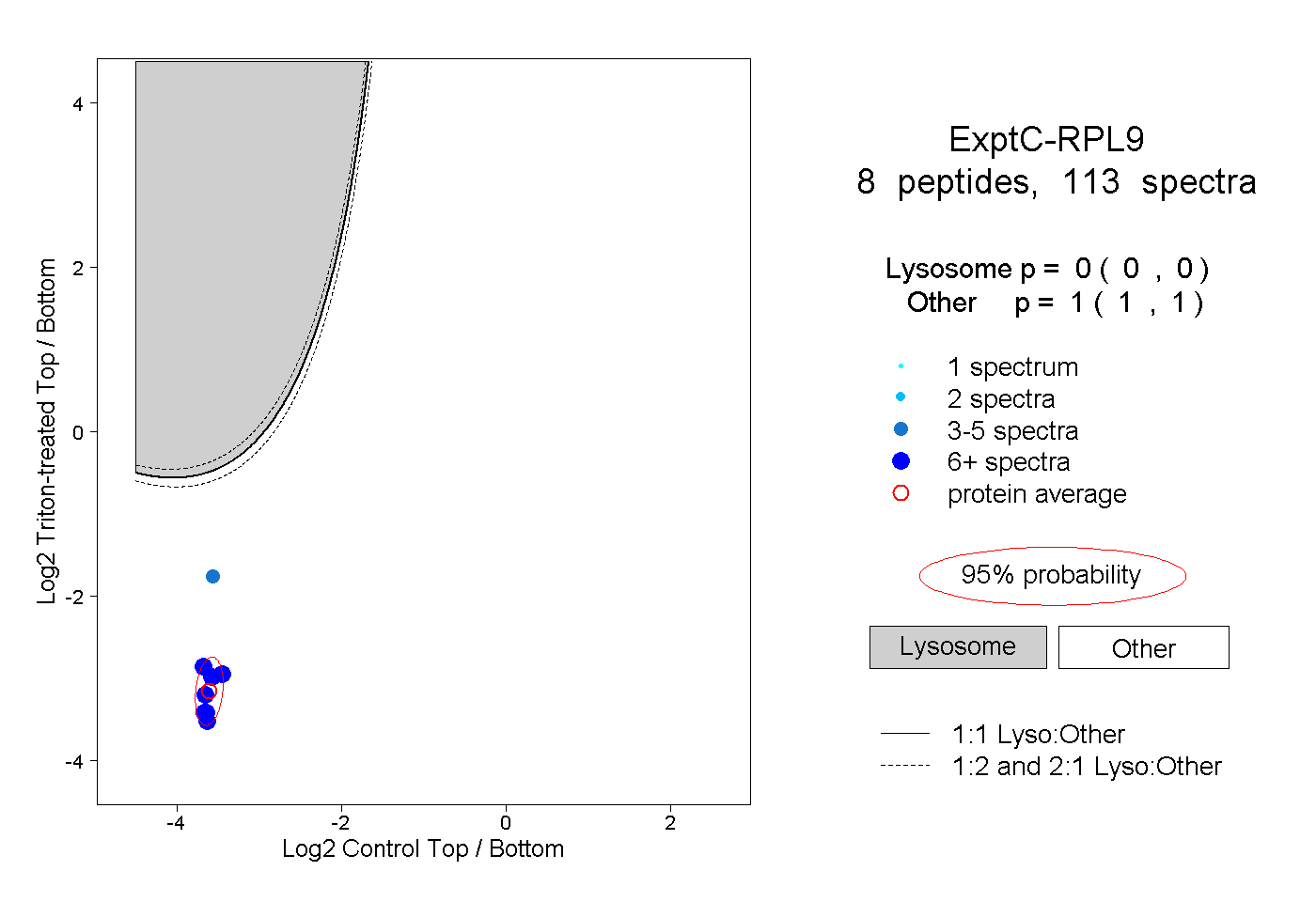 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
17 spectra |
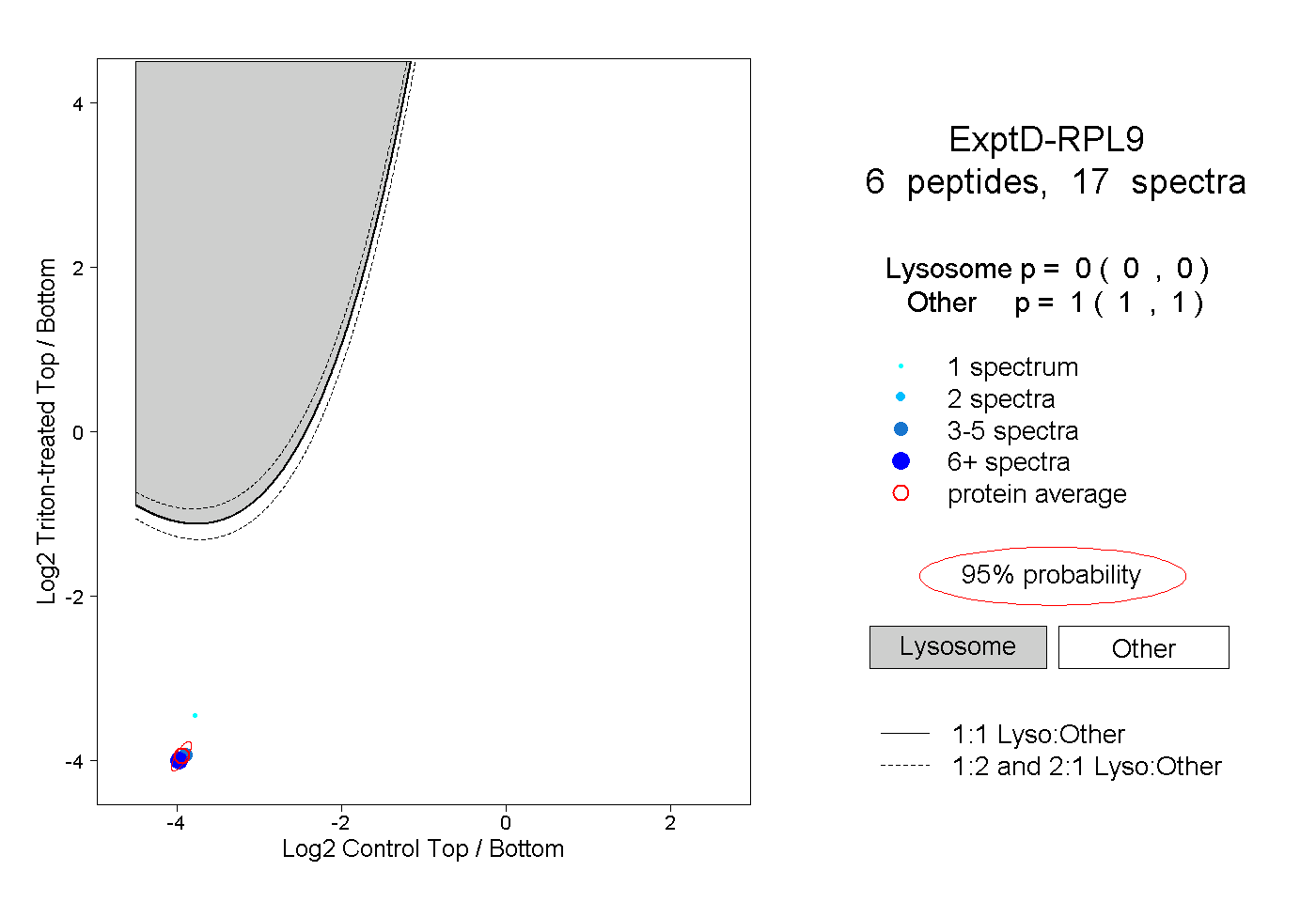 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |