peptides
spectra
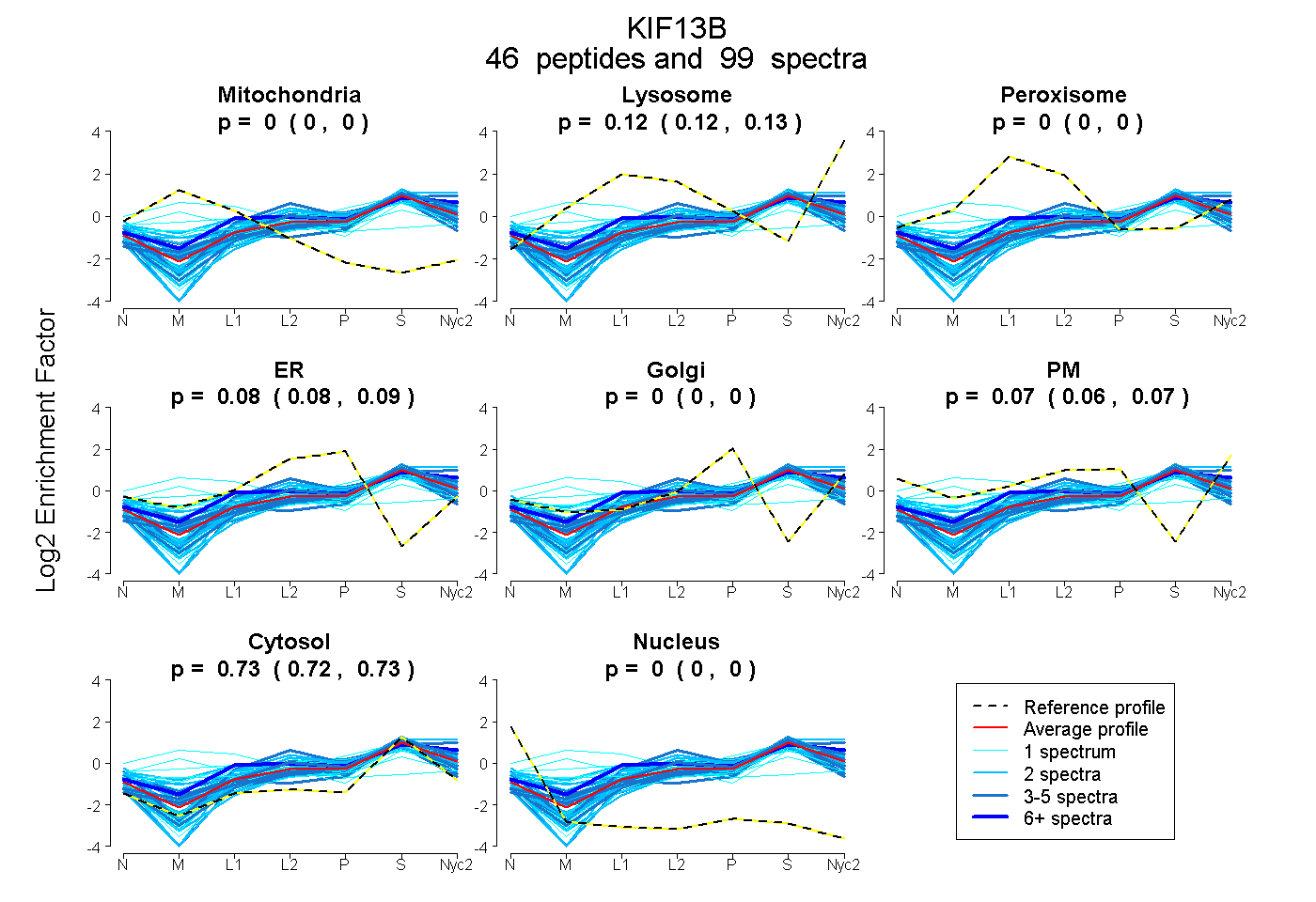
0.000 | 0.000
0.121 | 0.126
0.000 | 0.000
0.080 | 0.088
0.000 | 0.000
0.061 | 0.072
0.723 | 0.727
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
99 spectra |
 |
0.000 0.000 | 0.000 |
0.124 0.121 | 0.126 |
0.000 0.000 | 0.000 |
0.084 0.080 | 0.088 |
0.000 0.000 | 0.000 |
0.067 0.061 | 0.072 |
0.725 0.723 | 0.727 |
0.000 0.000 | 0.000 |
| 4 spectra, SISSPSMNR | 0.000 | 0.013 | 0.000 | 0.018 | 0.099 | 0.000 | 0.870 | 0.000 | ||
| 1 spectrum, VILNPINTNLSK | 0.000 | 0.000 | 0.000 | 0.011 | 0.107 | 0.000 | 0.882 | 0.000 | ||
| 3 spectra, WLNALTK | 0.000 | 0.249 | 0.000 | 0.064 | 0.013 | 0.000 | 0.673 | 0.000 | ||
| 1 spectrum, IAGGDDPTEVSSEK | 0.000 | 0.074 | 0.000 | 0.034 | 0.047 | 0.000 | 0.845 | 0.000 | ||
| 1 spectrum, EGSNINK | 0.000 | 0.079 | 0.000 | 0.004 | 0.070 | 0.000 | 0.847 | 0.000 | ||
| 1 spectrum, VAVQLSHPADMQLVLR | 0.003 | 0.191 | 0.073 | 0.000 | 0.000 | 0.136 | 0.597 | 0.000 | ||
| 2 spectra, EGEYVVVGTNK | 0.000 | 0.122 | 0.056 | 0.093 | 0.000 | 0.000 | 0.729 | 0.000 | ||
| 4 spectra, LHVEVMR | 0.000 | 0.082 | 0.000 | 0.000 | 0.152 | 0.000 | 0.766 | 0.000 | ||
| 1 spectrum, ITLTHTLYDVK | 0.000 | 0.000 | 0.000 | 0.155 | 0.008 | 0.000 | 0.837 | 0.000 | ||
| 7 spectra, VRPMNR | 0.000 | 0.206 | 0.101 | 0.000 | 0.000 | 0.108 | 0.585 | 0.000 | ||
| 2 spectra, TEEIAQER | 0.000 | 0.127 | 0.008 | 0.021 | 0.000 | 0.230 | 0.613 | 0.000 | ||
| 3 spectra, ILWGNNHFFR | 0.000 | 0.031 | 0.067 | 0.175 | 0.000 | 0.113 | 0.614 | 0.000 | ||
| 3 spectra, LMYEHELEQLR | 0.000 | 0.006 | 0.055 | 0.000 | 0.083 | 0.000 | 0.856 | 0.000 | ||
| 2 spectra, HIINHAVVNEDPNAR | 0.000 | 0.119 | 0.064 | 0.076 | 0.000 | 0.114 | 0.627 | 0.000 | ||
| 2 spectra, SVLAVENLLTLDR | 0.000 | 0.073 | 0.000 | 0.000 | 0.073 | 0.000 | 0.854 | 0.000 | ||
| 2 spectra, VTLQIPASSLDANR | 0.000 | 0.085 | 0.000 | 0.072 | 0.051 | 0.000 | 0.791 | 0.000 | ||
| 2 spectra, LIQEMTVTWEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.237 | 0.742 | 0.020 | ||
| 2 spectra, DVPTGGIFQLR | 0.000 | 0.043 | 0.000 | 0.047 | 0.162 | 0.000 | 0.748 | 0.000 | ||
| 1 spectrum, MAAPTVK | 0.000 | 0.064 | 0.000 | 0.202 | 0.039 | 0.000 | 0.695 | 0.000 | ||
| 1 spectrum, LVCMVK | 0.000 | 0.000 | 0.280 | 0.062 | 0.182 | 0.000 | 0.477 | 0.000 | ||
| 1 spectrum, LSFHSPSAQQR | 0.349 | 0.000 | 0.280 | 0.000 | 0.000 | 0.156 | 0.214 | 0.000 | ||
| 2 spectra, EQLTGK | 0.000 | 0.000 | 0.298 | 0.000 | 0.137 | 0.080 | 0.485 | 0.000 | ||
| 1 spectrum, ANLLVR | 0.006 | 0.000 | 0.292 | 0.000 | 0.000 | 0.088 | 0.613 | 0.000 | ||
| 1 spectrum, QIWSLEK | 0.224 | 0.040 | 0.186 | 0.000 | 0.072 | 0.059 | 0.420 | 0.000 | ||
| 4 spectra, ISLVDLAGSER | 0.000 | 0.066 | 0.000 | 0.058 | 0.065 | 0.013 | 0.798 | 0.000 | ||
| 1 spectrum, EATLNNSLMR | 0.000 | 0.183 | 0.000 | 0.063 | 0.000 | 0.043 | 0.712 | 0.000 | ||
| 2 spectra, EAQLLEMR | 0.000 | 0.198 | 0.000 | 0.000 | 0.041 | 0.000 | 0.761 | 0.000 | ||
| 2 spectra, SSGLQPQGAPEAR | 0.000 | 0.224 | 0.000 | 0.009 | 0.024 | 0.036 | 0.706 | 0.000 | ||
| 1 spectrum, QLESLGISLQTSGIK | 0.000 | 0.133 | 0.000 | 0.036 | 0.000 | 0.088 | 0.744 | 0.000 | ||
| 2 spectra, GEVAGR | 0.000 | 0.041 | 0.071 | 0.000 | 0.094 | 0.041 | 0.752 | 0.000 | ||
| 3 spectra, QGFAQSLLK | 0.000 | 0.202 | 0.000 | 0.000 | 0.000 | 0.195 | 0.603 | 0.000 | ||
| 2 spectra, TGAAGDR | 0.000 | 0.000 | 0.178 | 0.000 | 0.044 | 0.195 | 0.583 | 0.000 | ||
| 1 spectrum, HHDGEVK | 0.000 | 0.185 | 0.000 | 0.000 | 0.000 | 0.004 | 0.811 | 0.000 | ||
| 2 spectra, LSGAIGER | 0.000 | 0.099 | 0.109 | 0.000 | 0.022 | 0.110 | 0.660 | 0.000 | ||
| 2 spectra, LTLTEER | 0.000 | 0.076 | 0.000 | 0.073 | 0.030 | 0.038 | 0.783 | 0.000 | ||
| 2 spectra, GSLLSEPAIQVR | 0.000 | 0.000 | 0.000 | 0.029 | 0.106 | 0.000 | 0.865 | 0.000 | ||
| 5 spectra, CNPGYGLLVRPGR | 0.000 | 0.000 | 0.145 | 0.246 | 0.000 | 0.000 | 0.609 | 0.000 | ||
| 1 spectrum, MAANVENAASADSEACIEK | 0.116 | 0.147 | 0.193 | 0.000 | 0.000 | 0.044 | 0.500 | 0.000 | ||
| 1 spectrum, ILVQPTFSDAR | 0.000 | 0.275 | 0.000 | 0.072 | 0.000 | 0.000 | 0.654 | 0.000 | ||
| 1 spectrum, DSLGGNSK | 0.000 | 0.083 | 0.117 | 0.000 | 0.000 | 0.204 | 0.597 | 0.000 | ||
| 2 spectra, DSVLTWLLK | 0.000 | 0.094 | 0.000 | 0.000 | 0.120 | 0.000 | 0.786 | 0.000 | ||
| 2 spectra, LQYAVPIINQK | 0.000 | 0.076 | 0.000 | 0.075 | 0.026 | 0.006 | 0.817 | 0.000 | ||
| 4 spectra, DIESLMSEGNK | 0.000 | 0.087 | 0.000 | 0.080 | 0.000 | 0.084 | 0.750 | 0.000 | ||
| 1 spectrum, LAVTSYK | 0.000 | 0.100 | 0.000 | 0.000 | 0.000 | 0.173 | 0.727 | 0.000 | ||
| 3 spectra, TVAATNMNEESSR | 0.000 | 0.110 | 0.000 | 0.001 | 0.073 | 0.000 | 0.816 | 0.000 | ||
| 5 spectra, YAGQDDVFK | 0.000 | 0.110 | 0.000 | 0.110 | 0.013 | 0.000 | 0.767 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
12 spectra |
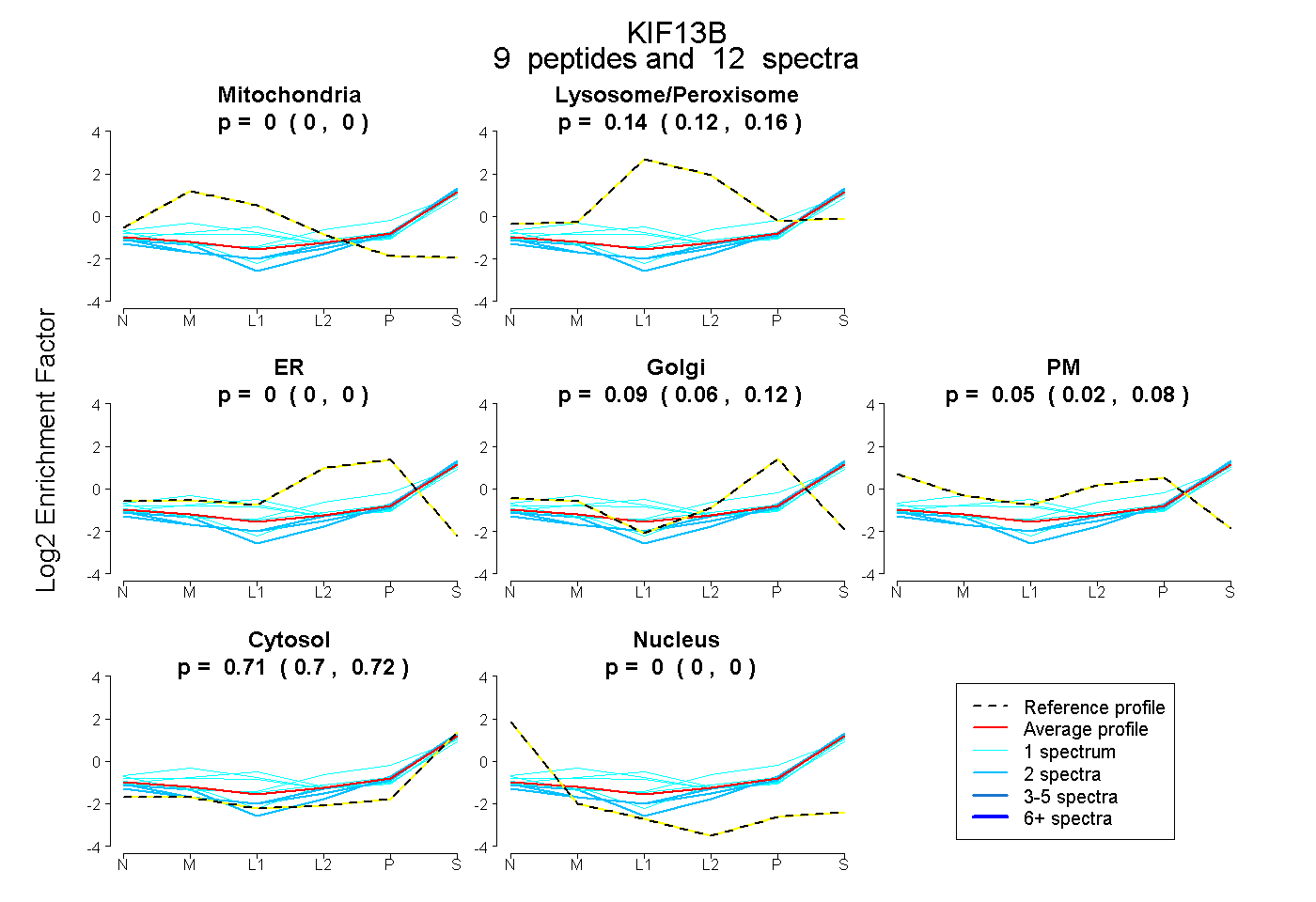 |
0.000 0.000 | 0.000 |
0.142 0.116 | 0.164 |
0.000 0.000 | 0.000 |
0.094 0.064 | 0.117 |
0.051 0.015 | 0.080 |
0.712 0.700 | 0.722 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
71 spectra |
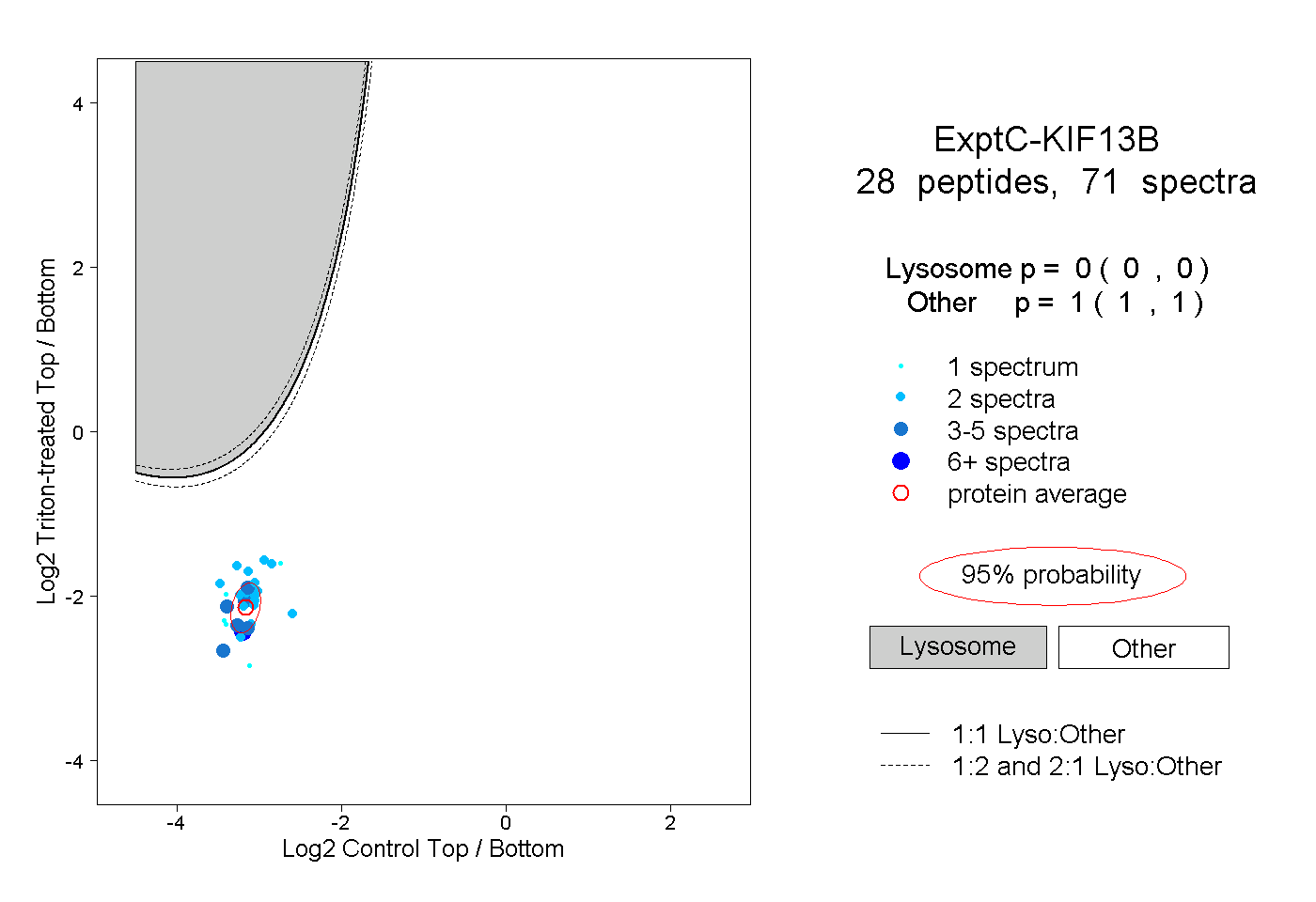 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
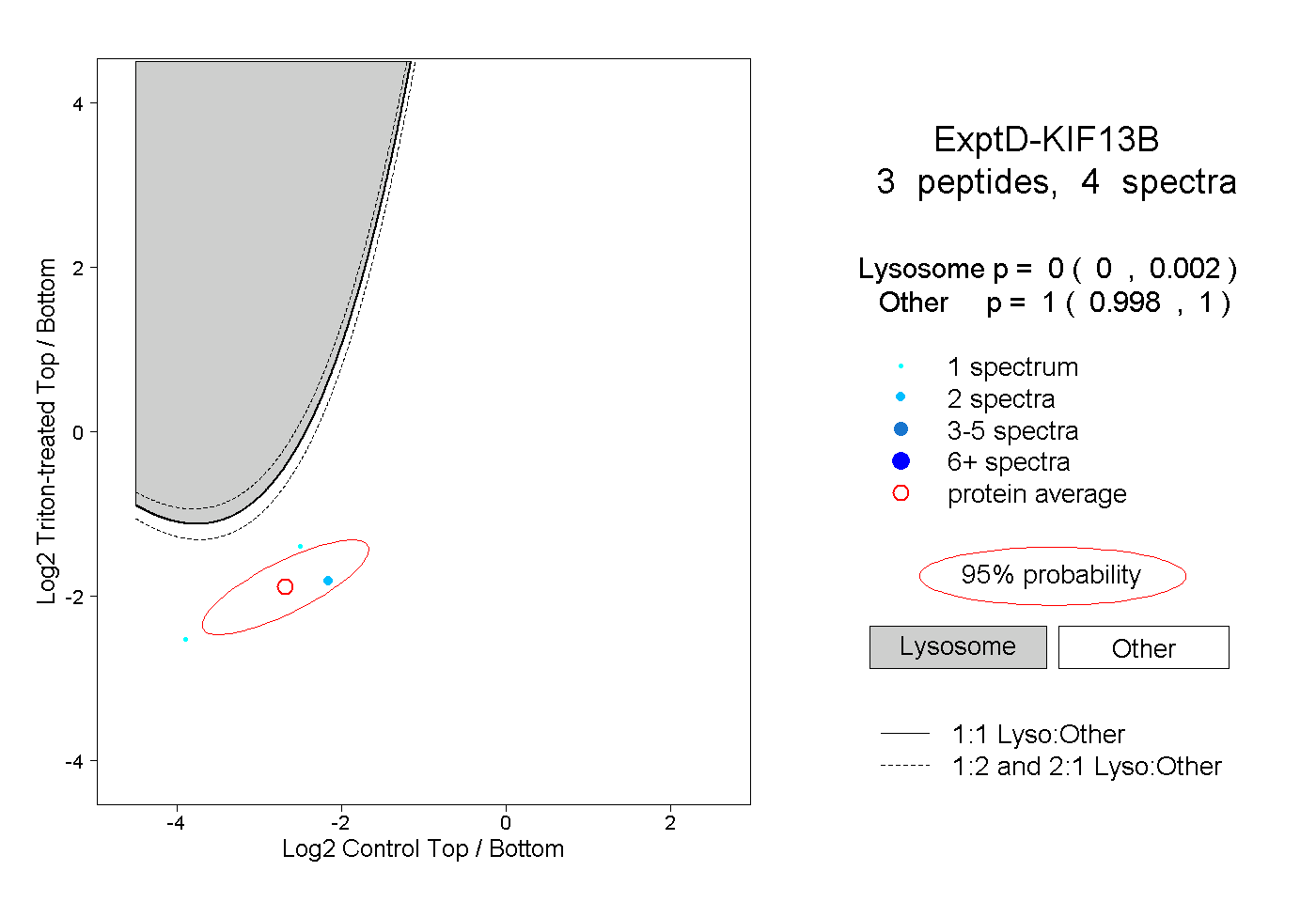 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |