peptides
spectra
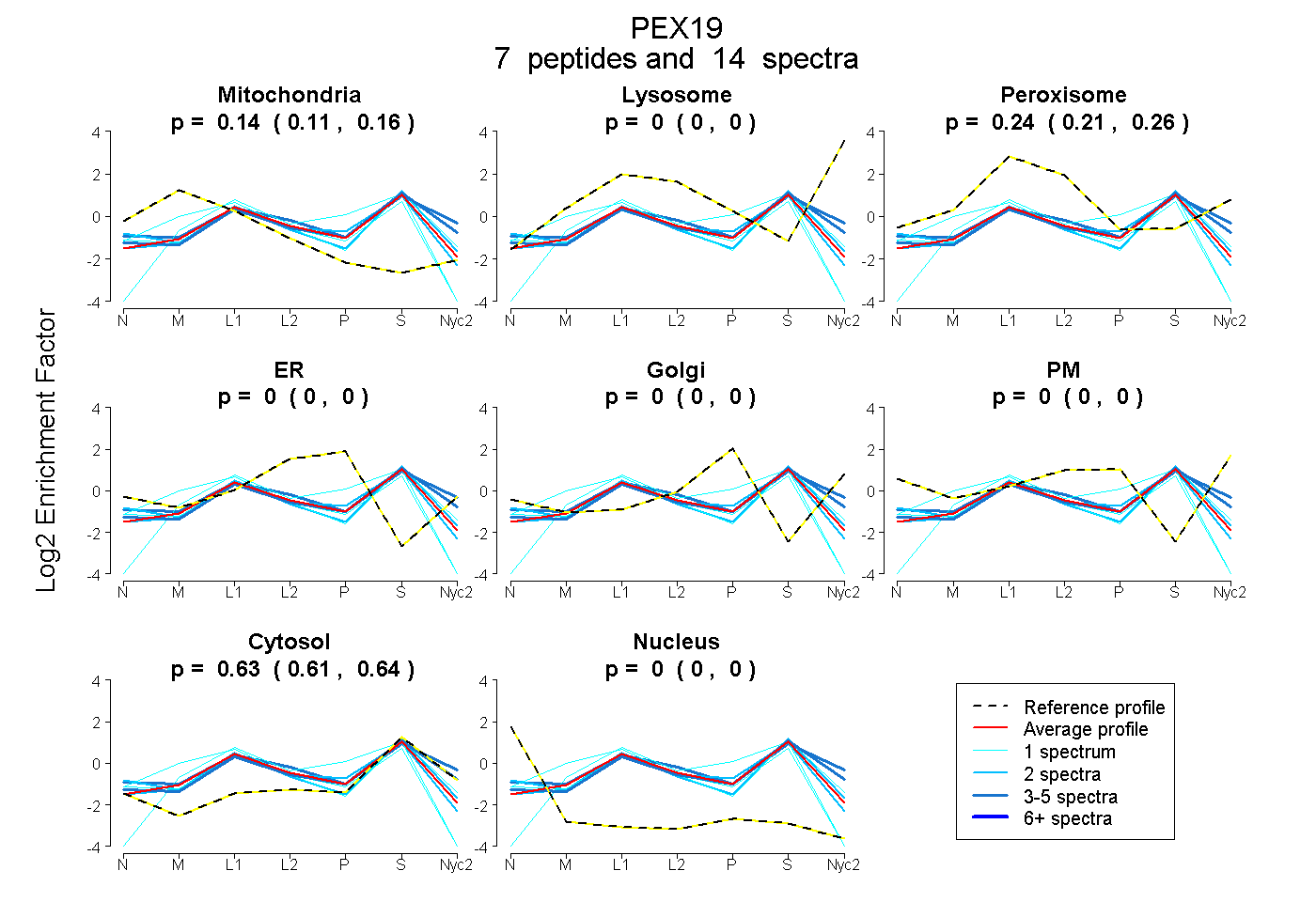
0.109 | 0.162
0.000 | 0.000
0.211 | 0.258
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.613 | 0.635
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.138 0.109 | 0.162 |
0.000 0.000 | 0.000 |
0.236 0.211 | 0.258 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.626 0.613 | 0.635 |
0.000 0.000 | 0.000 |
| 4 spectra, DALFASQEK | 0.011 | 0.000 | 0.403 | 0.000 | 0.000 | 0.000 | 0.586 | 0.000 | ||
| 2 spectra, DVLYPSLK | 0.112 | 0.000 | 0.220 | 0.000 | 0.000 | 0.000 | 0.668 | 0.000 | ||
| 1 spectrum, NATDLQNAGMSEEELTK | 0.215 | 0.000 | 0.130 | 0.024 | 0.000 | 0.000 | 0.631 | 0.000 | ||
| 1 spectrum, ICEQFEAETPTDSEATHR | 0.501 | 0.000 | 0.058 | 0.000 | 0.000 | 0.000 | 0.441 | 0.000 | ||
| 2 spectra, ELAEEEPHLVEQFQK | 0.178 | 0.000 | 0.189 | 0.000 | 0.000 | 0.000 | 0.633 | 0.000 | ||
| 3 spectra, YQQQHSVMGK | 0.013 | 0.000 | 0.318 | 0.000 | 0.000 | 0.000 | 0.669 | 0.000 | ||
| 1 spectrum, ETLSGLAK | 0.119 | 0.000 | 0.228 | 0.000 | 0.000 | 0.000 | 0.653 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
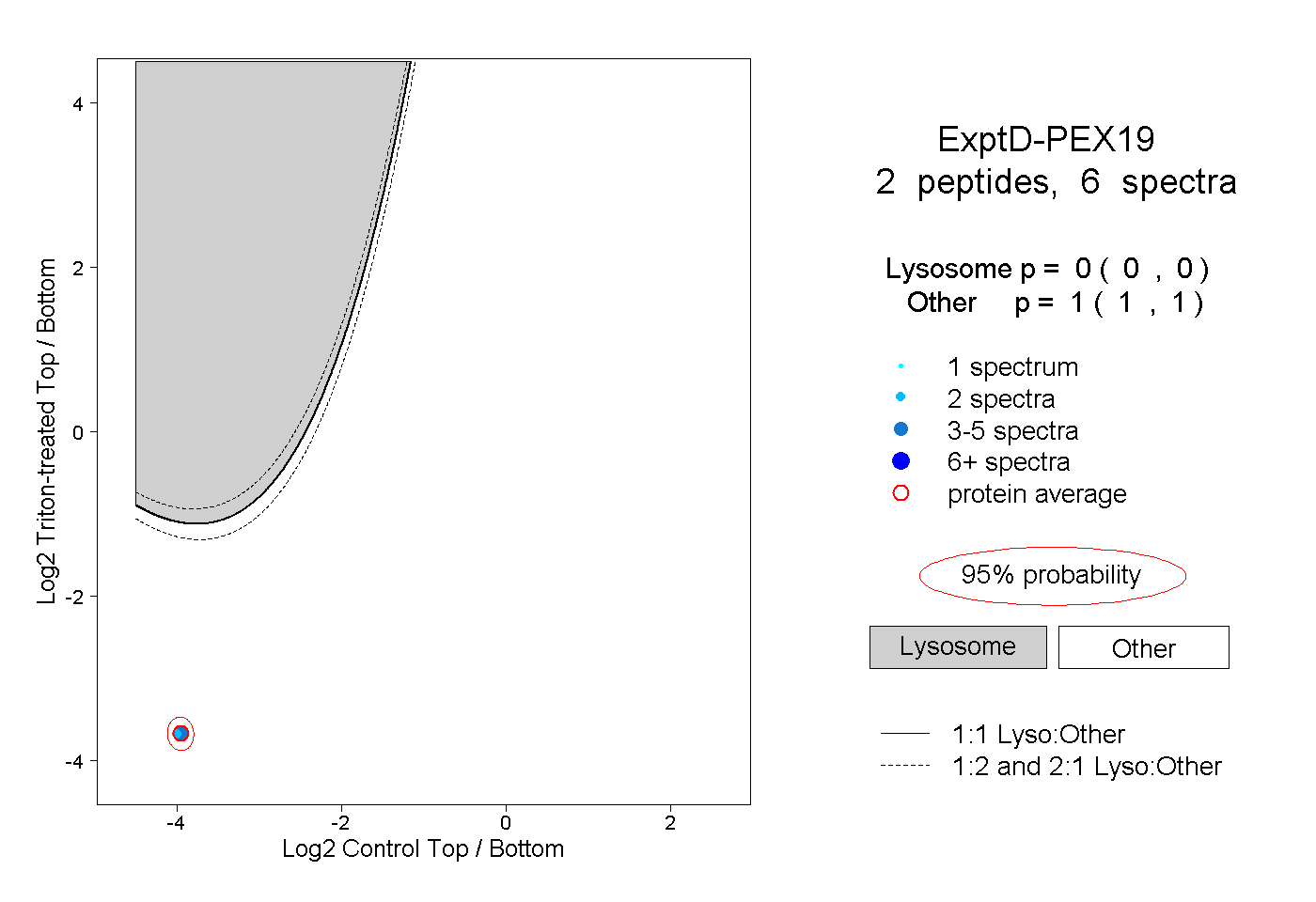 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |