peptides
spectra
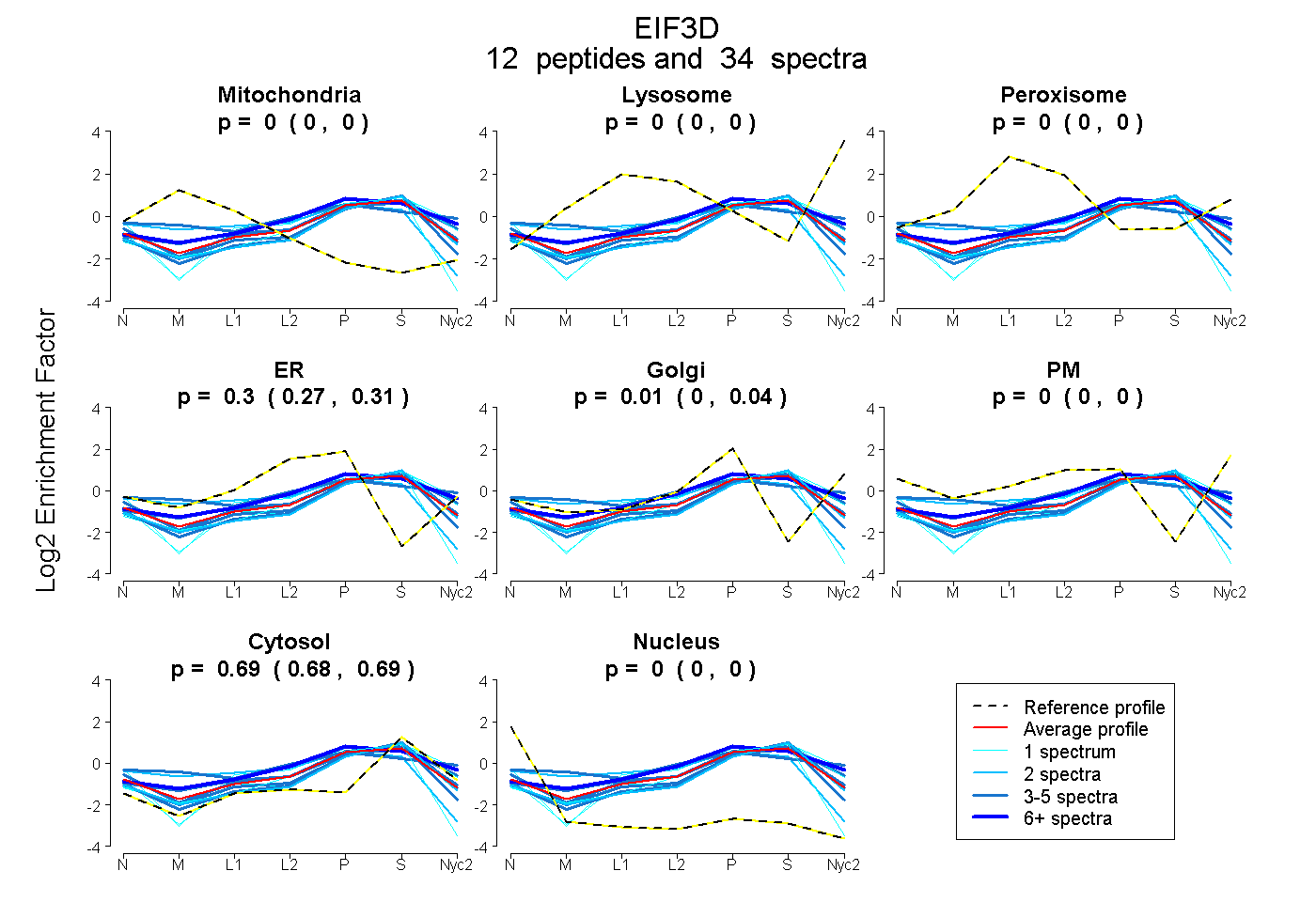
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.272 | 0.311
0.000 | 0.039
0.000 | 0.000
0.681 | 0.694
0.000 | 0.000
peptides
spectra
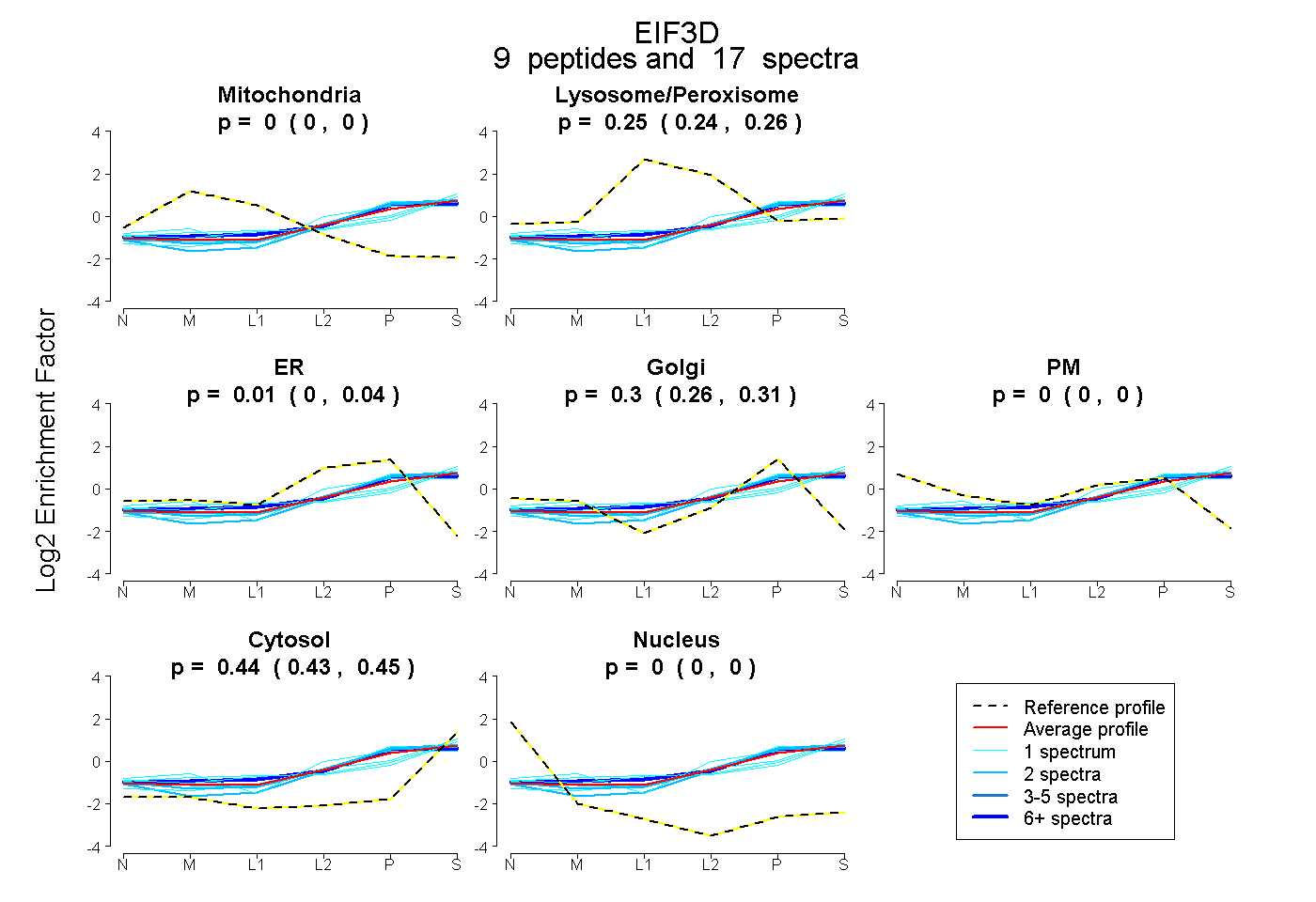
0.000 | 0.000
0.237 | 0.262
0.000 | 0.040
0.262 | 0.311
0.000 | 0.000
0.430 | 0.451
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.297 0.272 | 0.311 |
0.015 0.000 | 0.039 |
0.000 0.000 | 0.000 |
0.688 0.681 | 0.694 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.254 0.237 | 0.262 |
0.009 0.000 | 0.040 |
0.297 0.262 | 0.311 |
0.000 0.000 | 0.000 |
0.440 0.430 | 0.451 |
0.000 0.000 | 0.000 |
| 1 spectrum, NLAMEATYINHNFSQQCLR | 0.000 | 0.199 | 0.217 | 0.000 | 0.000 | 0.584 | 0.000 | |||
| 2 spectra, GAVIATELK | 0.000 | 0.204 | 0.080 | 0.277 | 0.000 | 0.438 | 0.000 | |||
| 1 spectrum, WTCCALLAGSEYLK | 0.000 | 0.309 | 0.000 | 0.193 | 0.000 | 0.498 | 0.000 | |||
| 2 spectra, TLNEWDSR | 0.000 | 0.210 | 0.093 | 0.267 | 0.000 | 0.430 | 0.000 | |||
| 1 spectrum, SVYSWDIVVQR | 0.000 | 0.153 | 0.252 | 0.201 | 0.000 | 0.395 | 0.000 | |||
| 1 spectrum, DSSVEVR | 0.000 | 0.235 | 0.000 | 0.380 | 0.000 | 0.385 | 0.000 | |||
| 2 spectra, LGDDIDLIVR | 0.000 | 0.092 | 0.285 | 0.104 | 0.000 | 0.519 | 0.000 | |||
| 1 spectrum, VADWTGATYQDK | 0.000 | 0.320 | 0.000 | 0.178 | 0.000 | 0.502 | 0.000 | |||
| 6 spectra, LGYVSR | 0.000 | 0.284 | 0.000 | 0.332 | 0.000 | 0.384 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
32 spectra |
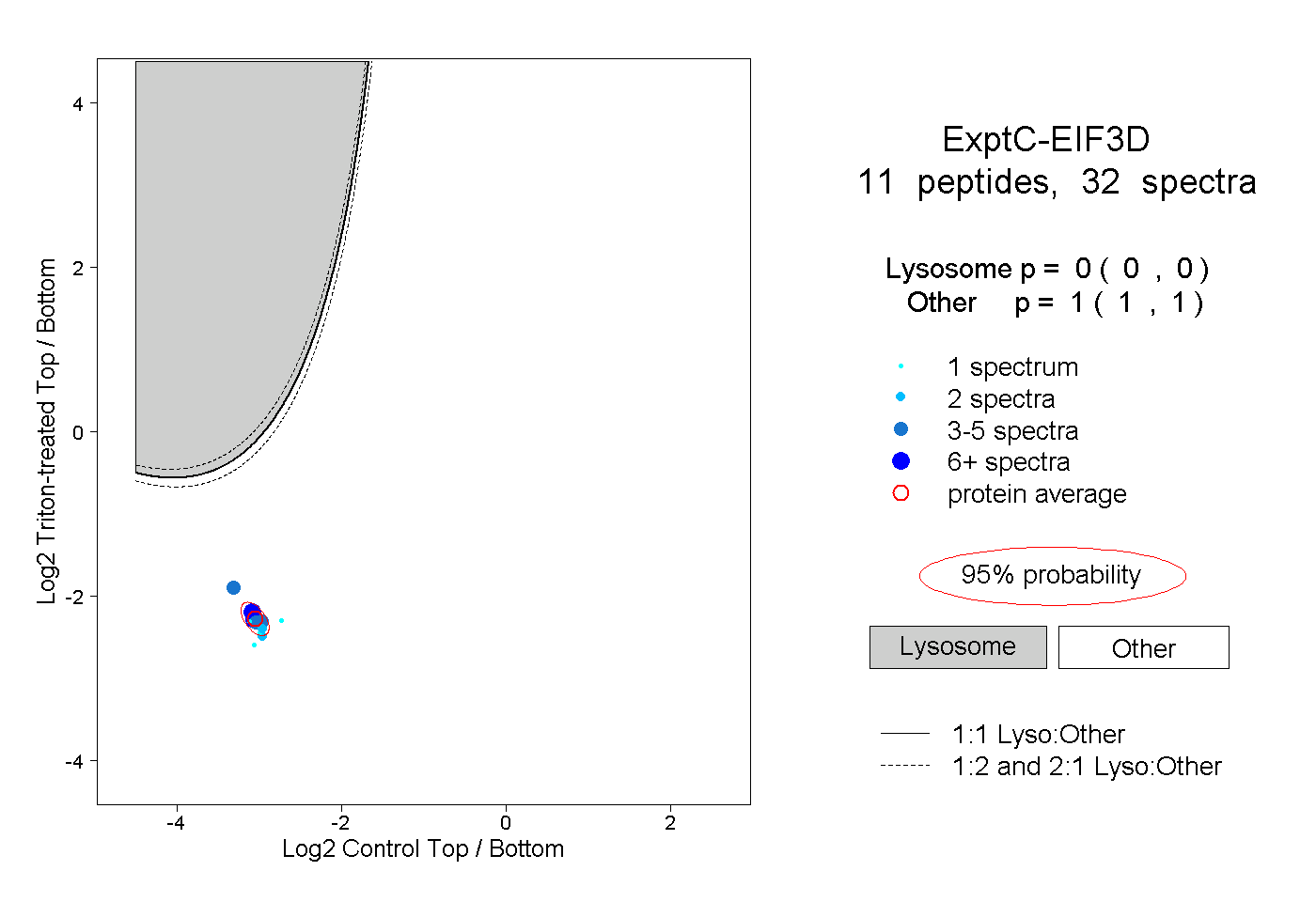 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
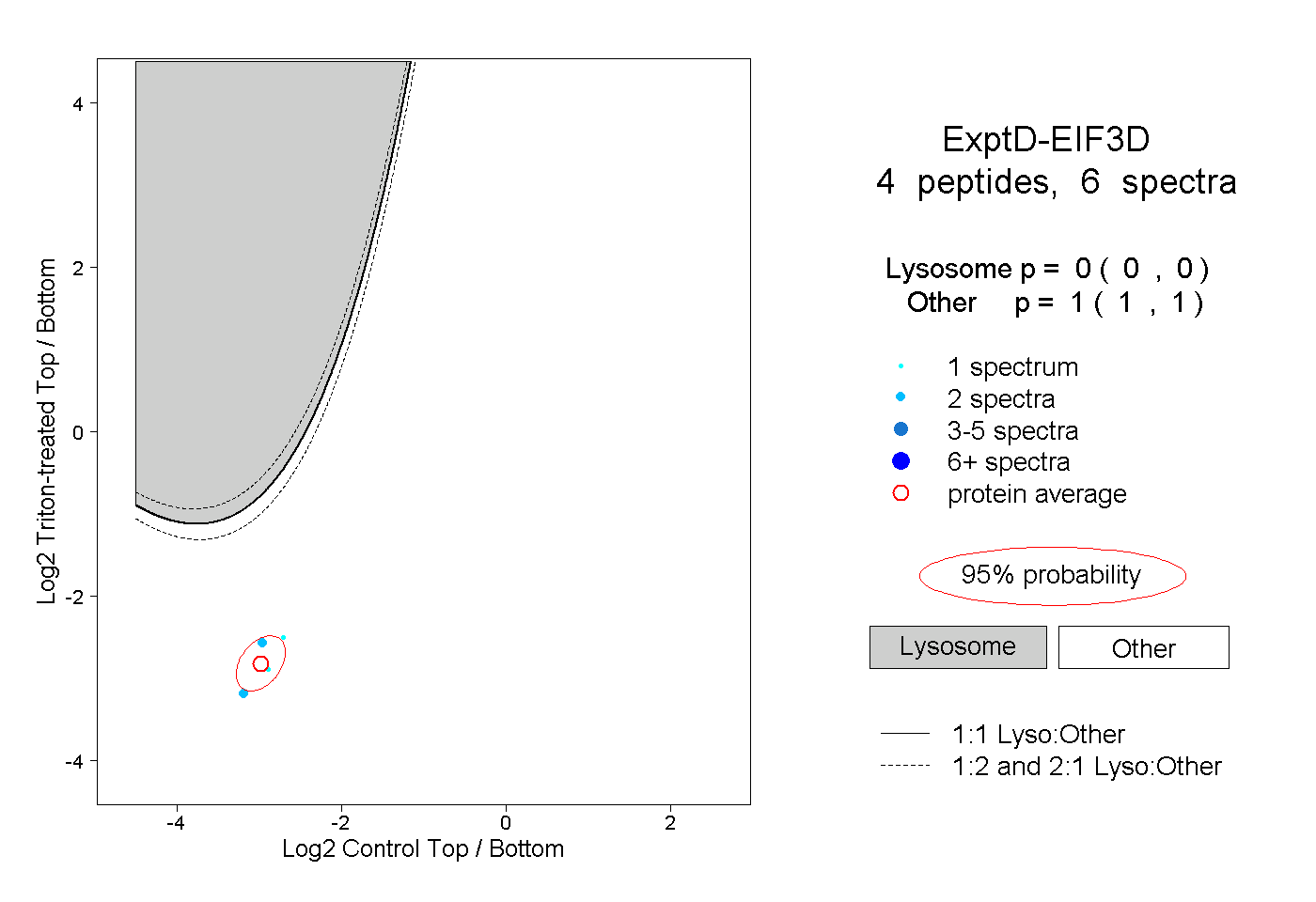 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |