peptides
spectra
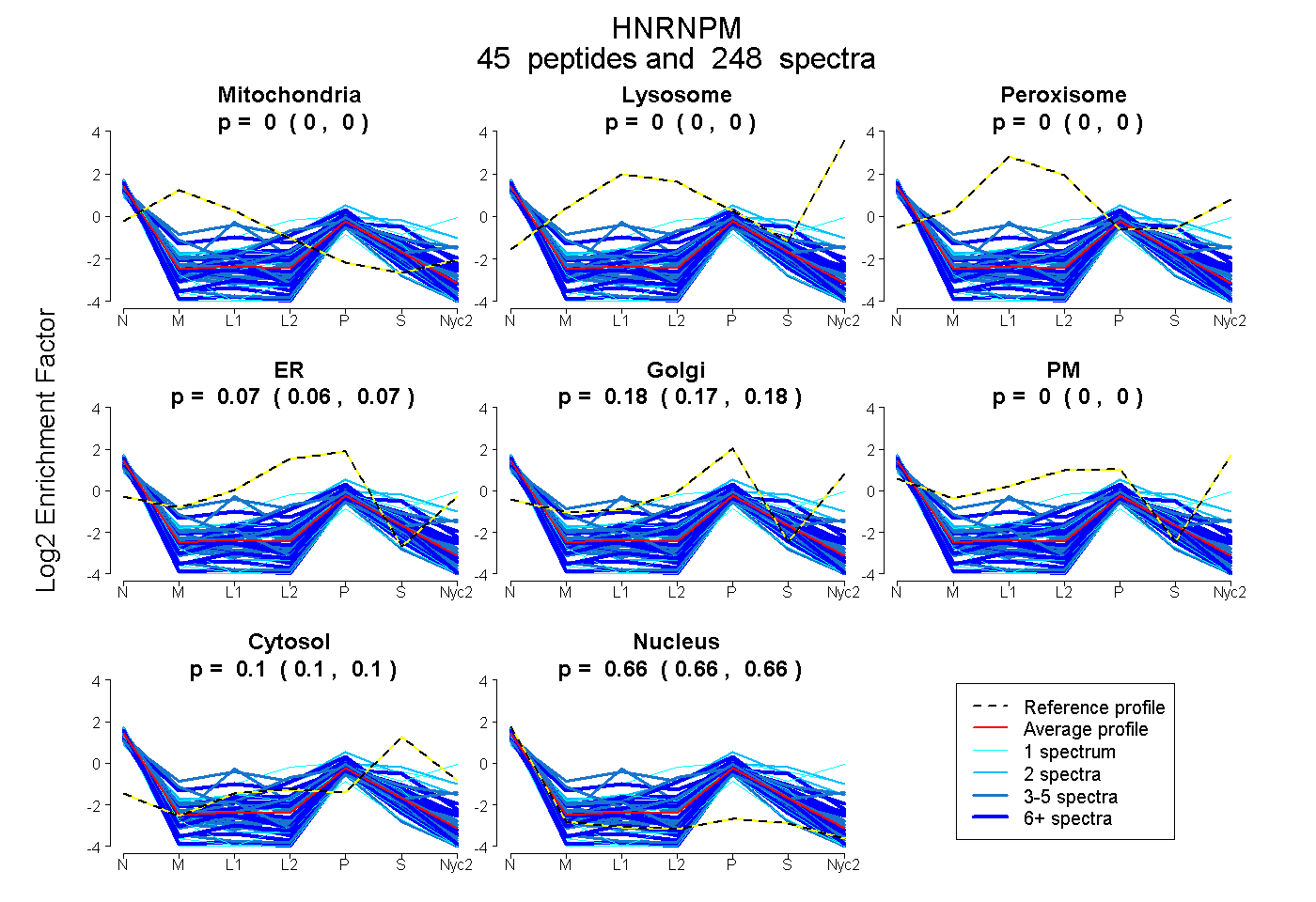
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.059 | 0.073
0.168 | 0.183
0.000 | 0.000
0.097 | 0.101
0.656 | 0.660
peptides
spectra
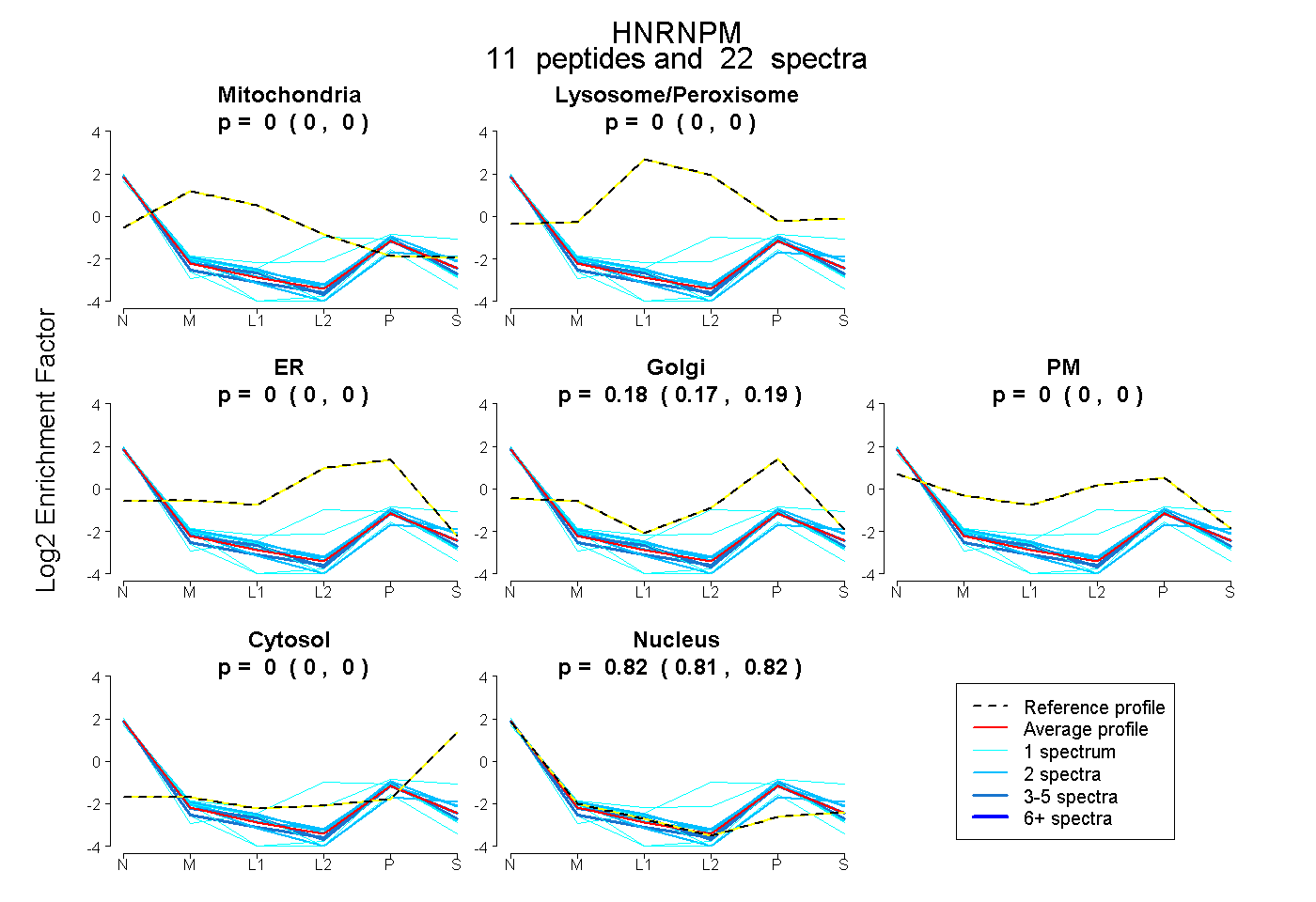
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.174 | 0.188
0.000 | 0.000
0.000 | 0.000
0.810 | 0.825
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
248 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.067 0.059 | 0.073 |
0.176 0.168 | 0.183 |
0.000 0.000 | 0.000 |
0.099 0.097 | 0.101 |
0.658 0.656 | 0.660 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.182 0.174 | 0.188 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.818 0.810 | 0.825 |
| 2 spectra, GNFGGSFAGSFGGAGGHAPGVAR | 0.000 | 0.000 | 0.000 | 0.062 | 0.000 | 0.015 | 0.923 | |||
| 1 spectrum, AIEMER | 0.000 | 0.000 | 0.341 | 0.000 | 0.000 | 0.000 | 0.659 | |||
| 1 spectrum, MAAPIDR | 0.000 | 0.000 | 0.000 | 0.030 | 0.307 | 0.140 | 0.523 | |||
| 4 spectra, FESPEVAER | 0.000 | 0.000 | 0.000 | 0.156 | 0.000 | 0.000 | 0.844 | |||
| 1 spectrum, VGSEIER | 0.000 | 0.000 | 0.000 | 0.157 | 0.000 | 0.000 | 0.843 | |||
| 1 spectrum, AFITNIPFDVK | 0.000 | 0.000 | 0.000 | 0.012 | 0.000 | 0.000 | 0.988 | |||
| 2 spectra, INEILSNALK | 0.000 | 0.000 | 0.000 | 0.209 | 0.000 | 0.000 | 0.791 | |||
| 5 spectra, VGQTIER | 0.000 | 0.000 | 0.000 | 0.165 | 0.000 | 0.000 | 0.835 | |||
| 2 spectra, ACQIFVR | 0.000 | 0.000 | 0.000 | 0.217 | 0.000 | 0.000 | 0.783 | |||
| 1 spectrum, HSLSGRPLK | 0.000 | 0.000 | 0.000 | 0.149 | 0.000 | 0.000 | 0.851 | |||
| 2 spectra, ISGAGMER | 0.000 | 0.000 | 0.000 | 0.243 | 0.000 | 0.000 | 0.757 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
16 spectra |
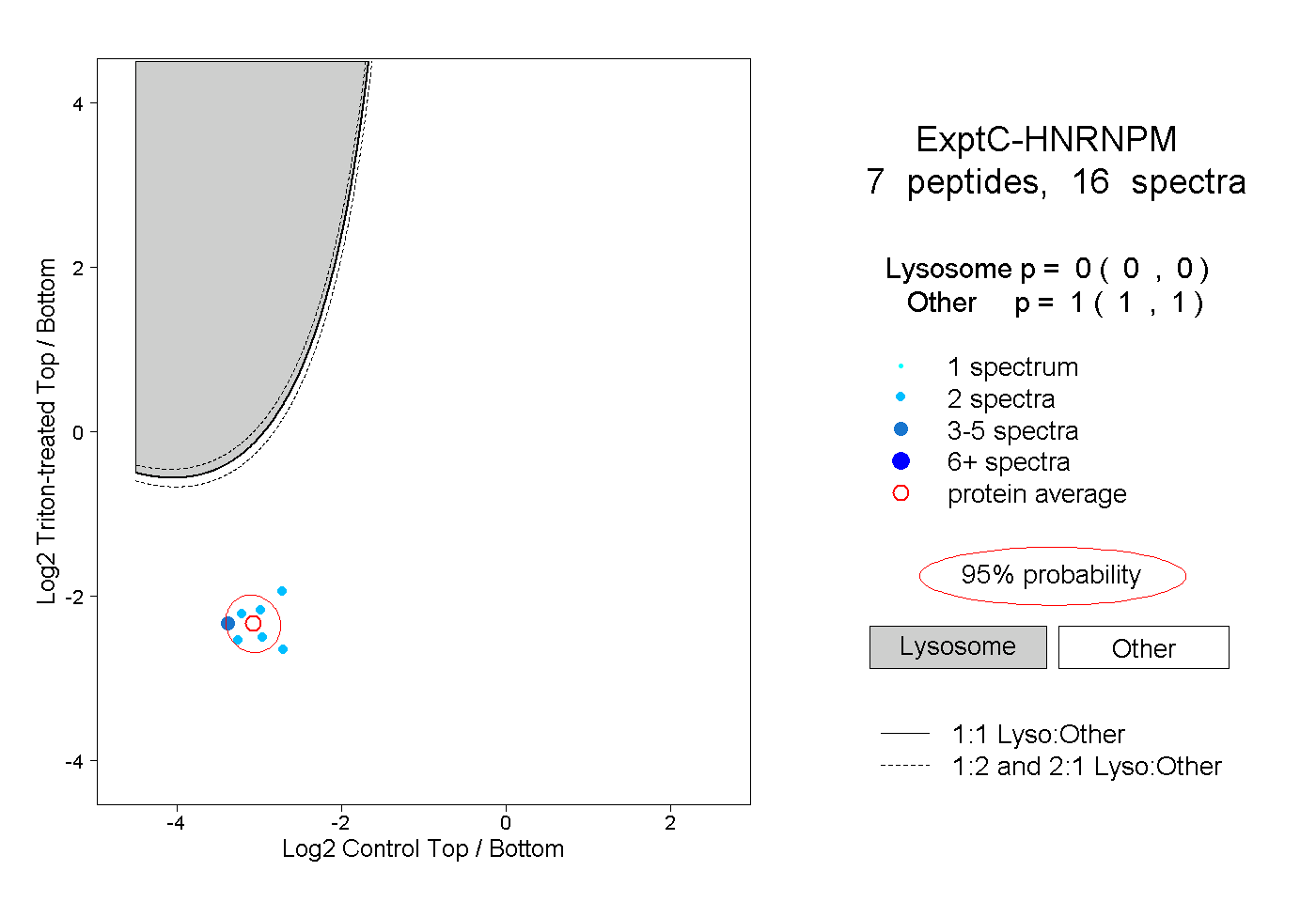 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
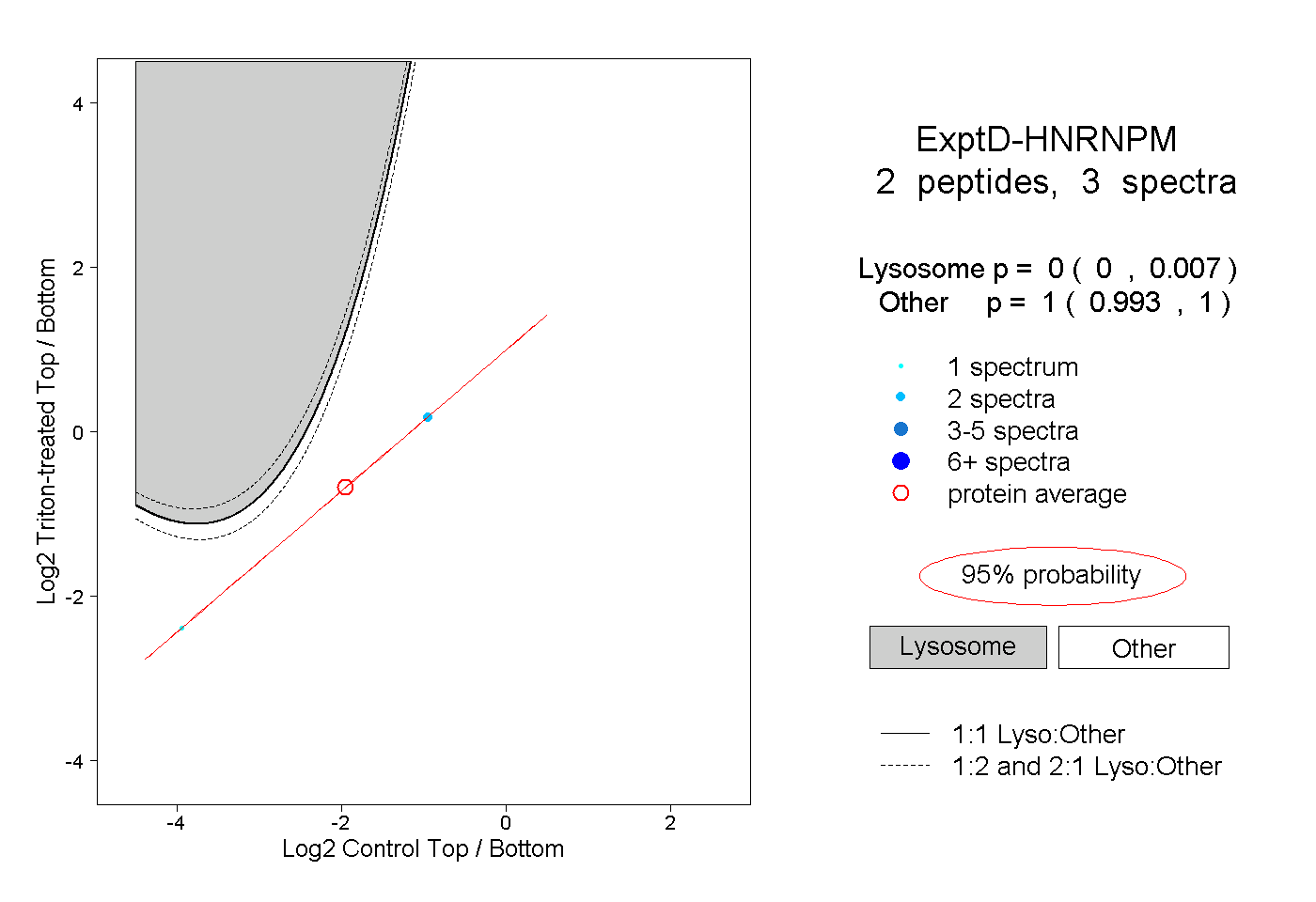 |
0.000 0.000 | 0.007 |
1.000 0.993 | 1.000 |