peptides
spectra
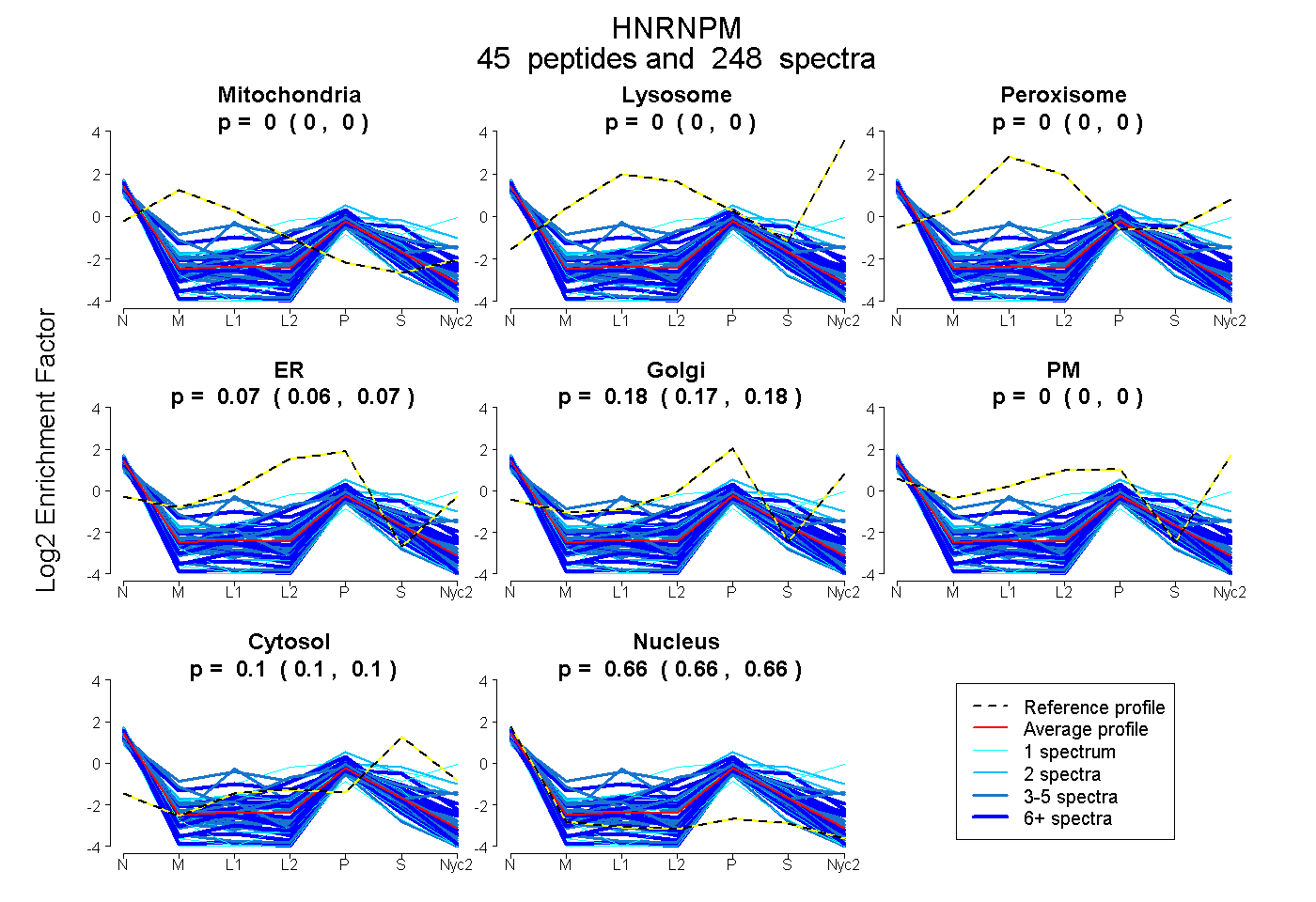
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.059 | 0.073
0.168 | 0.183
0.000 | 0.000
0.097 | 0.101
0.656 | 0.660
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
248 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.067 0.059 | 0.073 |
0.176 0.168 | 0.183 |
0.000 0.000 | 0.000 |
0.099 0.097 | 0.101 |
0.658 0.656 | 0.660 |
| 4 spectra, ADILEDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.170 | 0.000 | 0.000 | 0.830 | ||
| 10 spectra, MGPGIDR | 0.000 | 0.000 | 0.000 | 0.295 | 0.000 | 0.000 | 0.110 | 0.594 | ||
| 1 spectrum, MGPAIER | 0.000 | 0.000 | 0.000 | 0.192 | 0.000 | 0.000 | 0.132 | 0.676 | ||
| 1 spectrum, VGEVTYVELLMDAEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.082 | 0.000 | 0.000 | 0.918 | ||
| 3 spectra, MATGLER | 0.000 | 0.000 | 0.000 | 0.060 | 0.103 | 0.000 | 0.039 | 0.799 | ||
| 7 spectra, VGSEIER | 0.000 | 0.000 | 0.000 | 0.000 | 0.107 | 0.000 | 0.076 | 0.817 | ||
| 2 spectra, MEESMK | 0.000 | 0.000 | 0.000 | 0.199 | 0.224 | 0.000 | 0.302 | 0.275 | ||
| 1 spectrum, MGPLGLDHMASSIER | 0.000 | 0.000 | 0.000 | 0.000 | 0.123 | 0.305 | 0.283 | 0.289 | ||
| 5 spectra, VGQTIER | 0.014 | 0.000 | 0.000 | 0.115 | 0.054 | 0.000 | 0.089 | 0.729 | ||
| 10 spectra, IGGMEGPFGGGMENMGR | 0.000 | 0.000 | 0.171 | 0.175 | 0.075 | 0.000 | 0.151 | 0.429 | ||
| 7 spectra, MGLAMGGAGGASFDR | 0.000 | 0.000 | 0.000 | 0.205 | 0.151 | 0.000 | 0.134 | 0.511 | ||
| 5 spectra, GNFGGSFAGSFGGAGGHAPGVAR | 0.136 | 0.000 | 0.113 | 0.337 | 0.000 | 0.000 | 0.026 | 0.388 | ||
| 2 spectra, AAEVLNK | 0.000 | 0.000 | 0.000 | 0.191 | 0.000 | 0.000 | 0.060 | 0.750 | ||
| 8 spectra, MVPTGMGAGLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 | 0.000 | 0.950 | ||
| 20 spectra, MGQTMER | 0.000 | 0.000 | 0.000 | 0.000 | 0.275 | 0.000 | 0.064 | 0.661 | ||
| 3 spectra, MGLSMDR | 0.000 | 0.000 | 0.000 | 0.093 | 0.241 | 0.000 | 0.038 | 0.629 | ||
| 4 spectra, MAAPIDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.209 | 0.000 | 0.023 | 0.768 | ||
| 4 spectra, MGPAMGPALGAGIER | 0.000 | 0.000 | 0.000 | 0.250 | 0.000 | 0.134 | 0.257 | 0.359 | ||
| 4 spectra, AFITNIPFDVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.201 | 0.000 | 0.167 | 0.632 | ||
| 3 spectra, MGPVMDR | 0.032 | 0.000 | 0.000 | 0.000 | 0.396 | 0.046 | 0.059 | 0.466 | ||
| 4 spectra, ACQIFVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.360 | 0.000 | 0.020 | 0.620 | ||
| 2 spectra, GCAVVEFK | 0.000 | 0.000 | 0.000 | 0.052 | 0.091 | 0.212 | 0.414 | 0.231 | ||
| 4 spectra, MGLVMDR | 0.000 | 0.000 | 0.000 | 0.260 | 0.000 | 0.000 | 0.102 | 0.638 | ||
| 1 spectrum, INDIIAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.233 | 0.767 | ||
| 14 spectra, FGSGMNMGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.170 | 0.000 | 0.015 | 0.814 | ||
| 3 spectra, NLPFDFTWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 | 0.000 | 0.000 | 0.941 | ||
| 3 spectra, INEILSNALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.285 | 0.000 | 0.002 | 0.713 | ||
| 1 spectrum, FNECGHVLYADIK | 0.000 | 0.000 | 0.065 | 0.196 | 0.000 | 0.216 | 0.327 | 0.195 | ||
| 1 spectrum, HSLSGRPLK | 0.000 | 0.000 | 0.000 | 0.233 | 0.000 | 0.000 | 0.025 | 0.742 | ||
| 5 spectra, IGSGVER | 0.000 | 0.000 | 0.000 | 0.033 | 0.135 | 0.000 | 0.045 | 0.786 | ||
| 2 spectra, LGSTVFVANLDYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.188 | 0.000 | 0.035 | 0.776 | ||
| 4 spectra, MGAGMGFGLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 | 0.000 | 0.861 | ||
| 19 spectra, MGSGIER | 0.000 | 0.000 | 0.000 | 0.266 | 0.000 | 0.000 | 0.083 | 0.651 | ||
| 1 spectrum, QGGGGAGGSVPGIER | 0.000 | 0.000 | 0.000 | 0.000 | 0.041 | 0.000 | 0.000 | 0.959 | ||
| 4 spectra, GEERPTQNEK | 0.000 | 0.000 | 0.000 | 0.083 | 0.085 | 0.000 | 0.037 | 0.795 | ||
| 3 spectra, GCGVVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.243 | 0.000 | 0.069 | 0.687 | ||
| 4 spectra, FESPEVAER | 0.000 | 0.000 | 0.000 | 0.154 | 0.000 | 0.000 | 0.165 | 0.681 | ||
| 8 spectra, MGANNLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.140 | 0.000 | 0.363 | 0.496 | ||
| 15 spectra, MGANSLER | 0.000 | 0.000 | 0.000 | 0.294 | 0.024 | 0.000 | 0.204 | 0.479 | ||
| 5 spectra, EVFSMAGVVVR | 0.000 | 0.000 | 0.000 | 0.116 | 0.000 | 0.000 | 0.135 | 0.749 | ||
| 12 spectra, MGAGLGHGMDR | 0.000 | 0.000 | 0.000 | 0.434 | 0.000 | 0.000 | 0.085 | 0.482 | ||
| 6 spectra, MGSGVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.088 | 0.000 | 0.000 | 0.912 | ||
| 3 spectra, MGSVER | 0.000 | 0.000 | 0.000 | 0.261 | 0.046 | 0.000 | 0.094 | 0.599 | ||
| 15 spectra, ISGAGMER | 0.000 | 0.000 | 0.000 | 0.000 | 0.183 | 0.000 | 0.044 | 0.773 | ||
| 5 spectra, MATGELR | 0.000 | 0.000 | 0.126 | 0.224 | 0.000 | 0.000 | 0.015 | 0.634 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
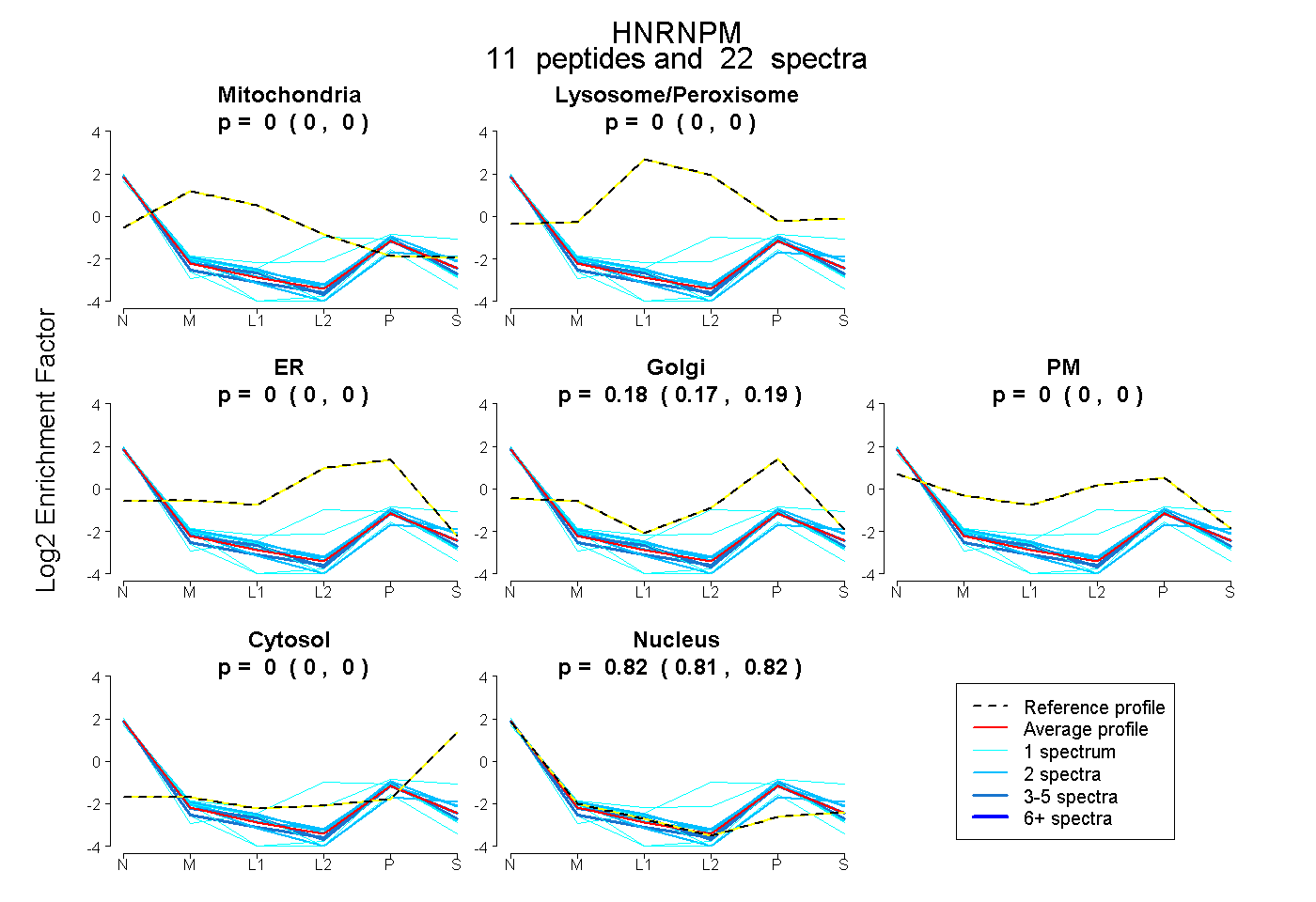 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.182 0.174 | 0.188 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.818 0.810 | 0.825 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
16 spectra |
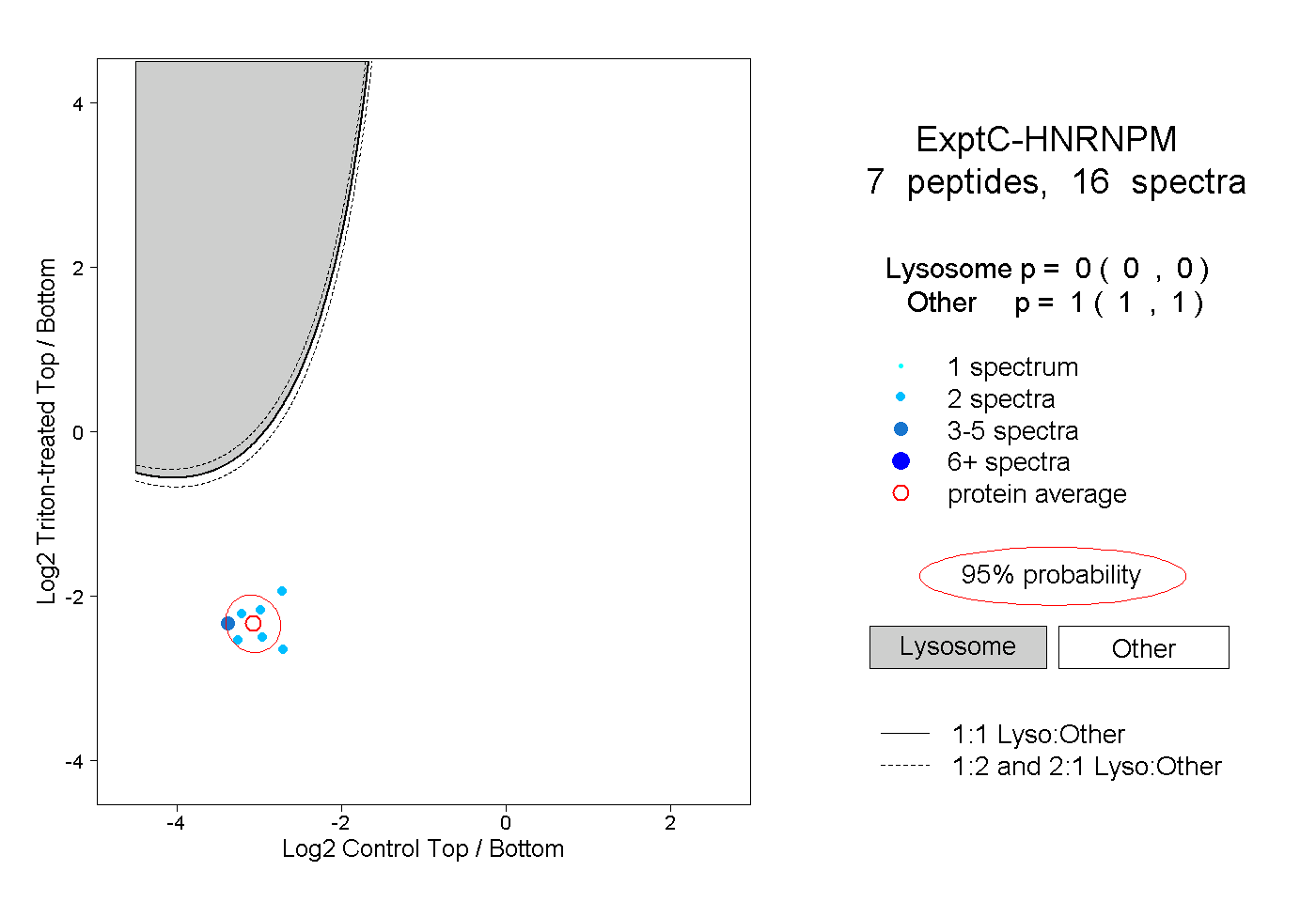 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
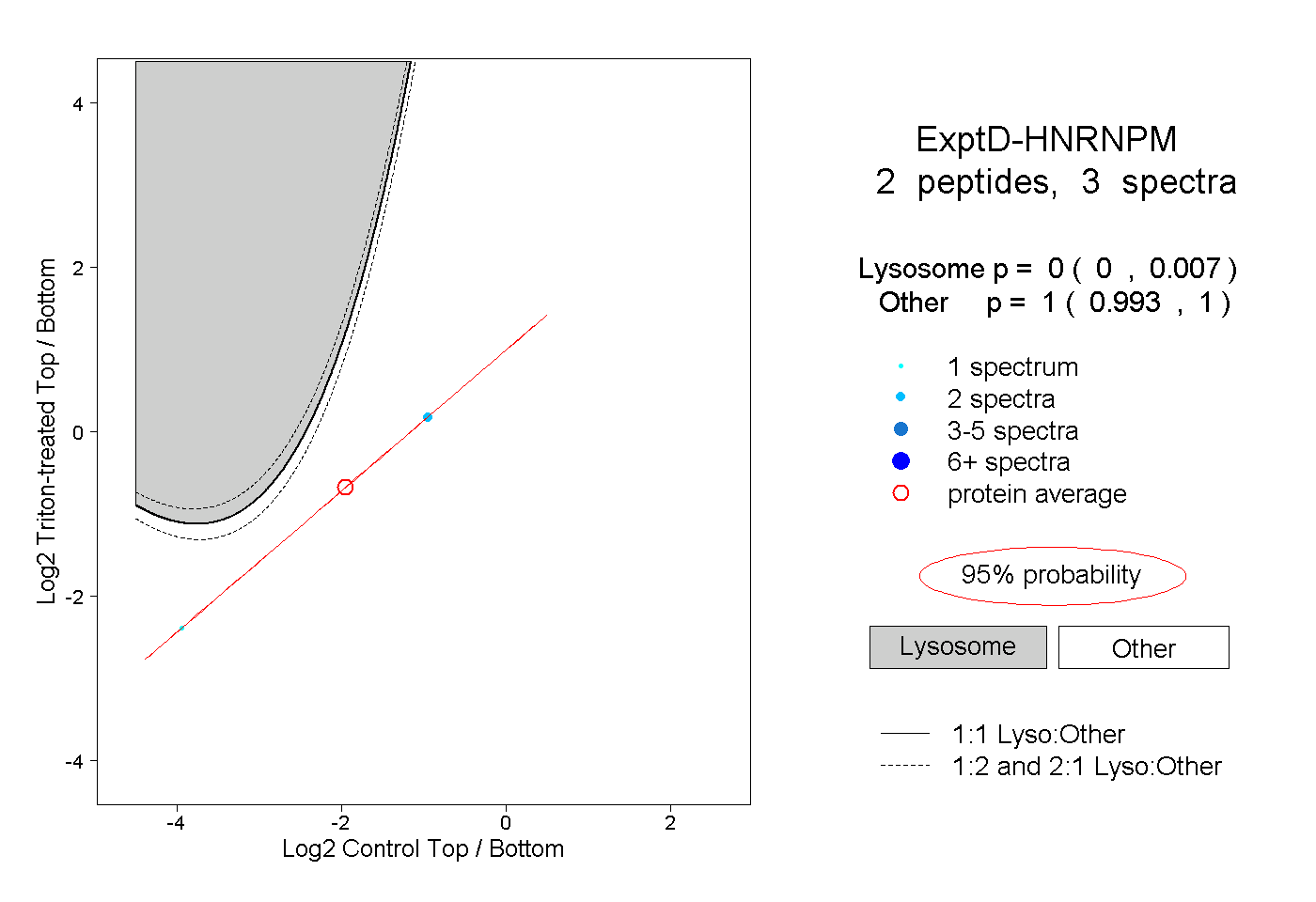 |
0.000 0.000 | 0.007 |
1.000 0.993 | 1.000 |