CYBB
[ENSRNOP00000031063]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 15
15
peptides |
38
spectra |
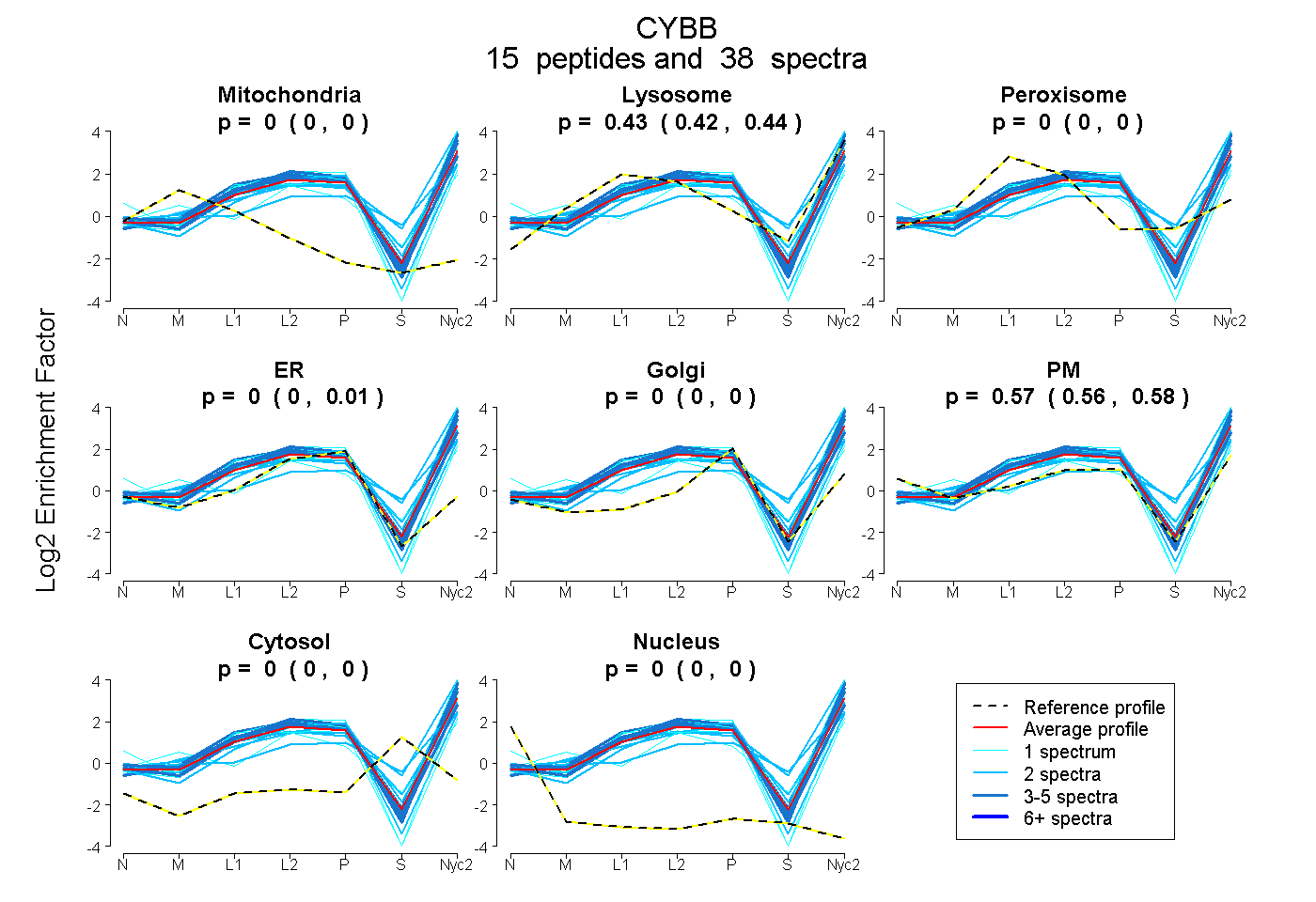 |
0.000
0.000 | 0.000 |
0.431
0.420 | 0.441 |
|
0.000
0.000 | 0.000 |
0.000
0.000 | 0.005 |
0.000
0.000 | 0.000 |
0.569
0.557 | 0.578 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 5
5
peptides |
13
spectra |
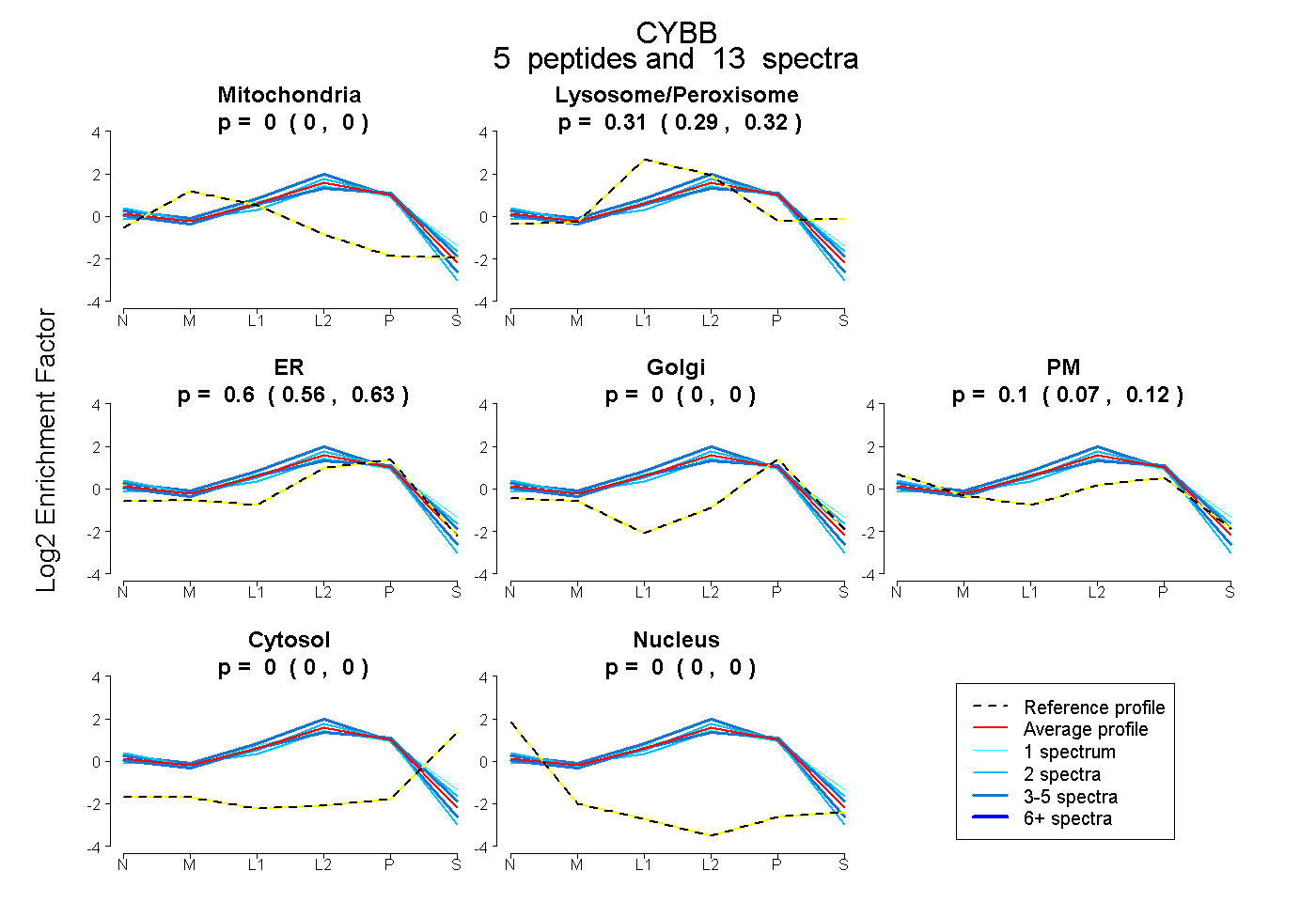 |
0.000
0.000 | 0.000 |
|
0.305
0.287 | 0.321 |
|
0.598
0.562 | 0.628 |
0.000
0.000 | 0.000 |
0.097
0.067 | 0.122 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt C |
 20
20
peptides |
105
spectra |
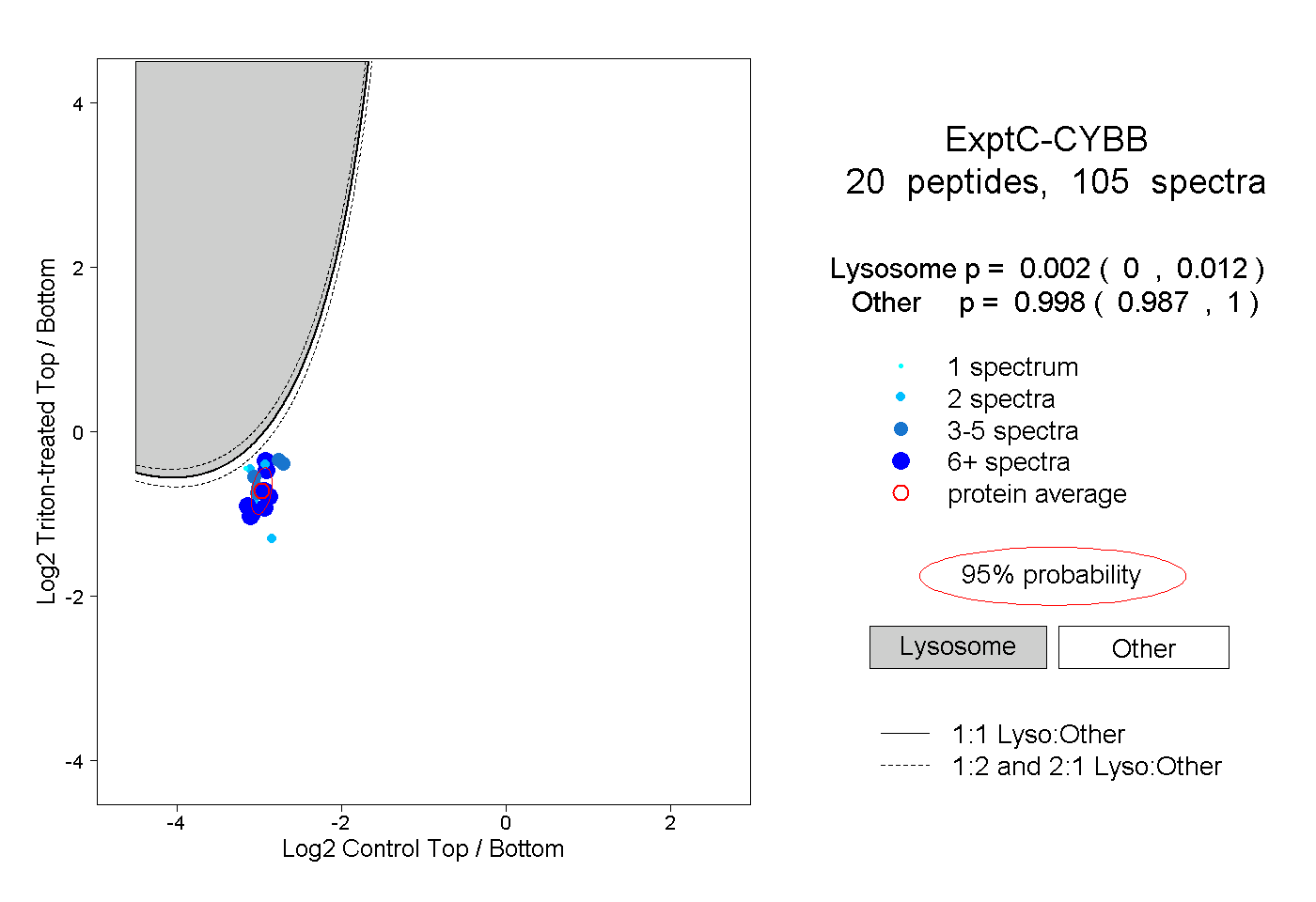 |
|
0.002
0.000 | 0.012 |
|
|
|
|
|
|
|
0.998
0.987 | 1.000 |
| 1 spectrum, YNYTR |
|
0.102 |
|
|
|
|
|
|
|
0.898 |
| 7 spectra, GQTSDSLK |
|
0.010 |
|
|
|
|
|
|
|
0.990 |
| 6 spectra, FAGNPPMTWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IGVFLCGPEALAK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 6 spectra, CPQVSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, VVTHPFK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 4 spectra, MEVGQYIFVK |
|
0.019 |
|
|
|
|
|
|
|
0.981 |
| 9 spectra, LLGSALALAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, NLLSFLR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 5 spectra, TLYGRPNWDNEFK |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 6 spectra, NLTFHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TIELQMK |
|
0.019 |
|
|
|
|
|
|
|
0.981 |
| 5 spectra, EHNLDVCADK |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 3 spectra, VYDDEPK |
|
0.006 |
|
|
|
|
|
|
|
0.994 |
| 15 spectra, YCDNATSLR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 7 spectra, QSISNSESGPR |
|
0.031 |
|
|
|
|
|
|
|
0.969 |
| 3 spectra, ECPVPK |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 2 spectra, DVITGLK |
|
0.062 |
|
|
|
|
|
|
|
0.938 |
| 2 spectra, TIASQHPNTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GVHFIFNK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt D |
 8
8
peptides |
11
spectra |
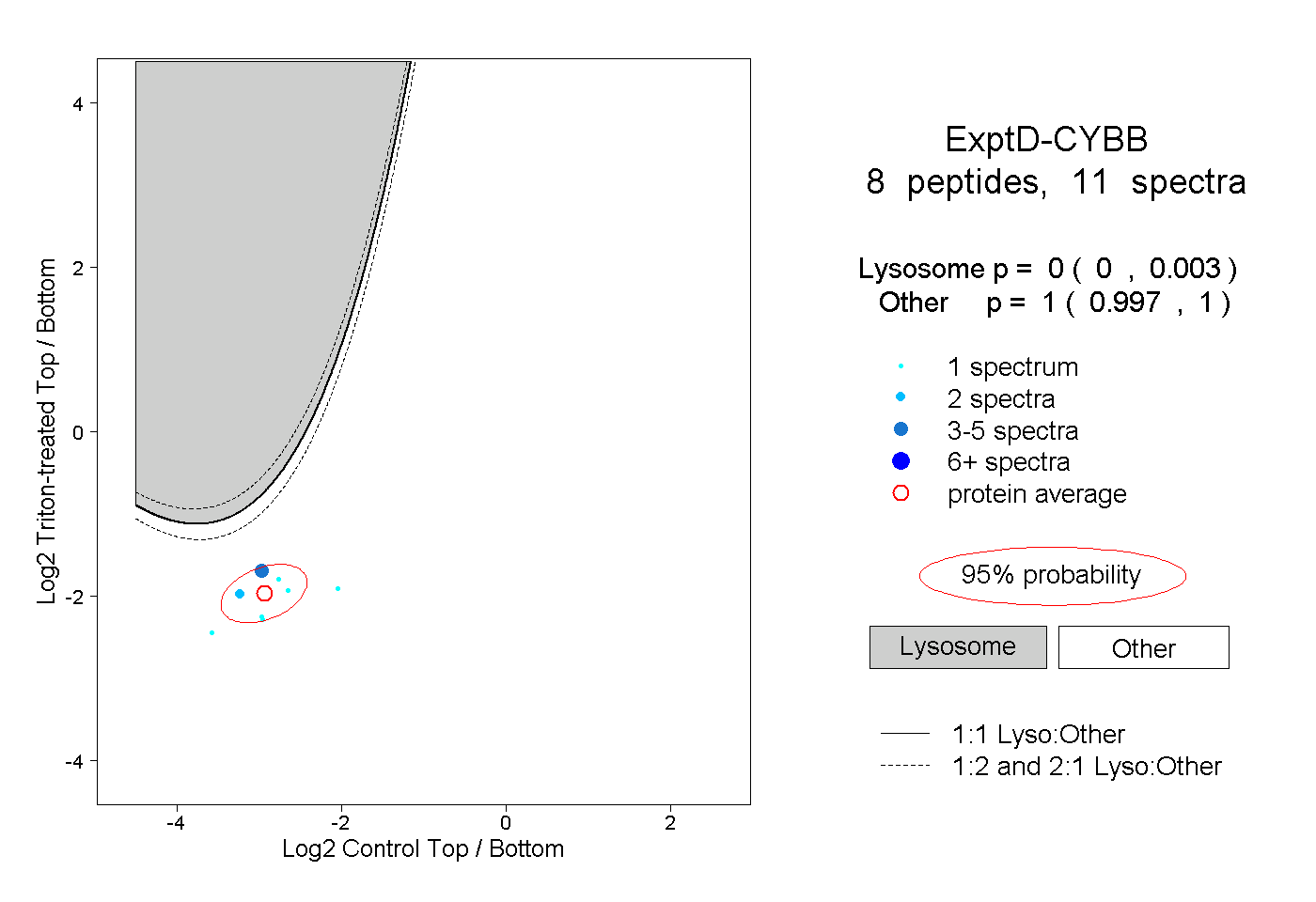 |
|
0.000
0.000 | 0.003 |
|
|
|
|
|
|
|
1.000
0.997 | 1.000 |



