peptides
spectra
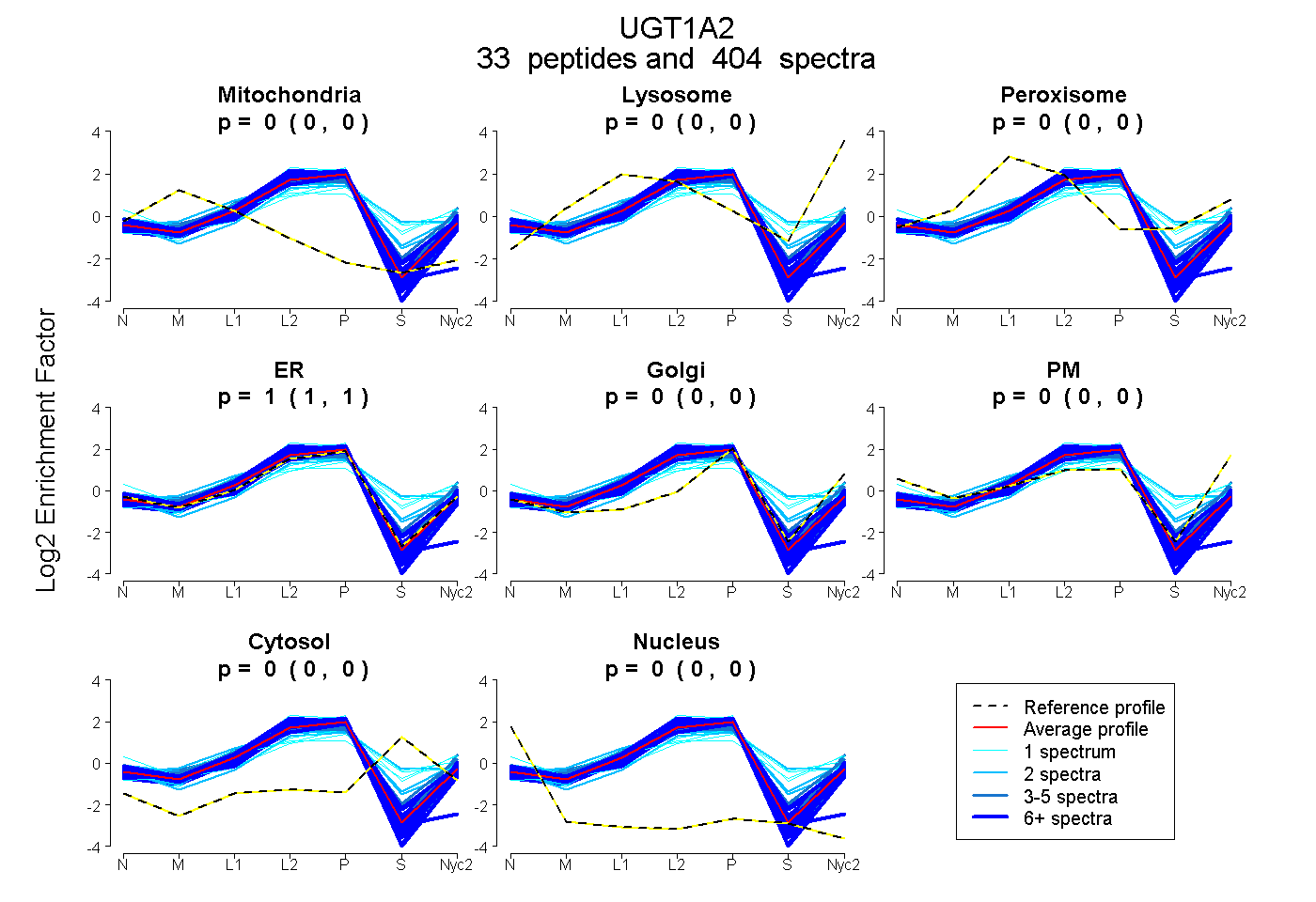
0.000 | 0.000
0.001 | 0.004
0.000 | 0.000
0.996 | 0.998
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
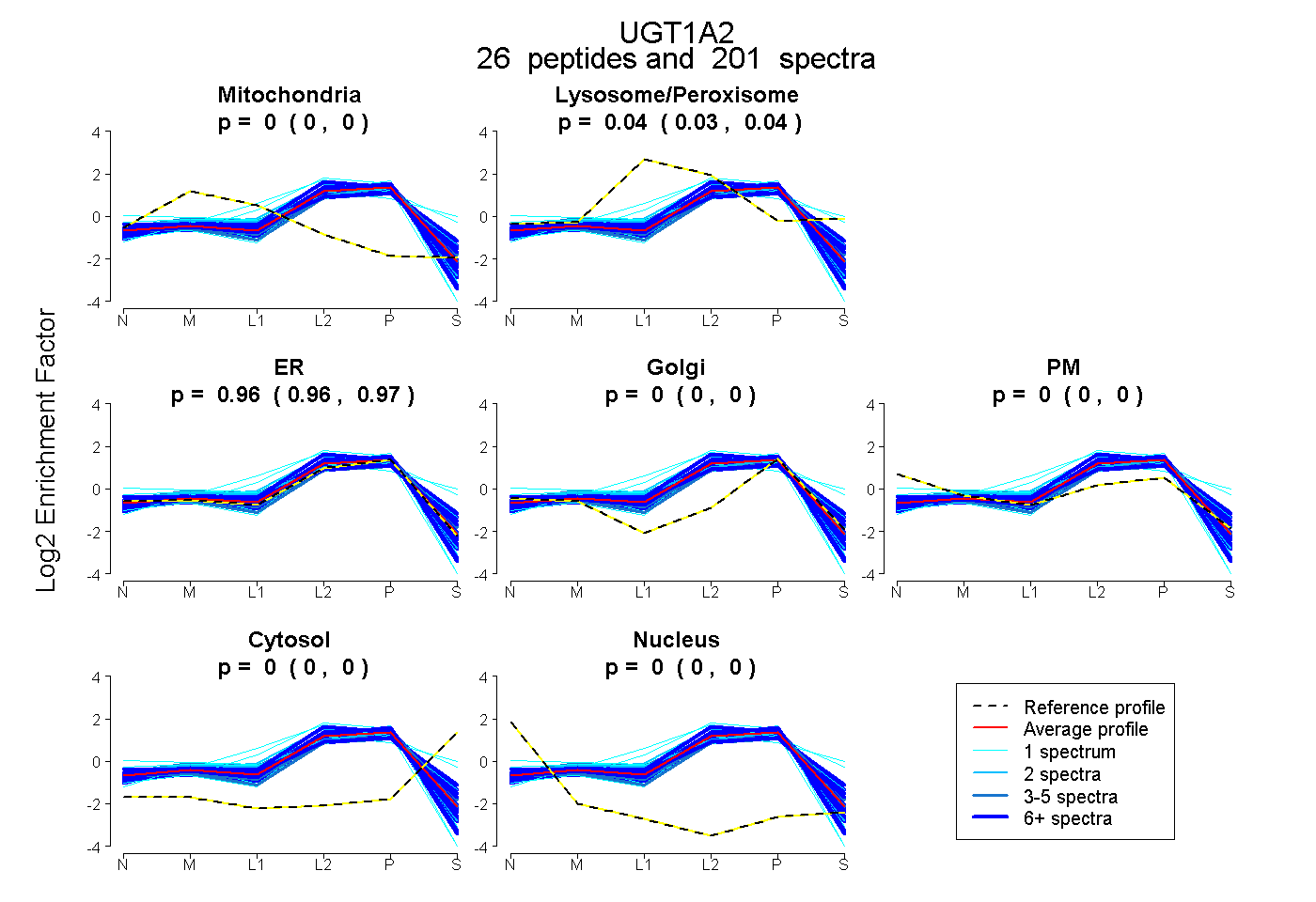
0.000 | 0.000
0.035 | 0.039
0.960 | 0.965
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
404 spectra |
 |
0.000 0.000 | 0.000 |
0.003 0.001 | 0.004 |
0.000 0.000 | 0.000 |
0.997 0.996 | 0.998 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
201 spectra |
 |
0.000 0.000 | 0.000 |
0.037 0.035 | 0.039 |
0.963 0.960 | 0.965 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, SFGNNHFAASSPLMAPLR | 0.000 | 0.175 | 0.581 | 0.000 | 0.000 | 0.244 | 0.000 | |||
| 1 spectrum, LSSLHK | 0.000 | 0.123 | 0.877 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LLVVPQDGSHWLSMK | 0.000 | 0.241 | 0.618 | 0.000 | 0.000 | 0.141 | 0.000 | |||
| 4 spectra, SLSSNTDR | 0.000 | 0.000 | 0.867 | 0.133 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, IPQTVLWR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, DYPRPIMPNMVFIGGINCLQK | 0.000 | 0.079 | 0.867 | 0.000 | 0.000 | 0.054 | 0.000 | |||
| 1 spectrum, NMIIALTENFLCR | 0.030 | 0.000 | 0.970 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, YEILASDLLK | 0.000 | 0.059 | 0.941 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TVINNK | 0.057 | 0.000 | 0.943 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GHEVVVIAPEASIHIK | 0.000 | 0.323 | 0.677 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, VVYSPYGSLATEILQK | 0.000 | 0.135 | 0.731 | 0.103 | 0.005 | 0.026 | 0.000 | |||
| 18 spectra, GAGVTLNVLEMTADDLENALK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, LPSVYLFR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, NTILVK | 0.000 | 0.277 | 0.414 | 0.224 | 0.085 | 0.000 | 0.000 | |||
| 7 spectra, DSATLSFLR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, SVFDQDPFLLR | 0.000 | 0.014 | 0.939 | 0.000 | 0.000 | 0.047 | 0.000 | |||
| 13 spectra, EGSFYTMR | 0.000 | 0.027 | 0.904 | 0.000 | 0.000 | 0.069 | 0.000 | |||
| 5 spectra, DVSLPALHQNSLWLLR | 0.000 | 0.239 | 0.679 | 0.034 | 0.000 | 0.048 | 0.000 | |||
| 2 spectra, FFIDSQWK | 0.000 | 0.046 | 0.954 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, DLLSPASIWLMR | 0.000 | 0.075 | 0.833 | 0.000 | 0.000 | 0.092 | 0.000 | |||
| 8 spectra, GHDIVVLVPEVNLLLGESK | 0.000 | 0.243 | 0.538 | 0.170 | 0.000 | 0.048 | 0.000 | |||
| 1 spectrum, SFPVPYNLEELR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, EIVEHLSER | 0.082 | 0.135 | 0.738 | 0.046 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, YTGTRPSNLAK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 31 spectra, AMEIAEALGR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 25 spectra, MNFLQR | 0.000 | 0.039 | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
492 spectra |
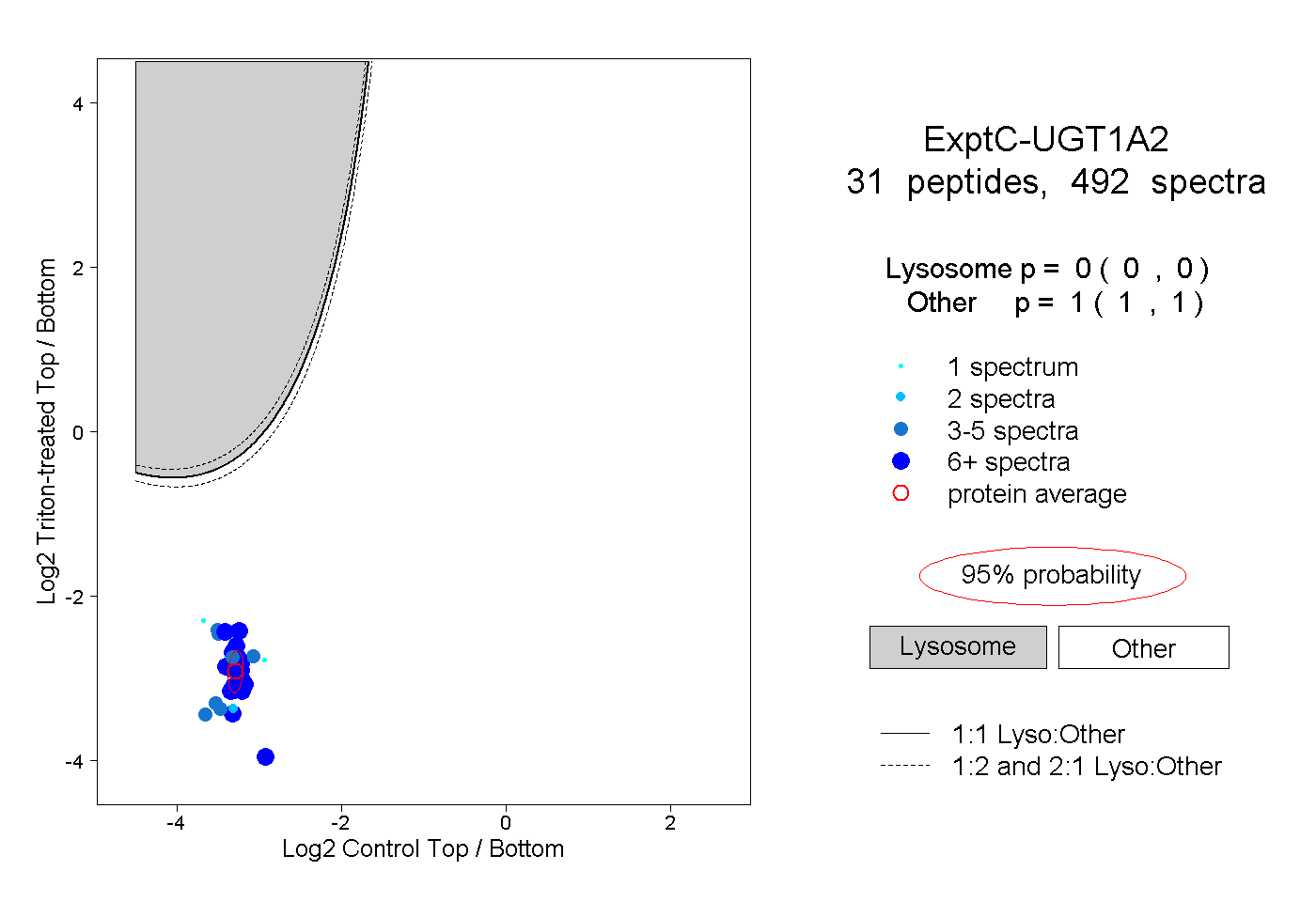 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
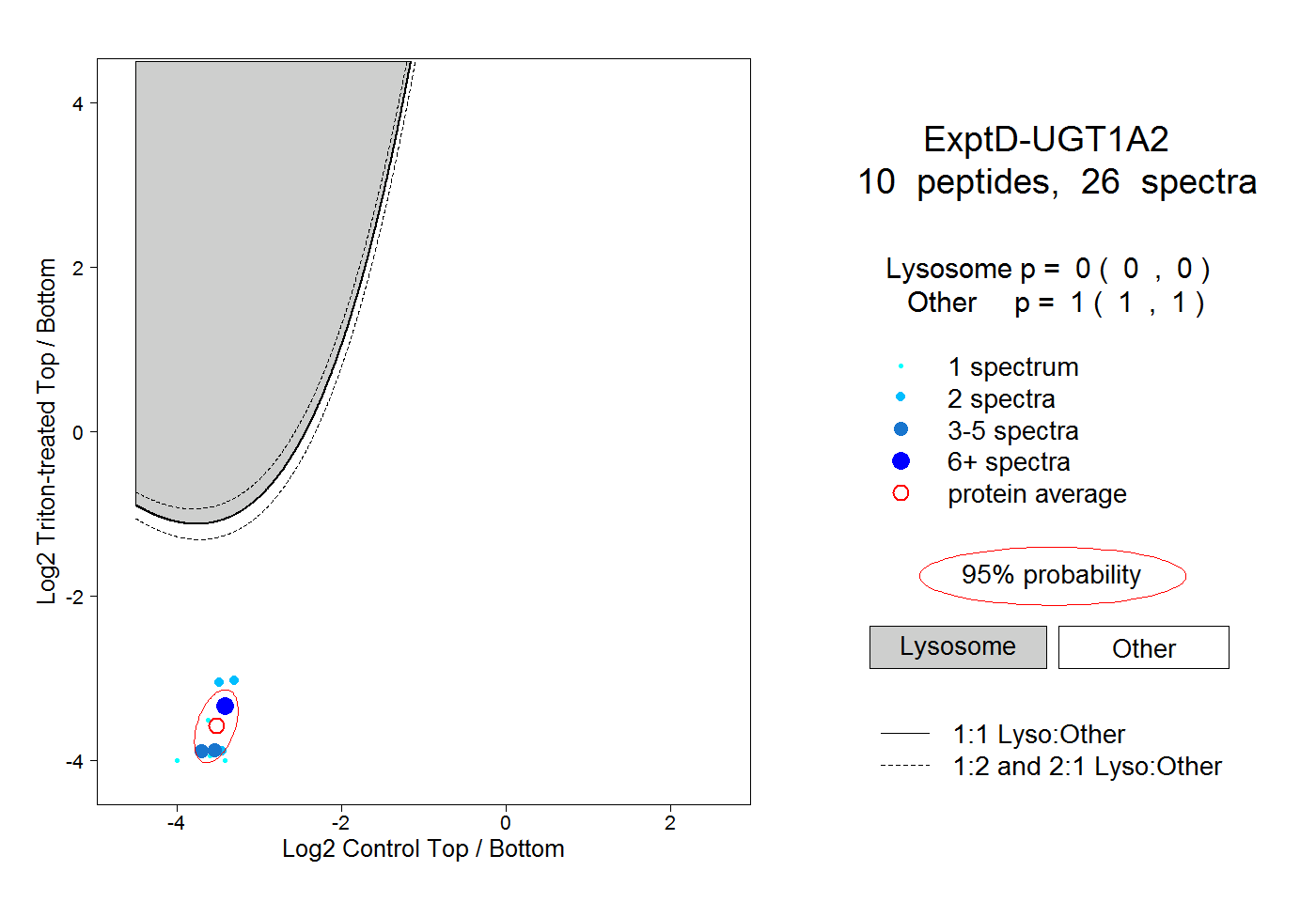 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |