peptides
spectra
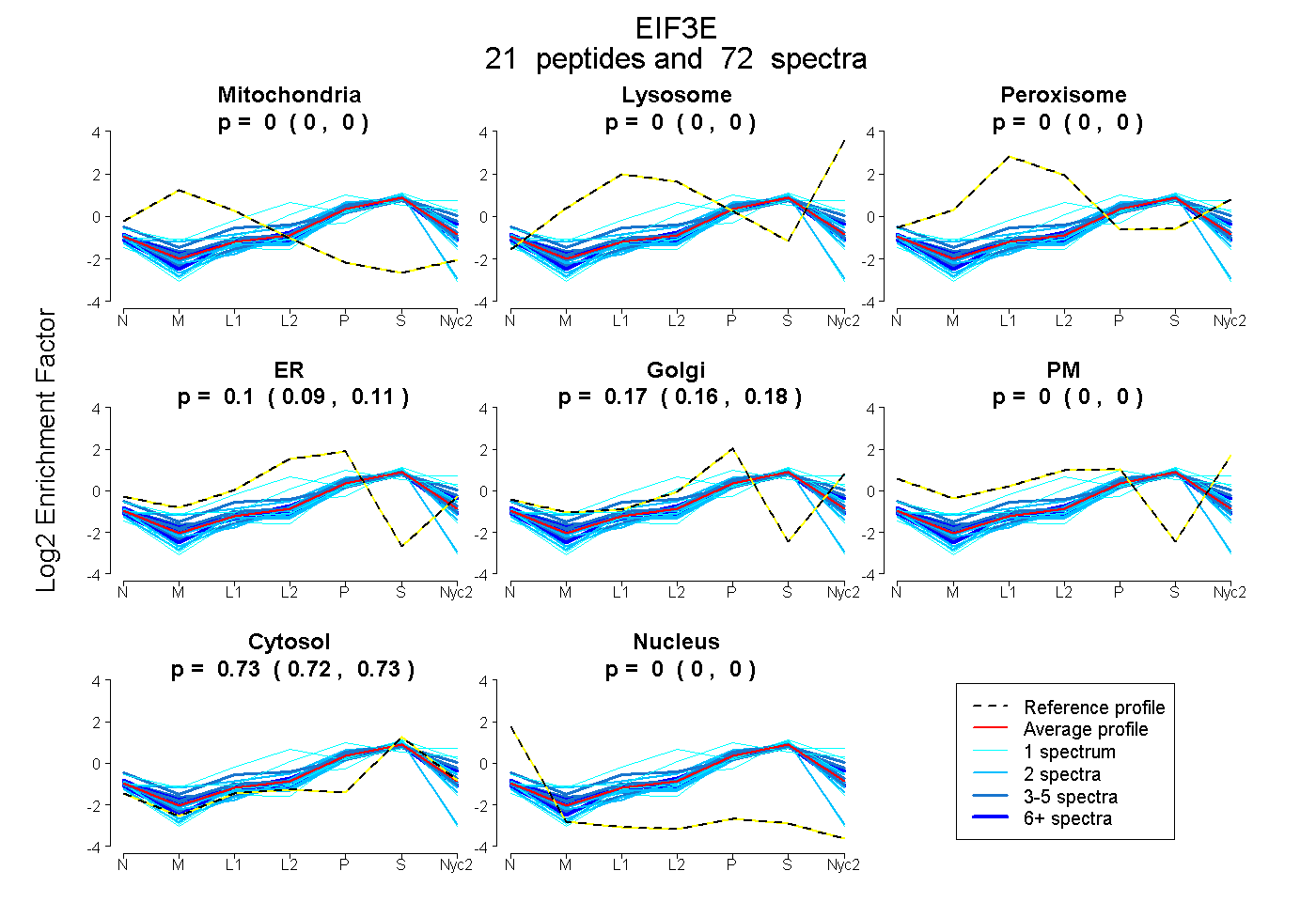
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.093 | 0.113
0.156 | 0.180
0.000 | 0.000
0.723 | 0.729
0.000 | 0.000
peptides
spectra
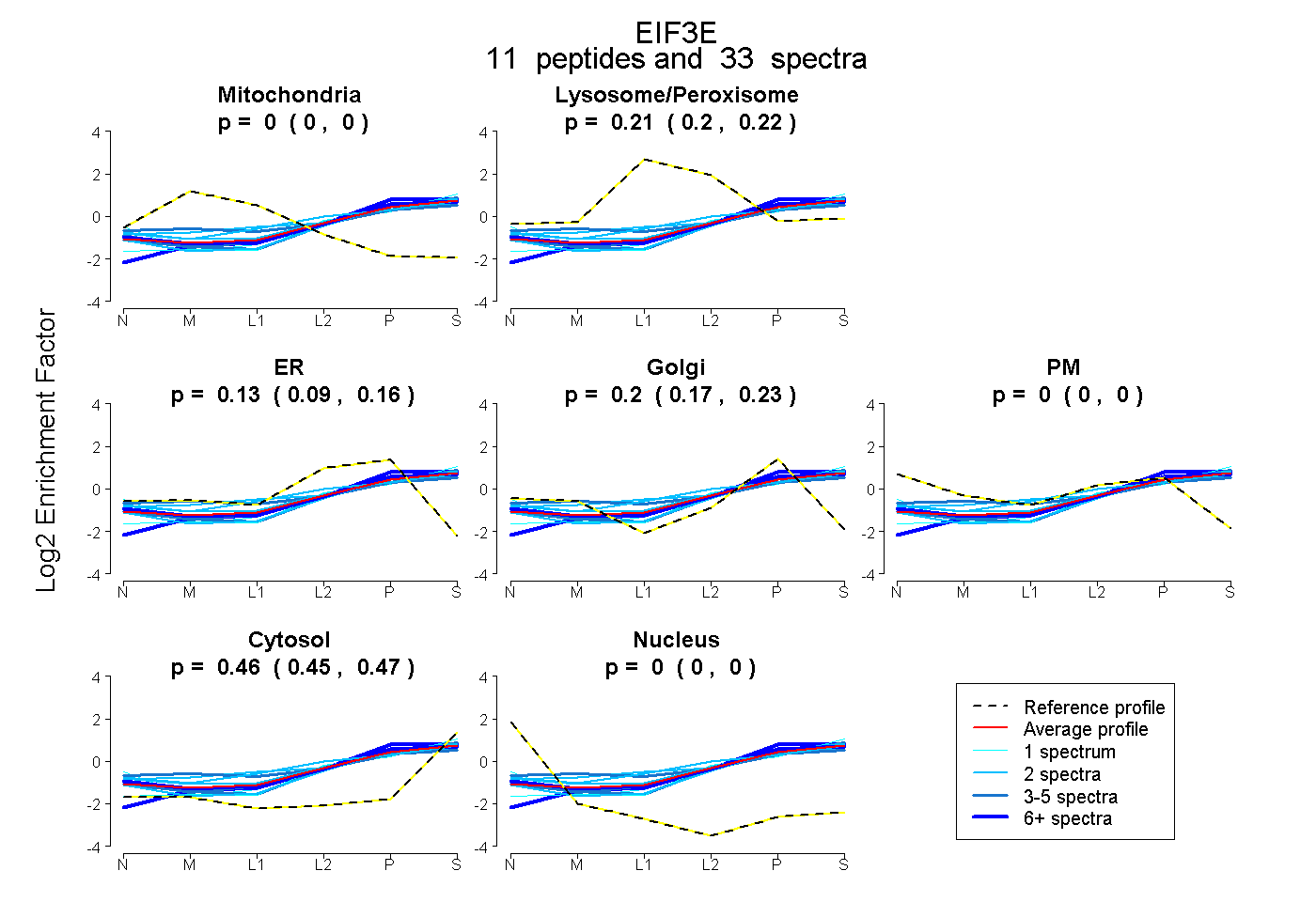
0.000 | 0.000
0.198 | 0.224
0.094 | 0.155
0.175 | 0.230
0.000 | 0.000
0.445 | 0.466
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
72 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.104 0.093 | 0.113 |
0.169 0.156 | 0.180 |
0.000 0.000 | 0.000 |
0.726 0.723 | 0.729 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
 |
0.000 0.000 | 0.000 |
0.212 0.198 | 0.224 |
0.128 0.094 | 0.155 |
0.204 0.175 | 0.230 |
0.000 0.000 | 0.000 |
0.457 0.445 | 0.466 |
0.000 0.000 | 0.000 |
| 2 spectra, QEYLDTLYR | 0.000 | 0.083 | 0.309 | 0.063 | 0.000 | 0.545 | 0.000 | |||
| 2 spectra, NLYSDDIPHALR | 0.000 | 0.279 | 0.000 | 0.324 | 0.000 | 0.396 | 0.000 | |||
| 6 spectra, VLVPATDR | 0.000 | 0.220 | 0.061 | 0.295 | 0.000 | 0.424 | 0.000 | |||
| 3 spectra, LFIFETFCR | 0.000 | 0.205 | 0.141 | 0.155 | 0.000 | 0.499 | 0.000 | |||
| 2 spectra, YLTTAVITNK | 0.000 | 0.366 | 0.000 | 0.259 | 0.000 | 0.375 | 0.000 | |||
| 7 spectra, IAHFLDR | 0.000 | 0.074 | 0.386 | 0.000 | 0.000 | 0.541 | 0.000 | |||
| 1 spectrum, ELLQGK | 0.000 | 0.191 | 0.136 | 0.225 | 0.000 | 0.448 | 0.000 | |||
| 3 spectra, NALSSLWGK | 0.000 | 0.321 | 0.000 | 0.331 | 0.000 | 0.348 | 0.000 | |||
| 4 spectra, MFEDPETTR | 0.000 | 0.079 | 0.320 | 0.076 | 0.000 | 0.525 | 0.000 | |||
| 1 spectrum, MLFDYLADK | 0.000 | 0.091 | 0.309 | 0.000 | 0.000 | 0.601 | 0.000 | |||
| 2 spectra, AEYDLTTR | 0.000 | 0.350 | 0.000 | 0.297 | 0.000 | 0.352 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
52 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
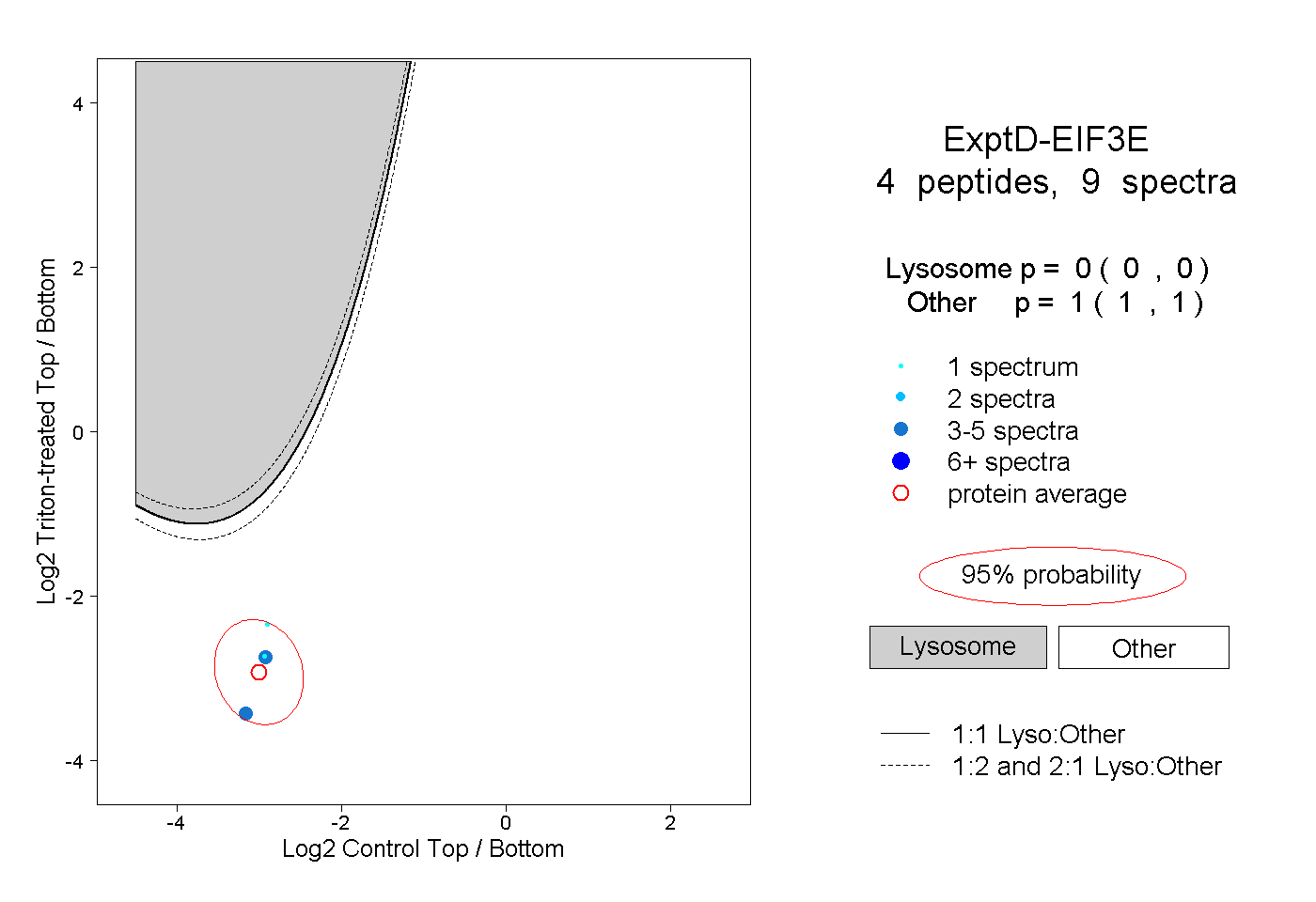 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |