peptides
spectra
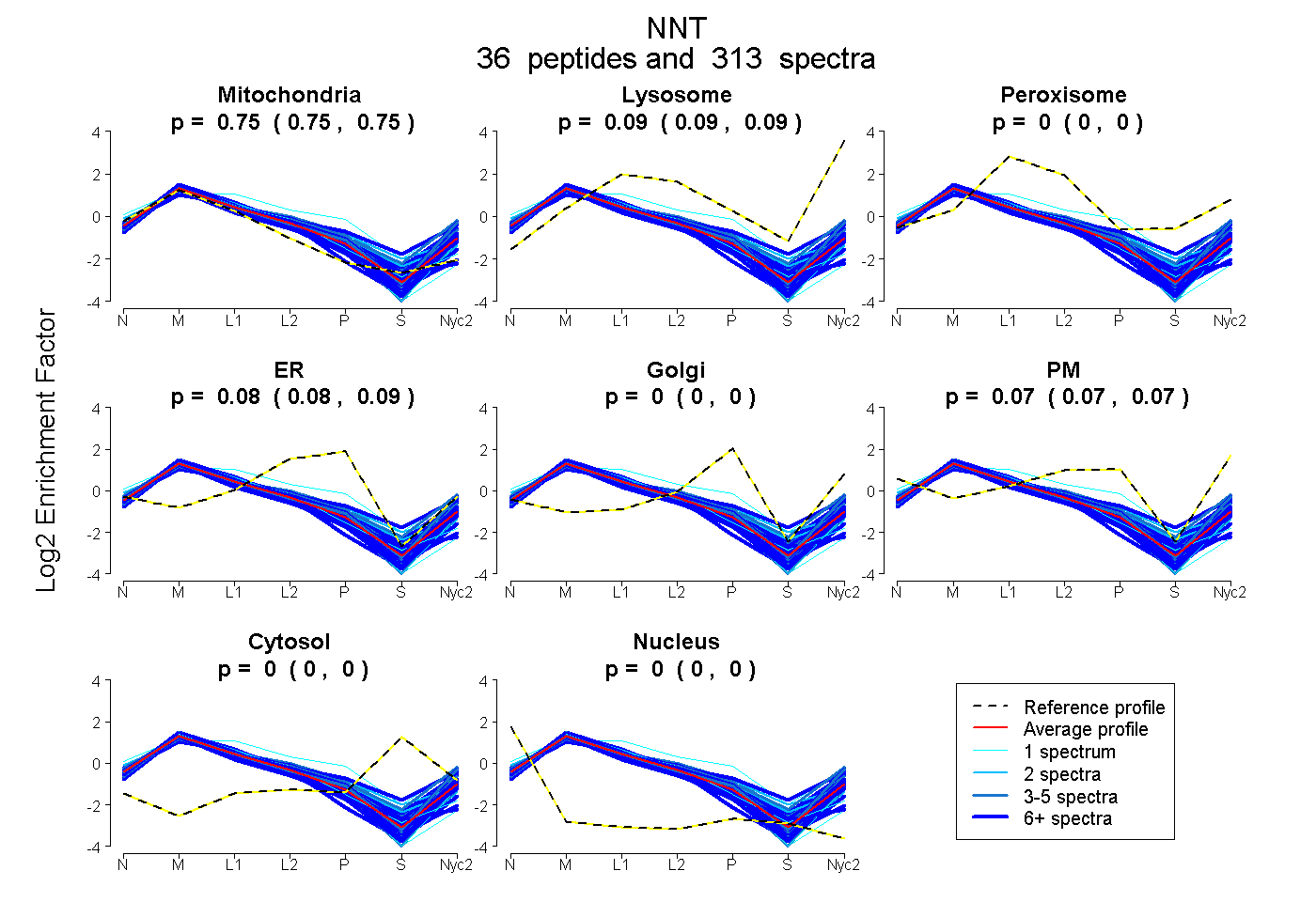
0.751 | 0.753
0.091 | 0.094
0.000 | 0.000
0.081 | 0.087
0.000 | 0.000
0.068 | 0.074
0.000 | 0.000
0.000 | 0.000
peptides
spectra
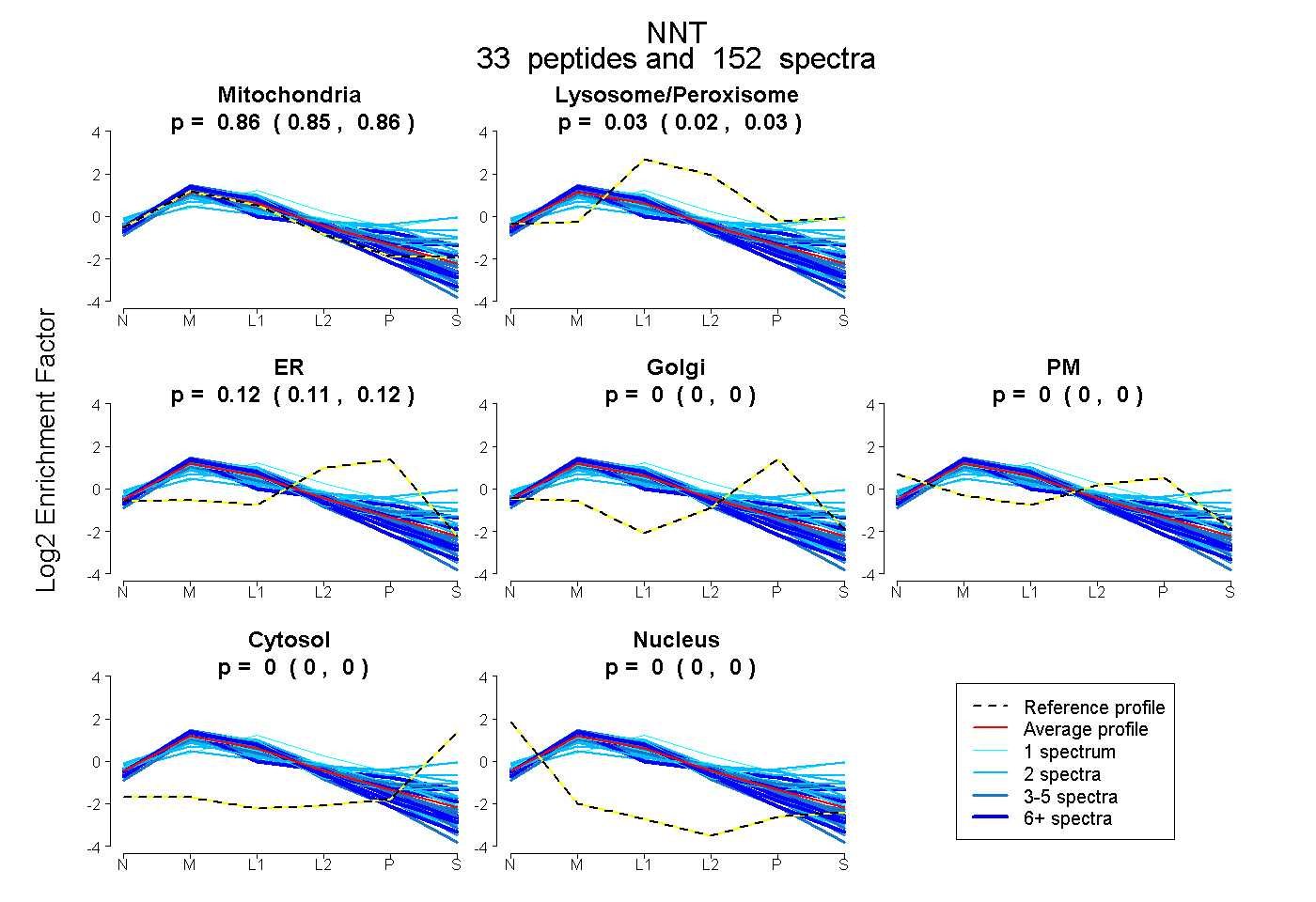
0.855 | 0.860
0.022 | 0.028
0.114 | 0.120
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
313 spectra |
 |
0.752 0.751 | 0.753 |
0.092 0.091 | 0.094 |
0.000 0.000 | 0.000 |
0.084 0.081 | 0.087 |
0.000 0.000 | 0.000 |
0.071 0.068 | 0.074 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
152 spectra |
 |
0.857 0.855 | 0.860 |
0.025 0.022 | 0.028 |
0.117 0.114 | 0.120 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 4 spectra, FPDDLYR | 0.878 | 0.000 | 0.122 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EVDILISTALIPGK | 0.284 | 0.307 | 0.000 | 0.194 | 0.000 | 0.214 | 0.000 | |||
| 1 spectrum, MLTEQGK | 0.901 | 0.000 | 0.099 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, AAALEQFK | 0.832 | 0.069 | 0.099 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VTIAQGYDALSSMANISGYK | 0.486 | 0.238 | 0.000 | 0.238 | 0.000 | 0.038 | 0.000 | |||
| 4 spectra, AQYPIADLVK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, SAPLLLPGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QLTVGVPK | 0.966 | 0.000 | 0.034 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, SMGAVVR | 0.886 | 0.000 | 0.114 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EVLASDLVVK | 0.991 | 0.000 | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, VALSPAGVQALVK | 0.997 | 0.000 | 0.003 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TTVLAMDQVPR | 0.784 | 0.105 | 0.000 | 0.000 | 0.050 | 0.060 | 0.000 | |||
| 4 spectra, AGTVSMYTK | 0.754 | 0.047 | 0.084 | 0.000 | 0.116 | 0.000 | 0.000 | |||
| 10 spectra, GITHIGYTDLPSR | 0.772 | 0.160 | 0.000 | 0.044 | 0.000 | 0.024 | 0.000 | |||
| 17 spectra, AVVLAANHFGR | 0.645 | 0.197 | 0.000 | 0.158 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, AAGAQIQGTK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 16 spectra, FGIHPVAGR | 0.916 | 0.000 | 0.084 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DDFDFGTMSHVIR | 0.696 | 0.085 | 0.171 | 0.000 | 0.000 | 0.048 | 0.000 | |||
| 2 spectra, FFTGQITAAGK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, LFAQQCK | 0.988 | 0.012 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, MATQASTLYSNNITK | 0.639 | 0.131 | 0.000 | 0.044 | 0.100 | 0.085 | 0.000 | |||
| 1 spectrum, DGNVIFPAPTPK | 0.255 | 0.524 | 0.000 | 0.000 | 0.078 | 0.143 | 0.000 | |||
| 1 spectrum, MLDMFK | 0.761 | 0.054 | 0.185 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, QVIVMK | 0.686 | 0.151 | 0.018 | 0.094 | 0.000 | 0.050 | 0.000 | |||
| 4 spectra, SLGAEPLEVDLK | 0.875 | 0.000 | 0.125 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ILIVGGGVAGLASAGAAK | 0.414 | 0.261 | 0.000 | 0.002 | 0.212 | 0.111 | 0.000 | |||
| 7 spectra, EFIEAEMK | 0.886 | 0.009 | 0.105 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EANSIVITPGYGLCAAK | 0.705 | 0.033 | 0.021 | 0.000 | 0.240 | 0.000 | 0.000 | |||
| 3 spectra, APVLFSK | 0.930 | 0.002 | 0.068 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GTVVMK | 0.521 | 0.150 | 0.017 | 0.059 | 0.254 | 0.000 | 0.000 | |||
| 2 spectra, QGFNVVVESGAGEASK | 0.709 | 0.056 | 0.000 | 0.000 | 0.236 | 0.000 | 0.000 | |||
| 2 spectra, LQGILK | 0.923 | 0.016 | 0.061 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, TVAELEAEK | 0.898 | 0.000 | 0.102 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1225 spectra |
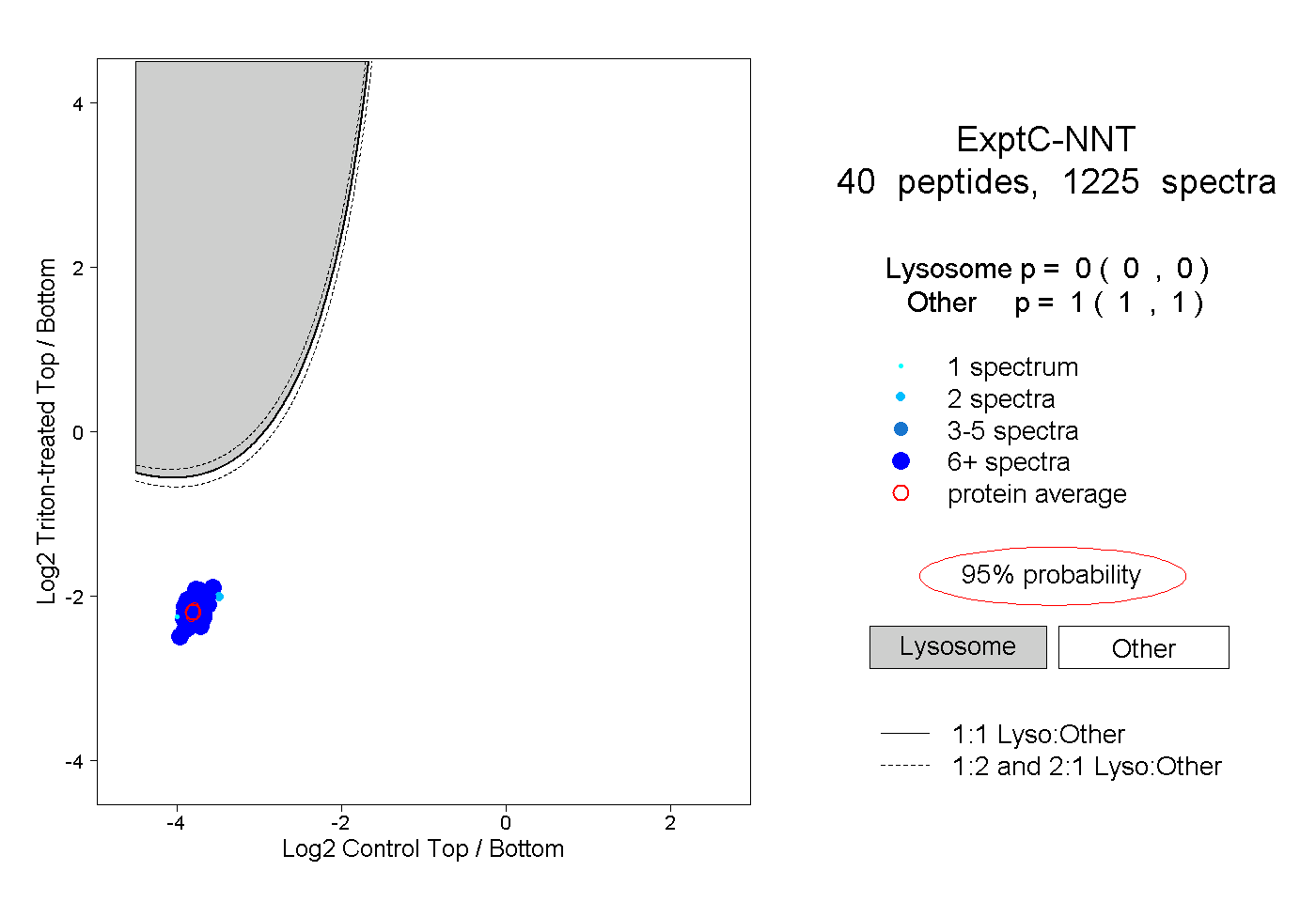 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
84 spectra |
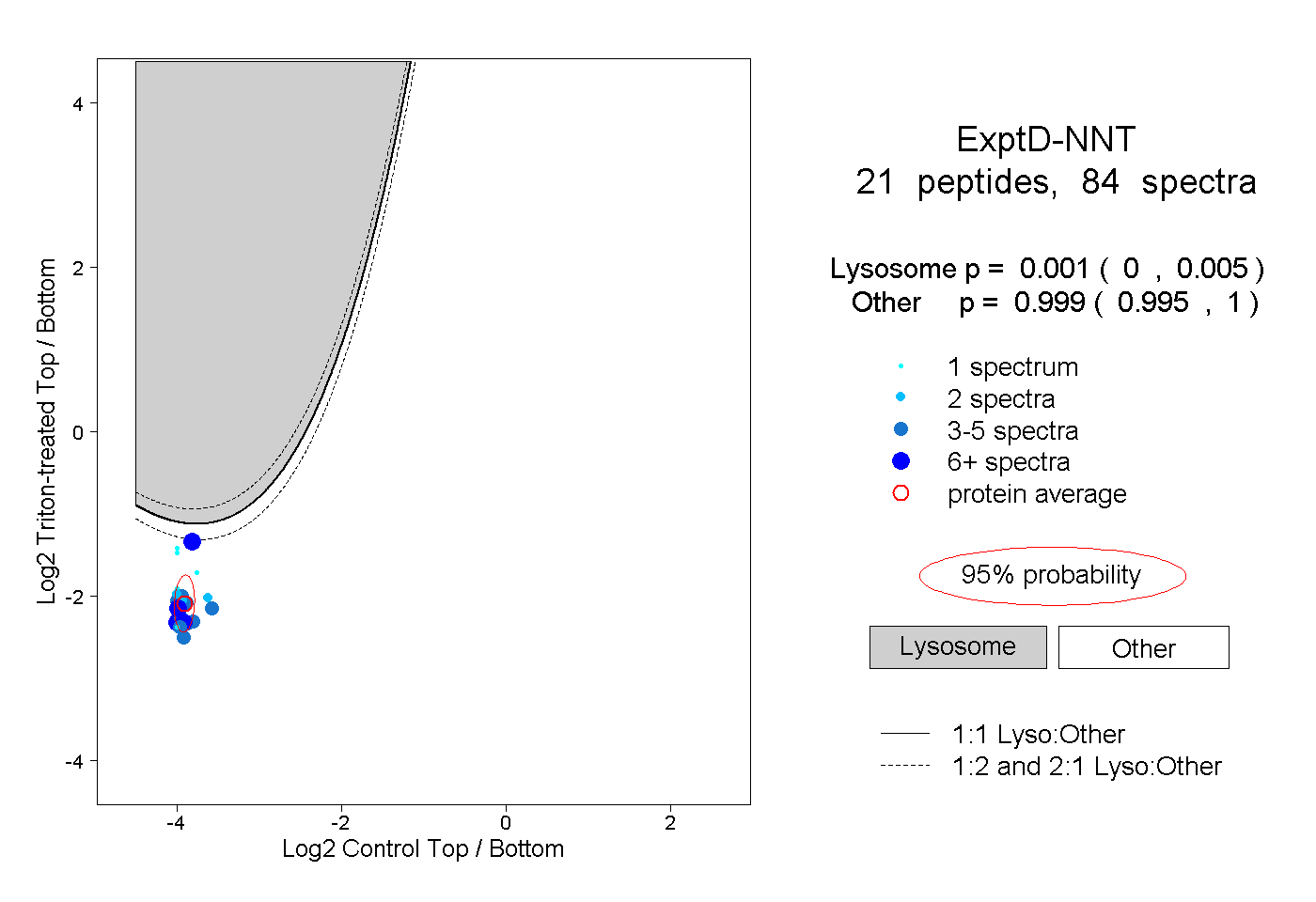 |
0.001 0.000 | 0.005 |
0.999 0.995 | 1.000 |