peptides
spectra
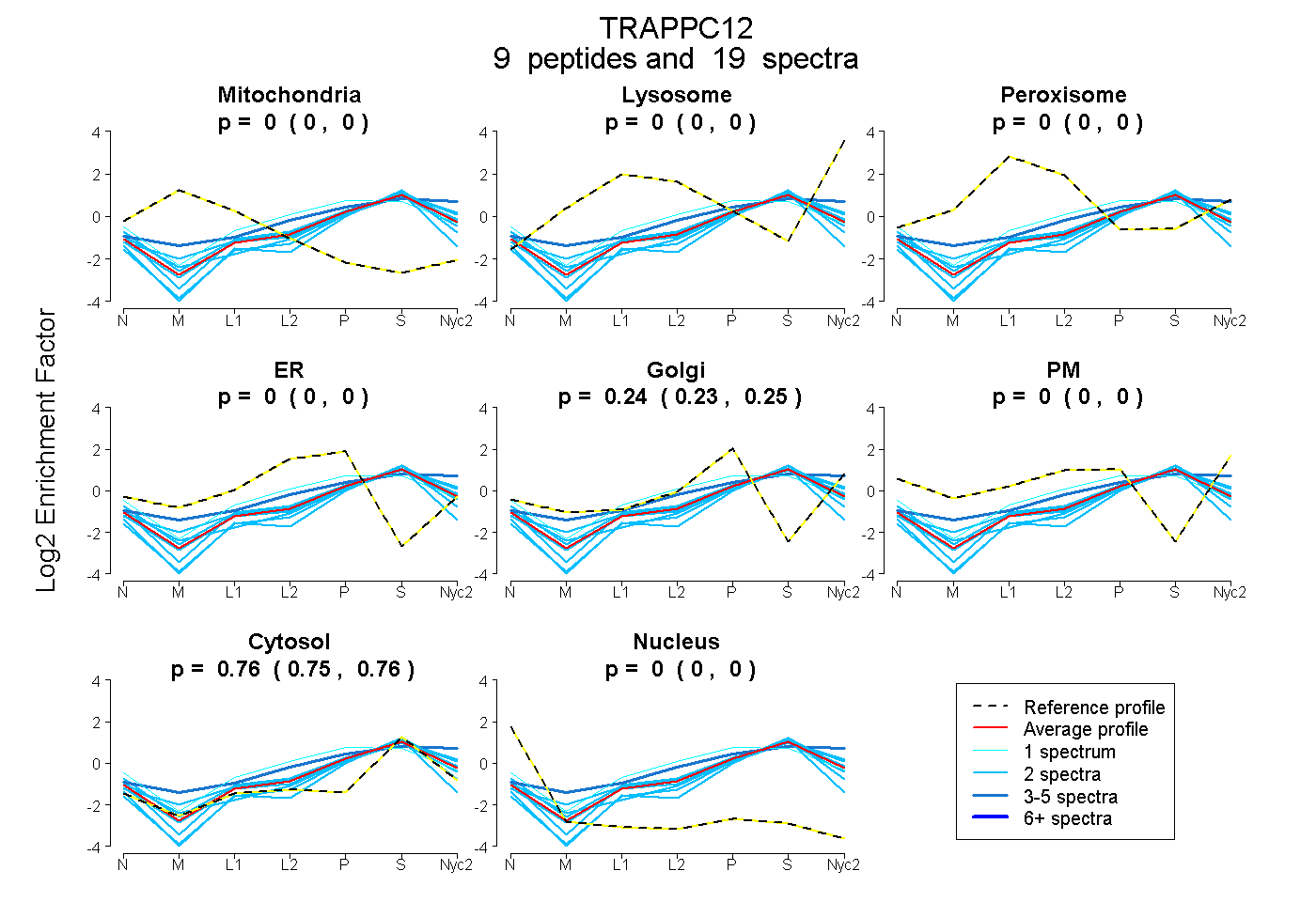
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.234 | 0.251
0.000 | 0.000
0.747 | 0.765
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
19 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.244 0.234 | 0.251 |
0.000 0.000 | 0.000 |
0.756 0.747 | 0.765 |
0.000 0.000 | 0.000 |
| 4 spectra, FFTEILR | 0.000 | 0.204 | 0.000 | 0.000 | 0.234 | 0.000 | 0.562 | 0.000 | ||
| 2 spectra, DISDMTPDSR | 0.000 | 0.000 | 0.000 | 0.058 | 0.189 | 0.000 | 0.753 | 0.000 | ||
| 1 spectrum, LLTAHGQGYGK | 0.000 | 0.011 | 0.008 | 0.346 | 0.033 | 0.001 | 0.602 | 0.000 | ||
| 2 spectra, AFLYLGQNNFAEAHK | 0.000 | 0.005 | 0.000 | 0.000 | 0.242 | 0.000 | 0.754 | 0.000 | ||
| 2 spectra, IMVLMNR | 0.000 | 0.049 | 0.000 | 0.000 | 0.232 | 0.000 | 0.719 | 0.000 | ||
| 2 spectra, SPDSTSPSYSTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.069 | 0.000 | 0.931 | 0.000 | ||
| 2 spectra, LALLVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.120 | 0.000 | 0.880 | 0.000 | ||
| 2 spectra, QLISCR | 0.000 | 0.000 | 0.000 | 0.152 | 0.000 | 0.000 | 0.848 | 0.000 | ||
| 2 spectra, EGDSFNTQCLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.250 | 0.000 | 0.750 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
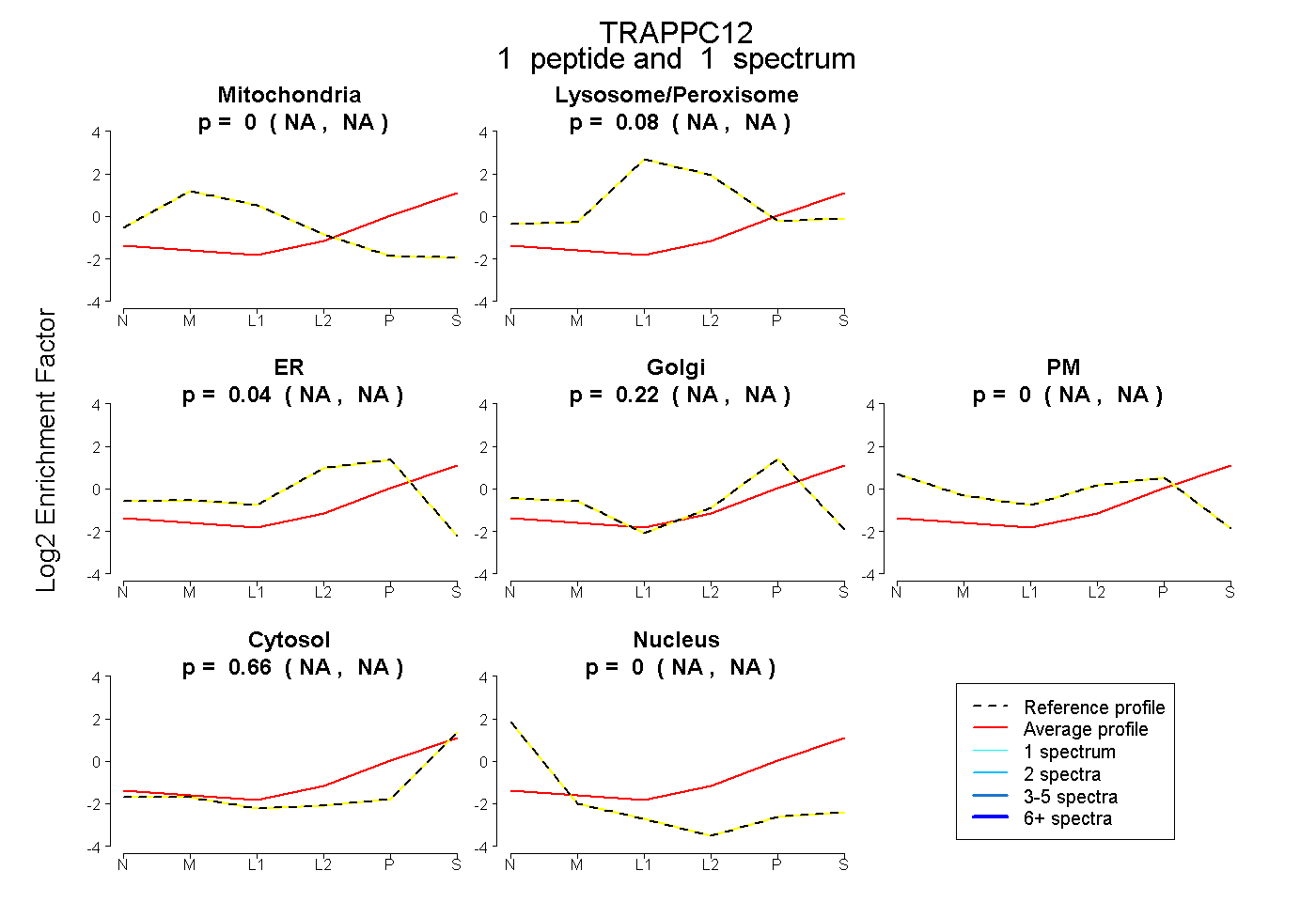 |
0.000 NA | NA |
0.083 NA | NA |
0.042 NA | NA |
0.217 NA | NA |
0.000 NA | NA |
0.658 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
20 spectra |
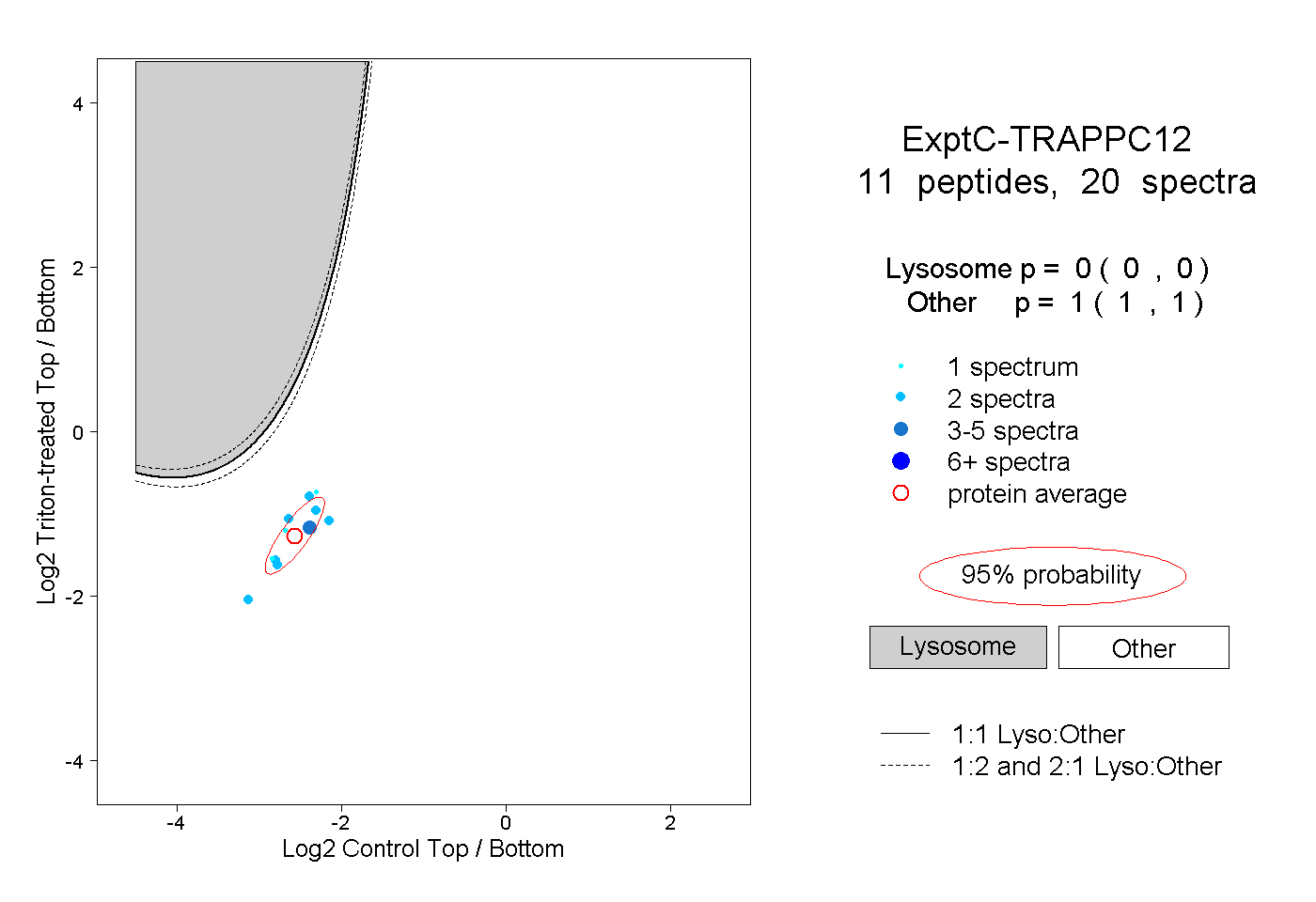 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
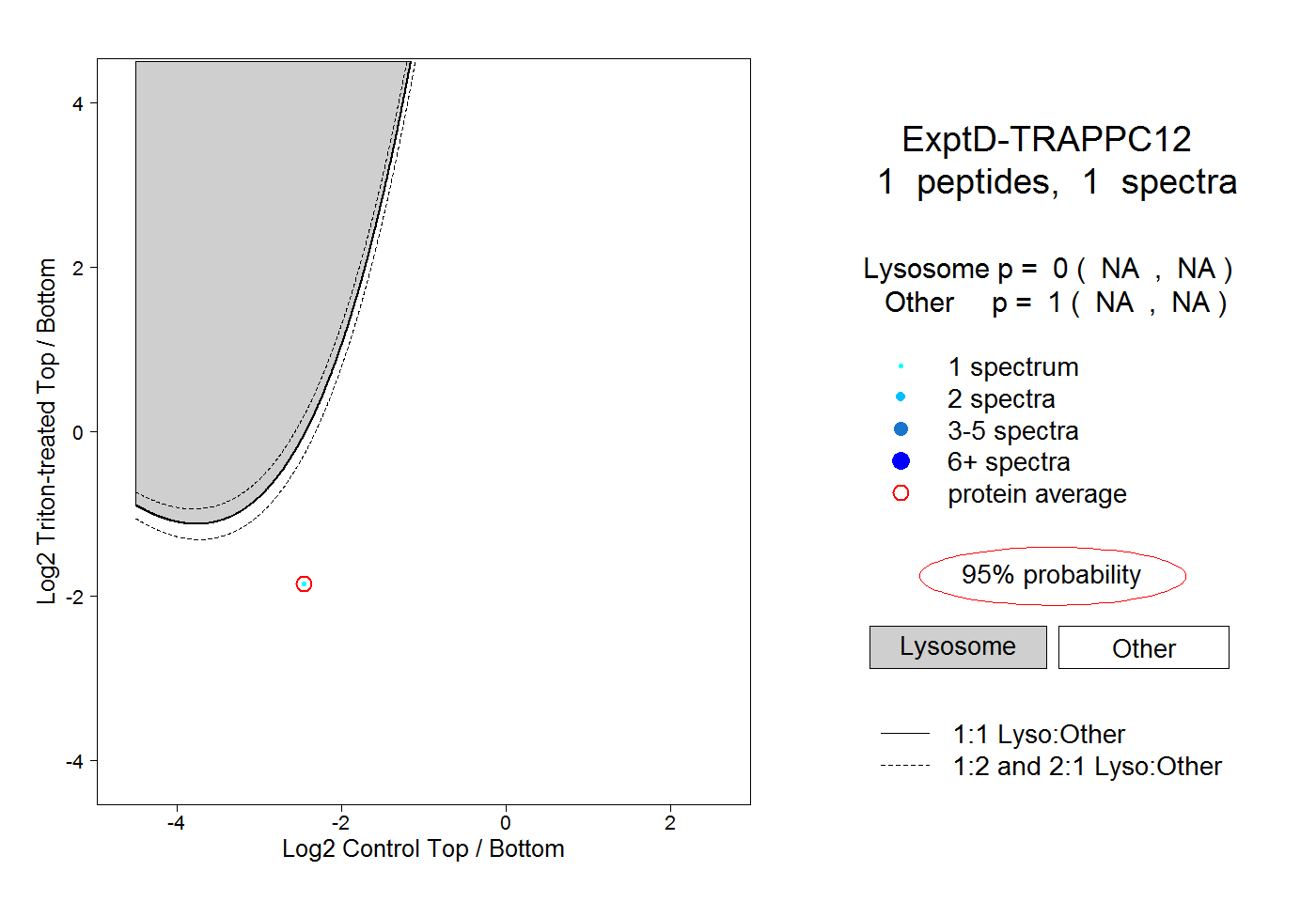 |
0.000 NA | NA |
1.000 NA | NA |