peptides
spectra
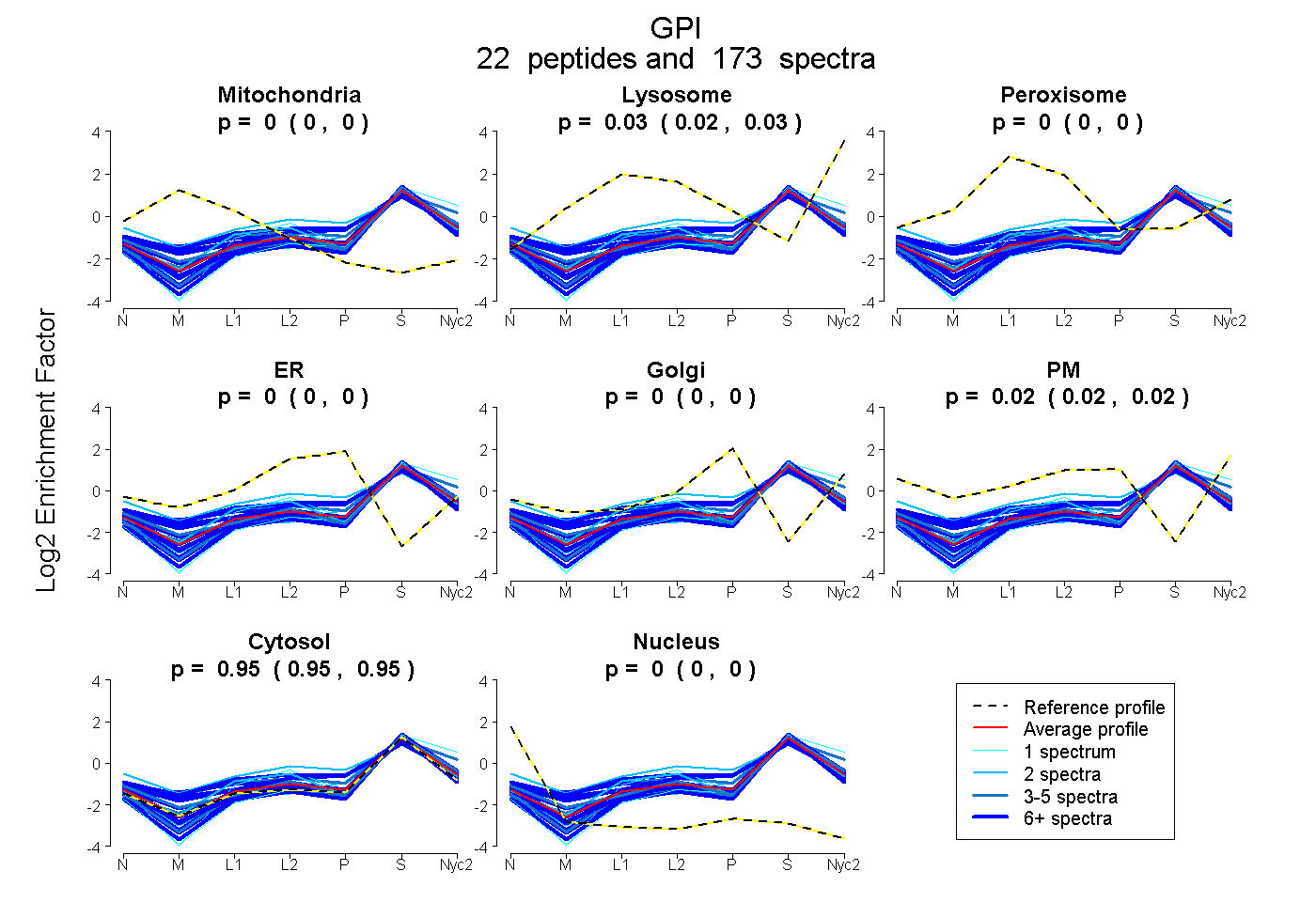
0.000 | 0.000
0.024 | 0.029
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.020 | 0.024
0.949 | 0.952
0.000 | 0.000
peptides
spectra
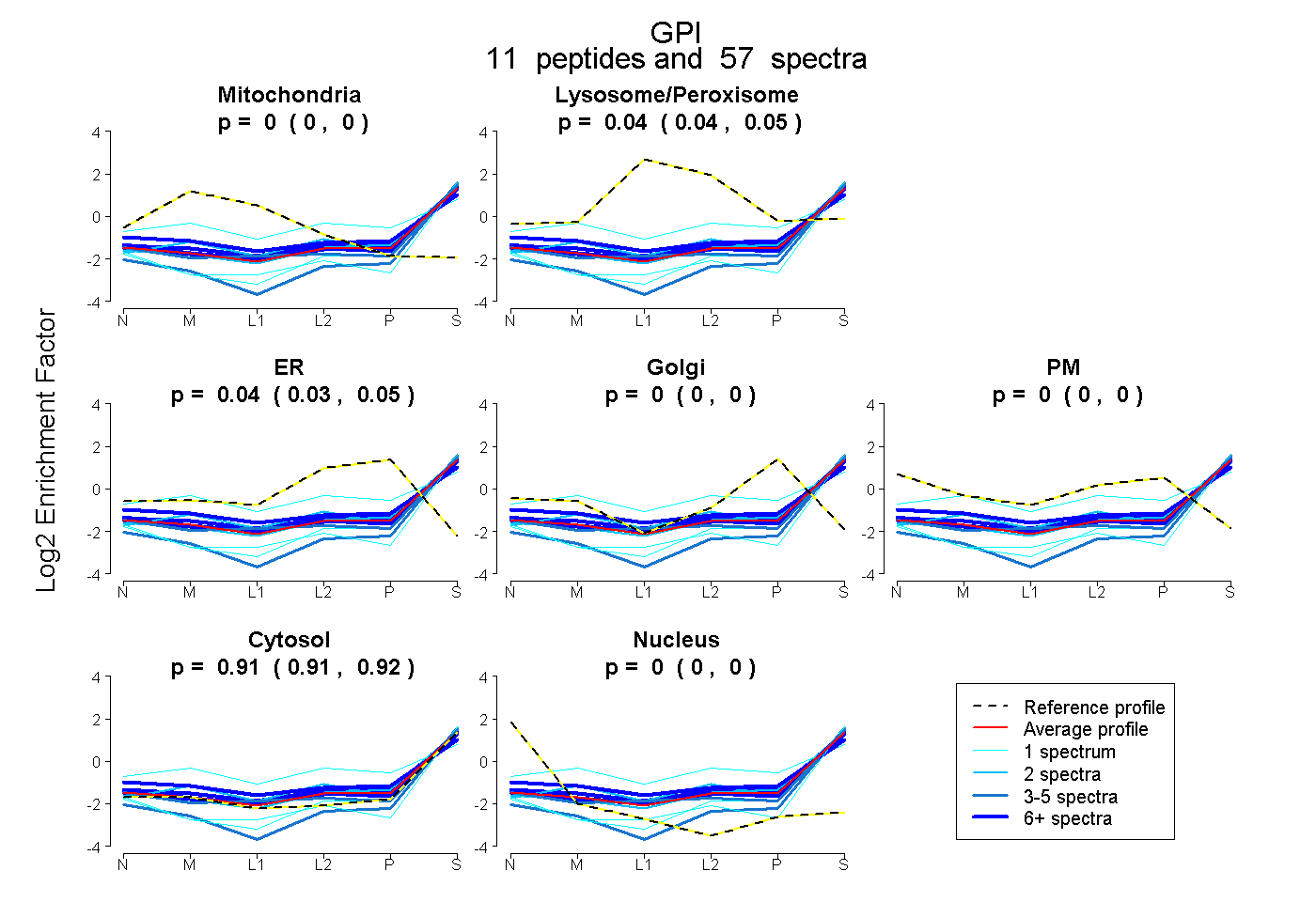
0.000 | 0.000
0.035 | 0.052
0.034 | 0.049
0.000 | 0.000
0.000 | 0.001
0.908 | 0.917
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
173 spectra |
 |
0.000 0.000 | 0.000 |
0.027 0.024 | 0.029 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.022 0.020 | 0.024 |
0.951 0.949 | 0.952 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
57 spectra |
 |
0.000 0.000 | 0.000 |
0.045 0.035 | 0.052 |
0.042 0.034 | 0.049 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.913 0.908 | 0.917 |
0.000 0.000 | 0.000 |
| 13 spectra, LLEWHR | 0.000 | 0.075 | 0.000 | 0.000 | 0.000 | 0.925 | 0.000 | |||
| 4 spectra, ELFEADPER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 12 spectra, AVLHVALR | 0.000 | 0.050 | 0.030 | 0.000 | 0.037 | 0.884 | 0.000 | |||
| 11 spectra, EVLHMLVDLAK | 0.000 | 0.086 | 0.039 | 0.000 | 0.015 | 0.860 | 0.000 | |||
| 3 spectra, VFEGNRPTNSIVFTK | 0.000 | 0.056 | 0.000 | 0.000 | 0.000 | 0.944 | 0.000 | |||
| 2 spectra, ILLANFLAQTEALMK | 0.000 | 0.138 | 0.000 | 0.000 | 0.000 | 0.862 | 0.000 | |||
| 7 spectra, MIPCDFLIPVQTQHPIR | 0.000 | 0.100 | 0.000 | 0.000 | 0.154 | 0.746 | 0.000 | |||
| 1 spectrum, INSTEDR | 0.000 | 0.250 | 0.000 | 0.067 | 0.179 | 0.503 | 0.000 | |||
| 1 spectrum, NMFEFWDWVGGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.983 | 0.017 | |||
| 2 spectra, FAAYFQQGDMESNGK | 0.000 | 0.019 | 0.070 | 0.000 | 0.000 | 0.911 | 0.000 | |||
| 1 spectrum, EWFLQAAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
188 spectra |
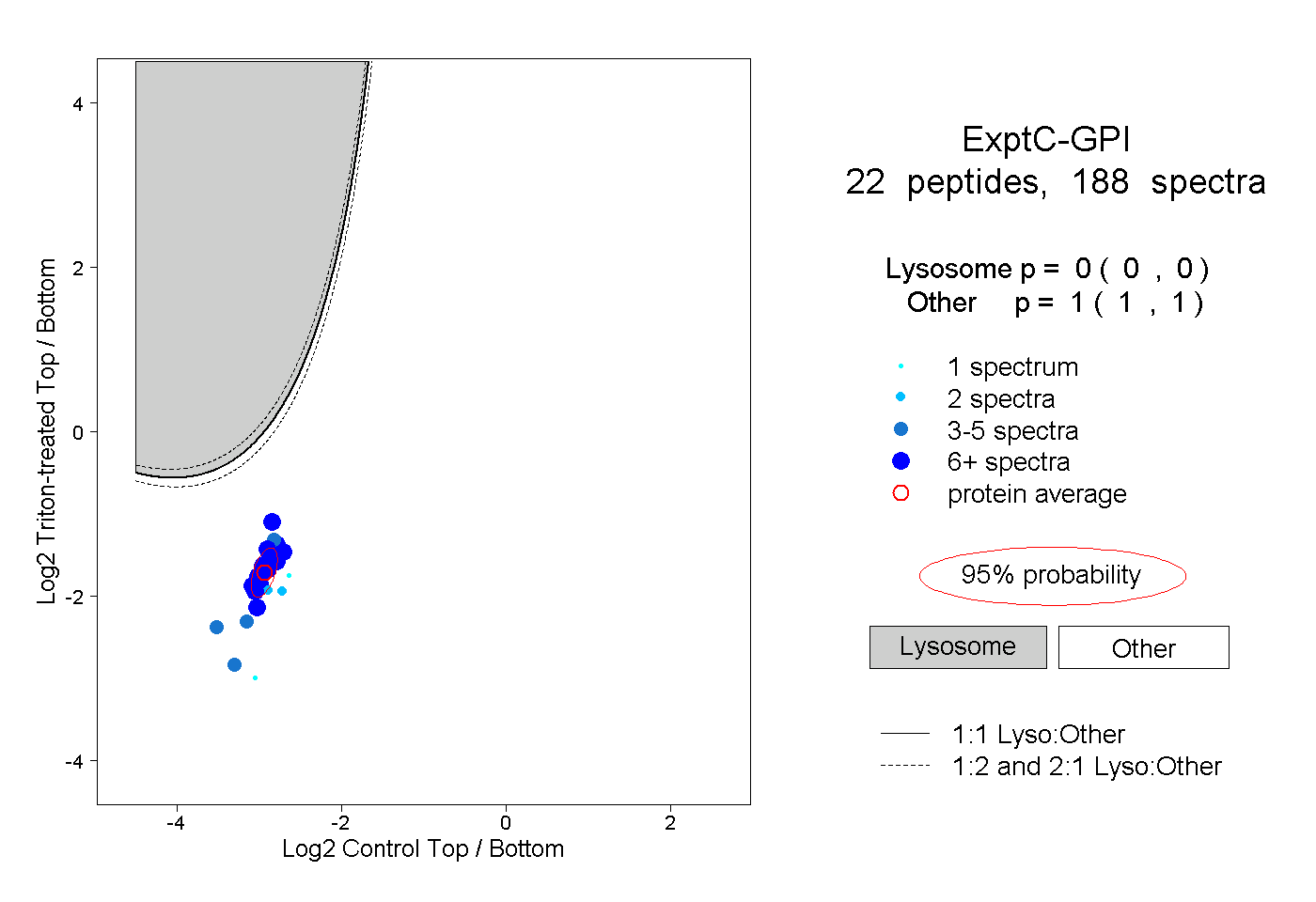 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
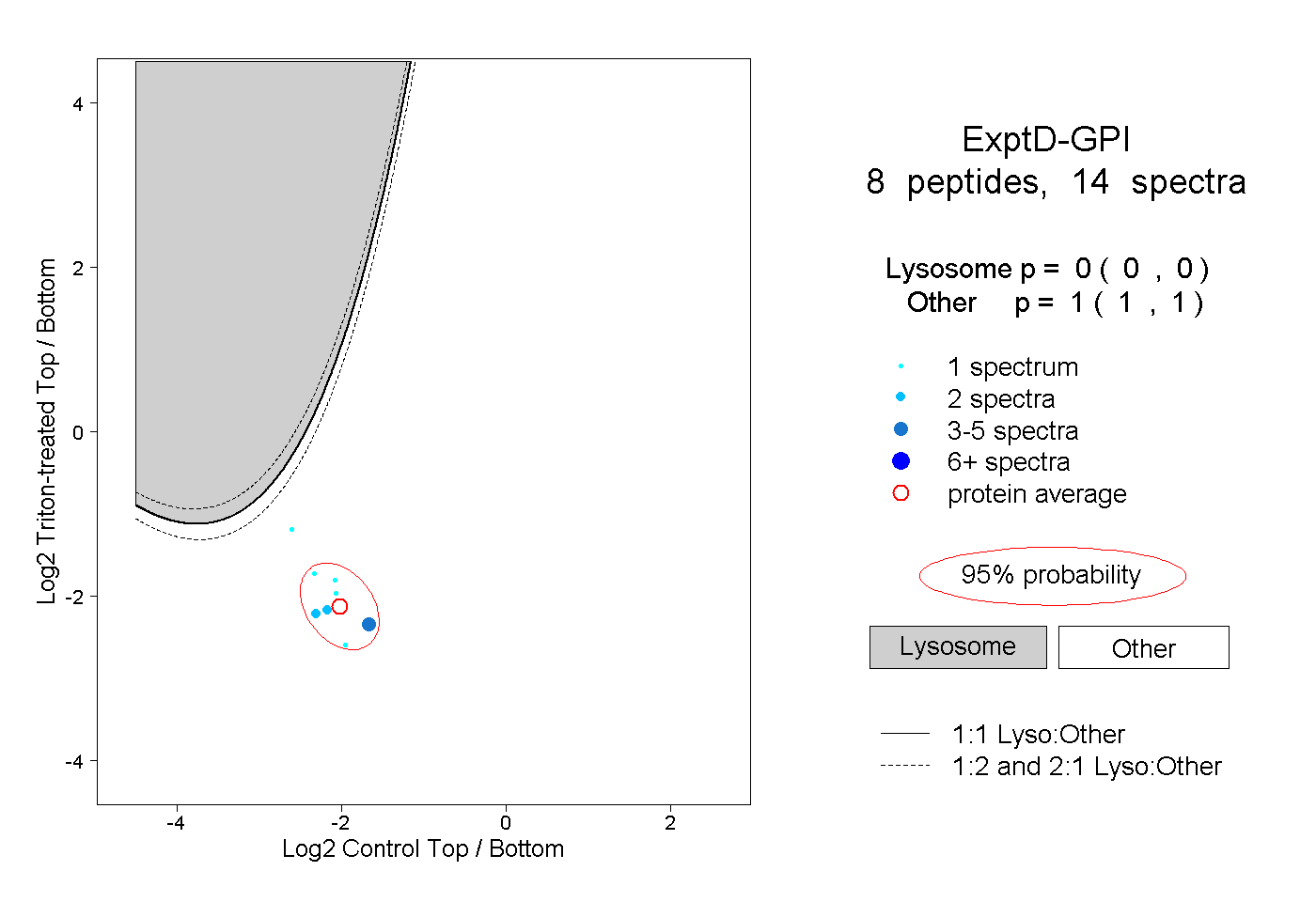 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |