peptides
spectra
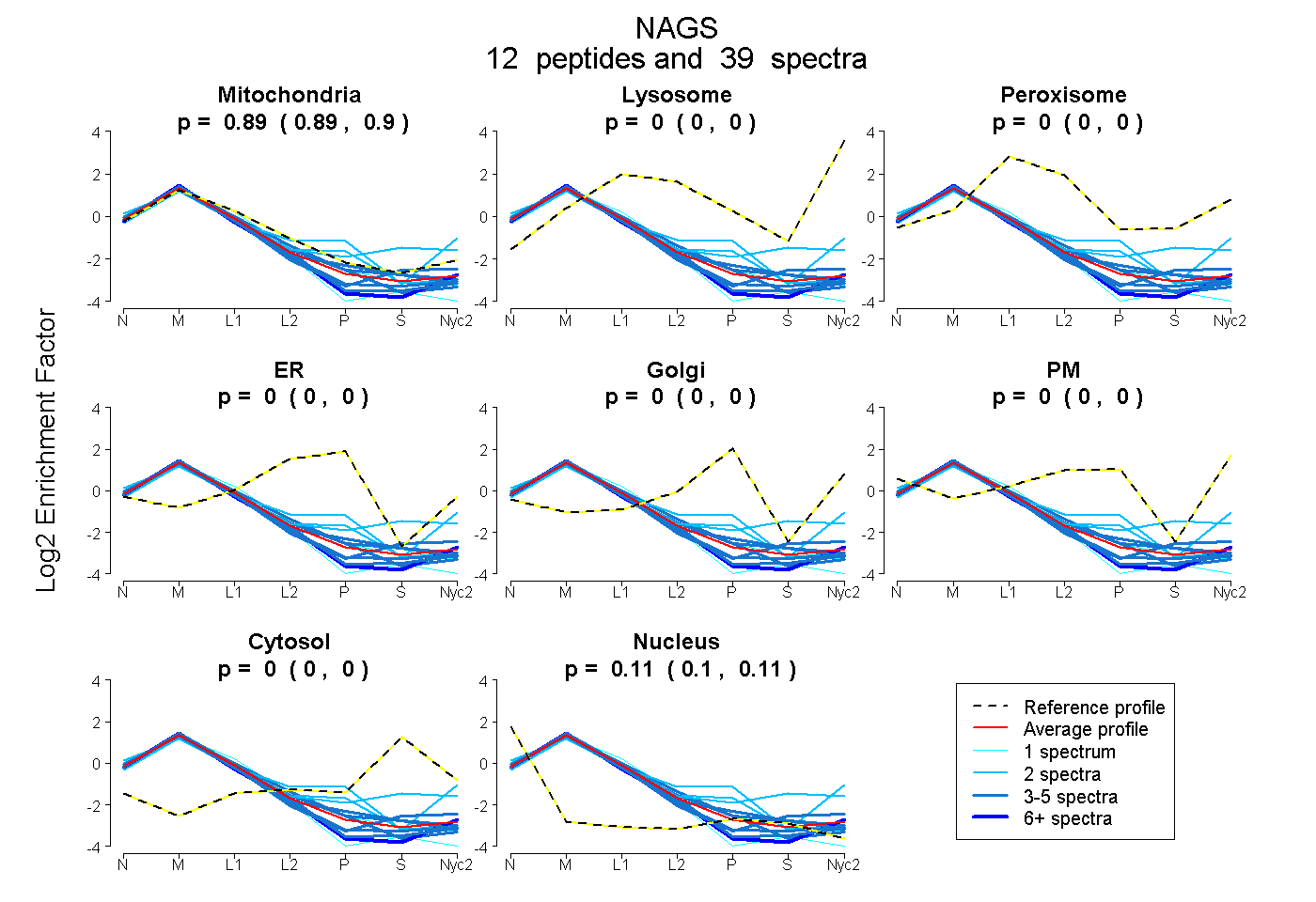
0.891 | 0.897
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.102 | 0.109
peptides
spectra
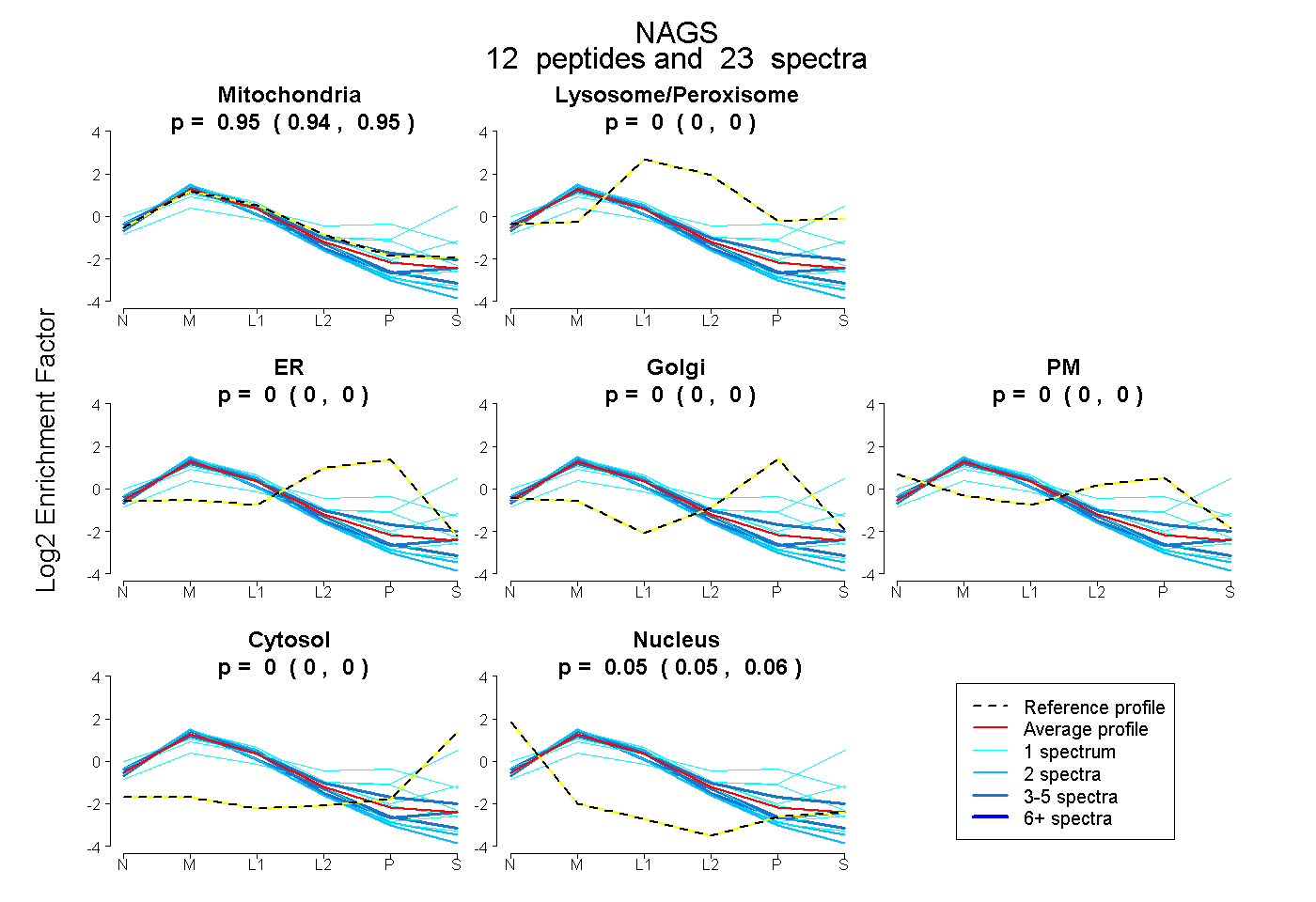
0.939 | 0.950
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.049 | 0.060
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
39 spectra |
 |
0.894 0.891 | 0.897 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.106 0.102 | 0.109 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.945 0.939 | 0.950 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.055 0.049 | 0.060 |
| 4 spectra, LIVDVLSR | 0.935 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.065 | |||
| 3 spectra, FVVSSSR | 0.912 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.088 | |||
| 1 spectrum, AQLAQSCK | 0.820 | 0.064 | 0.000 | 0.000 | 0.000 | 0.062 | 0.054 | |||
| 1 spectrum, AHVEDNEGTK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SLDSLDQGR | 0.874 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.126 | |||
| 2 spectra, DLQTLFWR | 0.930 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.070 | |||
| 1 spectrum, IIFLNNSGGLR | 0.921 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.079 | |||
| 5 spectra, VLVNELR | 0.940 | 0.000 | 0.000 | 0.031 | 0.000 | 0.000 | 0.029 | |||
| 1 spectrum, VTNPINPWYFK | 0.535 | 0.204 | 0.000 | 0.260 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LVNLVNASFGK | 0.982 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.018 | |||
| 1 spectrum, ALQPTK | 0.864 | 0.000 | 0.022 | 0.079 | 0.035 | 0.000 | 0.000 | |||
| 1 spectrum, GCGTLFK | 0.346 | 0.226 | 0.000 | 0.000 | 0.000 | 0.428 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
113 spectra |
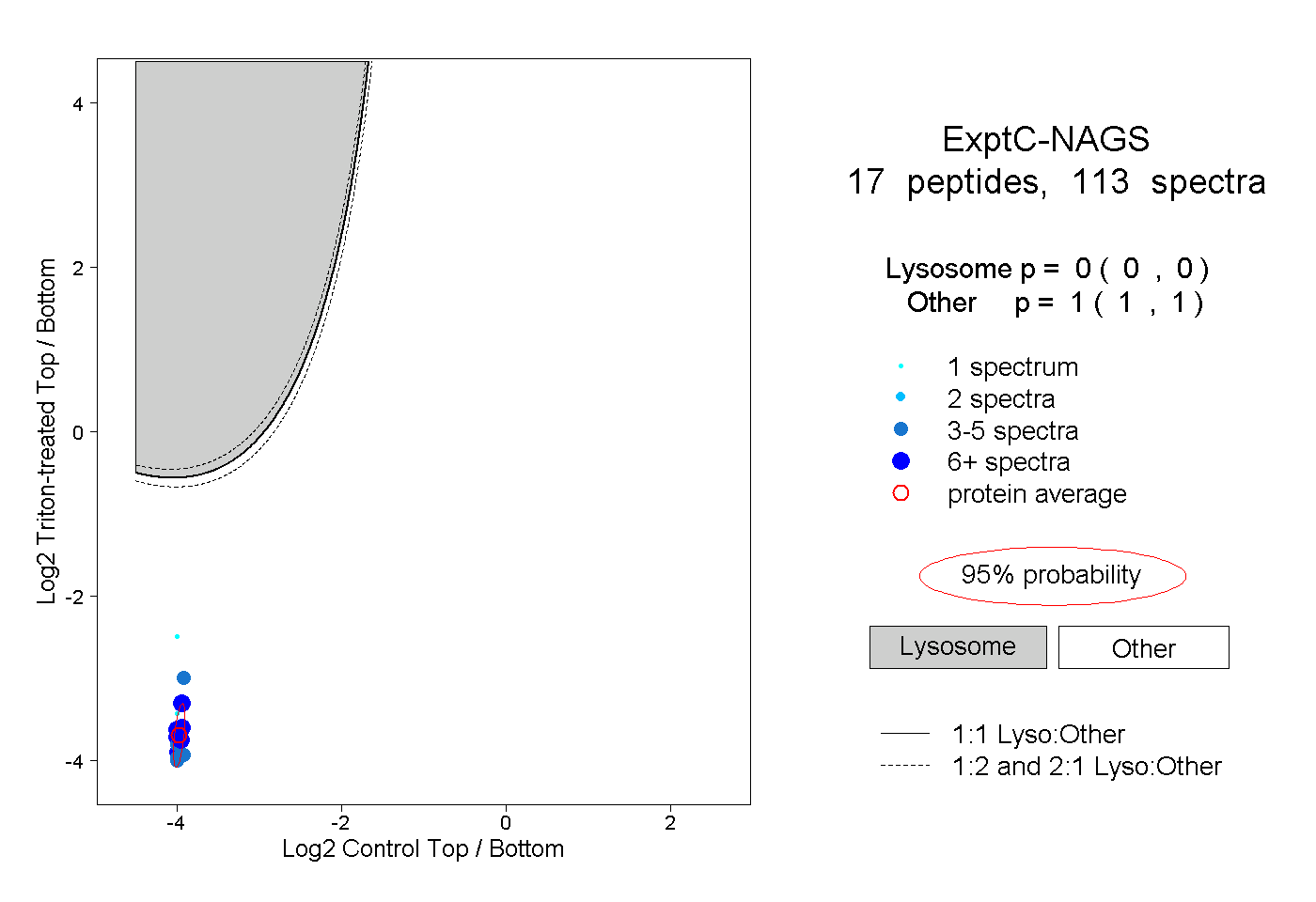 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
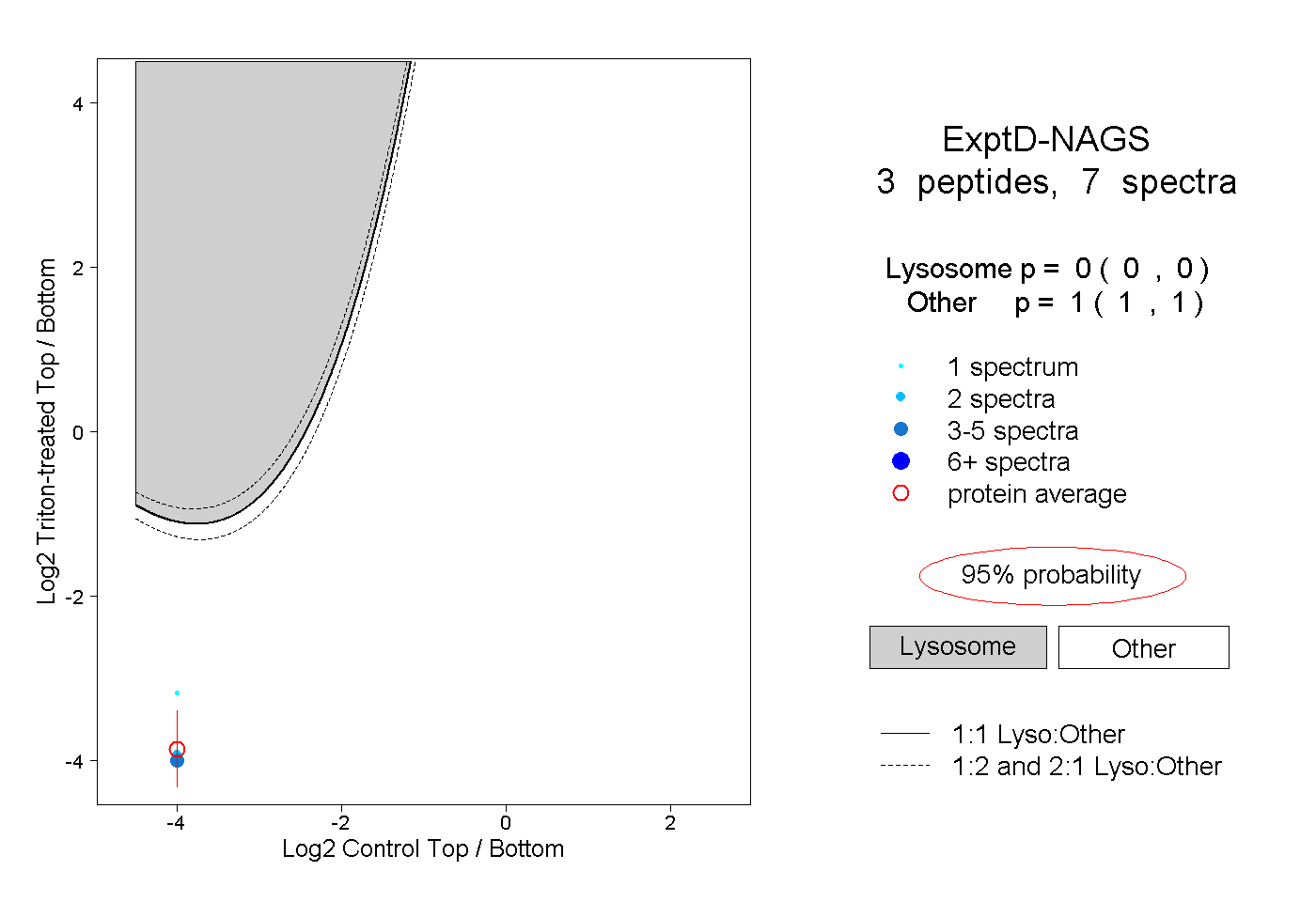 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |