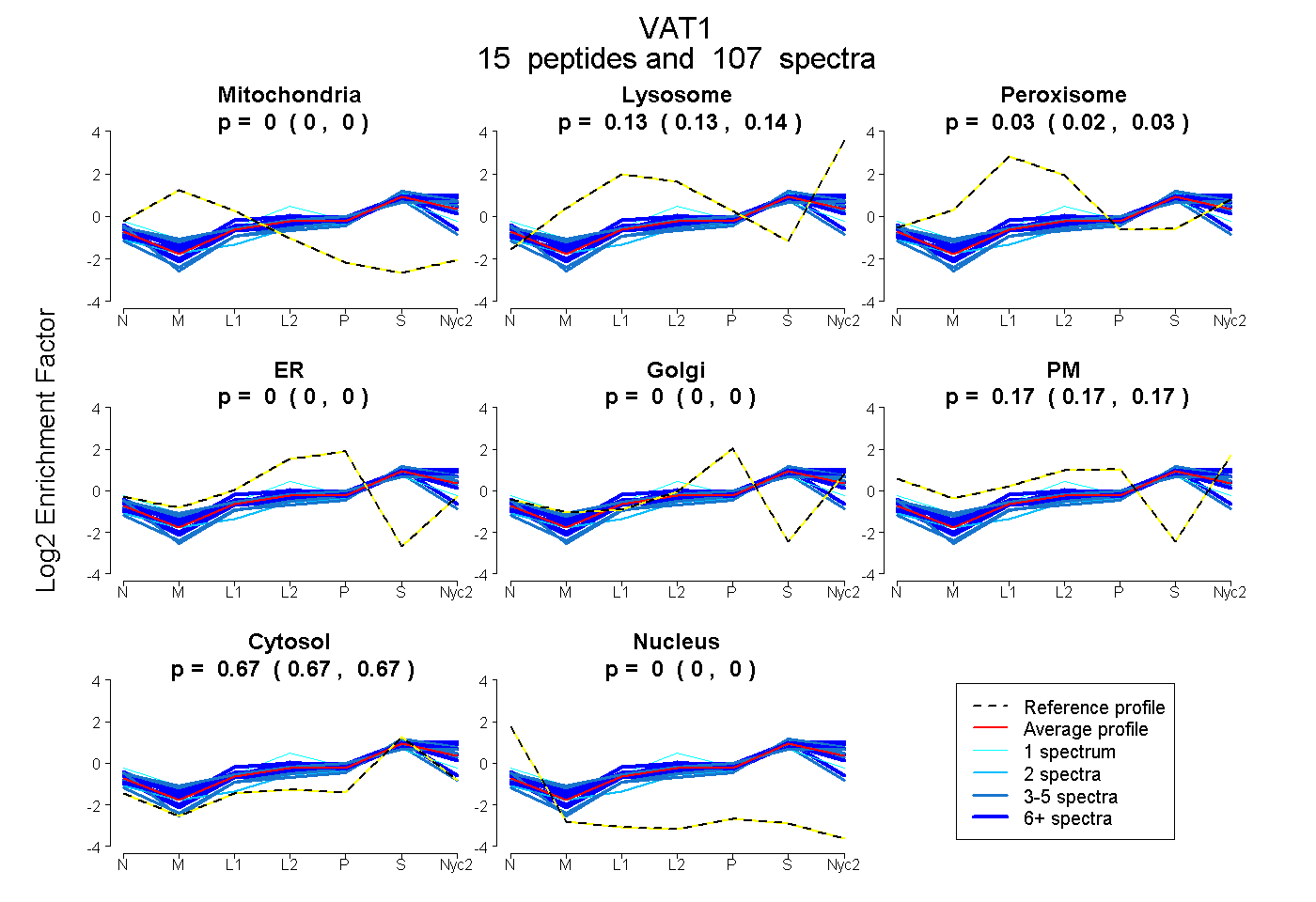
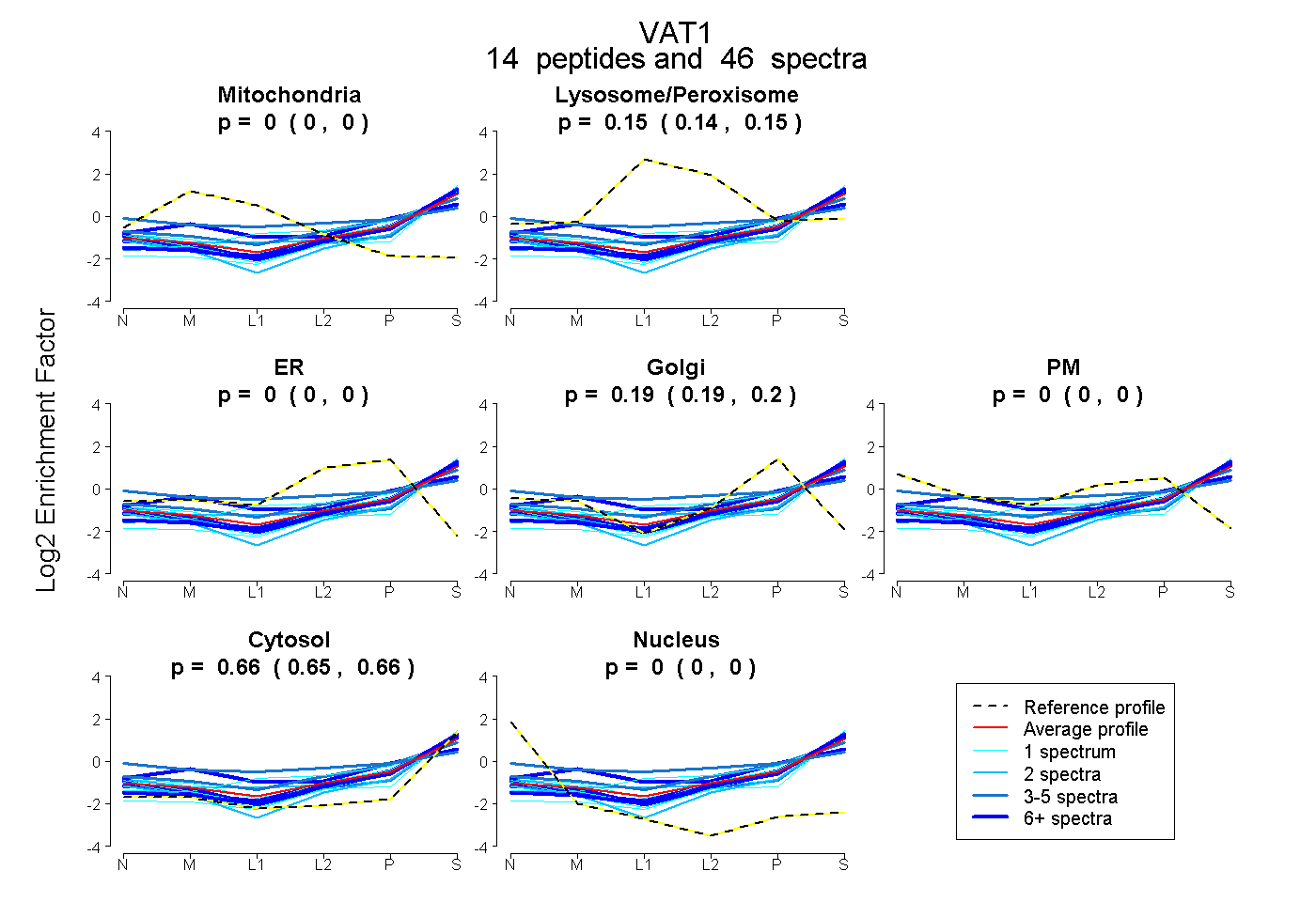
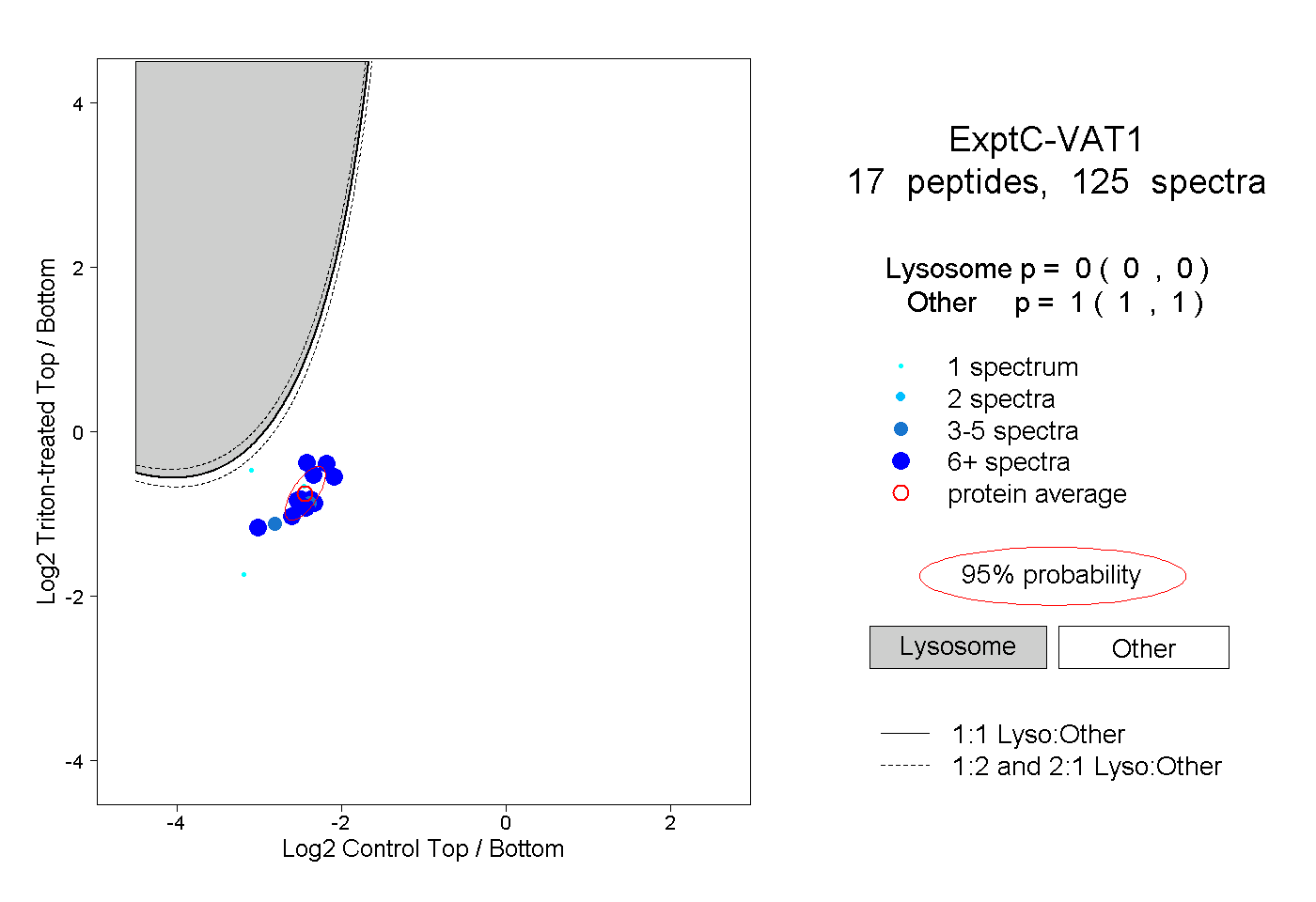
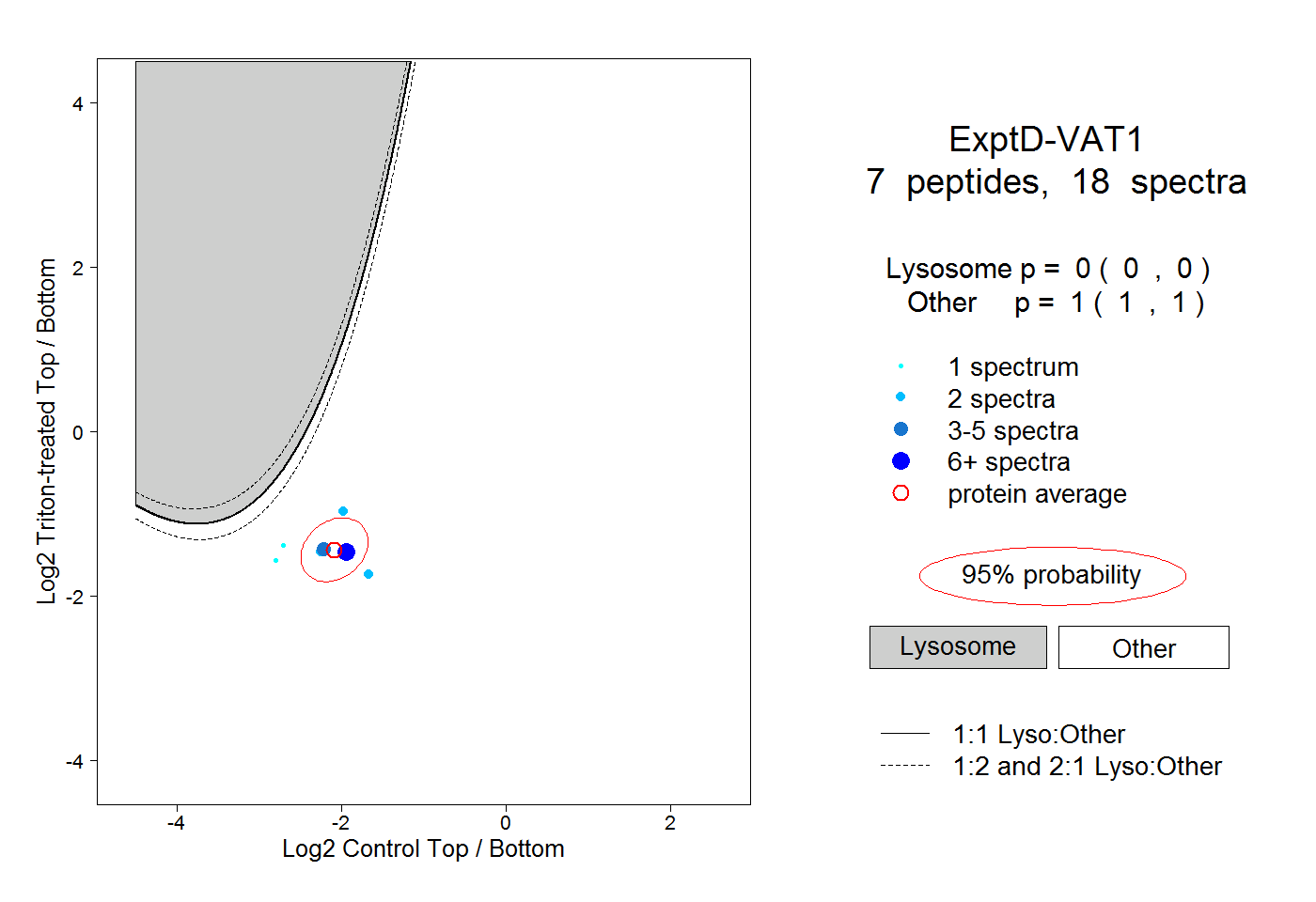
| 7 spectra, EATEAATVAAAAEAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VADAMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GVDIVMDPLGGSDTAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, IDSVWPFEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, GYHLLKPMGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, ACGLNFADLMGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, CLVLTGFGGYDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LQSRPAVPPAPGPGQVTLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, NLMAMAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VMVLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, VLLVPGPEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AVCGFHLGYLDGEVELVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, QGLYDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, VVTYGMANLLTGPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TVENVTVFGTASASK |
|
0.049 |
|
|
|
|
|
|
|
0.951 |
| 5 spectra, QMQEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LPPLPVTPGMEGAGVVVAVGEGVSDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |