peptides
spectra
0.000 | 0.000
0.125 | 0.139
0.019 | 0.031
0.000 | 0.000
0.000 | 0.000
0.169 | 0.174
0.668 | 0.671
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.142 | 0.155
0.000 | 0.000
0.188 | 0.201
0.000 | 0.000
0.651 | 0.661
0.000 | 0.000
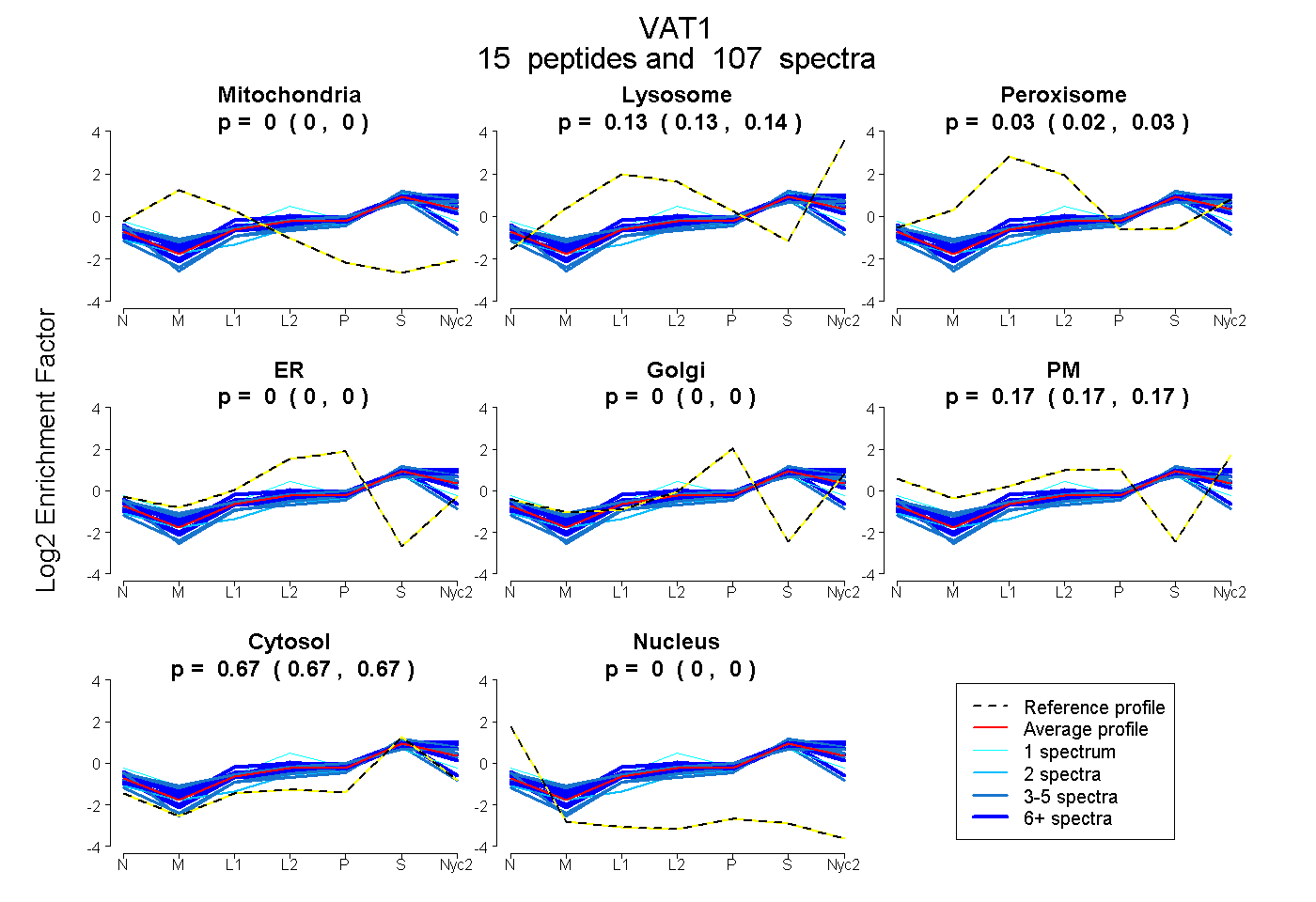
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
107 spectra |
 |
0.000 0.000 | 0.000 |
0.133 0.125 | 0.139 |
0.026 0.019 | 0.031 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.172 0.169 | 0.174 |
0.670 0.668 | 0.671 |
0.000 0.000 | 0.000 |
||
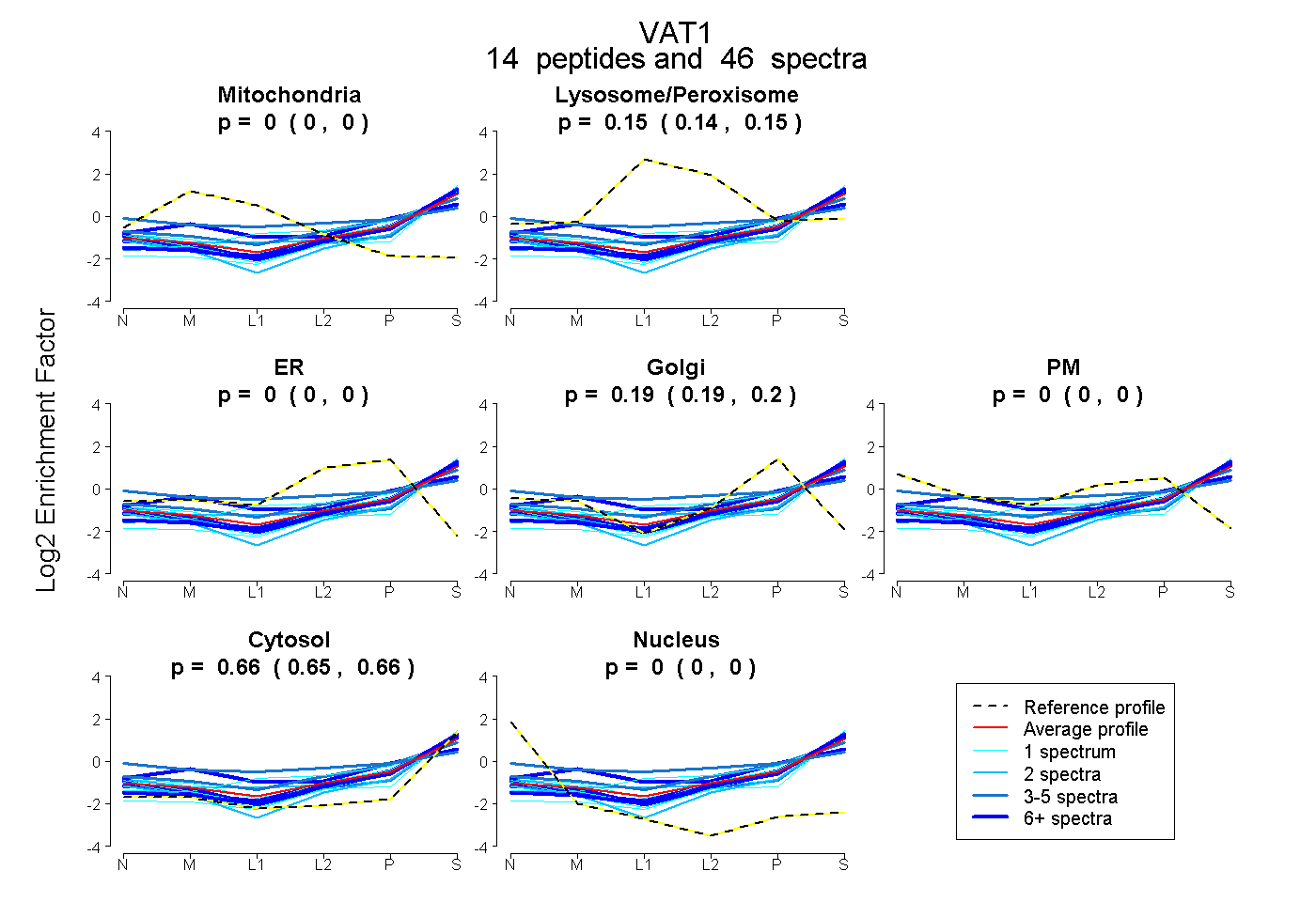
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
46 spectra |
 |
0.000 0.000 | 0.000 |
0.149 0.142 | 0.155 |
0.000 0.000 | 0.000 |
0.195 0.188 | 0.201 |
0.000 0.000 | 0.000 |
0.656 0.651 | 0.661 |
0.000 0.000 | 0.000 |
| 5 spectra, LQSRPAVPPAPGPGQVTLR | 0.000 | 0.222 | 0.000 | 0.261 | 0.000 | 0.517 | 0.000 | |||
| 7 spectra, EATEAATVAAAAEAR | 0.000 | 0.248 | 0.000 | 0.296 | 0.000 | 0.456 | 0.000 | |||
| 1 spectrum, NLMAMAR | 0.000 | 0.022 | 0.230 | 0.000 | 0.000 | 0.748 | 0.000 | |||
| 6 spectra, VMVLNR | 0.000 | 0.022 | 0.185 | 0.000 | 0.000 | 0.793 | 0.000 | |||
| 2 spectra, VADAMR | 0.000 | 0.000 | 0.000 | 0.182 | 0.000 | 0.818 | 0.000 | |||
| 6 spectra, GVDIVMDPLGGSDTAK | 0.000 | 0.076 | 0.000 | 0.219 | 0.000 | 0.705 | 0.000 | |||
| 1 spectrum, VLLVPGPEK | 0.000 | 0.291 | 0.000 | 0.150 | 0.000 | 0.560 | 0.000 | |||
| 6 spectra, IDSVWPFEK | 0.000 | 0.110 | 0.000 | 0.204 | 0.000 | 0.686 | 0.000 | |||
| 1 spectrum, AVCGFHLGYLDGEVELVSR | 0.000 | 0.084 | 0.000 | 0.014 | 0.179 | 0.722 | 0.000 | |||
| 3 spectra, VVTYGMANLLTGPK | 0.000 | 0.259 | 0.000 | 0.000 | 0.368 | 0.373 | 0.000 | |||
| 1 spectrum, TVENVTVFGTASASK | 0.000 | 0.050 | 0.000 | 0.215 | 0.000 | 0.735 | 0.000 | |||
| 1 spectrum, GYHLLKPMGK | 0.000 | 0.011 | 0.085 | 0.000 | 0.000 | 0.904 | 0.000 | |||
| 4 spectra, ACGLNFADLMGR | 0.000 | 0.051 | 0.124 | 0.000 | 0.000 | 0.825 | 0.000 | |||
| 2 spectra, CLVLTGFGGYDK | 0.000 | 0.201 | 0.000 | 0.158 | 0.000 | 0.641 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
125 spectra |
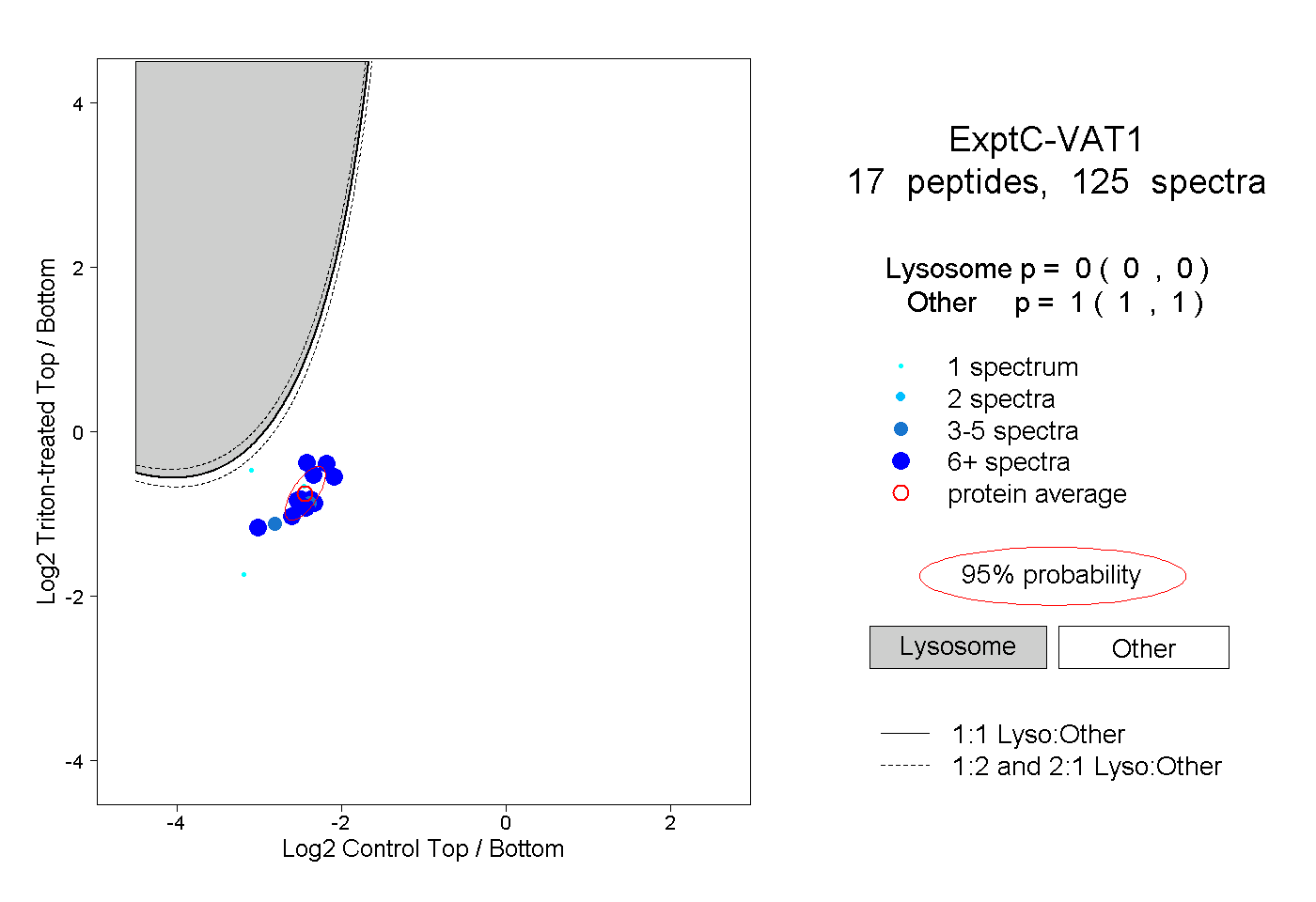 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
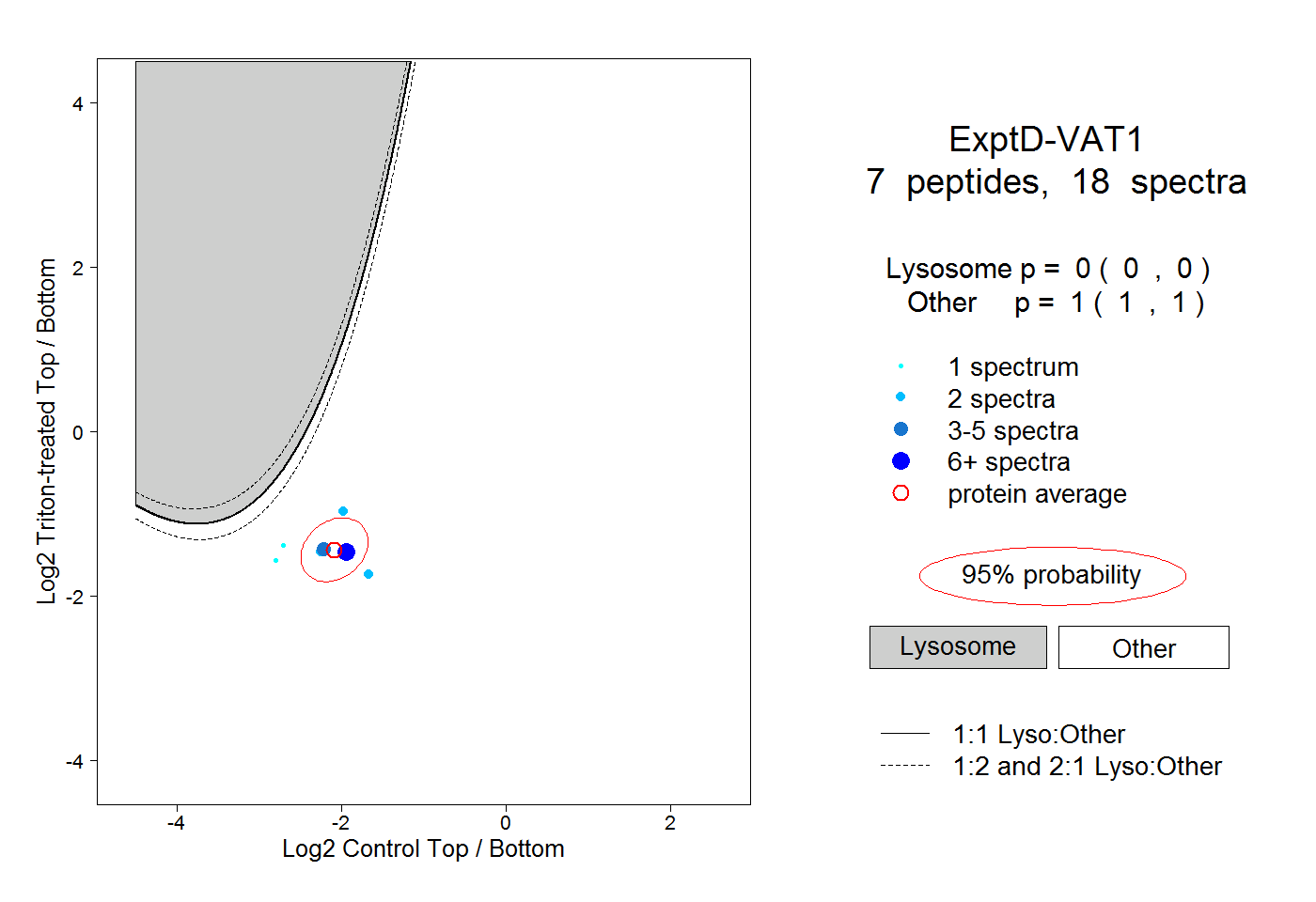 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |