peptides
spectra
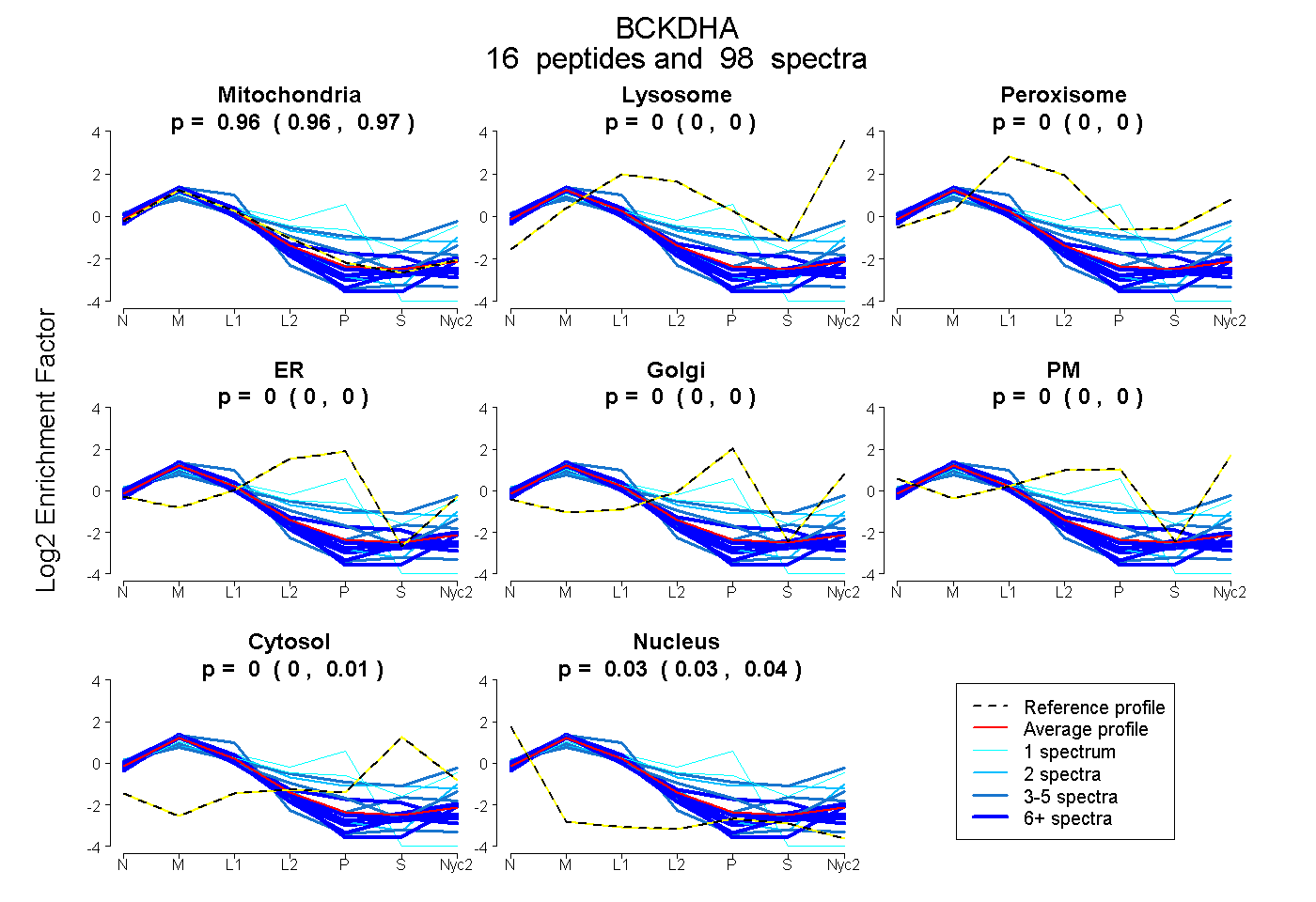
0.960 | 0.966
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.007
0.030 | 0.037
peptides
spectra
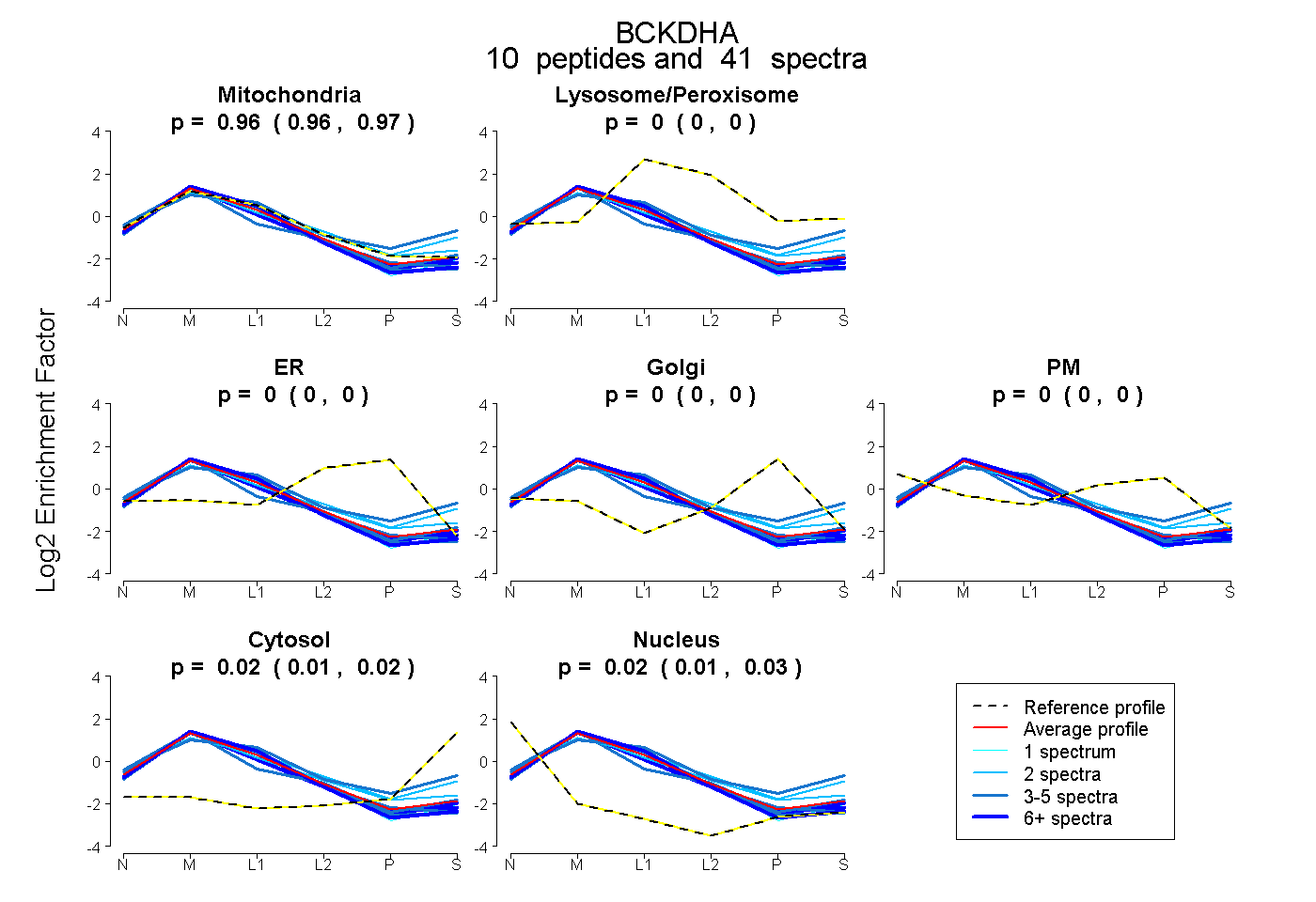
0.957 | 0.968
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.006 | 0.025
0.014 | 0.026
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
98 spectra |
 |
0.964 0.960 | 0.966 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.003 0.000 | 0.007 |
0.034 0.030 | 0.037 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
41 spectra |
 |
0.963 0.957 | 0.968 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.016 0.006 | 0.025 |
0.021 0.014 | 0.026 |
| 4 spectra, TDLVFGQYR | 0.960 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.040 | |||
| 2 spectra, SVDEVNYWDK | 0.779 | 0.095 | 0.000 | 0.000 | 0.000 | 0.126 | 0.000 | |||
| 4 spectra, QQESLAR | 0.957 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.043 | |||
| 1 spectrum, DYPLELFMAQCYGNVSDPGK | 0.982 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.018 | |||
| 7 spectra, VMEAFEQAER | 0.979 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.021 | |||
| 3 spectra, VDGNDVFAVYNATK | 0.702 | 0.155 | 0.000 | 0.000 | 0.000 | 0.143 | 0.000 | |||
| 6 spectra, EAGVLMYR | 0.978 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | |||
| 2 spectra, QMPVHYGCK | 0.929 | 0.000 | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | |||
| 3 spectra, SMTLLNTMDR | 0.889 | 0.000 | 0.000 | 0.000 | 0.000 | 0.081 | 0.030 | |||
| 9 spectra, GPGYGIMSIR | 0.941 | 0.000 | 0.000 | 0.000 | 0.000 | 0.023 | 0.036 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
277 spectra |
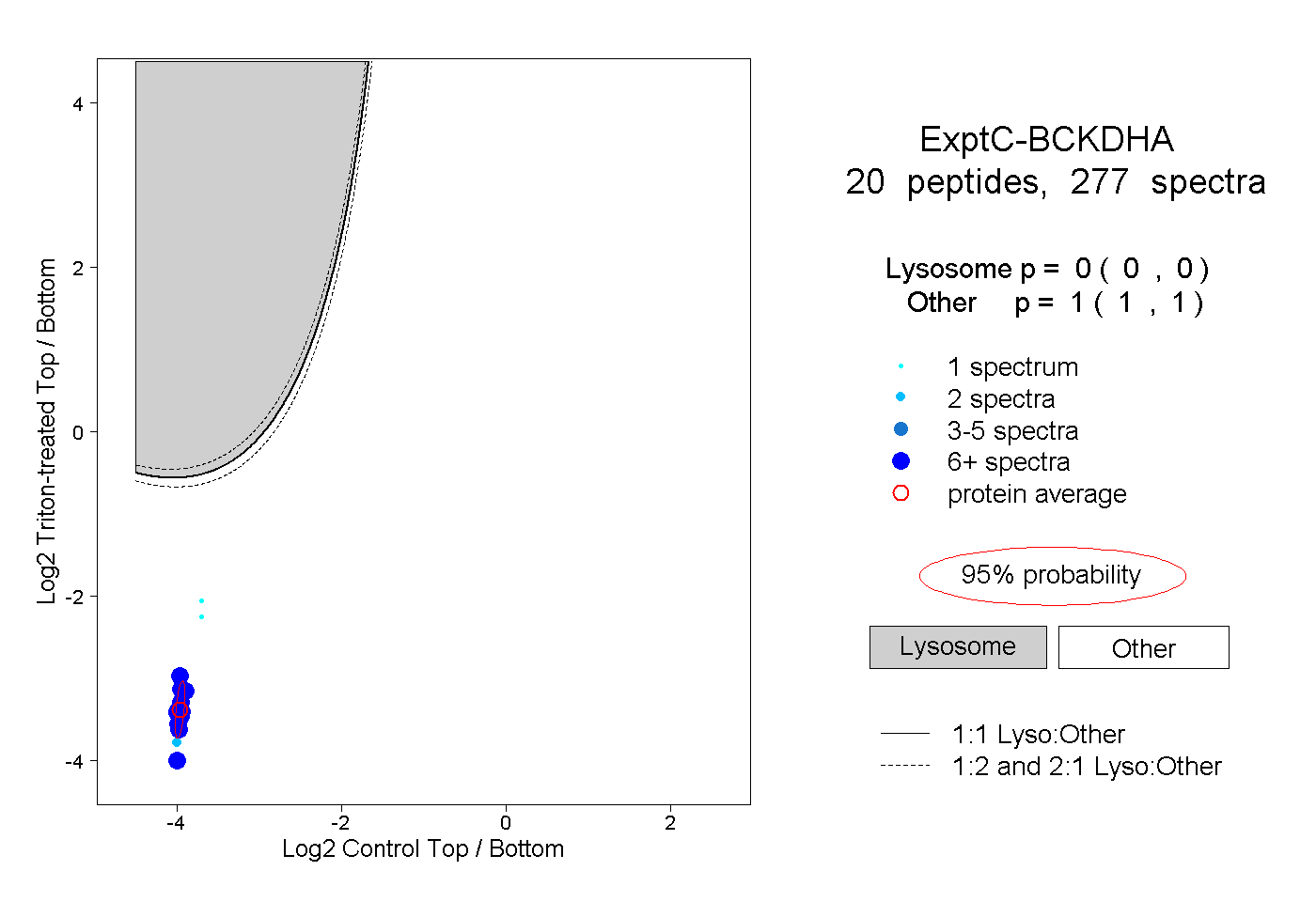 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
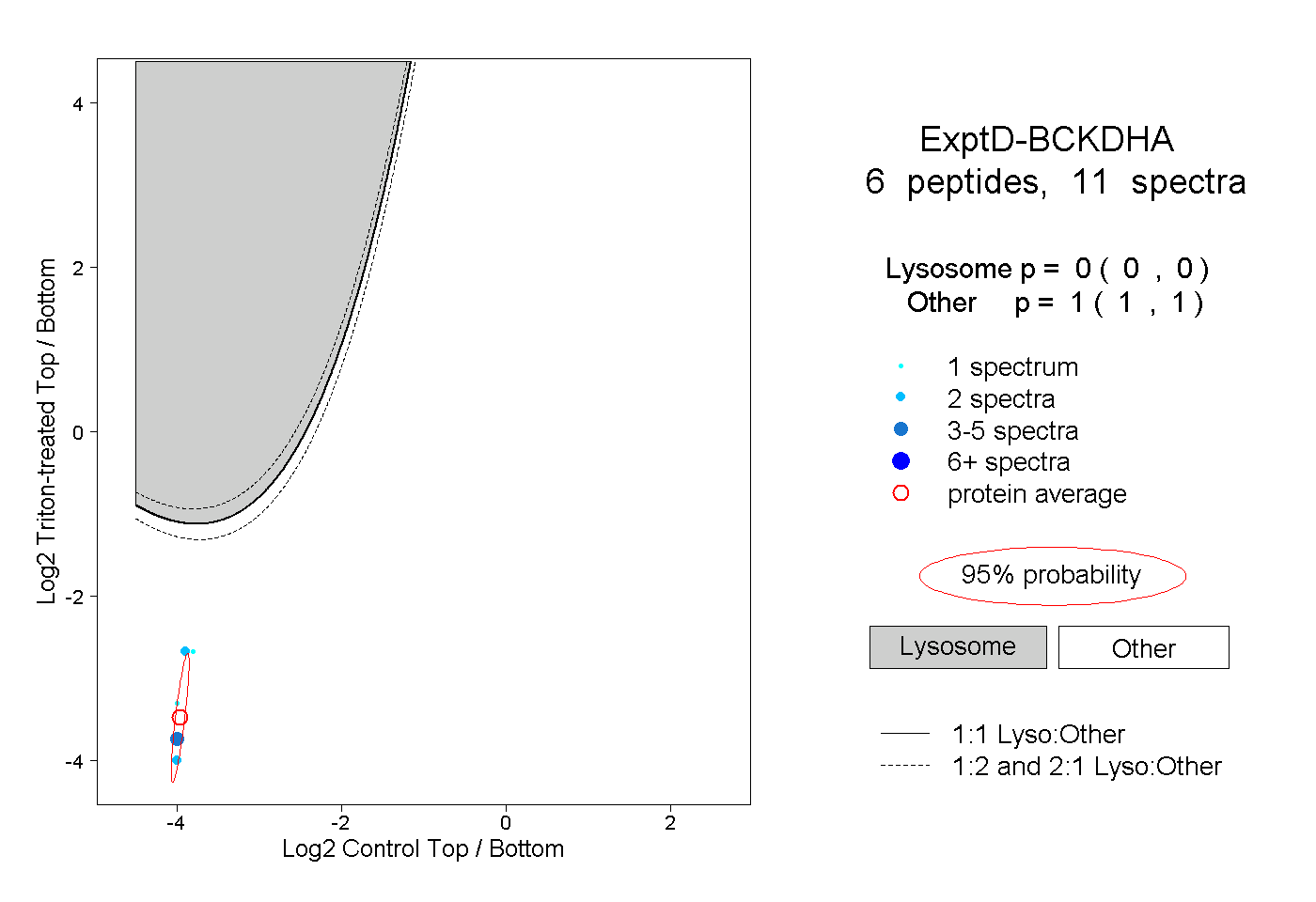 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |